peptides
spectra
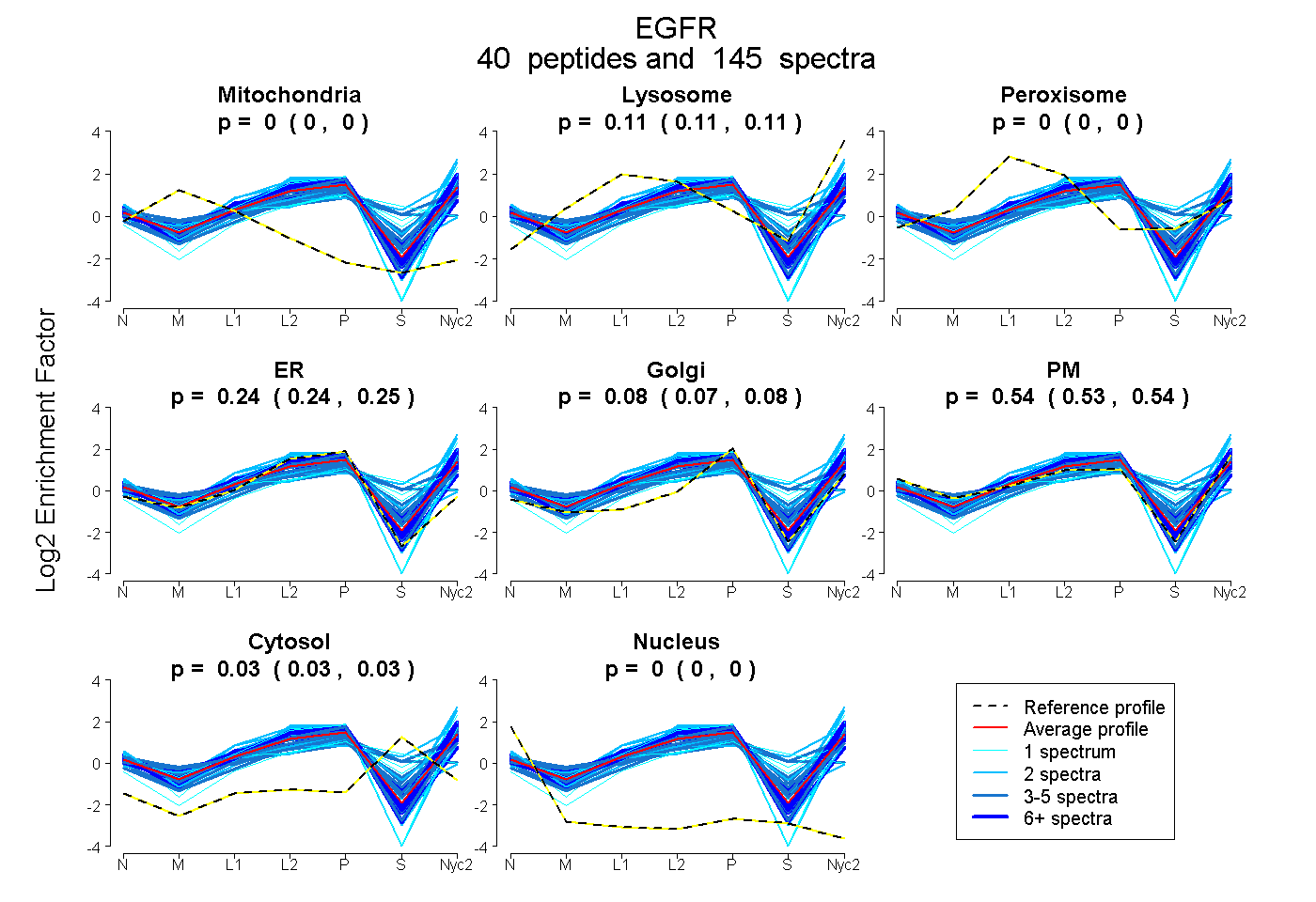
0.000 | 0.000
0.106 | 0.112
0.000 | 0.000
0.237 | 0.248
0.072 | 0.084
0.534 | 0.542
0.027 | 0.033
0.000 | 0.000
peptides
spectra
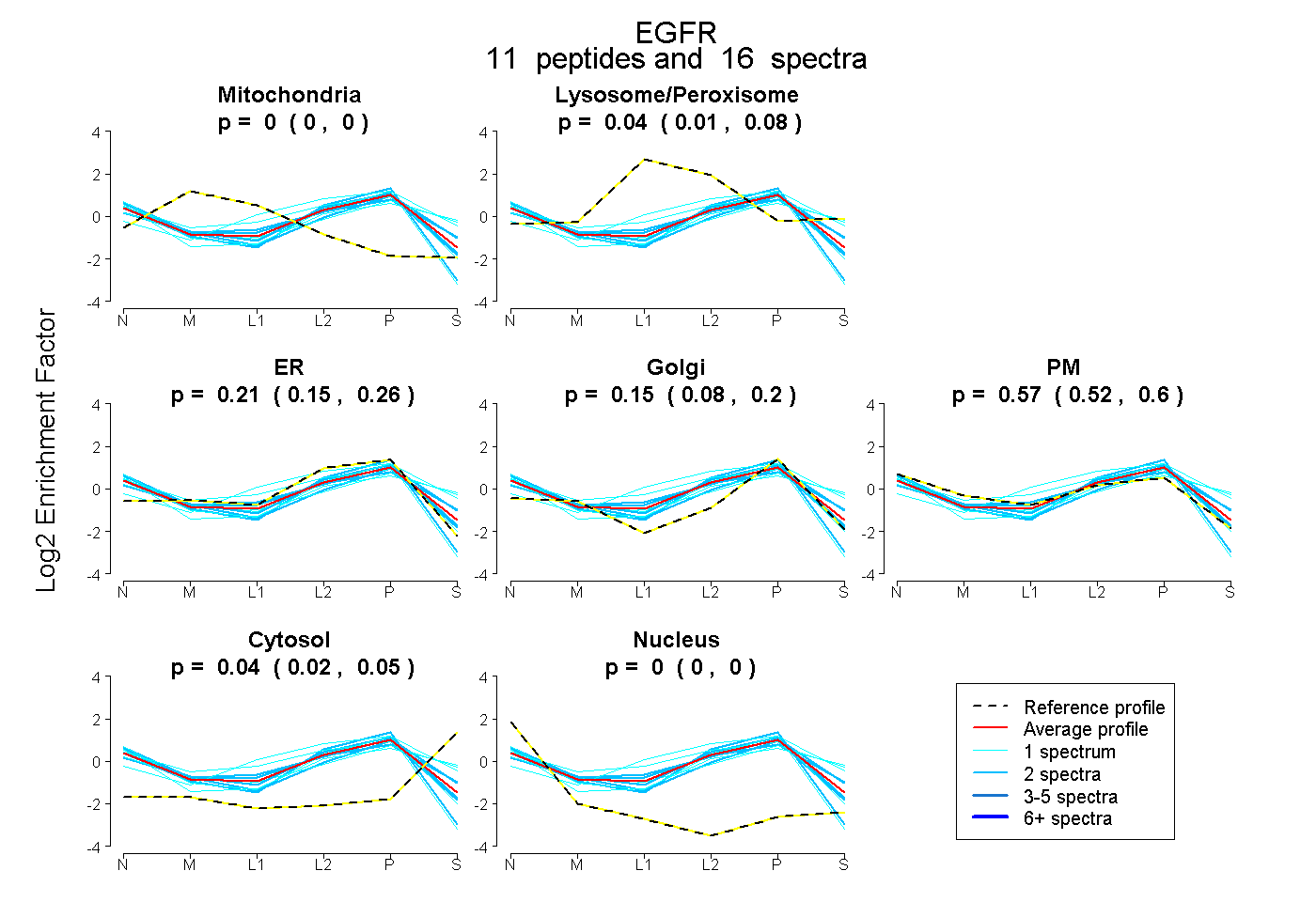
0.000 | 0.000
0.005 | 0.076
0.148 | 0.260
0.084 | 0.196
0.525 | 0.601
0.020 | 0.050
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
145 spectra |
 |
0.000 0.000 | 0.000 |
0.109 0.106 | 0.112 |
0.000 0.000 | 0.000 |
0.243 0.237 | 0.248 |
0.079 0.072 | 0.084 |
0.538 0.534 | 0.542 |
0.031 0.027 | 0.033 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
16 spectra |
 |
0.000 0.000 | 0.000 |
0.044 0.005 | 0.076 |
0.207 0.148 | 0.260 |
0.146 0.084 | 0.196 |
0.567 0.525 | 0.601 |
0.036 0.020 | 0.050 |
0.000 0.000 | 0.000 |
| 1 spectrum, RPAGSVQNPVYHNQPLHPAPGR | 0.000 | 0.423 | 0.197 | 0.324 | 0.000 | 0.056 | 0.000 | |||
| 2 spectra, LTQLGTFEDHFLSLQR | 0.000 | 0.000 | 0.298 | 0.148 | 0.554 | 0.000 | 0.000 | |||
| 2 spectra, GEENCQK | 0.000 | 0.119 | 0.000 | 0.130 | 0.678 | 0.072 | 0.000 | |||
| 1 spectrum, NLQEILIGAVR | 0.000 | 0.179 | 0.133 | 0.098 | 0.590 | 0.000 | 0.000 | |||
| 2 spectra, ELILEFSK | 0.000 | 0.000 | 0.820 | 0.054 | 0.000 | 0.000 | 0.126 | |||
| 2 spectra, IPLENLQIIR | 0.000 | 0.252 | 0.000 | 0.459 | 0.272 | 0.016 | 0.000 | |||
| 1 spectrum, TPQHVK | 0.000 | 0.042 | 0.074 | 0.000 | 0.621 | 0.263 | 0.000 | |||
| 1 spectrum, ITDFGLAK | 0.000 | 0.172 | 0.000 | 0.283 | 0.349 | 0.196 | 0.000 | |||
| 1 spectrum, LLGAEEK | 0.000 | 0.000 | 0.264 | 0.143 | 0.593 | 0.000 | 0.000 | |||
| 1 spectrum, VLGSGAFGTVYK | 0.000 | 0.000 | 0.739 | 0.000 | 0.097 | 0.000 | 0.163 | |||
| 2 spectra, IICAQQCSR | 0.000 | 0.000 | 0.000 | 0.307 | 0.682 | 0.000 | 0.011 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
214 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
34 spectra |
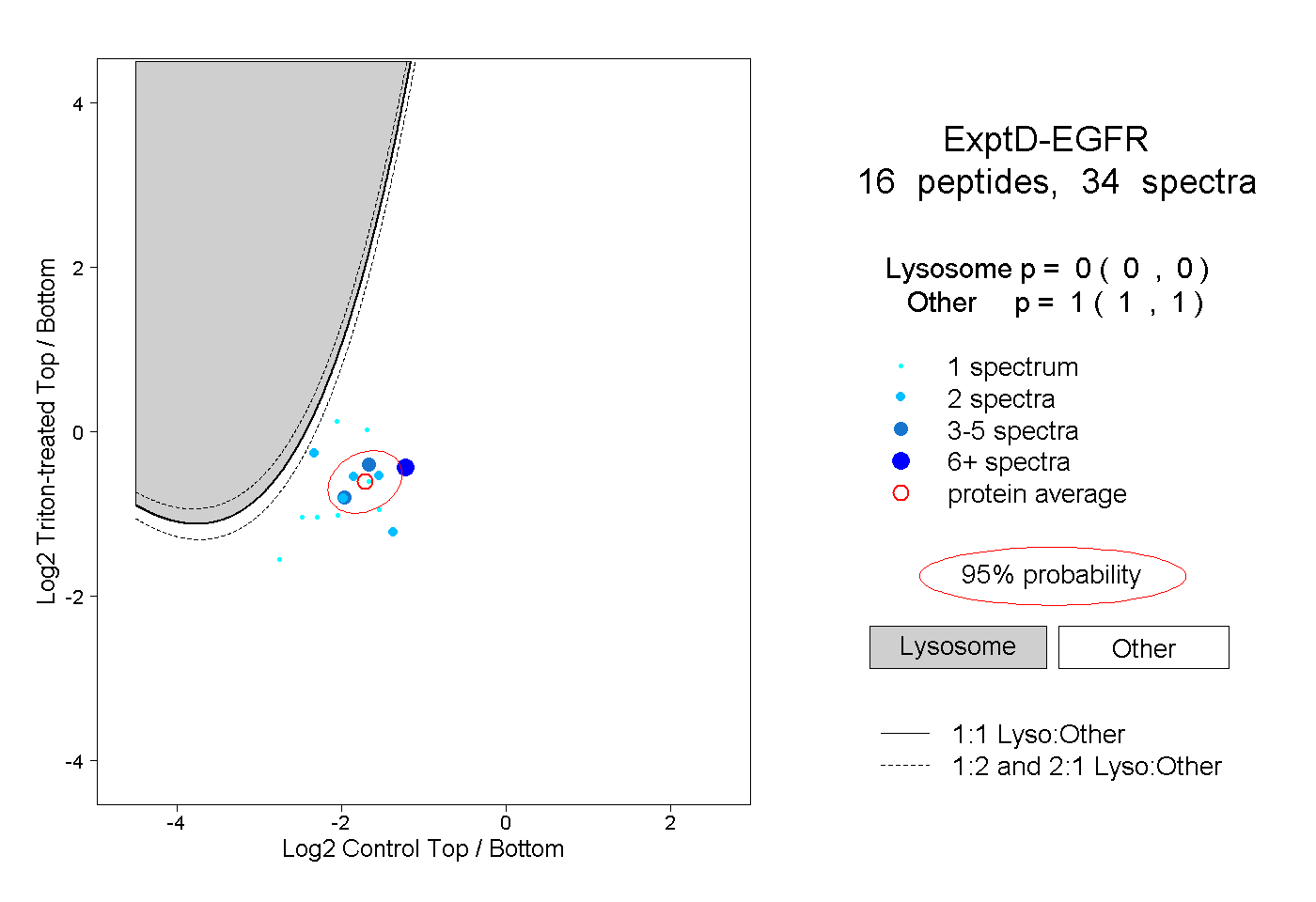 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |