peptides
spectra
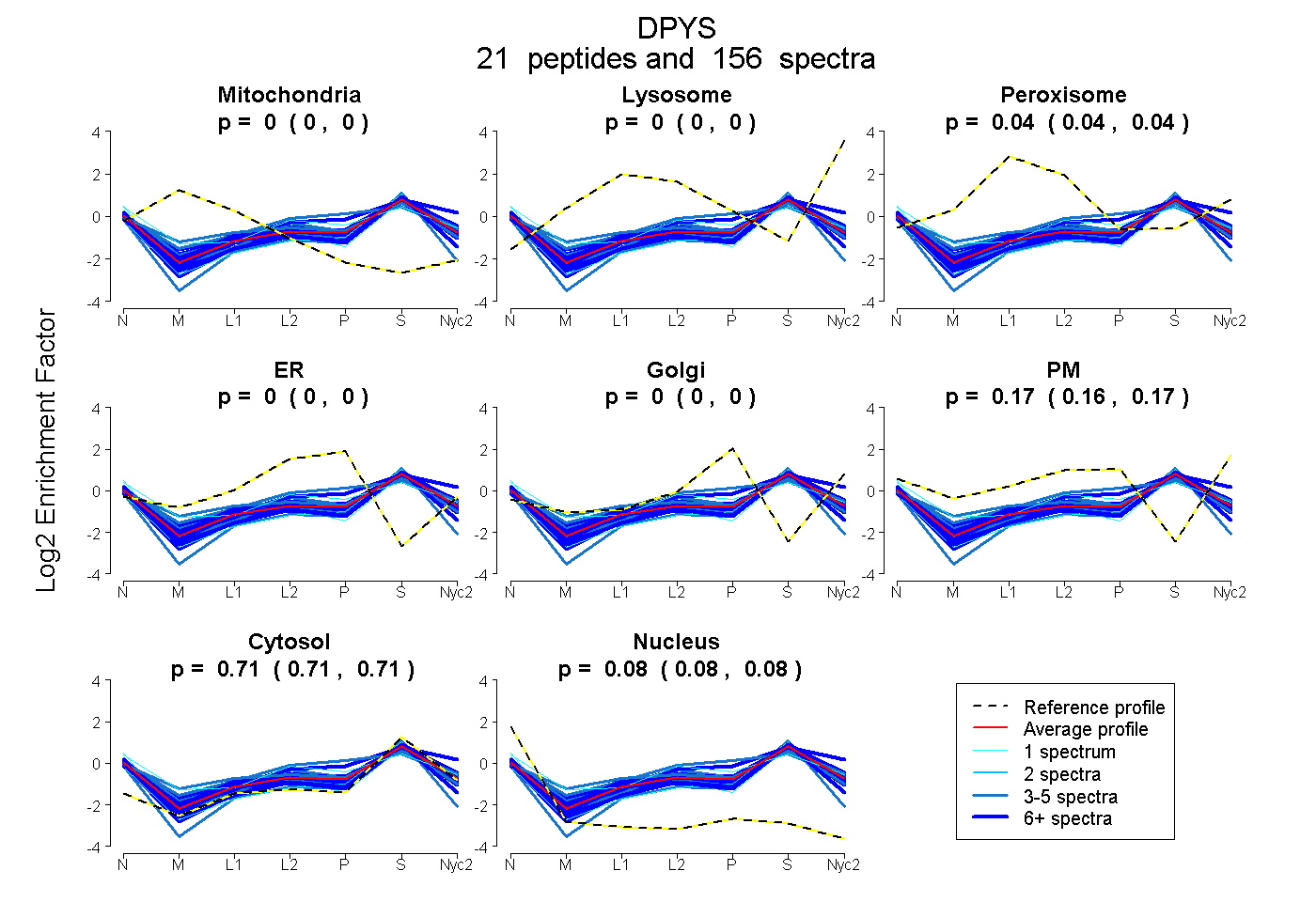
0.000 | 0.000
0.000 | 0.000
0.038 | 0.043
0.000 | 0.000
0.000 | 0.000
0.164 | 0.171
0.706 | 0.710
0.081 | 0.085
peptides
spectra
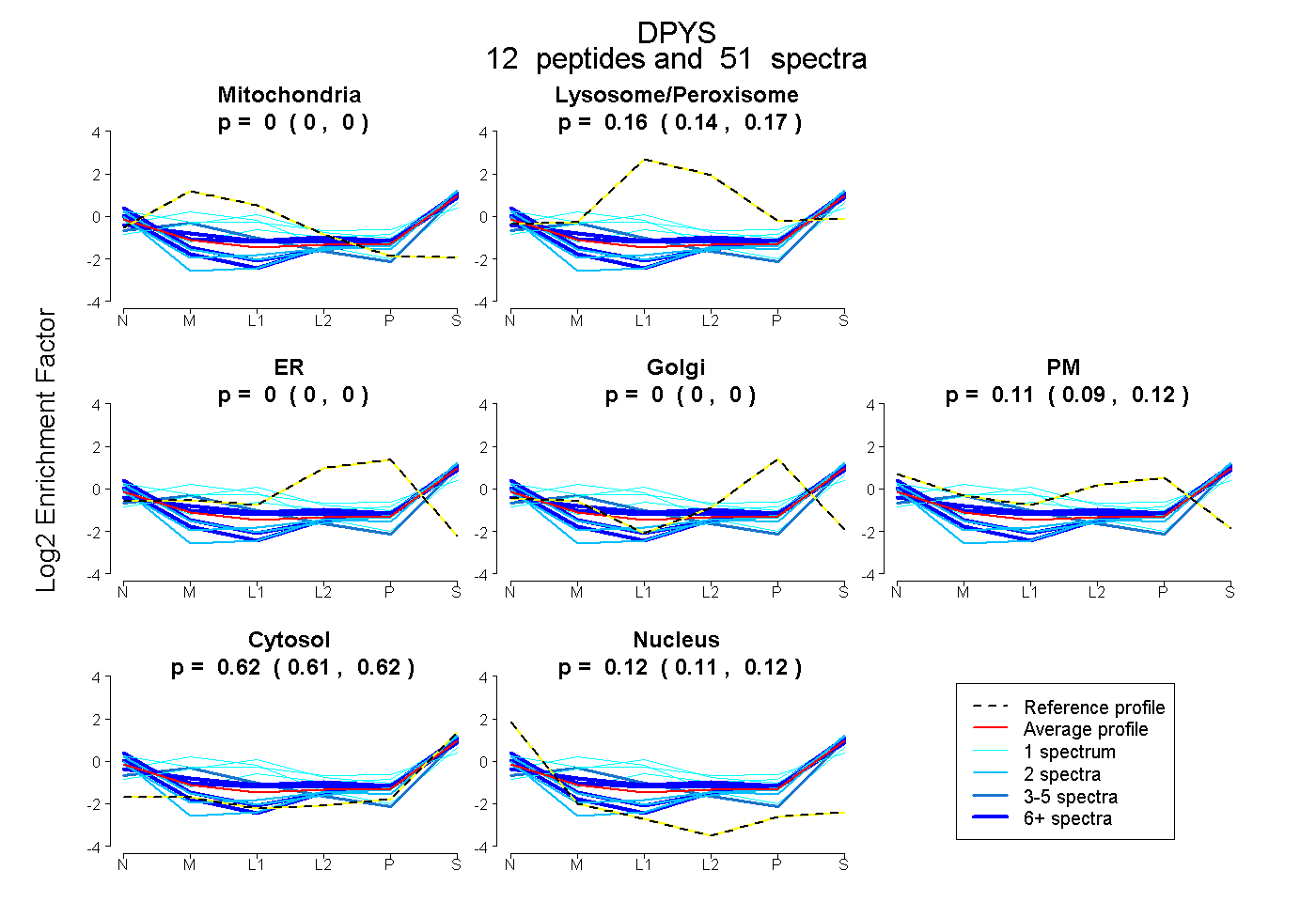
0.000 | 0.000
0.144 | 0.171
0.000 | 0.000
0.000 | 0.000
0.092 | 0.124
0.608 | 0.622
0.106 | 0.124
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
156 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.041 0.038 | 0.043 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.168 0.164 | 0.171 |
0.708 0.706 | 0.710 |
0.083 0.081 | 0.085 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
51 spectra |
 |
0.000 0.000 | 0.000 |
0.159 0.144 | 0.171 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.110 0.092 | 0.124 |
0.616 0.608 | 0.622 |
0.116 0.106 | 0.124 |
| 2 spectra, VVYEAGVFDVTAGHGK | 0.000 | 0.119 | 0.000 | 0.000 | 0.037 | 0.699 | 0.144 | |||
| 2 spectra, IPNGVNGVEDR | 0.000 | 0.037 | 0.000 | 0.000 | 0.177 | 0.642 | 0.145 | |||
| 1 spectrum, FVAVTSTNAAK | 0.032 | 0.299 | 0.000 | 0.000 | 0.249 | 0.349 | 0.071 | |||
| 1 spectrum, AALAGGTTMIIDFAIPQK | 0.000 | 0.305 | 0.000 | 0.000 | 0.074 | 0.542 | 0.079 | |||
| 3 spectra, DLYMVQDQQMYAAFSQCK | 0.303 | 0.046 | 0.000 | 0.000 | 0.000 | 0.647 | 0.004 | |||
| 8 spectra, EIGAIAQVHAENGDLIAEGAK | 0.000 | 0.198 | 0.000 | 0.000 | 0.121 | 0.563 | 0.118 | |||
| 6 spectra, GSSLIEAFETWR | 0.000 | 0.000 | 0.000 | 0.000 | 0.193 | 0.702 | 0.105 | |||
| 1 spectrum, THHQAVNFNIFEGMVCHGVPLVTISR | 0.114 | 0.372 | 0.000 | 0.000 | 0.000 | 0.514 | 0.000 | |||
| 1 spectrum, AITIASAVNCPLYIVHVMSK | 0.419 | 0.114 | 0.000 | 0.000 | 0.000 | 0.468 | 0.000 | |||
| 6 spectra, MLALGITGPEGHELCRPEAVEAEATLR | 0.000 | 0.202 | 0.000 | 0.000 | 0.147 | 0.616 | 0.035 | |||
| 18 spectra, DLLPPGDTSR | 0.000 | 0.026 | 0.000 | 0.000 | 0.209 | 0.601 | 0.164 | |||
| 2 spectra, QPFAEFIYK | 0.000 | 0.038 | 0.000 | 0.000 | 0.045 | 0.750 | 0.167 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
266 spectra |
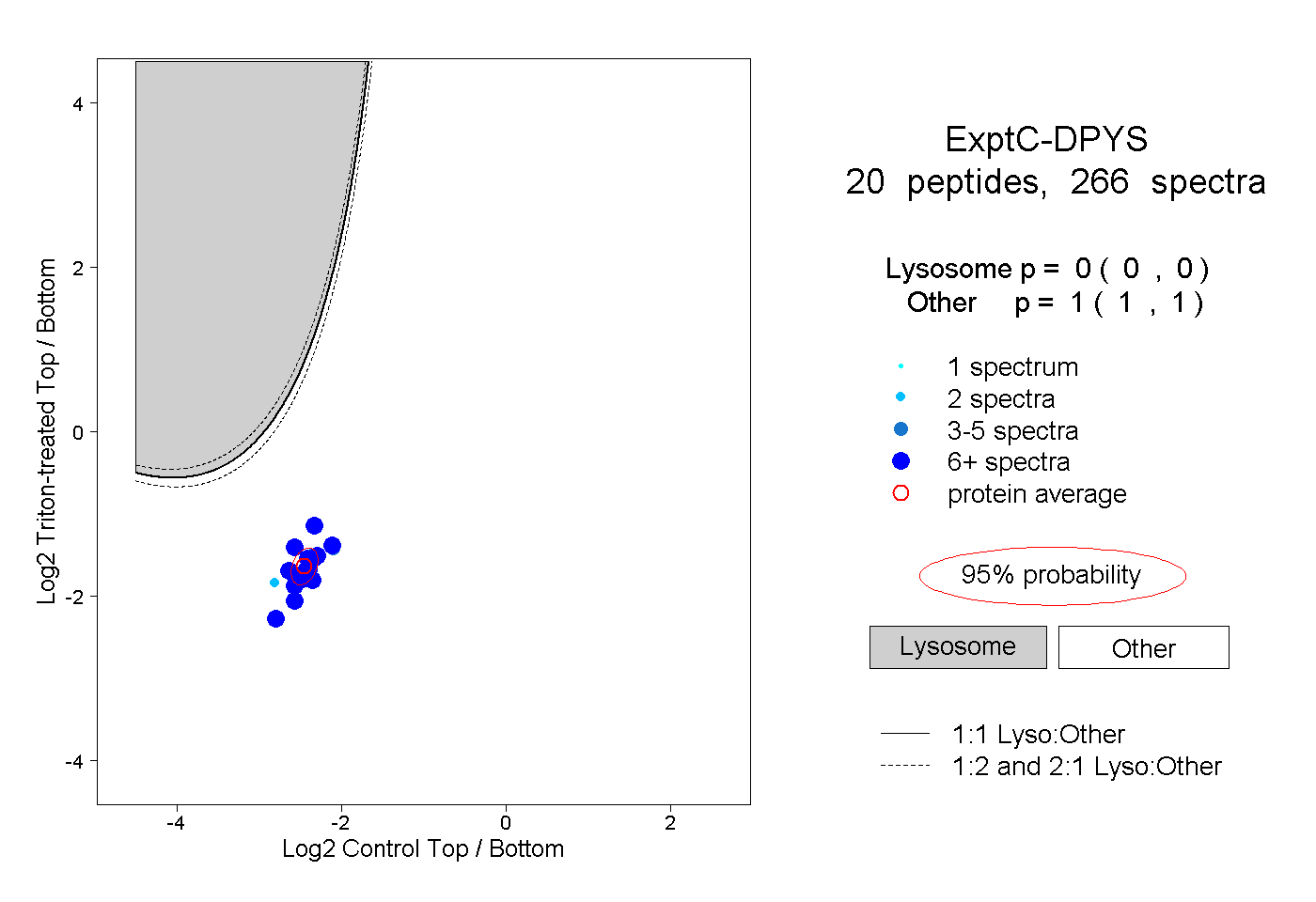 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
26 spectra |
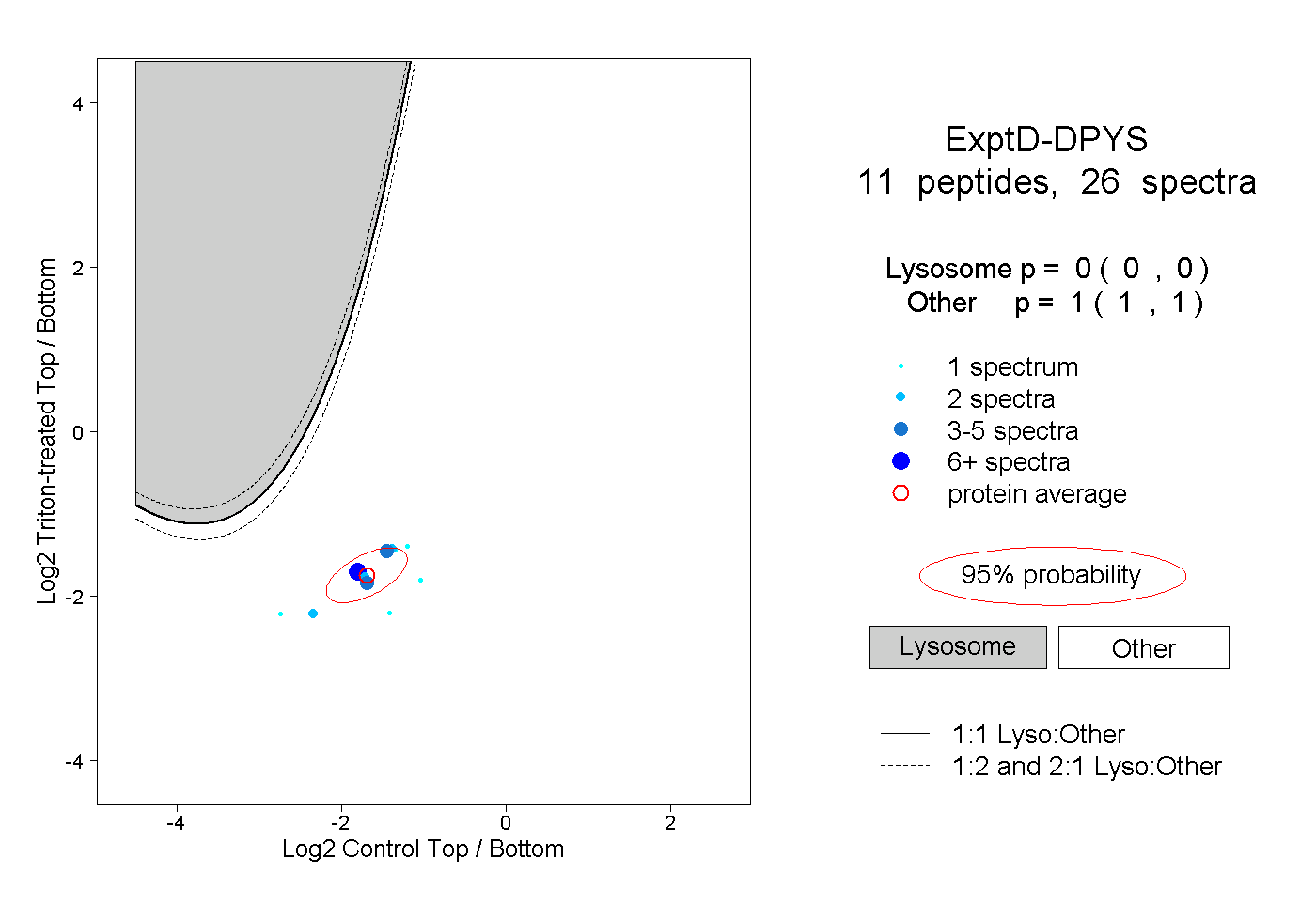 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |