peptides
spectra

0.000 | 0.000
0.015 | 0.032
0.000 | 0.017
0.243 | 0.268
0.601 | 0.631
0.022 | 0.042
0.058 | 0.066
0.000 | 0.000
peptides
spectra
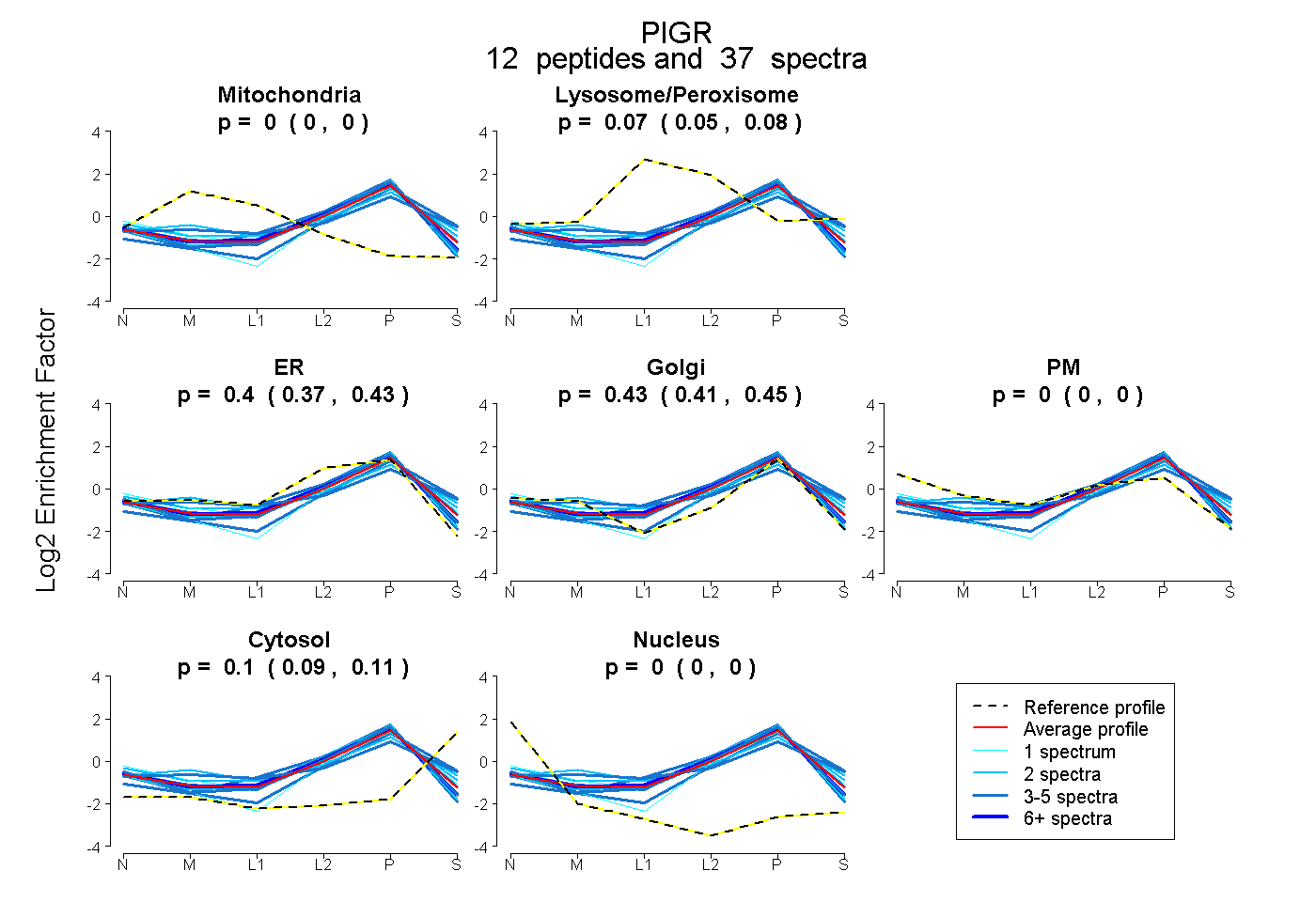
0.000 | 0.000
0.053 | 0.075
0.375 | 0.426
0.413 | 0.451
0.000 | 0.000
0.090 | 0.105
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
82 spectra |
 |
0.000 0.000 | 0.000 |
0.025 0.015 | 0.032 |
0.006 0.000 | 0.017 |
0.257 0.243 | 0.268 |
0.615 0.601 | 0.631 |
0.034 0.022 | 0.042 |
0.063 0.058 | 0.066 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
37 spectra |
 |
0.000 0.000 | 0.000 |
0.065 0.053 | 0.075 |
0.403 0.375 | 0.426 |
0.434 0.413 | 0.451 |
0.000 0.000 | 0.000 |
0.098 0.090 | 0.105 |
0.000 0.000 | 0.000 |
| 9 spectra, ILLTPR | 0.000 | 0.047 | 0.497 | 0.398 | 0.000 | 0.058 | 0.000 | |||
| 2 spectra, EDEGWYWCGVK | 0.000 | 0.237 | 0.000 | 0.714 | 0.000 | 0.050 | 0.000 | |||
| 1 spectrum, ETCDVIINTLGK | 0.000 | 0.153 | 0.181 | 0.614 | 0.000 | 0.052 | 0.000 | |||
| 2 spectra, DPAFEGR | 0.000 | 0.041 | 0.439 | 0.505 | 0.000 | 0.015 | 0.000 | |||
| 3 spectra, ASGNAGSAGGQSGSSK | 0.000 | 0.027 | 0.663 | 0.286 | 0.000 | 0.025 | 0.000 | |||
| 3 spectra, EIQNAGDQAQENR | 0.000 | 0.000 | 0.341 | 0.375 | 0.000 | 0.284 | 0.000 | |||
| 2 spectra, GVTGGSVAIVCPYNPK | 0.000 | 0.263 | 0.000 | 0.648 | 0.000 | 0.089 | 0.000 | |||
| 2 spectra, EVANDAK | 0.000 | 0.000 | 0.627 | 0.302 | 0.000 | 0.070 | 0.000 | |||
| 5 spectra, FSVLITGLR | 0.000 | 0.000 | 0.619 | 0.242 | 0.000 | 0.139 | 0.000 | |||
| 4 spectra, TVTIECR | 0.000 | 0.000 | 0.530 | 0.401 | 0.000 | 0.068 | 0.000 | |||
| 1 spectrum, SSVTFECDLGR | 0.000 | 0.000 | 0.198 | 0.791 | 0.000 | 0.011 | 0.000 | |||
| 3 spectra, TTIELQVAEATK | 0.000 | 0.274 | 0.000 | 0.574 | 0.000 | 0.152 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
189 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
16 spectra |
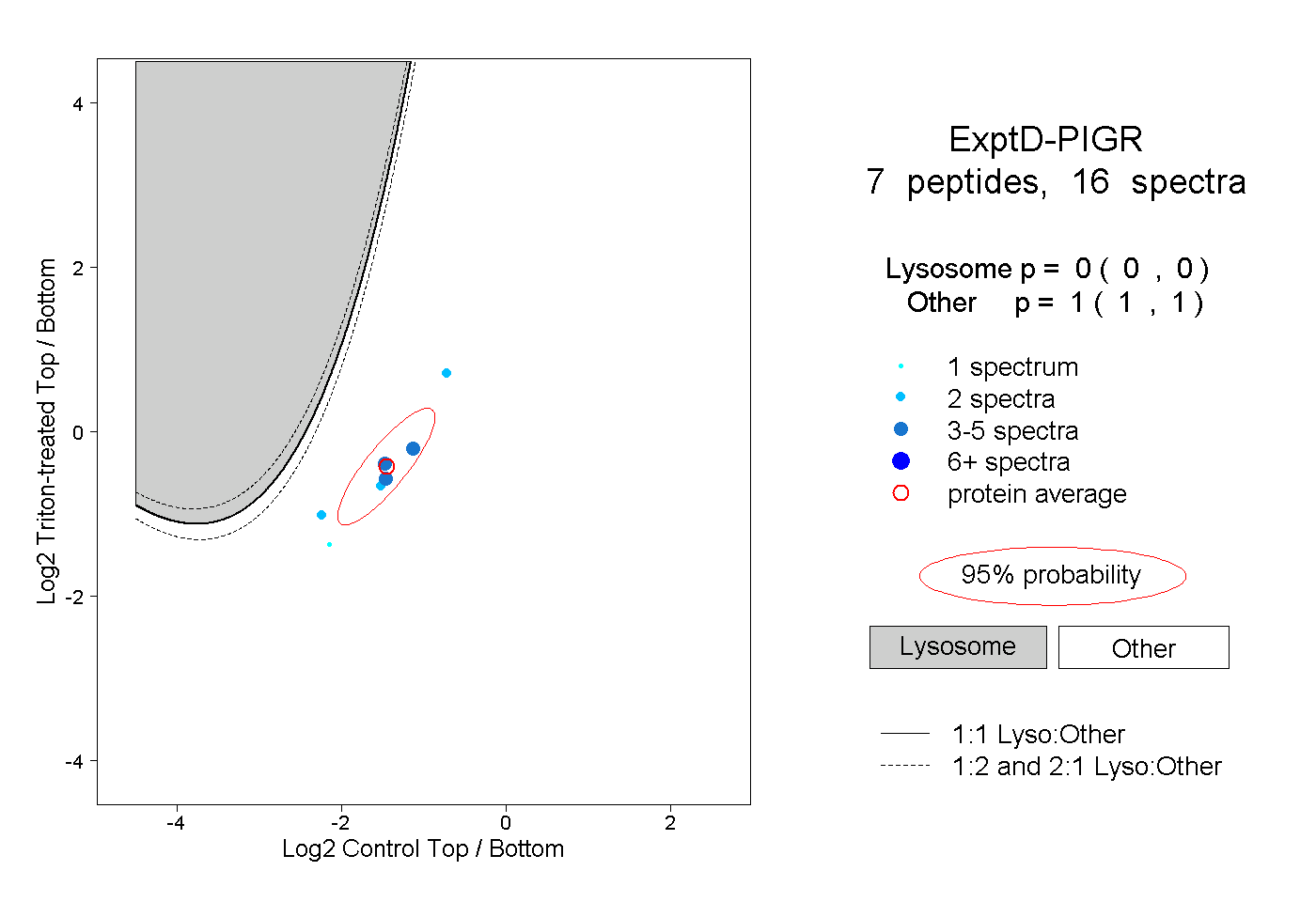 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |