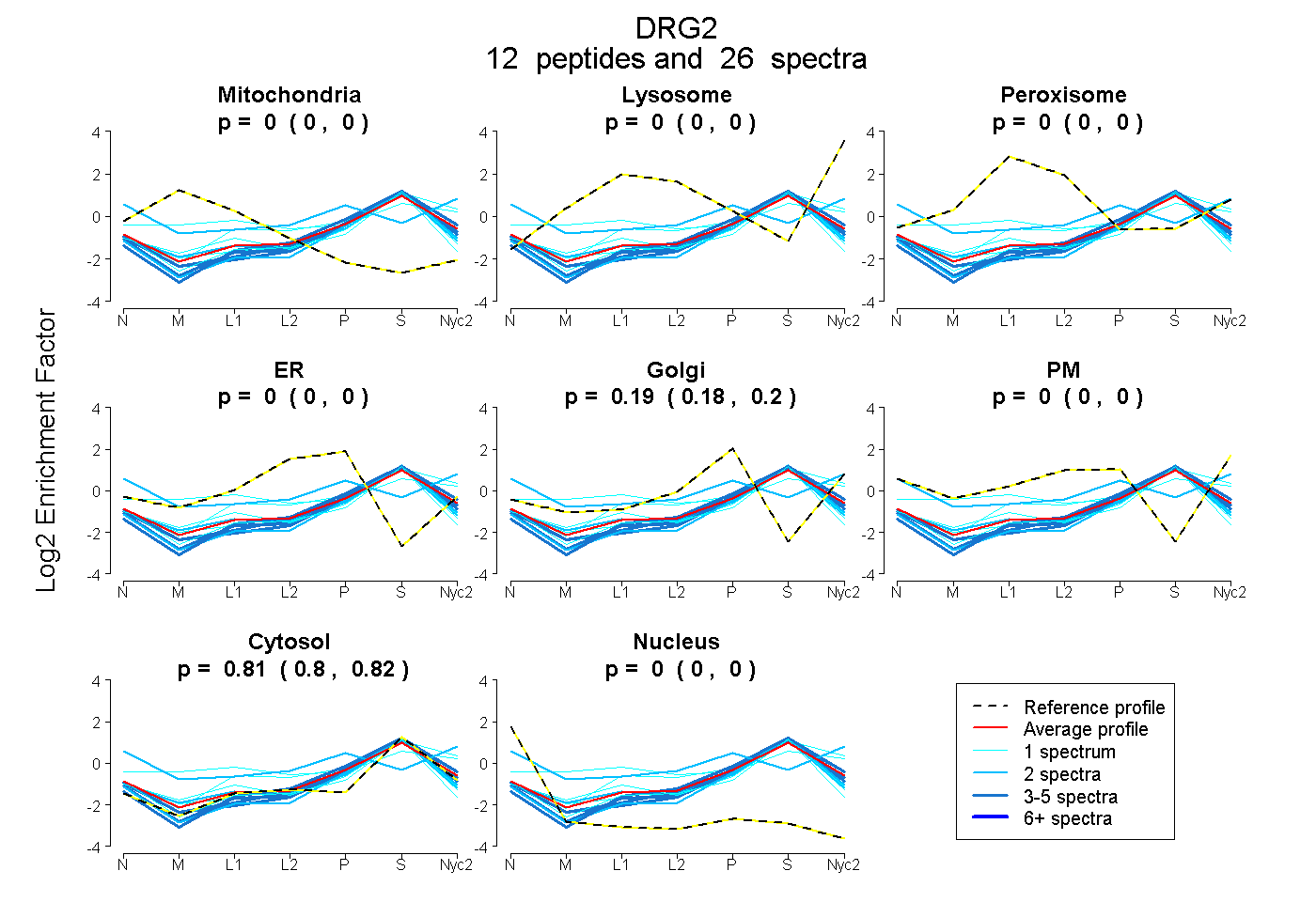
peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.179 | 0.196
0.000 | 0.000
0.802 | 0.819
0.000 | 0.002
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
26 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.188 0.179 | 0.196 |
0.000 0.000 | 0.000 |
0.812 0.802 | 0.819 |
0.000 0.000 | 0.002 |
| 1 spectrum, AQLLEPSK | 0.000 | 0.171 | 0.000 | 0.000 | 0.073 | 0.026 | 0.729 | 0.000 | ||
| 2 spectra, GQRPDFTDAIILR | 0.031 | 0.000 | 0.000 | 0.000 | 0.100 | 0.000 | 0.848 | 0.021 | ||
| 4 spectra, GEGFDVMK | 0.000 | 0.000 | 0.000 | 0.000 | 0.104 | 0.000 | 0.882 | 0.014 | ||
| 1 spectrum, KPNSVVISCGMK | 0.108 | 0.000 | 0.000 | 0.042 | 0.000 | 0.000 | 0.839 | 0.012 | ||
| 1 spectrum, GILEK | 0.079 | 0.087 | 0.155 | 0.000 | 0.000 | 0.159 | 0.520 | 0.000 | ||
| 5 spectra, IDQISMEEVDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.142 | 0.000 | 0.844 | 0.014 | ||
| 1 spectrum, VALIGFPSVGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.048 | 0.000 | 0.895 | 0.056 | ||
| 2 spectra, LVQLILHEYK | 0.000 | 0.000 | 0.000 | 0.000 | 0.046 | 0.000 | 0.899 | 0.054 | ||
| 1 spectrum, GANIQLLDLPGIIEGAAQGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.112 | 0.000 | 0.851 | 0.037 | ||
| 3 spectra, IFNAEVLFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.136 | 0.000 | 0.857 | 0.007 | ||
| 2 spectra, YALVWGTSTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.603 | 0.397 | 0.000 | ||
| 3 spectra, TADVVVMMLDATK | 0.000 | 0.000 | 0.000 | 0.000 | 0.134 | 0.000 | 0.866 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
6 spectra |
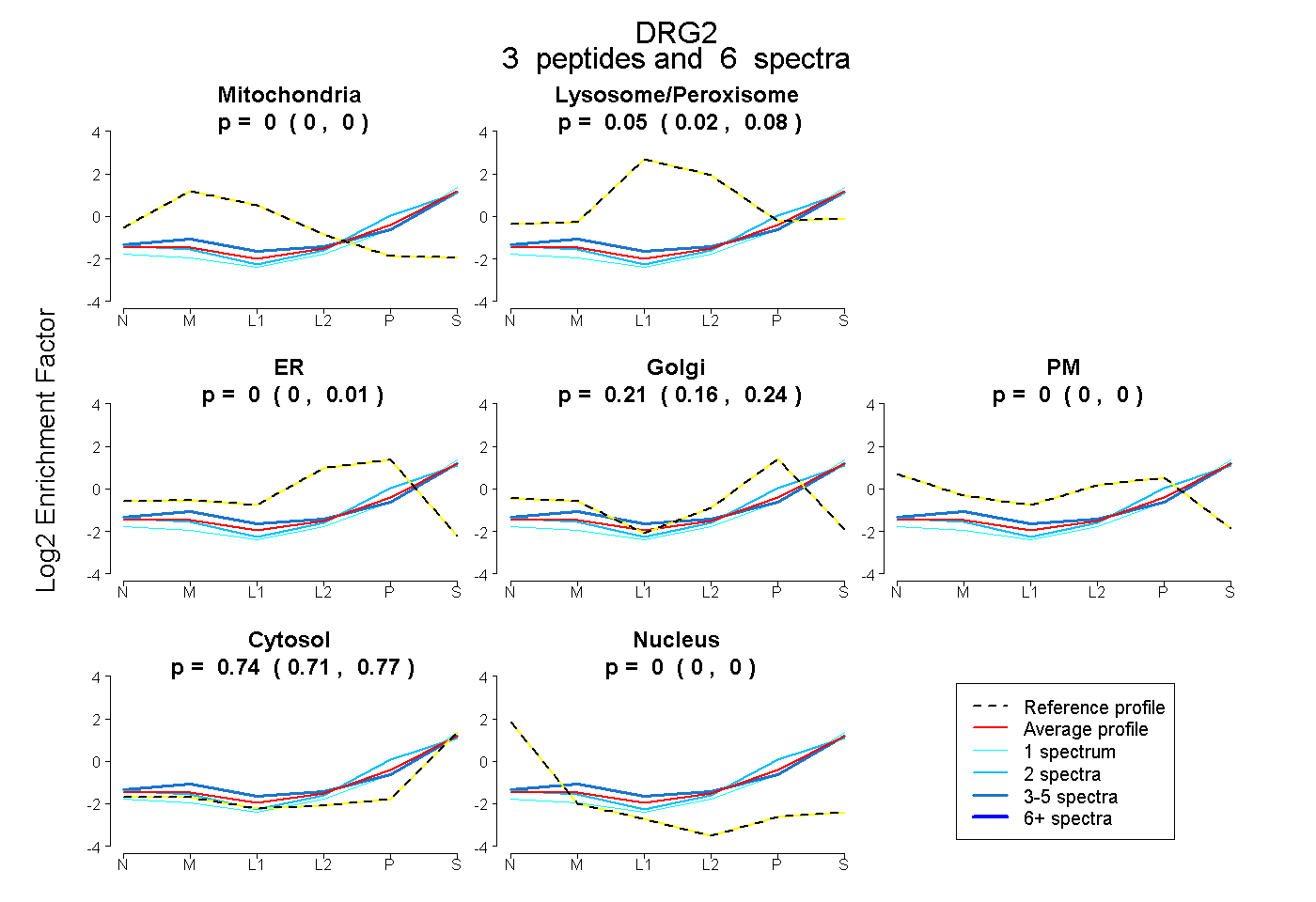 |
0.000 0.000 | 0.000 |
0.054 0.019 | 0.082 |
0.000 0.000 | 0.007 |
0.206 0.160 | 0.237 |
0.000 0.000 | 0.000 |
0.740 0.712 | 0.766 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
20 spectra |
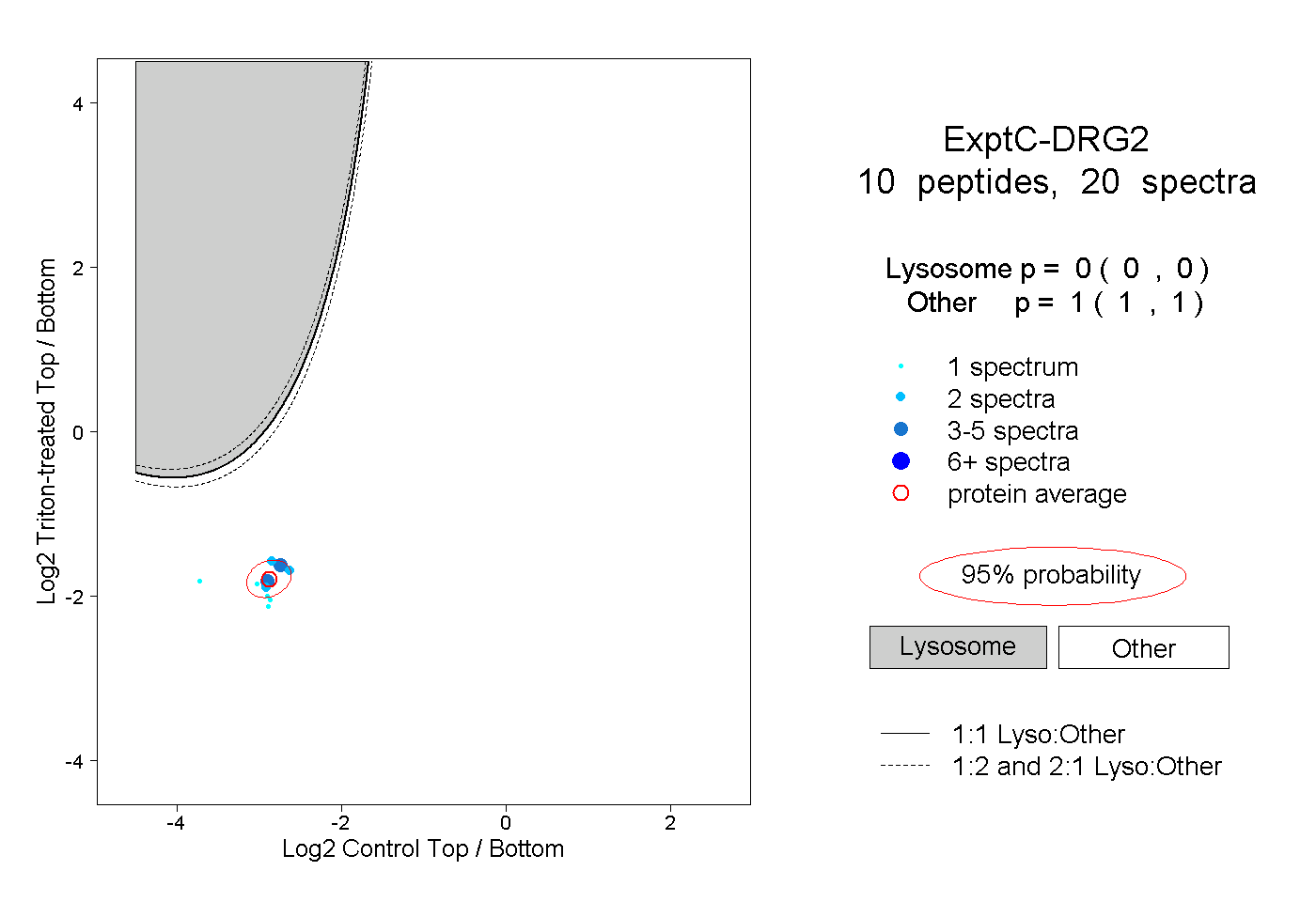 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |