peptides
spectra
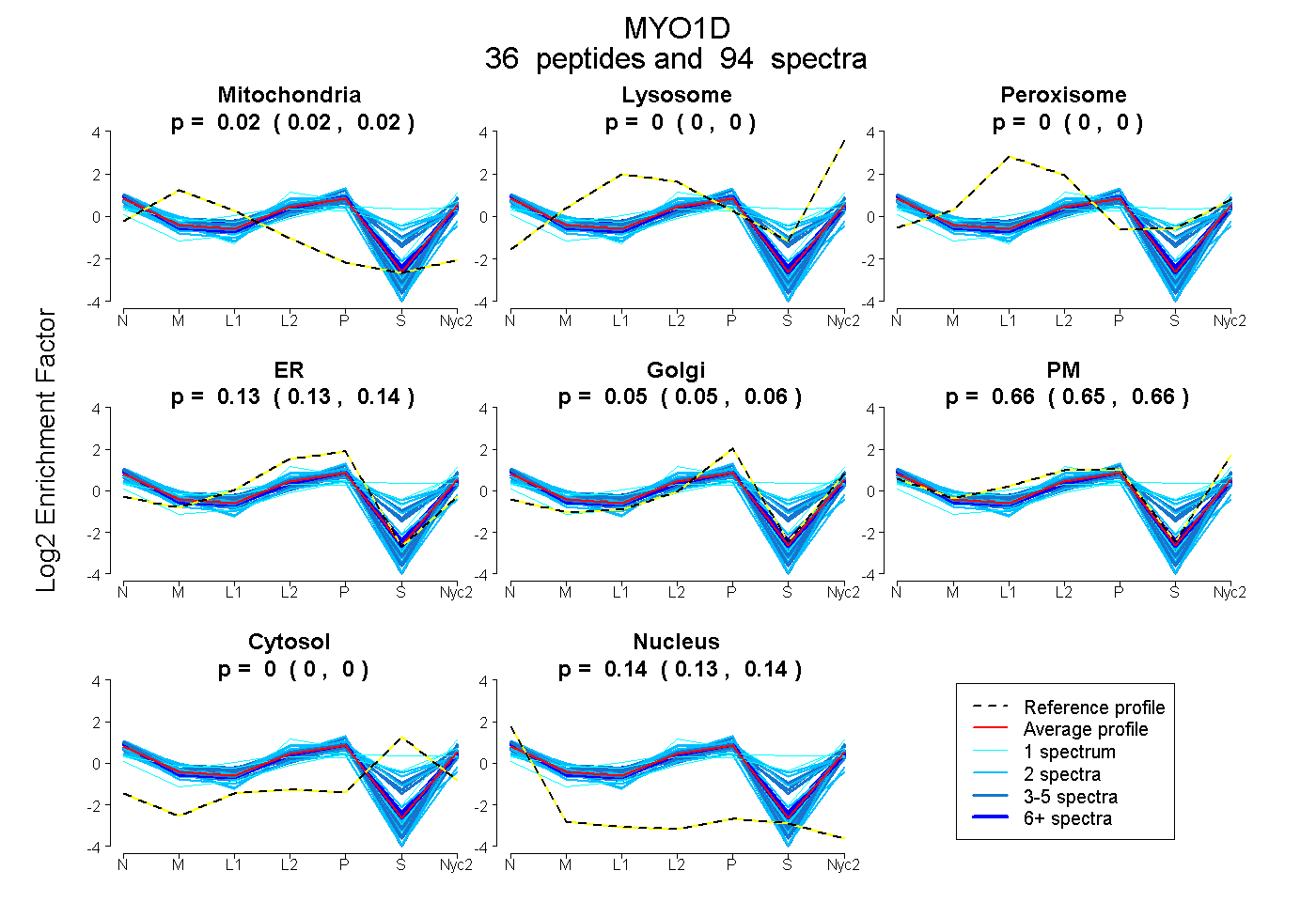
0.016 | 0.020
0.000 | 0.000
0.000 | 0.000
0.130 | 0.139
0.047 | 0.057
0.655 | 0.663
0.000 | 0.000
0.134 | 0.137
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
94 spectra |
 |
0.018 0.016 | 0.020 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.135 0.130 | 0.139 |
0.052 0.047 | 0.057 |
0.659 0.655 | 0.663 |
0.000 0.000 | 0.000 |
0.136 0.134 | 0.137 |
| 2 spectra, DTLFQDFK | 0.000 | 0.000 | 0.000 | 0.032 | 0.245 | 0.601 | 0.000 | 0.122 | ||
| 3 spectra, LLEFDR | 0.011 | 0.000 | 0.000 | 0.000 | 0.000 | 0.755 | 0.189 | 0.044 | ||
| 1 spectrum, LNQPQPDFTK | 0.000 | 0.000 | 0.164 | 0.000 | 0.134 | 0.496 | 0.206 | 0.000 | ||
| 1 spectrum, LMYNSSNPVLK | 0.020 | 0.000 | 0.000 | 0.123 | 0.029 | 0.735 | 0.000 | 0.093 | ||
| 4 spectra, TIPASDLPQVR | 0.000 | 0.000 | 0.000 | 0.238 | 0.000 | 0.590 | 0.000 | 0.172 | ||
| 2 spectra, TCASDK | 0.030 | 0.000 | 0.000 | 0.249 | 0.084 | 0.505 | 0.010 | 0.122 | ||
| 3 spectra, SLSSYNYIR | 0.046 | 0.000 | 0.000 | 0.004 | 0.127 | 0.694 | 0.000 | 0.129 | ||
| 2 spectra, VLNIYGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.595 | 0.353 | 0.052 | ||
| 6 spectra, VIVQQPGER | 0.000 | 0.000 | 0.000 | 0.140 | 0.079 | 0.626 | 0.000 | 0.155 | ||
| 2 spectra, NYDTTVHGK | 0.025 | 0.000 | 0.000 | 0.086 | 0.003 | 0.565 | 0.322 | 0.000 | ||
| 1 spectrum, QEQEEYQR | 0.000 | 0.000 | 0.000 | 0.196 | 0.000 | 0.662 | 0.000 | 0.142 | ||
| 3 spectra, SSINDAAEFK | 0.052 | 0.000 | 0.000 | 0.094 | 0.000 | 0.722 | 0.000 | 0.132 | ||
| 2 spectra, QHTEQEASYGR | 0.000 | 0.000 | 0.000 | 0.108 | 0.000 | 0.753 | 0.000 | 0.140 | ||
| 3 spectra, LSITEVTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.126 | 0.569 | 0.245 | 0.059 | ||
| 1 spectrum, HQVEYLGLLENVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.852 | 0.048 | 0.100 | ||
| 2 spectra, CTVSVETR | 0.014 | 0.000 | 0.000 | 0.478 | 0.000 | 0.332 | 0.000 | 0.175 | ||
| 2 spectra, SNCVLEAFGNAK | 0.081 | 0.000 | 0.000 | 0.091 | 0.000 | 0.684 | 0.000 | 0.145 | ||
| 5 spectra, VVLFLQK | 0.000 | 0.000 | 0.000 | 0.075 | 0.016 | 0.778 | 0.000 | 0.132 | ||
| 4 spectra, ASQLIK | 0.000 | 0.000 | 0.000 | 0.223 | 0.000 | 0.637 | 0.000 | 0.139 | ||
| 1 spectrum, FIVDGDTPLIENGK | 0.094 | 0.000 | 0.000 | 0.086 | 0.000 | 0.705 | 0.000 | 0.114 | ||
| 3 spectra, INDIIEVK | 0.115 | 0.000 | 0.000 | 0.235 | 0.000 | 0.568 | 0.000 | 0.082 | ||
| 2 spectra, SPQIFDDER | 0.108 | 0.000 | 0.000 | 0.122 | 0.009 | 0.648 | 0.000 | 0.112 | ||
| 4 spectra, AALTIIR | 0.000 | 0.000 | 0.000 | 0.204 | 0.173 | 0.501 | 0.000 | 0.122 | ||
| 2 spectra, VAAMEMLK | 0.000 | 0.000 | 0.000 | 0.191 | 0.083 | 0.463 | 0.238 | 0.024 | ||
| 8 spectra, EPYYVR | 0.019 | 0.000 | 0.000 | 0.080 | 0.057 | 0.706 | 0.000 | 0.138 | ||
| 5 spectra, AQMLVR | 0.015 | 0.000 | 0.000 | 0.185 | 0.004 | 0.694 | 0.000 | 0.102 | ||
| 2 spectra, NSMIALVDNLASK | 0.033 | 0.000 | 0.000 | 0.139 | 0.000 | 0.756 | 0.000 | 0.072 | ||
| 2 spectra, GIIAILDDACMNVGK | 0.007 | 0.000 | 0.000 | 0.513 | 0.000 | 0.329 | 0.000 | 0.151 | ||
| 2 spectra, TVATGR | 0.000 | 0.000 | 0.000 | 0.163 | 0.000 | 0.690 | 0.000 | 0.147 | ||
| 1 spectrum, DTIEQYK | 0.051 | 0.000 | 0.000 | 0.199 | 0.000 | 0.610 | 0.000 | 0.140 | ||
| 3 spectra, ADMVEK | 0.021 | 0.000 | 0.000 | 0.103 | 0.053 | 0.611 | 0.157 | 0.054 | ||
| 1 spectrum, WPTPPK | 0.000 | 0.000 | 0.000 | 0.000 | 0.022 | 0.465 | 0.513 | 0.000 | ||
| 1 spectrum, YMNVLFSCHVR | 0.026 | 0.000 | 0.131 | 0.000 | 0.000 | 0.544 | 0.299 | 0.000 | ||
| 2 spectra, TLFTLEELR | 0.000 | 0.000 | 0.000 | 0.081 | 0.094 | 0.669 | 0.000 | 0.156 | ||
| 4 spectra, AGFAFR | 0.000 | 0.000 | 0.000 | 0.106 | 0.000 | 0.764 | 0.000 | 0.131 | ||
| 2 spectra, RPLTAATLFK | 0.000 | 0.000 | 0.000 | 0.153 | 0.000 | 0.739 | 0.000 | 0.108 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
16 spectra |
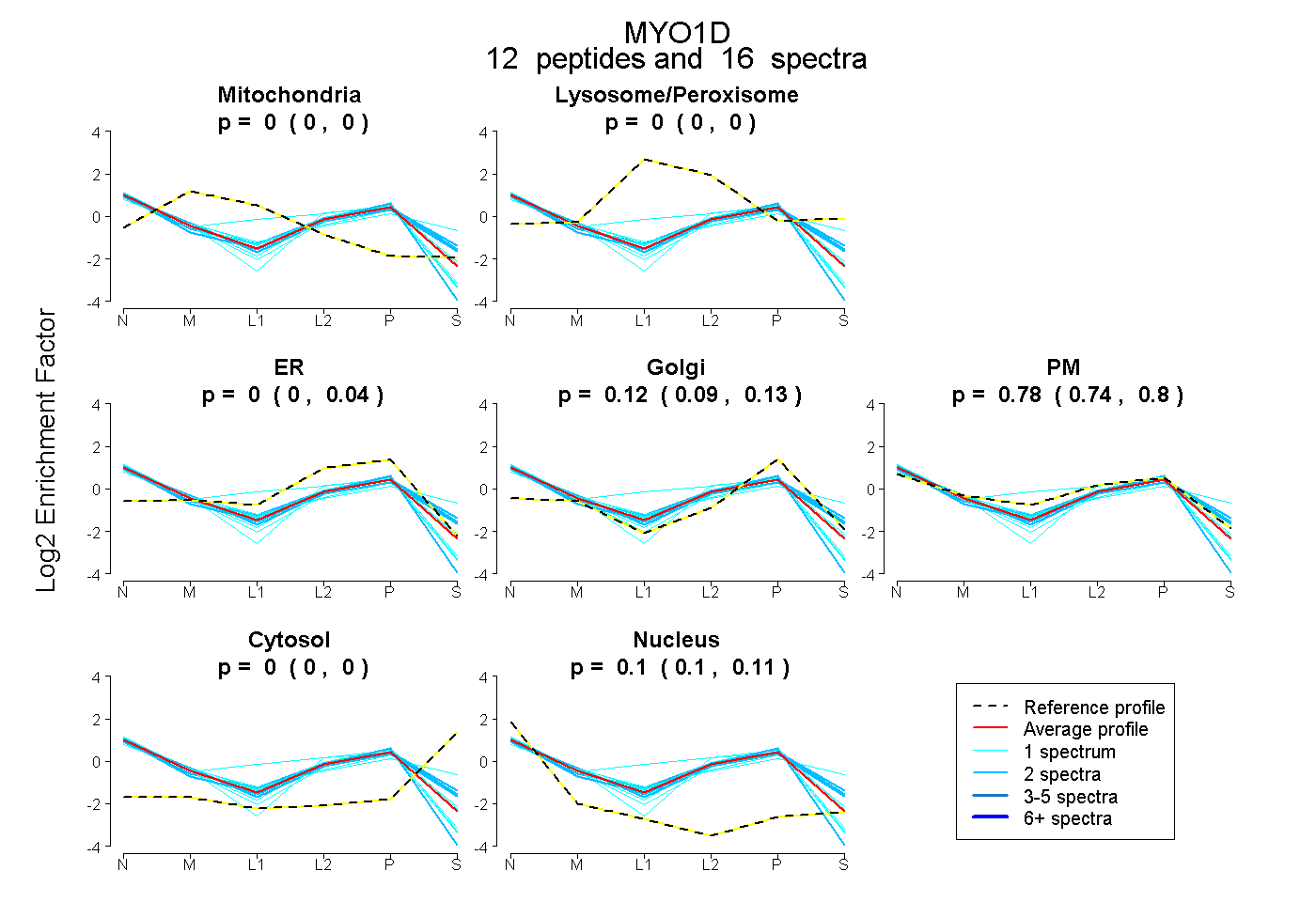 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.038 |
0.118 0.089 | 0.133 |
0.780 0.737 | 0.798 |
0.000 0.000 | 0.000 |
0.103 0.098 | 0.115 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
141 spectra |
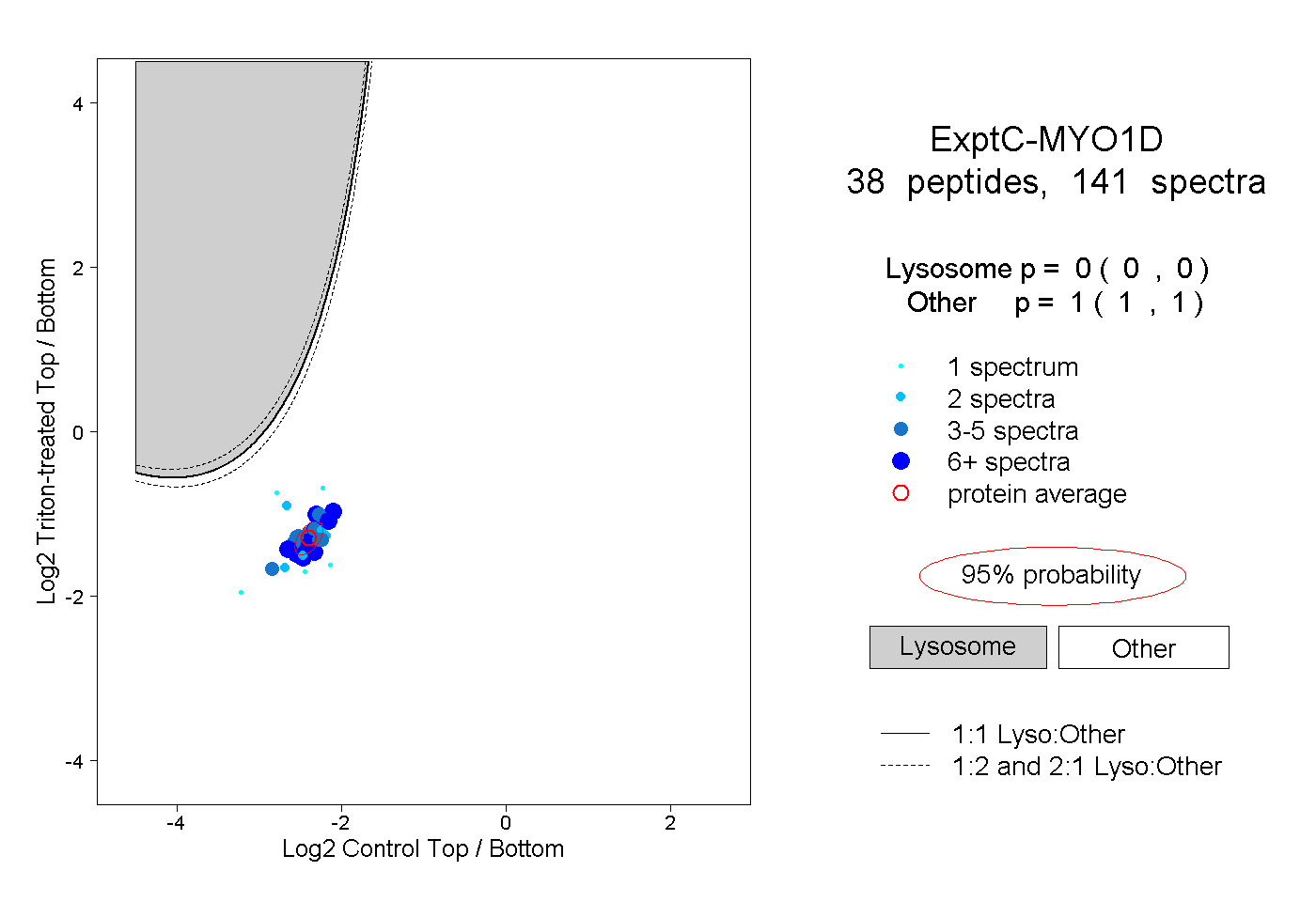 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
23 spectra |
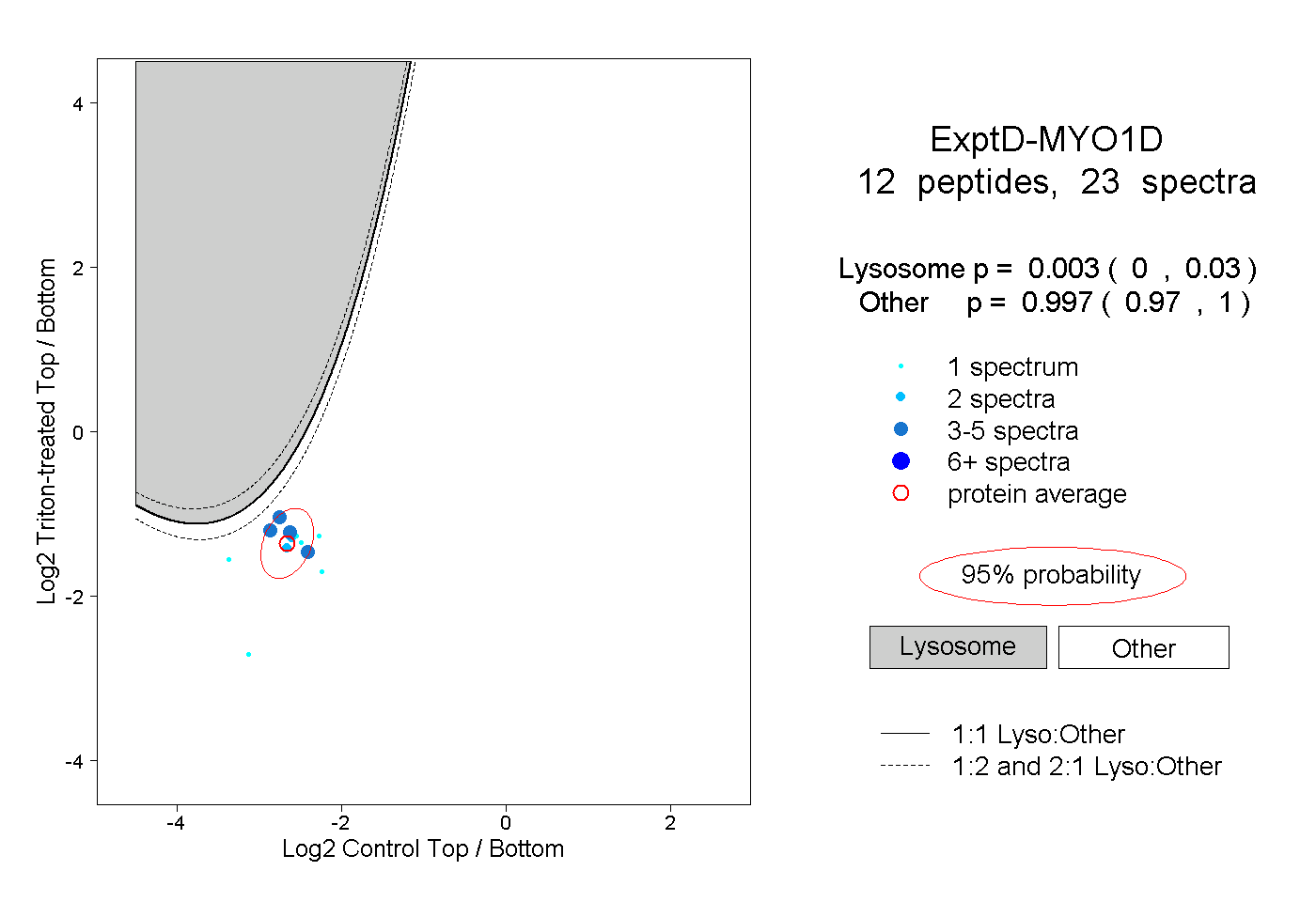 |
0.003 0.000 | 0.030 |
0.997 0.970 | 1.000 |