peptides
spectra

0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.369 | 0.380
0.000 | 0.000
0.000 | 0.000
0.021 | 0.035
0.590 | 0.602
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
56 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.375 0.369 | 0.380 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.029 0.021 | 0.035 |
0.596 0.590 | 0.602 |
| 1 spectrum, QEFEER | 0.000 | 0.000 | 0.000 | 0.282 | 0.000 | 0.000 | 0.000 | 0.718 | ||
| 2 spectra, NQHLAK | 0.000 | 0.000 | 0.000 | 0.193 | 0.000 | 0.251 | 0.149 | 0.407 | ||
| 3 spectra, SGVISGGASDLK | 0.000 | 0.000 | 0.000 | 0.277 | 0.000 | 0.208 | 0.148 | 0.367 | ||
| 1 spectrum, ENTSHK | 0.000 | 0.000 | 0.146 | 0.134 | 0.000 | 0.307 | 0.220 | 0.194 | ||
| 4 spectra, LIEIENFK | 0.000 | 0.000 | 0.000 | 0.456 | 0.000 | 0.000 | 0.000 | 0.544 | ||
| 1 spectrum, QSLEEQK | 0.000 | 0.000 | 0.000 | 0.255 | 0.077 | 0.061 | 0.106 | 0.502 | ||
| 5 spectra, AEEDTQFNYHR | 0.000 | 0.000 | 0.000 | 0.175 | 0.000 | 0.276 | 0.282 | 0.267 | ||
| 2 spectra, IDLEER | 0.000 | 0.000 | 0.078 | 0.450 | 0.000 | 0.000 | 0.000 | 0.472 | ||
| 2 spectra, QIIGPFQR | 0.000 | 0.000 | 0.000 | 0.338 | 0.000 | 0.000 | 0.000 | 0.662 | ||
| 1 spectrum, DLTLEENQVK | 0.000 | 0.000 | 0.000 | 0.470 | 0.000 | 0.000 | 0.000 | 0.530 | ||
| 3 spectra, SNLMDAISFVLGEK | 0.000 | 0.000 | 0.000 | 0.205 | 0.000 | 0.000 | 0.107 | 0.687 | ||
| 1 spectrum, SLQNAQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.154 | 0.433 | 0.000 | 0.413 | ||
| 3 spectra, AATLAQELEK | 0.000 | 0.000 | 0.000 | 0.194 | 0.000 | 0.000 | 0.000 | 0.806 | ||
| 2 spectra, YEPPHIK | 0.000 | 0.000 | 0.188 | 0.081 | 0.000 | 0.161 | 0.072 | 0.498 | ||
| 2 spectra, TALFEEISR | 0.000 | 0.000 | 0.000 | 0.181 | 0.000 | 0.000 | 0.043 | 0.776 | ||
| 1 spectrum, LGIQLDFEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.070 | 0.000 | 0.000 | 0.930 | ||
| 2 spectra, GDMDELEK | 0.000 | 0.000 | 0.000 | 0.363 | 0.000 | 0.000 | 0.015 | 0.622 | ||
| 1 spectrum, HNLLQACK | 0.000 | 0.000 | 0.038 | 0.688 | 0.000 | 0.000 | 0.091 | 0.182 | ||
| 2 spectra, MEEESQSQGR | 0.000 | 0.000 | 0.000 | 0.168 | 0.000 | 0.000 | 0.000 | 0.832 | ||
| 2 spectra, FQETSDEFEAAR | 0.000 | 0.000 | 0.000 | 0.128 | 0.000 | 0.000 | 0.057 | 0.815 | ||
| 2 spectra, VANYIK | 0.000 | 0.000 | 0.000 | 0.172 | 0.000 | 0.000 | 0.000 | 0.828 | ||
| 2 spectra, ELNQVMEQLGDAR | 0.000 | 0.000 | 0.000 | 0.368 | 0.000 | 0.000 | 0.000 | 0.632 | ||
| 1 spectrum, VVQLHEYSEELEK | 0.263 | 0.000 | 0.117 | 0.206 | 0.000 | 0.000 | 0.104 | 0.310 | ||
| 3 spectra, YSQSDLEQTK | 0.000 | 0.000 | 0.000 | 0.265 | 0.000 | 0.000 | 0.000 | 0.735 | ||
| 4 spectra, RPQYIK | 0.000 | 0.000 | 0.000 | 0.403 | 0.000 | 0.000 | 0.004 | 0.593 | ||
| 1 spectrum, EQQQIEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.402 | 0.392 | 0.206 | ||
| 2 spectra, LYPGSVYGR | 0.000 | 0.000 | 0.000 | 0.249 | 0.000 | 0.000 | 0.000 | 0.751 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
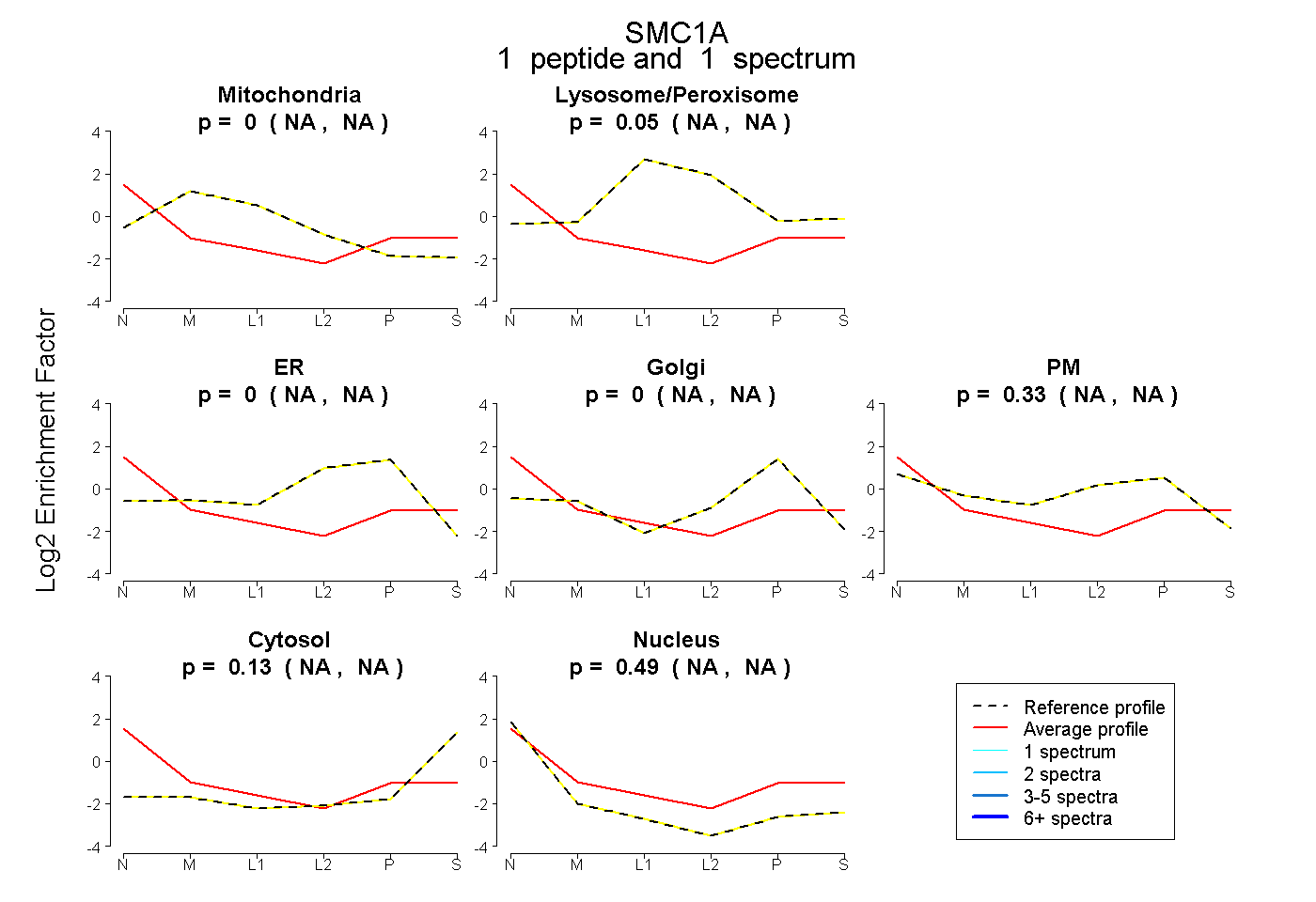 |
0.000 NA | NA |
0.050 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.330 NA | NA |
0.130 NA | NA |
0.490 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
4 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |