peptides
spectra
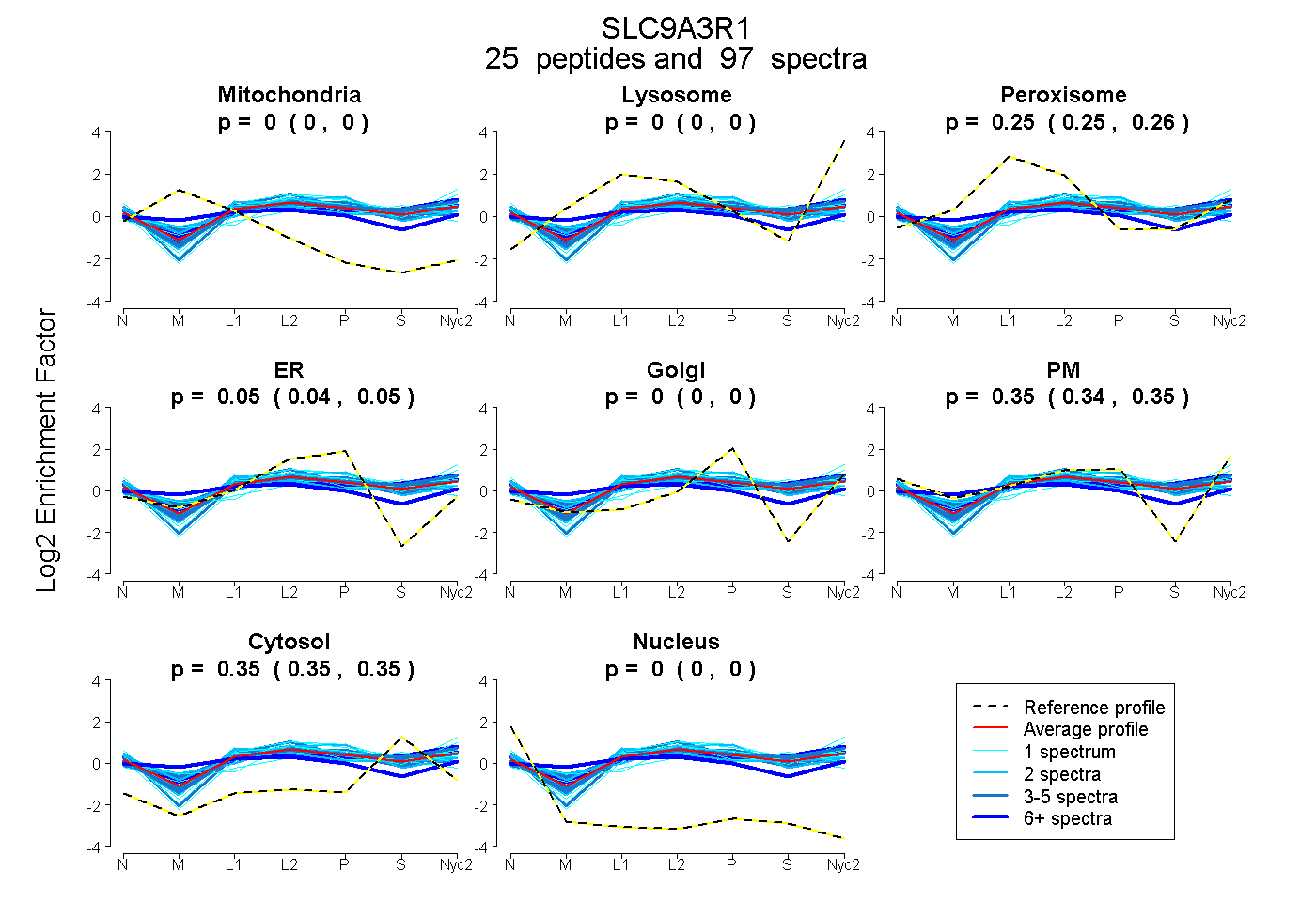
0.000 | 0.000
0.000 | 0.000
0.252 | 0.257
0.041 | 0.051
0.000 | 0.000
0.344 | 0.354
0.347 | 0.351
0.000 | 0.000
peptides
spectra
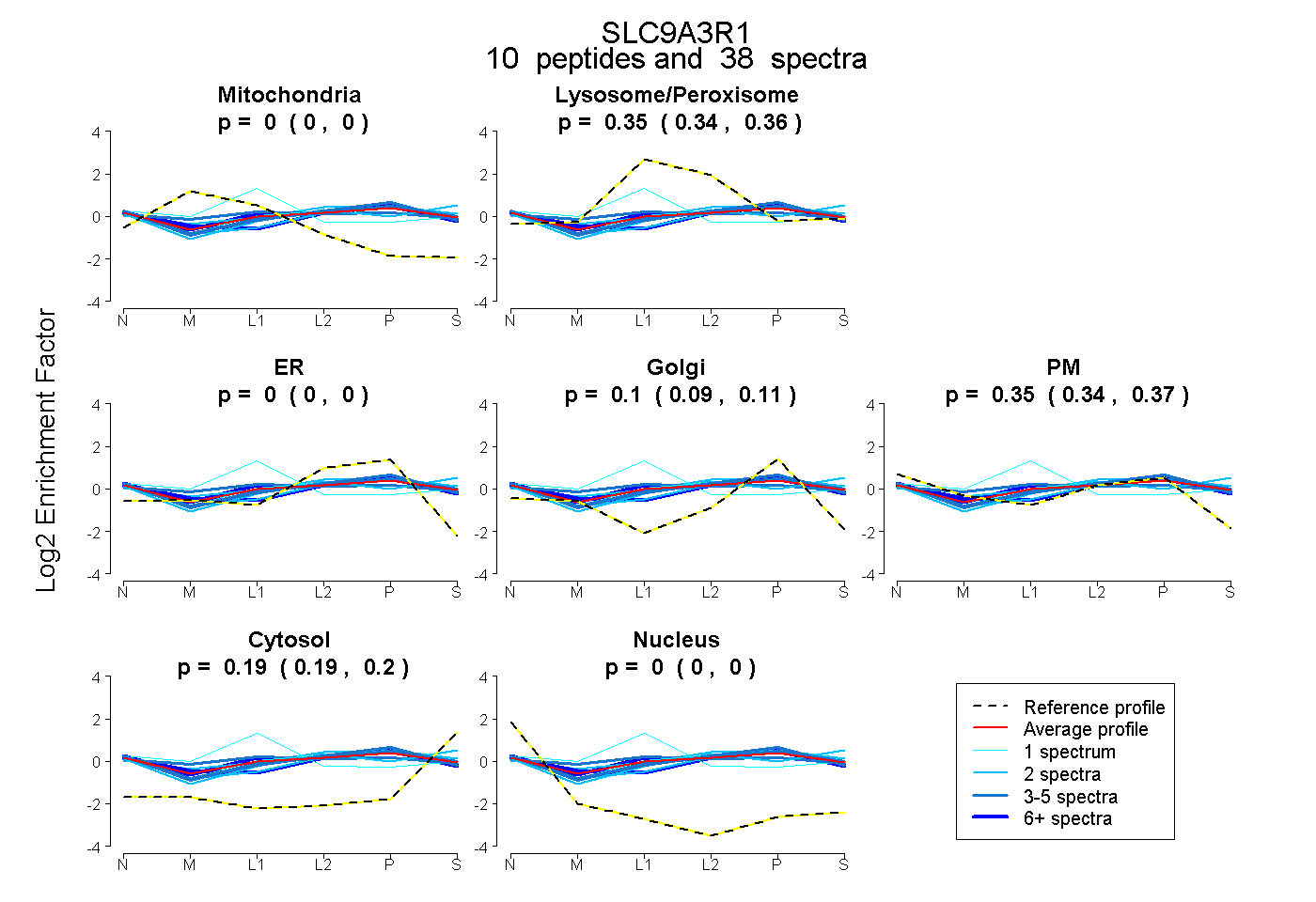
0.000 | 0.000
0.339 | 0.358
0.000 | 0.000
0.088 | 0.114
0.339 | 0.367
0.188 | 0.199
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
97 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.255 0.252 | 0.257 |
0.046 0.041 | 0.051 |
0.000 0.000 | 0.000 |
0.350 0.344 | 0.354 |
0.349 0.347 | 0.351 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
38 spectra |
 |
0.000 0.000 | 0.000 |
0.350 0.339 | 0.358 |
0.000 0.000 | 0.000 |
0.102 0.088 | 0.114 |
0.354 0.339 | 0.367 |
0.194 0.188 | 0.199 |
0.000 0.000 | 0.000 |
| 5 spectra, VGQFIR | 0.000 | 0.335 | 0.000 | 0.115 | 0.349 | 0.202 | 0.000 | |||
| 8 spectra, EALVEPASESPRPALAR | 0.000 | 0.258 | 0.000 | 0.170 | 0.392 | 0.180 | 0.000 | |||
| 2 spectra, LCCLEK | 0.000 | 0.352 | 0.000 | 0.000 | 0.324 | 0.323 | 0.000 | |||
| 1 spectrum, SADAAAGEPLPR | 0.119 | 0.579 | 0.000 | 0.022 | 0.065 | 0.109 | 0.105 | |||
| 2 spectra, AVDPDSPAEASGLR | 0.000 | 0.390 | 0.000 | 0.183 | 0.282 | 0.144 | 0.000 | |||
| 2 spectra, SGLLAGDR | 0.000 | 0.299 | 0.000 | 0.184 | 0.289 | 0.227 | 0.000 | |||
| 10 spectra, AALNAVR | 0.000 | 0.374 | 0.000 | 0.164 | 0.313 | 0.149 | 0.000 | |||
| 3 spectra, SKPGQFIR | 0.000 | 0.341 | 0.000 | 0.222 | 0.292 | 0.146 | 0.000 | |||
| 1 spectrum, LVEPGSPAEK | 0.000 | 0.364 | 0.000 | 0.169 | 0.325 | 0.142 | 0.000 | |||
| 4 spectra, GPNGYGFHLHGEK | 0.000 | 0.375 | 0.000 | 0.043 | 0.383 | 0.198 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
253 spectra |
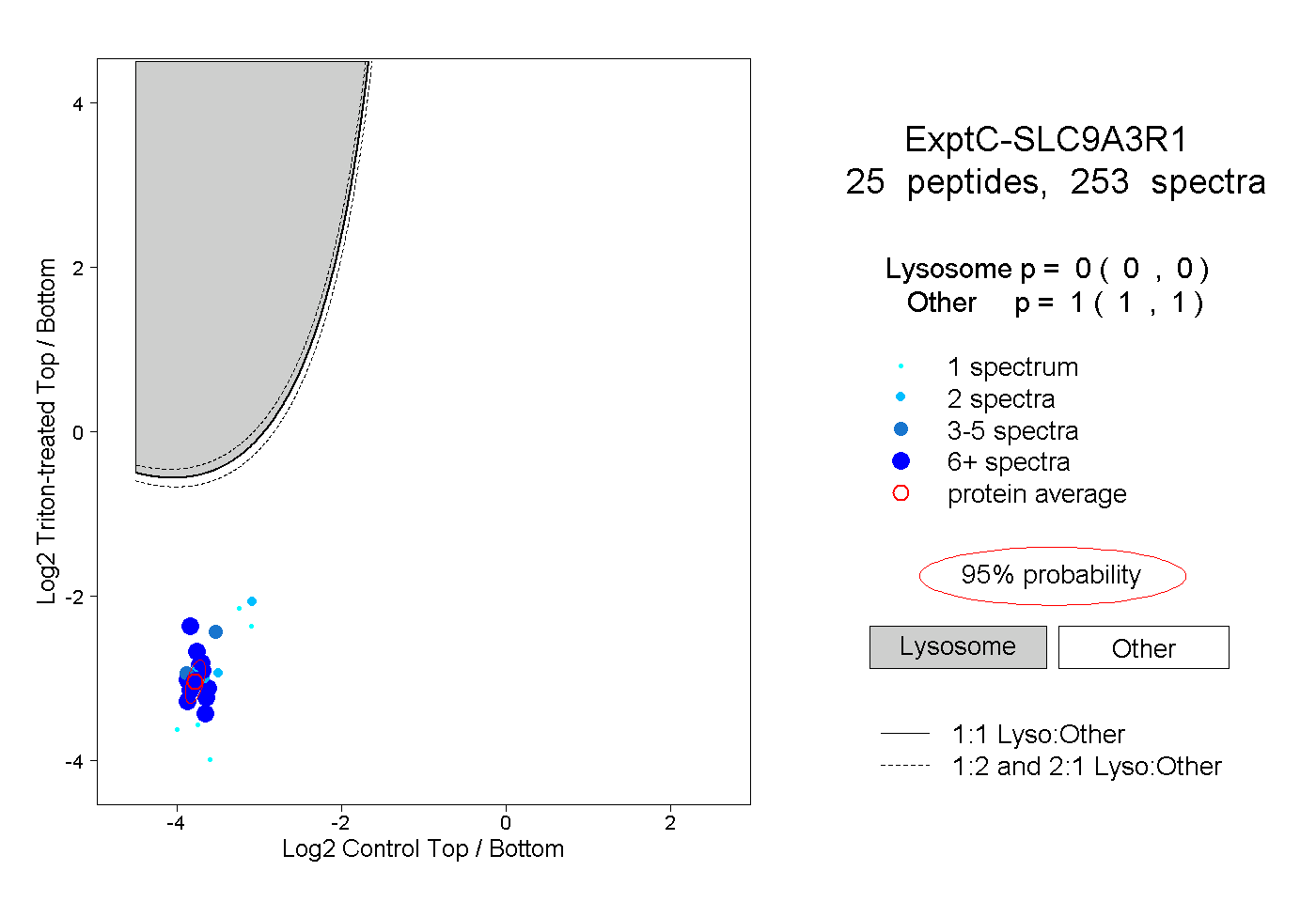 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
33 spectra |
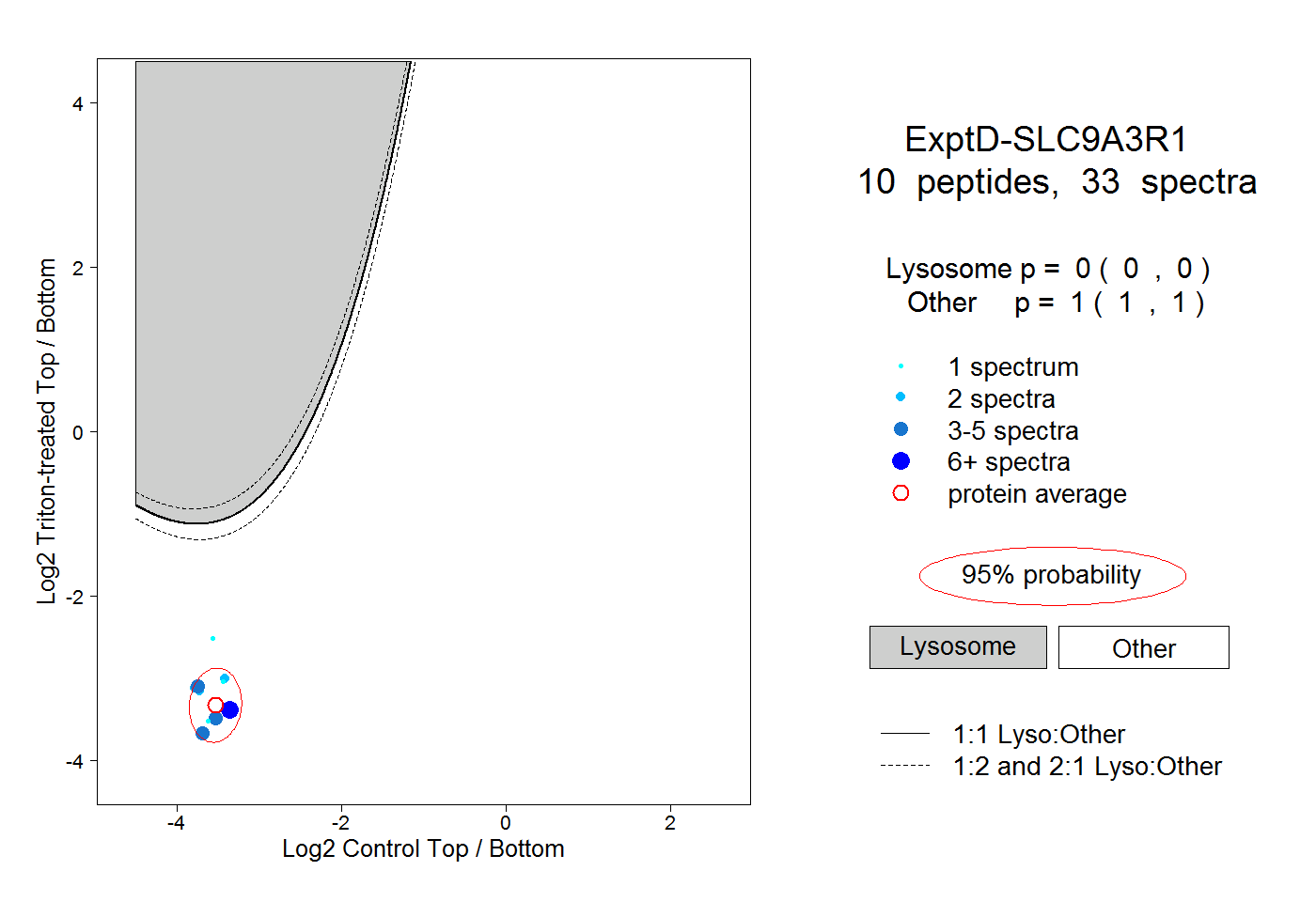 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |