peptides
spectra
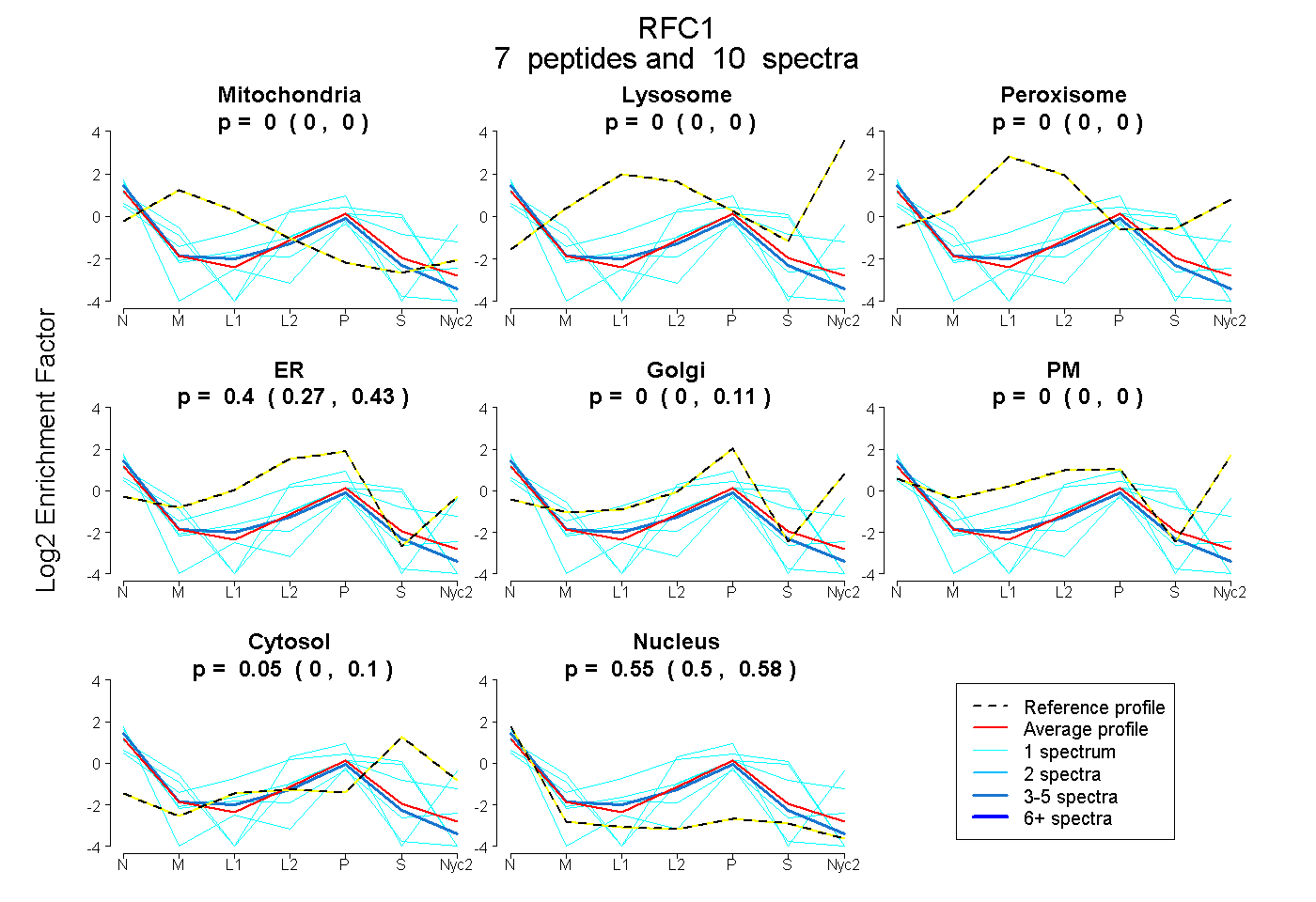
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.269 | 0.426
0.000 | 0.107
0.000 | 0.000
0.000 | 0.103
0.505 | 0.585
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
10 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.398 0.269 | 0.426 |
0.000 0.000 | 0.107 |
0.000 0.000 | 0.000 |
0.048 0.000 | 0.103 |
0.553 0.505 | 0.585 |
| 1 spectrum, AADSICDGDLVDNQIR | 0.000 | 0.000 | 0.000 | 0.190 | 0.000 | 0.000 | 0.323 | 0.487 | ||
| 1 spectrum, DALVRPLTSQGVEGVQR | 0.000 | 0.000 | 0.000 | 0.208 | 0.167 | 0.000 | 0.000 | 0.626 | ||
| 1 spectrum, GFYTSGASPSVSAR | 0.000 | 0.000 | 0.000 | 0.071 | 0.060 | 0.000 | 0.000 | 0.869 | ||
| 1 spectrum, HALIMDEVDGMAGNEDR | 0.029 | 0.000 | 0.000 | 0.392 | 0.000 | 0.000 | 0.336 | 0.243 | ||
| 4 spectra, HLMLLSR | 0.000 | 0.000 | 0.000 | 0.380 | 0.000 | 0.000 | 0.000 | 0.620 | ||
| 1 spectrum, EECLLWVDK | 0.000 | 0.000 | 0.000 | 0.048 | 0.650 | 0.000 | 0.000 | 0.302 | ||
| 1 spectrum, DDGSSFK | 0.000 | 0.000 | 0.000 | 0.100 | 0.159 | 0.151 | 0.270 | 0.321 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
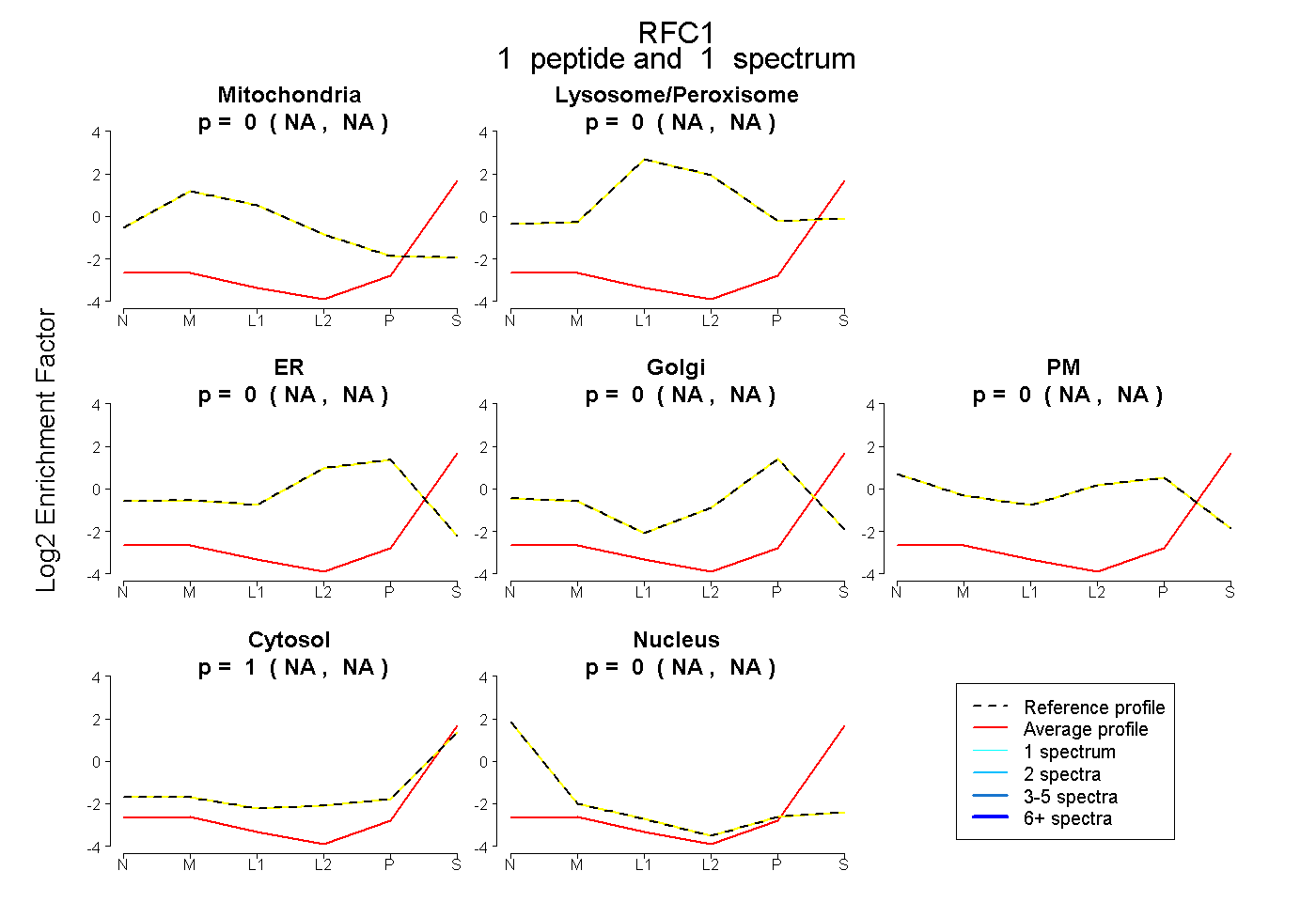 |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
1.000 NA | NA |
0.000 NA | NA |