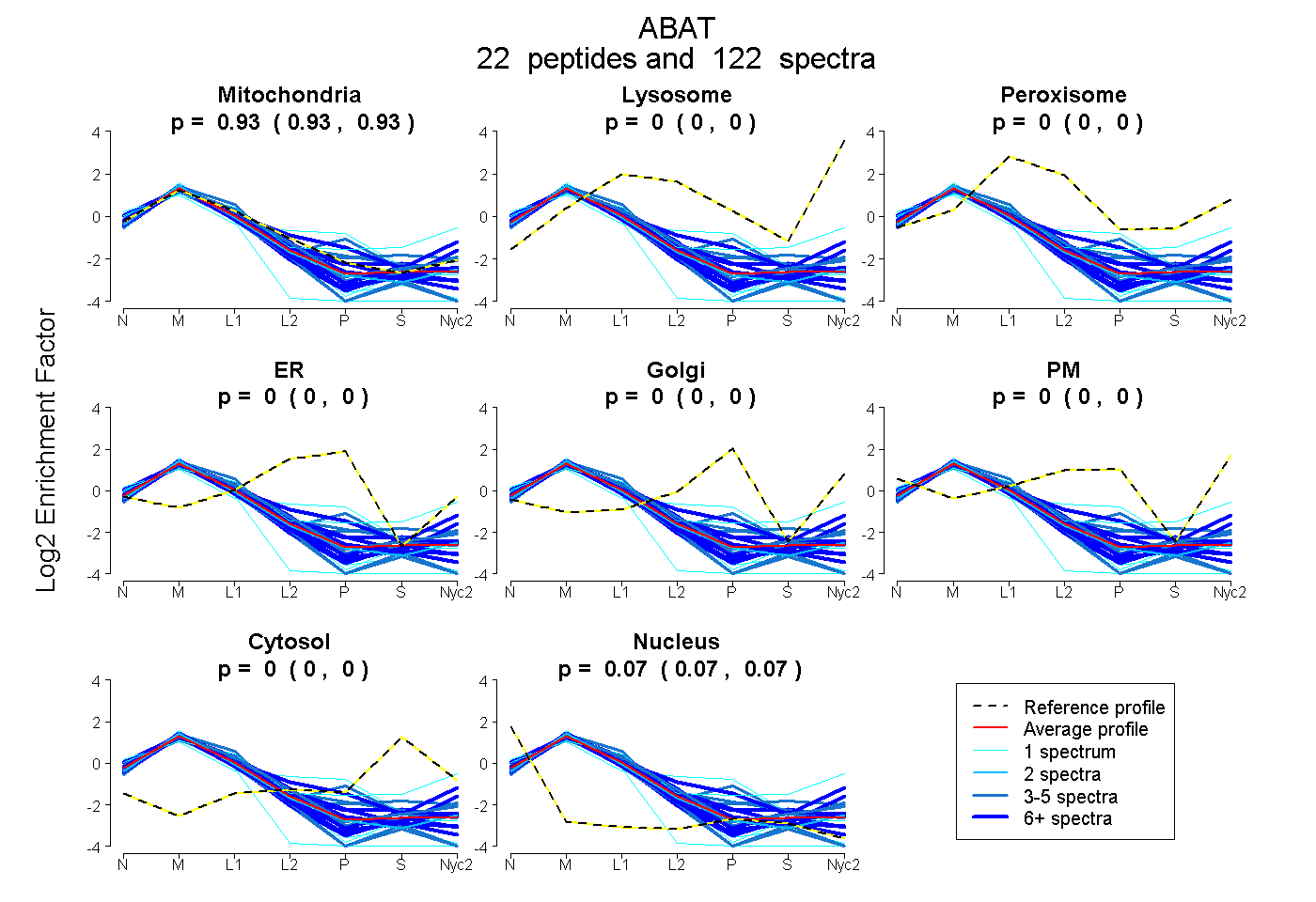
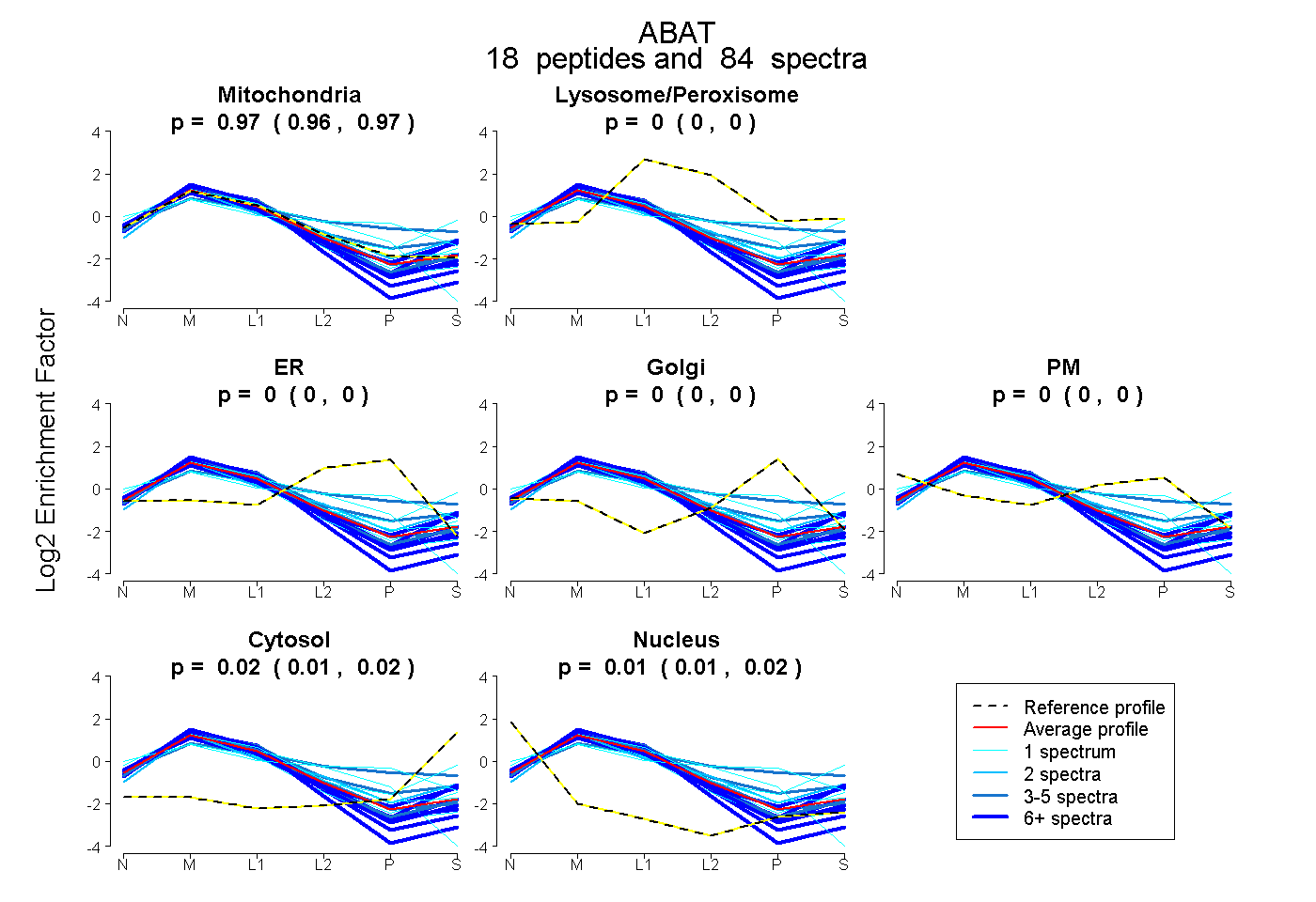
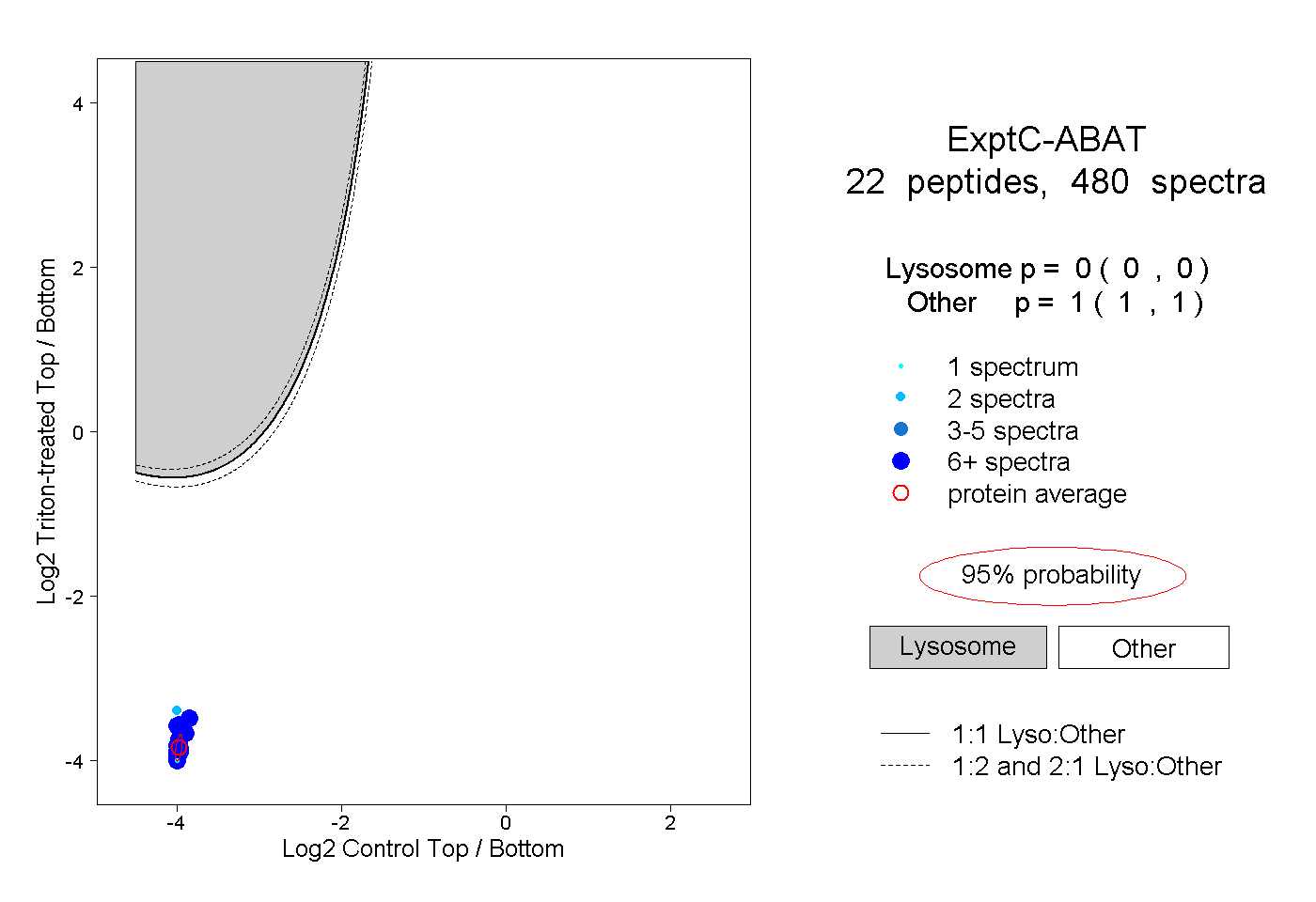
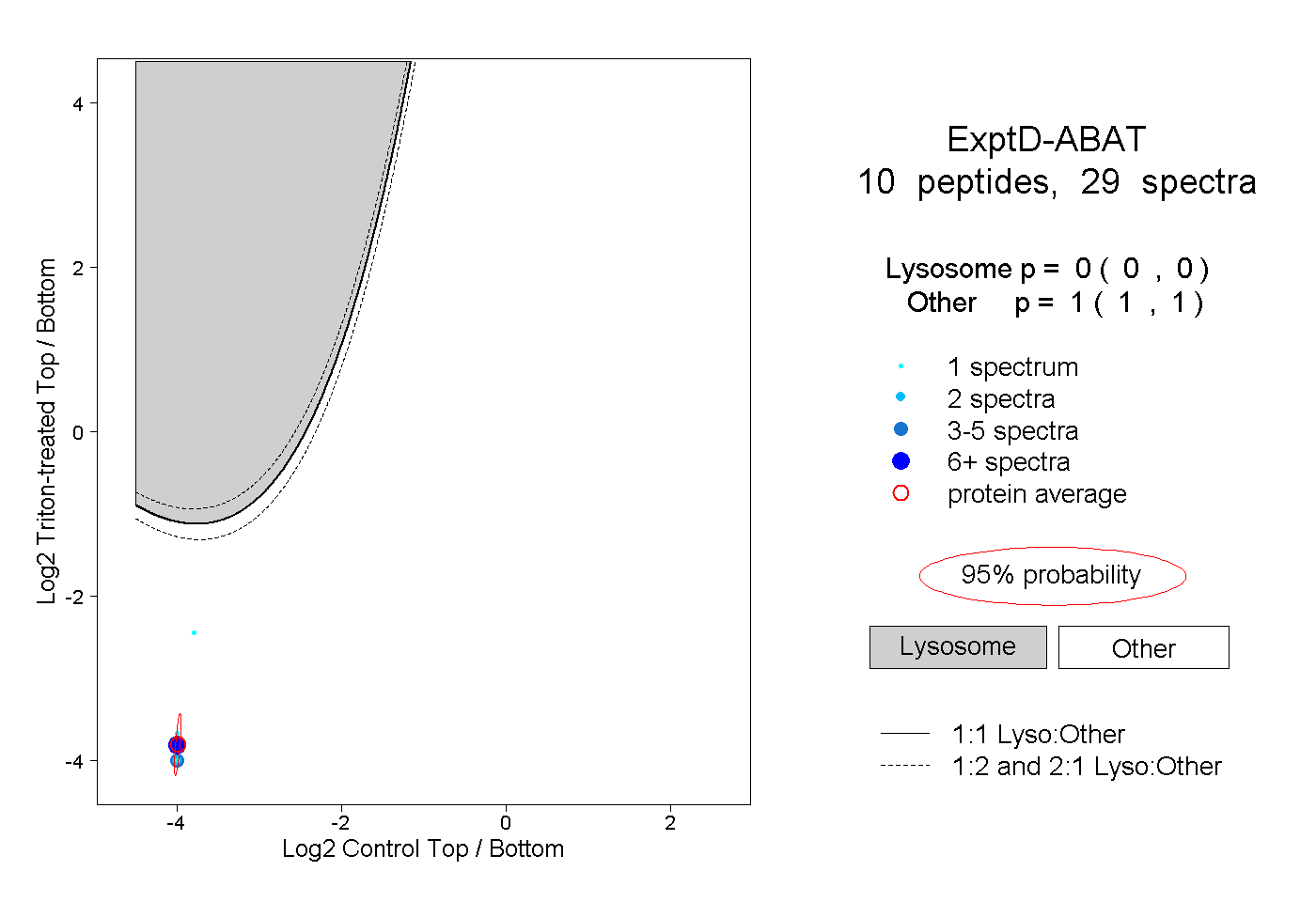
| 2 spectra, GMCQLITMACGSCSNENAFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 44 spectra, TEVPGPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 35 spectra, GTFCSFDTPDEAIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, HGCAFLVDEVQTGGGCTGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 23 spectra, GVVLGGCGDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, IFNTWLGDPSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, IDIPSFDWPIAPFPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 40 spectra, GNYLVDVDGNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 17 spectra, TMGCLATTHSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, CLEEVEDLIVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 29 spectra, ESLMSVAPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TVAGIIVEPIQSEGGDNHASDDFFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, NLLLAEVINIIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 41 spectra, EEFRPSAPYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 53 spectra, FRPTLVFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 62 spectra, LLLLAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 30 spectra, QLNTIQNAEAVHFFCNYEESR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 18 spectra, TIFMWYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 20 spectra, MMTGGFFHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, SQELMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, VDFEFDYDGPLMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 22 spectra, EDLLNNVAHAGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |