peptides
spectra
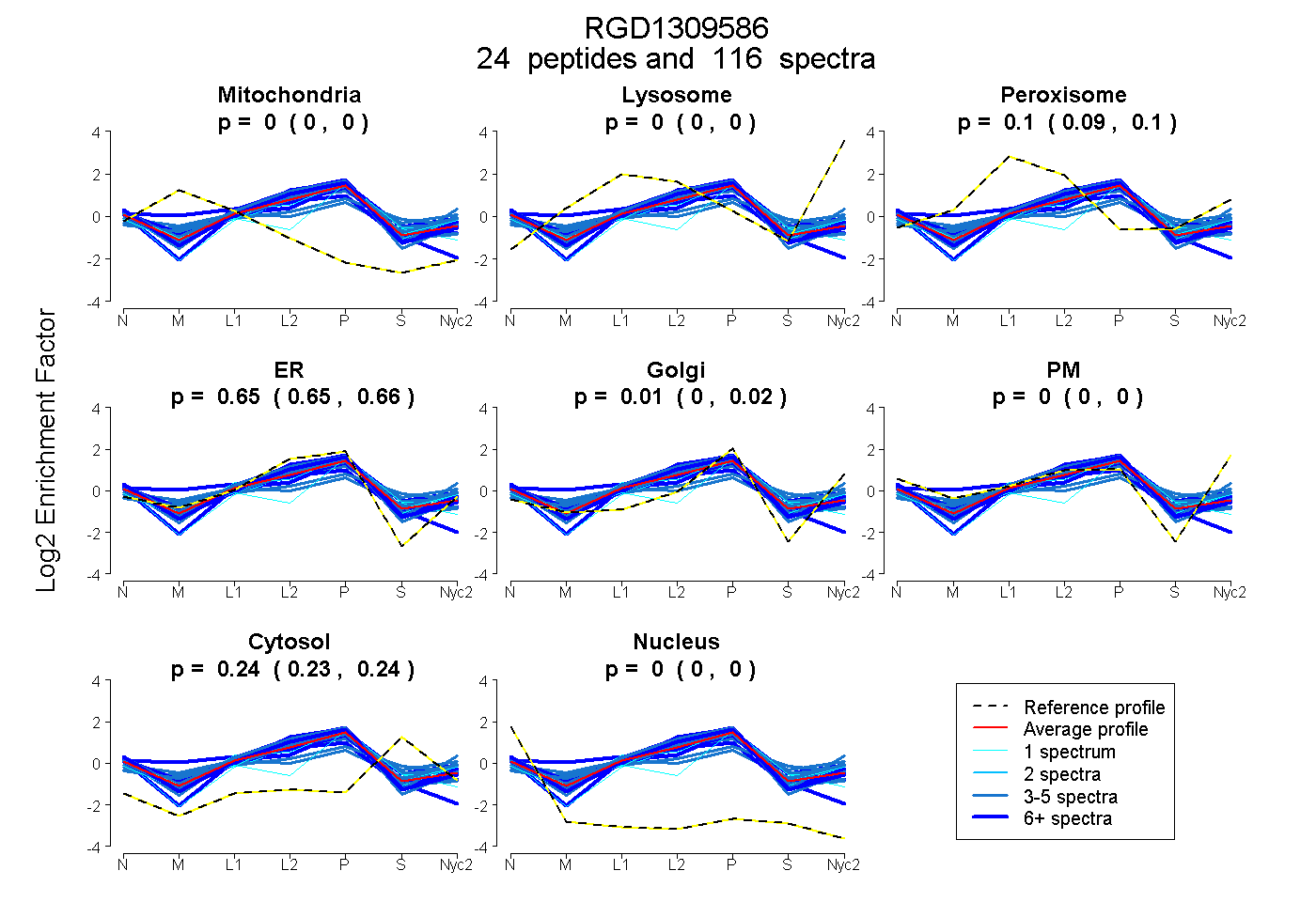
0.000 | 0.000
0.000 | 0.000
0.094 | 0.100
0.645 | 0.664
0.000 | 0.017
0.000 | 0.000
0.235 | 0.240
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
116 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.097 0.094 | 0.100 |
0.655 0.645 | 0.664 |
0.010 0.000 | 0.017 |
0.000 0.000 | 0.000 |
0.238 0.235 | 0.240 |
0.000 0.000 | 0.000 |
| 1 spectrum, QEVPSWLENMAFEHHYK | 0.000 | 0.000 | 0.125 | 0.573 | 0.032 | 0.000 | 0.270 | 0.000 | ||
| 5 spectra, VGSTSENITQK | 0.000 | 0.000 | 0.042 | 0.790 | 0.000 | 0.020 | 0.148 | 0.000 | ||
| 1 spectrum, YIPPHLR | 0.000 | 0.000 | 0.141 | 0.019 | 0.606 | 0.000 | 0.191 | 0.042 | ||
| 3 spectra, VGNLGLATSFFNER | 0.000 | 0.000 | 0.118 | 0.491 | 0.091 | 0.194 | 0.106 | 0.000 | ||
| 1 spectrum, NINITK | 0.000 | 0.000 | 0.045 | 0.683 | 0.000 | 0.085 | 0.188 | 0.000 | ||
| 3 spectra, DLMACAQTGSGK | 0.083 | 0.000 | 0.279 | 0.000 | 0.429 | 0.000 | 0.205 | 0.004 | ||
| 6 spectra, IGLDFCK | 0.053 | 0.000 | 0.044 | 0.650 | 0.000 | 0.000 | 0.186 | 0.067 | ||
| 4 spectra, GLDISNVK | 0.000 | 0.000 | 0.145 | 0.498 | 0.074 | 0.072 | 0.212 | 0.000 | ||
| 8 spectra, SPILVATAVAAR | 0.000 | 0.000 | 0.095 | 0.749 | 0.000 | 0.000 | 0.155 | 0.000 | ||
| 3 spectra, SFLLDLLNATGK | 0.000 | 0.000 | 0.073 | 0.529 | 0.000 | 0.166 | 0.232 | 0.000 | ||
| 4 spectra, HVINFDLPSDIEEYVHR | 0.000 | 0.000 | 0.159 | 0.339 | 0.070 | 0.063 | 0.369 | 0.000 | ||
| 4 spectra, YLVLDEADR | 0.000 | 0.000 | 0.114 | 0.526 | 0.042 | 0.096 | 0.223 | 0.000 | ||
| 6 spectra, ELAVQIYEEAR | 0.000 | 0.000 | 0.082 | 0.673 | 0.000 | 0.000 | 0.244 | 0.000 | ||
| 13 spectra, YTRPTPVQK | 0.000 | 0.000 | 0.034 | 0.770 | 0.000 | 0.000 | 0.196 | 0.000 | ||
| 6 spectra, DLLDLLVEAK | 0.000 | 0.000 | 0.079 | 0.672 | 0.000 | 0.000 | 0.249 | 0.000 | ||
| 4 spectra, IVEQDTMPPK | 0.000 | 0.000 | 0.103 | 0.591 | 0.019 | 0.000 | 0.286 | 0.000 | ||
| 1 spectrum, HAIPIIK | 0.000 | 0.000 | 0.000 | 0.658 | 0.000 | 0.000 | 0.342 | 0.000 | ||
| 4 spectra, HTMMFSATFPK | 0.000 | 0.000 | 0.282 | 0.298 | 0.203 | 0.000 | 0.216 | 0.000 | ||
| 4 spectra, EIQMLAR | 0.000 | 0.000 | 0.080 | 0.726 | 0.000 | 0.000 | 0.194 | 0.000 | ||
| 12 spectra, QYPISLVLAPTR | 0.000 | 0.000 | 0.036 | 0.778 | 0.000 | 0.000 | 0.186 | 0.000 | ||
| 4 spectra, LVDMMER | 0.000 | 0.000 | 0.058 | 0.731 | 0.000 | 0.000 | 0.212 | 0.000 | ||
| 6 spectra, GCHLLVATPGR | 0.122 | 0.000 | 0.221 | 0.442 | 0.104 | 0.000 | 0.112 | 0.000 | ||
| 3 spectra, DFLDEYIFLAVGR | 0.000 | 0.000 | 0.049 | 0.719 | 0.000 | 0.000 | 0.232 | 0.000 | ||
| 10 spectra, FSGGFGAR | 0.000 | 0.000 | 0.049 | 0.443 | 0.136 | 0.054 | 0.317 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
62 spectra |
 |
0.000 0.000 | 0.000 |
0.369 0.361 | 0.375 |
0.288 0.274 | 0.300 |
0.320 0.308 | 0.330 |
0.023 0.014 | 0.031 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
141 spectra |
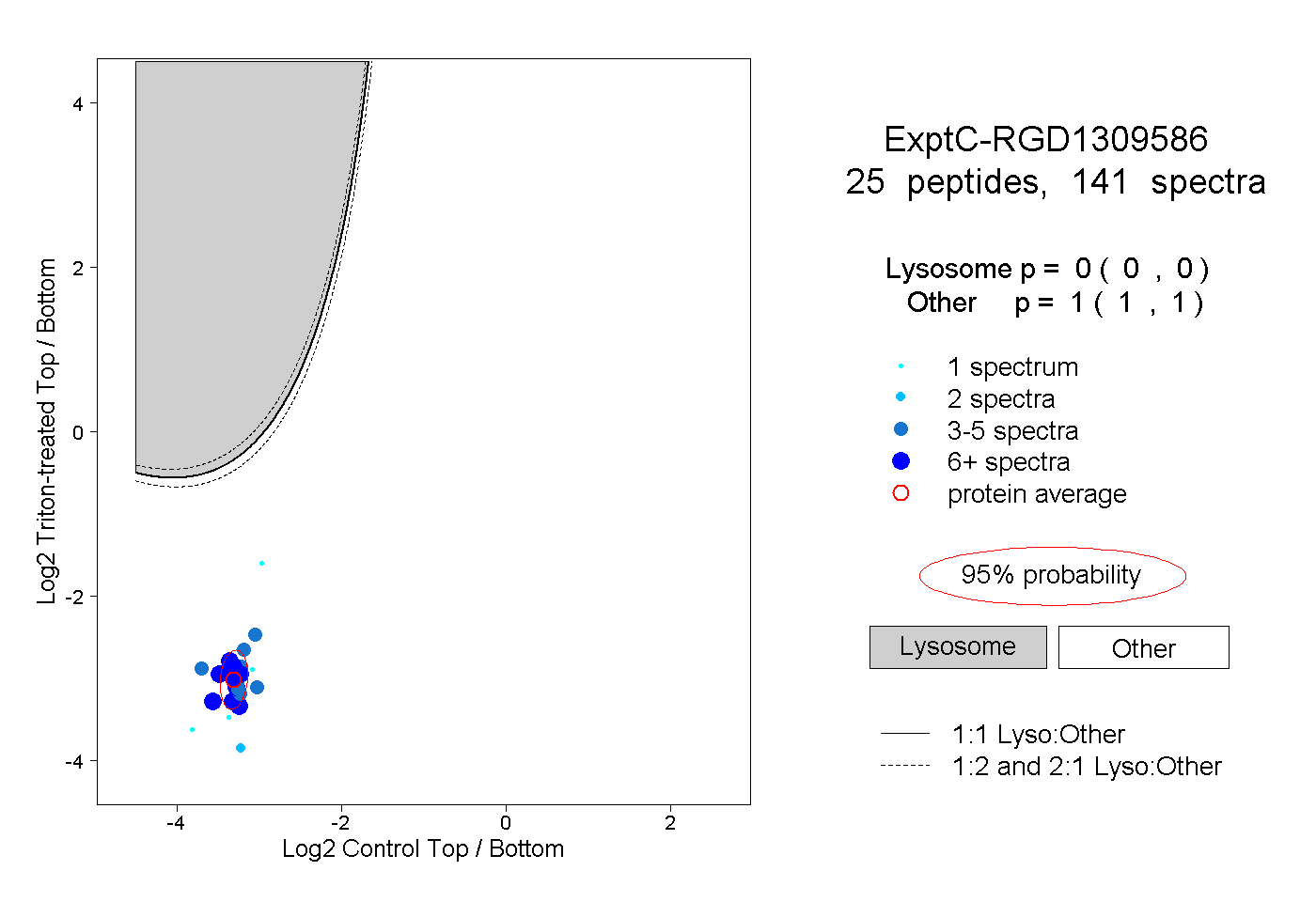 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
13 spectra |
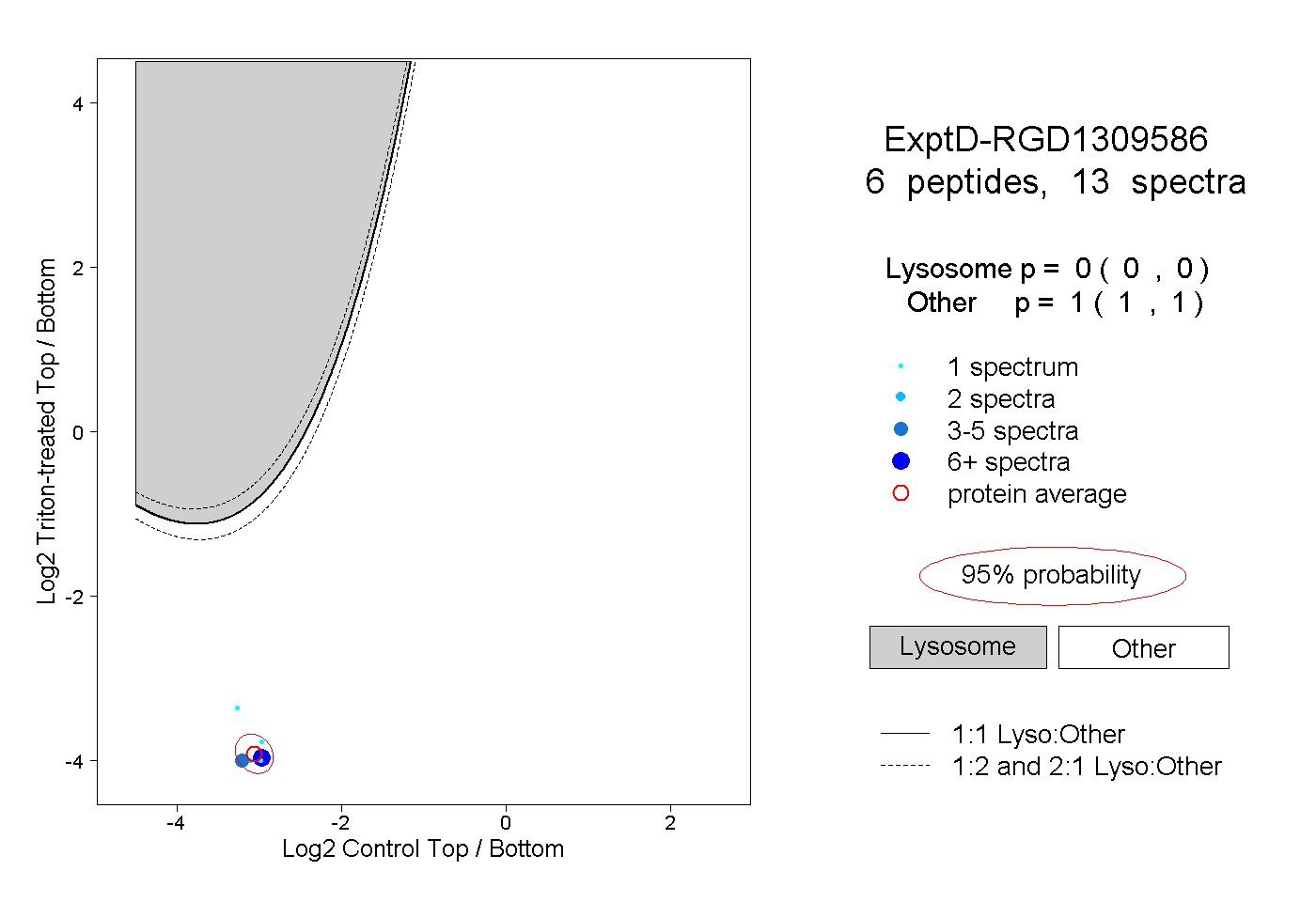 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |