peptides
spectra
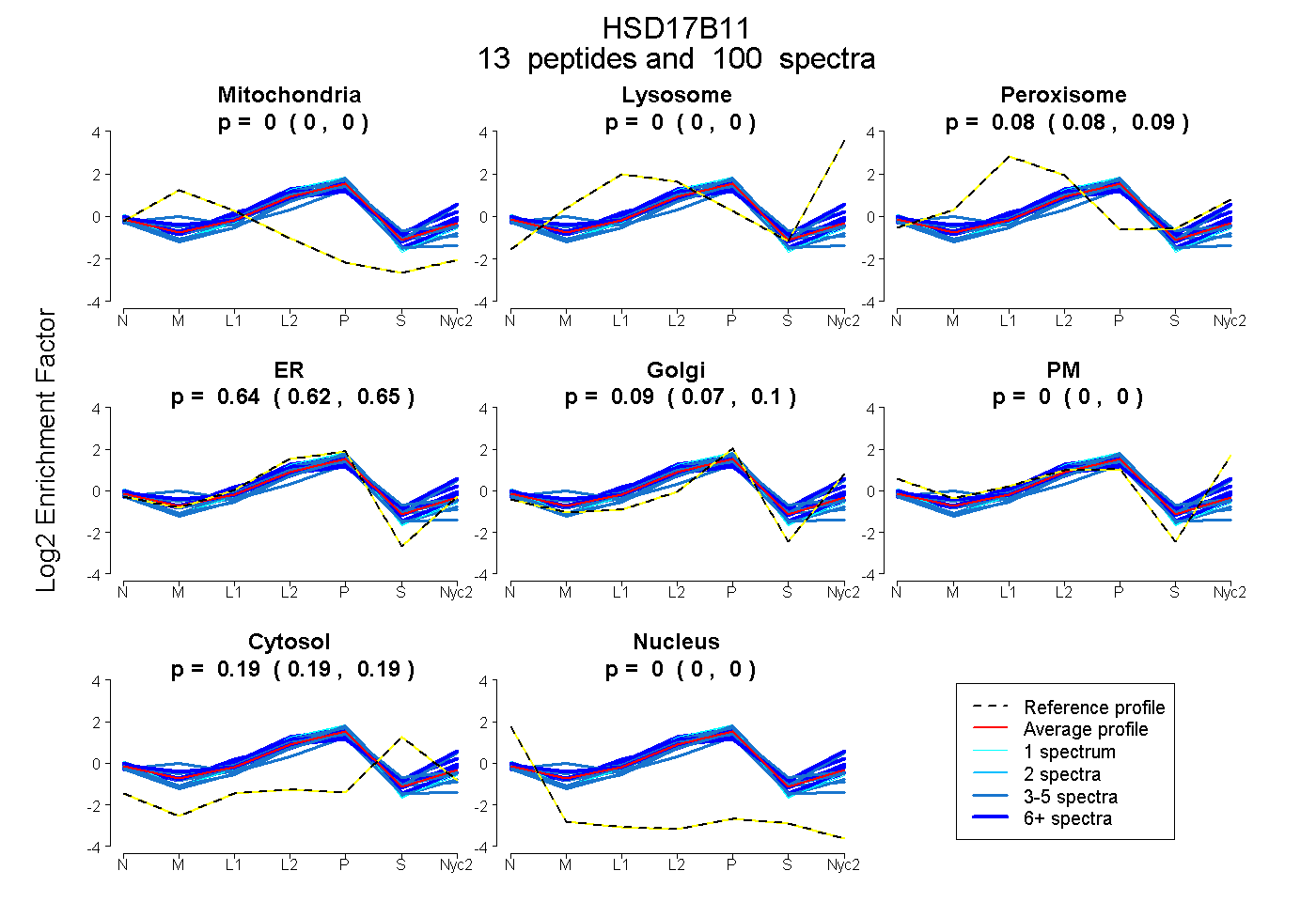
0.000 | 0.000
0.000 | 0.000
0.077 | 0.087
0.621 | 0.652
0.074 | 0.102
0.000 | 0.000
0.186 | 0.194
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
100 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.083 0.077 | 0.087 |
0.637 0.621 | 0.652 |
0.089 0.074 | 0.102 |
0.000 0.000 | 0.000 |
0.191 0.186 | 0.194 |
0.000 0.000 | 0.000 |
| 3 spectra, LVLWDINK | 0.000 | 0.000 | 0.000 | 0.668 | 0.094 | 0.000 | 0.238 | 0.000 | ||
| 17 spectra, LTAYEFAK | 0.000 | 0.000 | 0.138 | 0.456 | 0.000 | 0.203 | 0.203 | 0.000 | ||
| 5 spectra, FDAVVGYK | 0.000 | 0.000 | 0.000 | 0.833 | 0.000 | 0.000 | 0.153 | 0.013 | ||
| 18 spectra, AFLPAMMK | 0.000 | 0.000 | 0.095 | 0.519 | 0.183 | 0.000 | 0.203 | 0.000 | ||
| 3 spectra, TFEVNVLAHFWTTK | 0.000 | 0.000 | 0.004 | 0.635 | 0.055 | 0.006 | 0.300 | 0.000 | ||
| 7 spectra, SVAGEIVLITGAGHGIGR | 0.000 | 0.009 | 0.178 | 0.178 | 0.234 | 0.237 | 0.164 | 0.000 | ||
| 6 spectra, EEIYSAVR | 0.000 | 0.000 | 0.157 | 0.472 | 0.238 | 0.000 | 0.133 | 0.000 | ||
| 24 spectra, FAAVGFHR | 0.000 | 0.000 | 0.086 | 0.784 | 0.000 | 0.000 | 0.130 | 0.000 | ||
| 1 spectrum, FLDVLK | 0.000 | 0.000 | 0.000 | 0.863 | 0.000 | 0.000 | 0.137 | 0.000 | ||
| 5 spectra, LGAQVHPFVVDCSQR | 0.213 | 0.000 | 0.000 | 0.623 | 0.006 | 0.000 | 0.158 | 0.000 | ||
| 5 spectra, ALTDELAALGCTGVR | 0.000 | 0.000 | 0.000 | 0.759 | 0.000 | 0.000 | 0.241 | 0.000 | ||
| 5 spectra, NGIEETAAK | 0.000 | 0.030 | 0.151 | 0.308 | 0.238 | 0.149 | 0.123 | 0.000 | ||
| 1 spectrum, FDLVIK | 0.000 | 0.000 | 0.000 | 0.855 | 0.000 | 0.000 | 0.145 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
27 spectra |
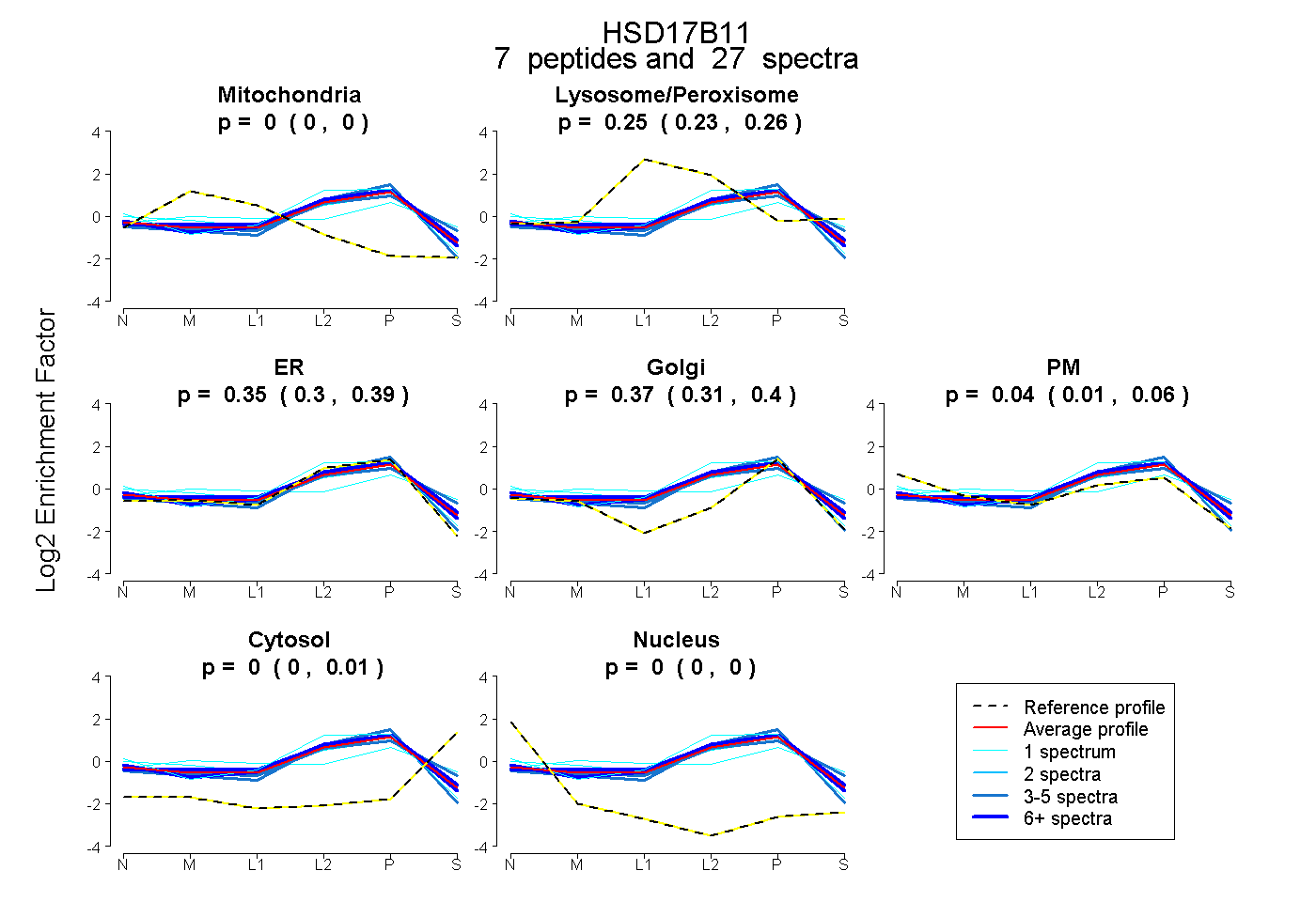 |
0.000 0.000 | 0.000 |
0.246 0.225 | 0.264 |
0.347 0.304 | 0.386 |
0.365 0.315 | 0.403 |
0.036 0.009 | 0.060 |
0.005 0.000 | 0.015 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
178 spectra |
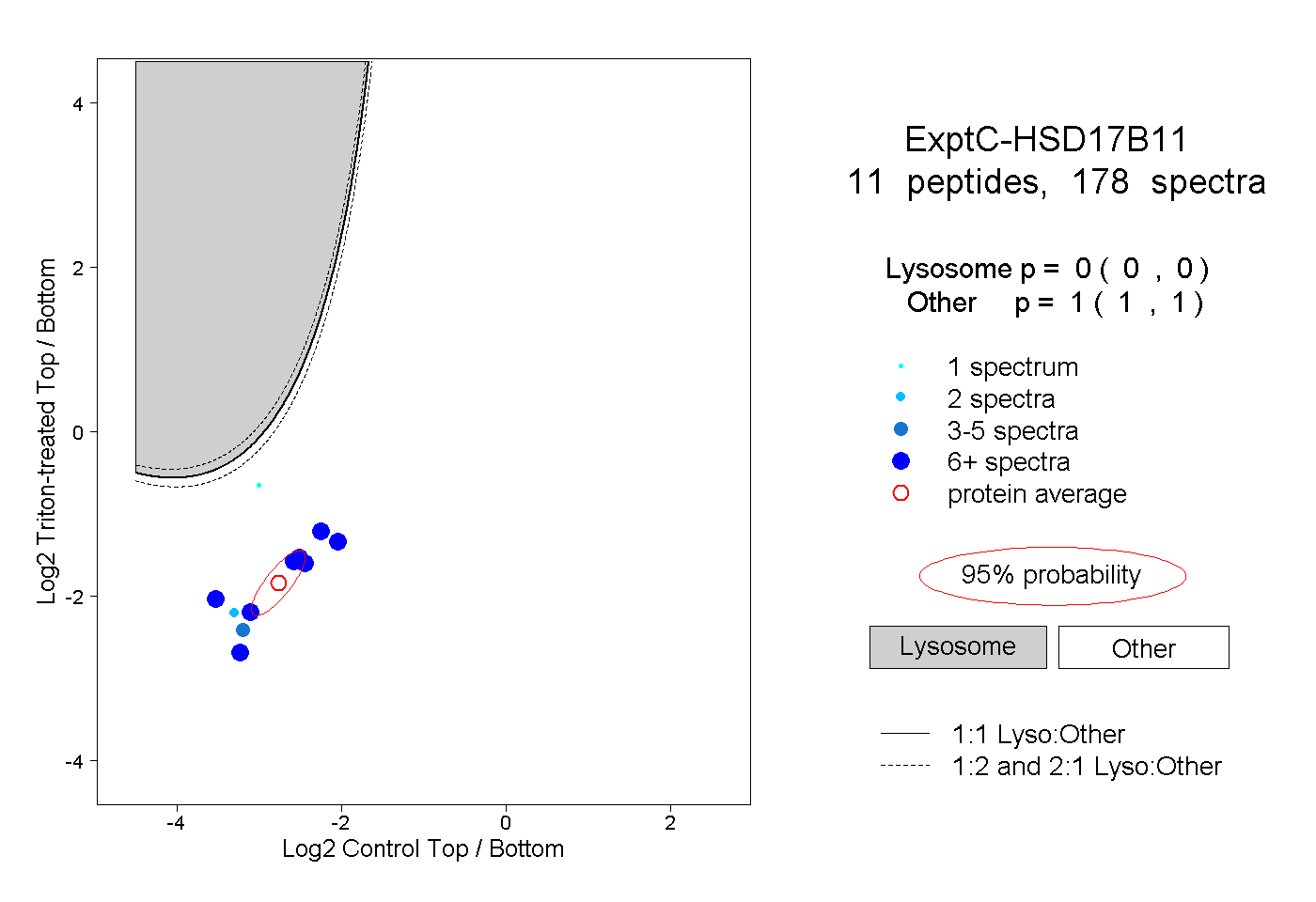 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
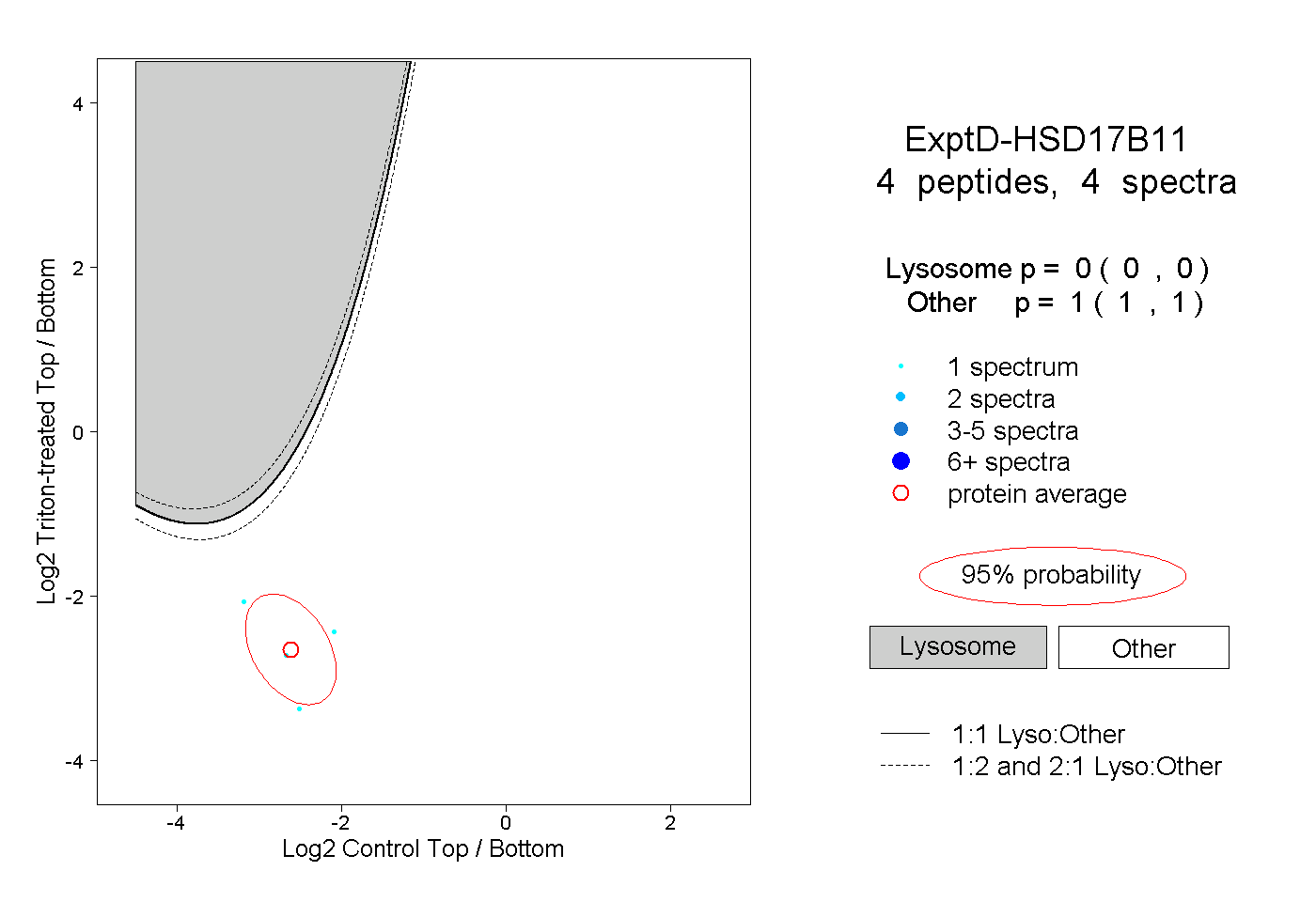 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |