peptides
spectra
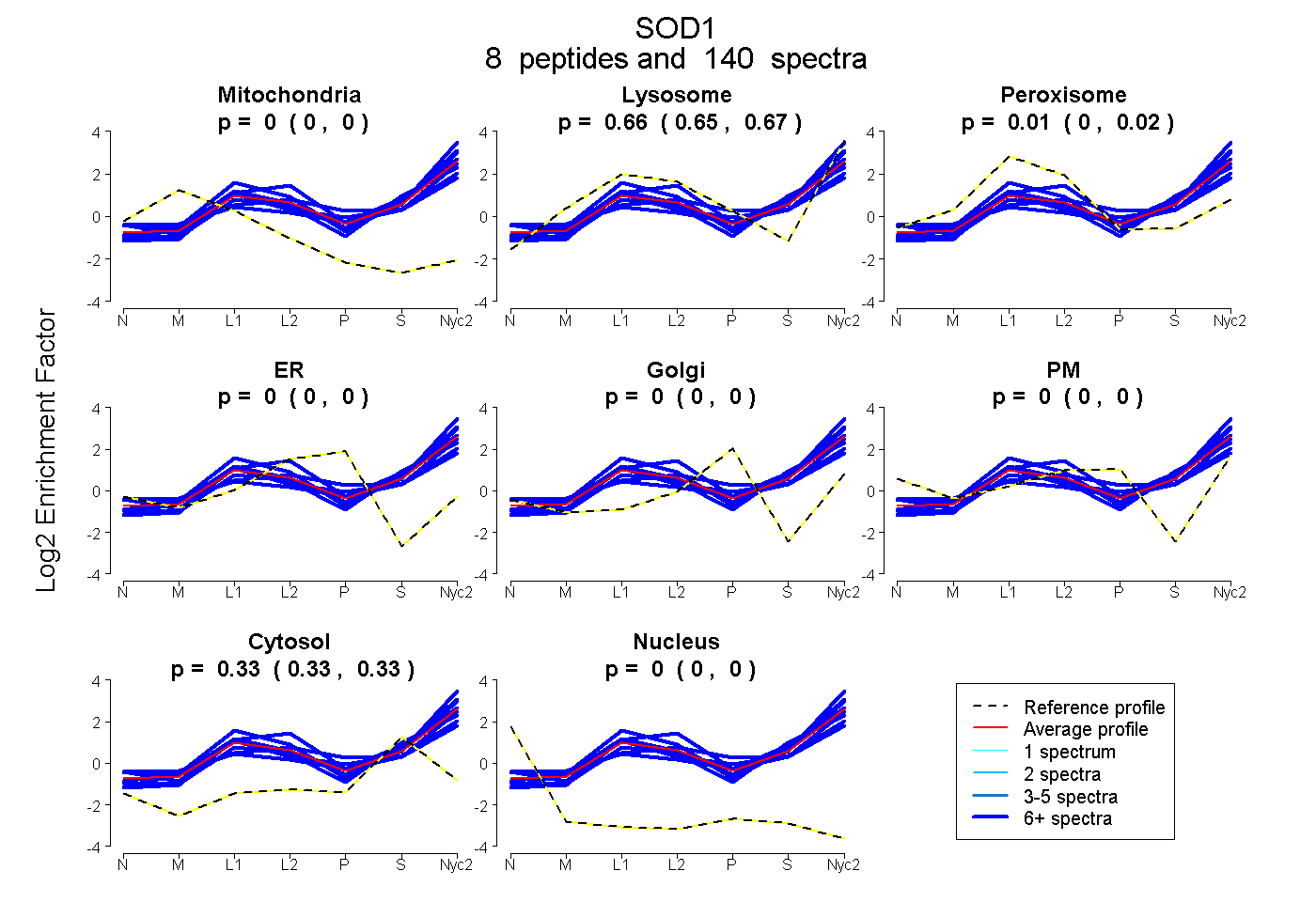
0.000 | 0.000
0.650 | 0.667
0.000 | 0.017
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.328 | 0.334
0.000 | 0.000
peptides
spectra

0.000 | 0.000
0.327 | 0.332
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.668 | 0.672
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
140 spectra |
 |
0.000 0.000 | 0.000 |
0.659 0.650 | 0.667 |
0.009 0.000 | 0.017 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.332 0.328 | 0.334 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
74 spectra |
 |
0.000 0.000 | 0.000 |
0.330 0.327 | 0.332 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.670 0.668 | 0.672 |
0.000 0.000 | 0.000 |
| 19 spectra, VISLSGEHSIIGR | 0.000 | 0.357 | 0.000 | 0.000 | 0.000 | 0.643 | 0.000 | |||
| 14 spectra, DGVANVSIEDR | 0.000 | 0.298 | 0.000 | 0.000 | 0.000 | 0.702 | 0.000 | |||
| 9 spectra, GDGPVQGVIHFEQK | 0.000 | 0.306 | 0.000 | 0.000 | 0.000 | 0.694 | 0.000 | |||
| 3 spectra, LACGVIGIAQ | 0.000 | 0.205 | 0.000 | 0.000 | 0.000 | 0.795 | 0.000 | |||
| 1 spectrum, HGGPADEER | 0.000 | 0.226 | 0.000 | 0.000 | 0.000 | 0.774 | 0.000 | |||
| 4 spectra, QDDLGK | 0.000 | 0.358 | 0.000 | 0.044 | 0.000 | 0.598 | 0.000 | |||
| 9 spectra, TMVVHEK | 0.000 | 0.306 | 0.000 | 0.072 | 0.000 | 0.622 | 0.000 | |||
| 6 spectra, AVCVLK | 0.000 | 0.313 | 0.000 | 0.000 | 0.000 | 0.687 | 0.000 | |||
| 9 spectra, HVGDLGNVAAGK | 0.010 | 0.402 | 0.000 | 0.034 | 0.000 | 0.554 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1729 spectra |
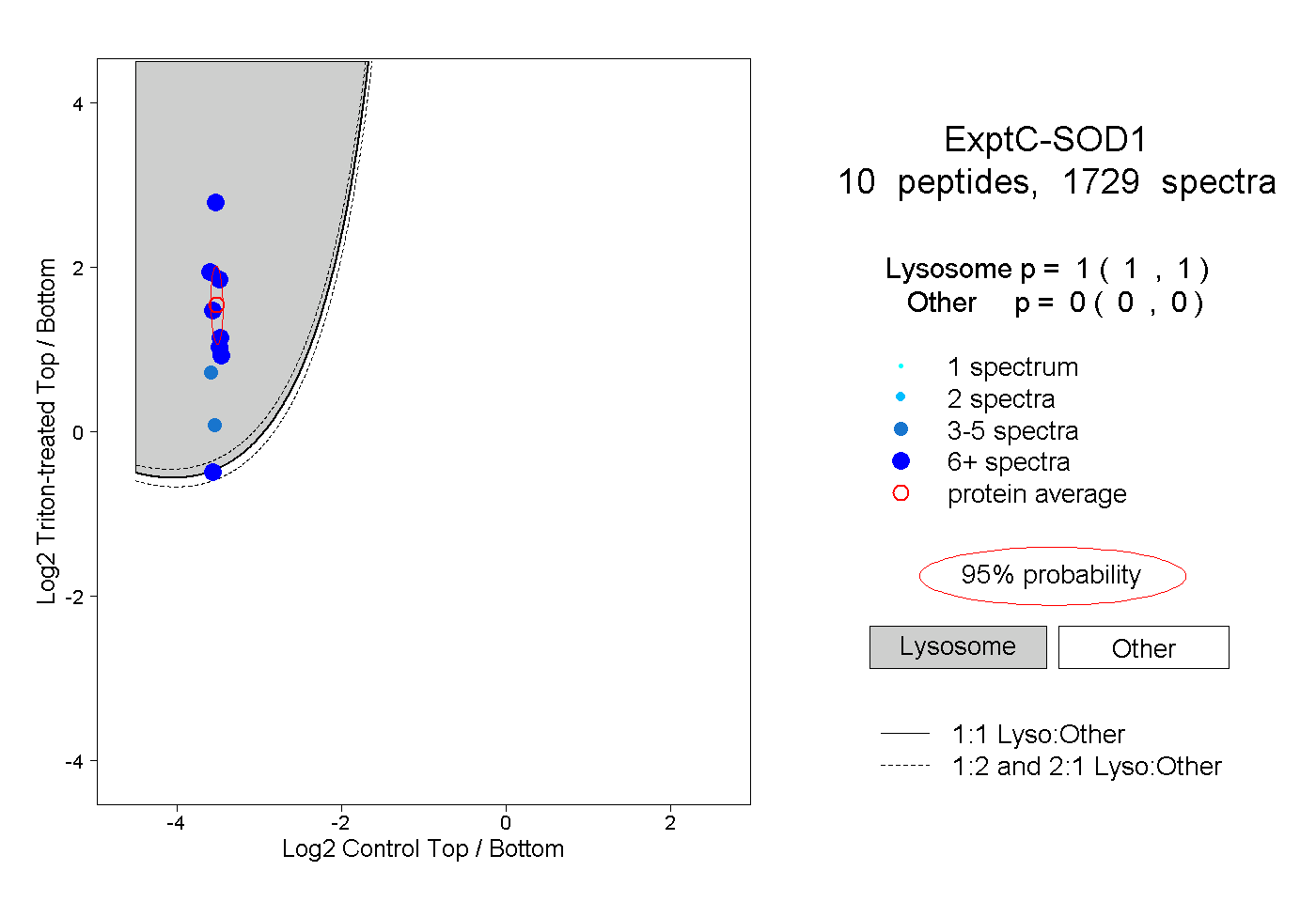 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
47 spectra |
 |
1.000 0.984 | 1.000 |
0.000 0.000 | 0.013 |