peptides
spectra
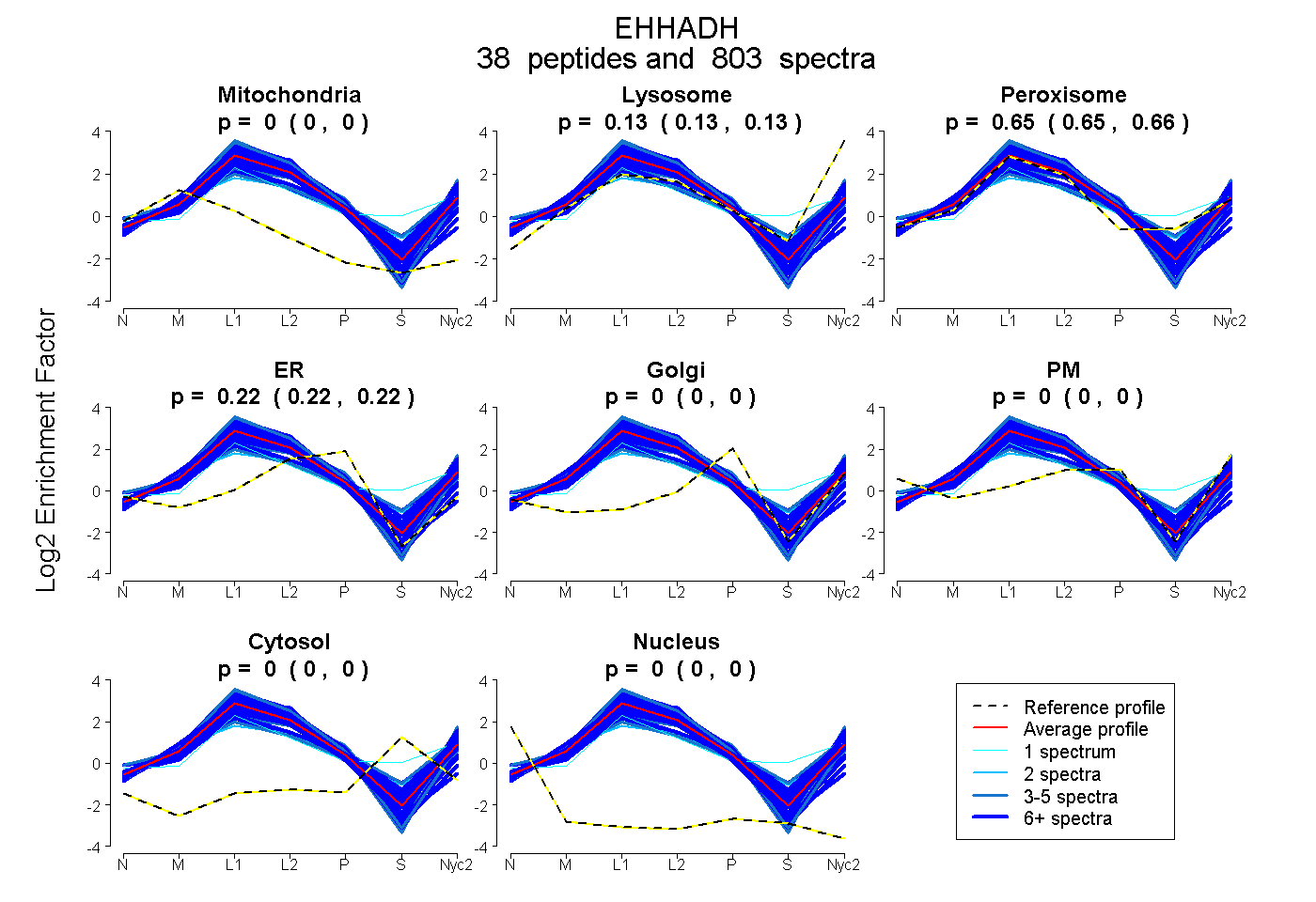
0.000 | 0.000
0.126 | 0.129
0.653 | 0.656
0.217 | 0.219
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
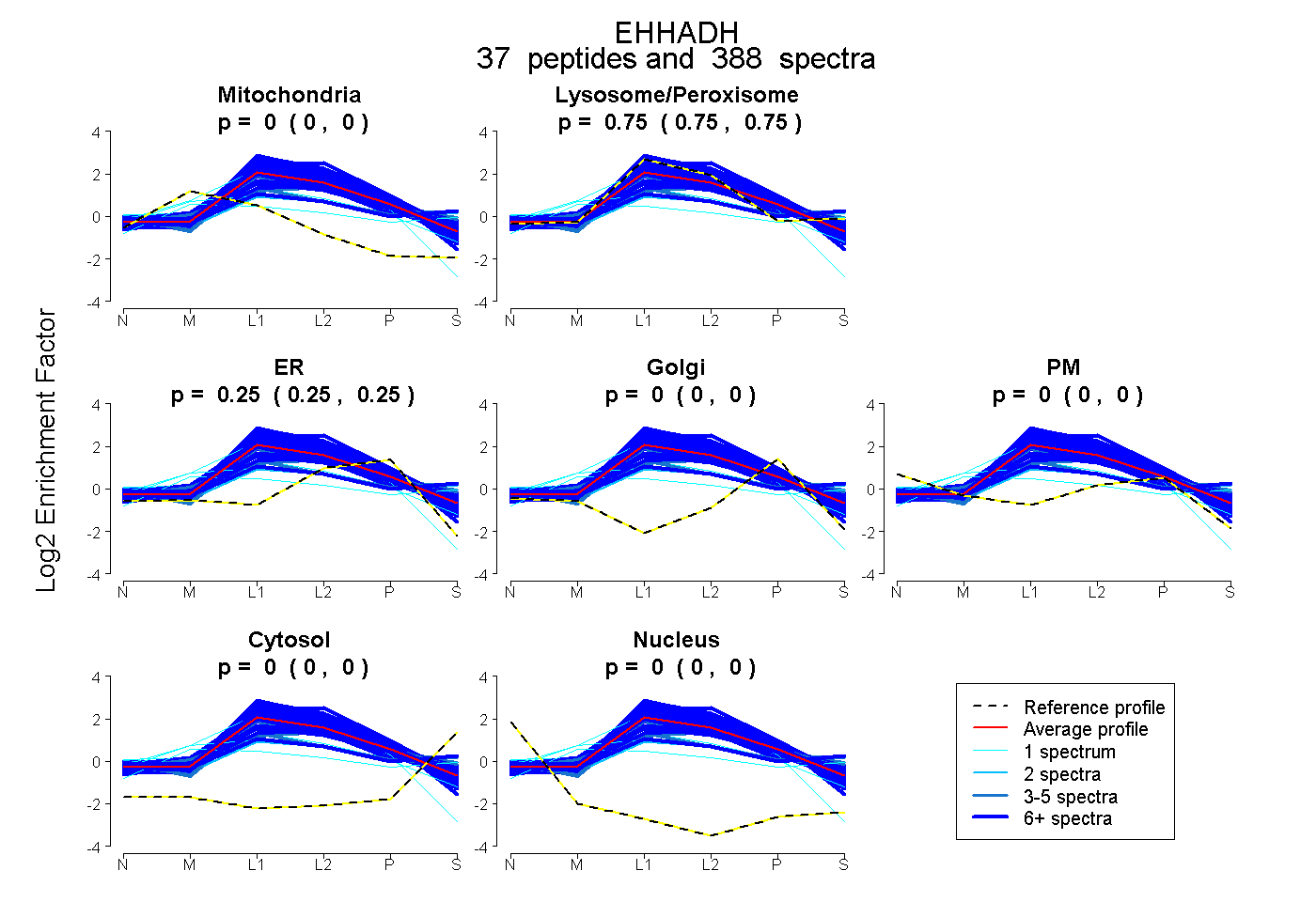
0.000 | 0.000
0.748 | 0.751
0.249 | 0.252
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
803 spectra |
 |
0.000 0.000 | 0.000 |
0.128 0.126 | 0.129 |
0.655 0.653 | 0.656 |
0.218 0.217 | 0.219 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
388 spectra |
 |
0.000 0.000 | 0.000 |
0.750 0.748 | 0.751 |
0.250 0.249 | 0.252 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 12 spectra, LFMYLR | 0.000 | 0.818 | 0.182 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 20 spectra, ALQYAFFAEK | 0.000 | 0.793 | 0.084 | 0.123 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, LCNPPVNAVSPTVIR | 0.016 | 0.809 | 0.175 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 25 spectra, LLEVIPSR | 0.000 | 0.790 | 0.210 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 20 spectra, VVGVPVALDLITSGK | 0.000 | 0.793 | 0.054 | 0.153 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, VSDLAGLDVGWK | 0.000 | 0.763 | 0.237 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 25 spectra, YLSADEALR | 0.000 | 0.763 | 0.237 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, GQGLTGPSLPPGTPVR | 0.000 | 0.576 | 0.000 | 0.026 | 0.228 | 0.170 | 0.000 | |||
| 16 spectra, IIDKPIEPR | 0.000 | 0.821 | 0.179 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, VGLPEVTLGILPGAR | 0.227 | 0.445 | 0.000 | 0.161 | 0.000 | 0.167 | 0.000 | |||
| 8 spectra, CLYSLINEAFR | 0.000 | 0.820 | 0.180 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, HPYEVGIK | 0.000 | 0.796 | 0.204 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, SIQASVK | 0.000 | 0.764 | 0.000 | 0.236 | 0.000 | 0.000 | 0.000 | |||
| 24 spectra, LPHSLAMIR | 0.000 | 0.741 | 0.259 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, IGVVVGNCYGFVGNR | 0.000 | 0.811 | 0.000 | 0.099 | 0.086 | 0.004 | 0.000 | |||
| 21 spectra, IHKPDPWLSTFLSQYR | 0.000 | 0.787 | 0.140 | 0.073 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, QYPGVLAPETCVR | 0.087 | 0.656 | 0.000 | 0.186 | 0.000 | 0.071 | 0.000 | |||
| 4 spectra, AGSDHTVK | 0.000 | 0.812 | 0.000 | 0.123 | 0.000 | 0.065 | 0.000 | |||
| 21 spectra, LGILDAVVK | 0.000 | 0.812 | 0.188 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, YSPLGDMLCEAGR | 0.000 | 0.620 | 0.000 | 0.045 | 0.153 | 0.182 | 0.000 | |||
| 1 spectrum, WSTPSGASWK | 0.316 | 0.380 | 0.254 | 0.000 | 0.050 | 0.000 | 0.000 | |||
| 8 spectra, EVHHIEQR | 0.000 | 0.731 | 0.221 | 0.000 | 0.047 | 0.000 | 0.000 | |||
| 6 spectra, FSSSTK | 0.000 | 0.834 | 0.166 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, ASGQAK | 0.080 | 0.604 | 0.000 | 0.046 | 0.246 | 0.024 | 0.000 | |||
| 14 spectra, IITFTLEK | 0.000 | 0.837 | 0.163 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 15 spectra, SDPVEEAIK | 0.000 | 0.761 | 0.239 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 10 spectra, GWYQYDKPLGR | 0.000 | 0.790 | 0.210 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, QNPDIPQLEPSDYLR | 0.000 | 0.740 | 0.050 | 0.210 | 0.000 | 0.000 | 0.000 | |||
| 23 spectra, GTQLLPR | 0.005 | 0.826 | 0.000 | 0.169 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, AHQNGQASAKPK | 0.000 | 0.909 | 0.091 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LVAQGSPPLK | 0.202 | 0.494 | 0.304 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, QLDAAK | 0.000 | 0.792 | 0.020 | 0.188 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, VGISVVAVESDPK | 0.000 | 0.656 | 0.215 | 0.003 | 0.126 | 0.000 | 0.000 | |||
| 1 spectrum, ELSTVDLVVEAVFEDMNLK | 0.000 | 0.767 | 0.000 | 0.233 | 0.000 | 0.000 | 0.000 | |||
| 26 spectra, GIAISFAR | 0.000 | 0.818 | 0.182 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, YSSPTTIATVMSLSK | 0.000 | 0.626 | 0.298 | 0.076 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, GGPMFYAASVGLPTVLEK | 0.000 | 0.722 | 0.017 | 0.220 | 0.000 | 0.041 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
3103 spectra |
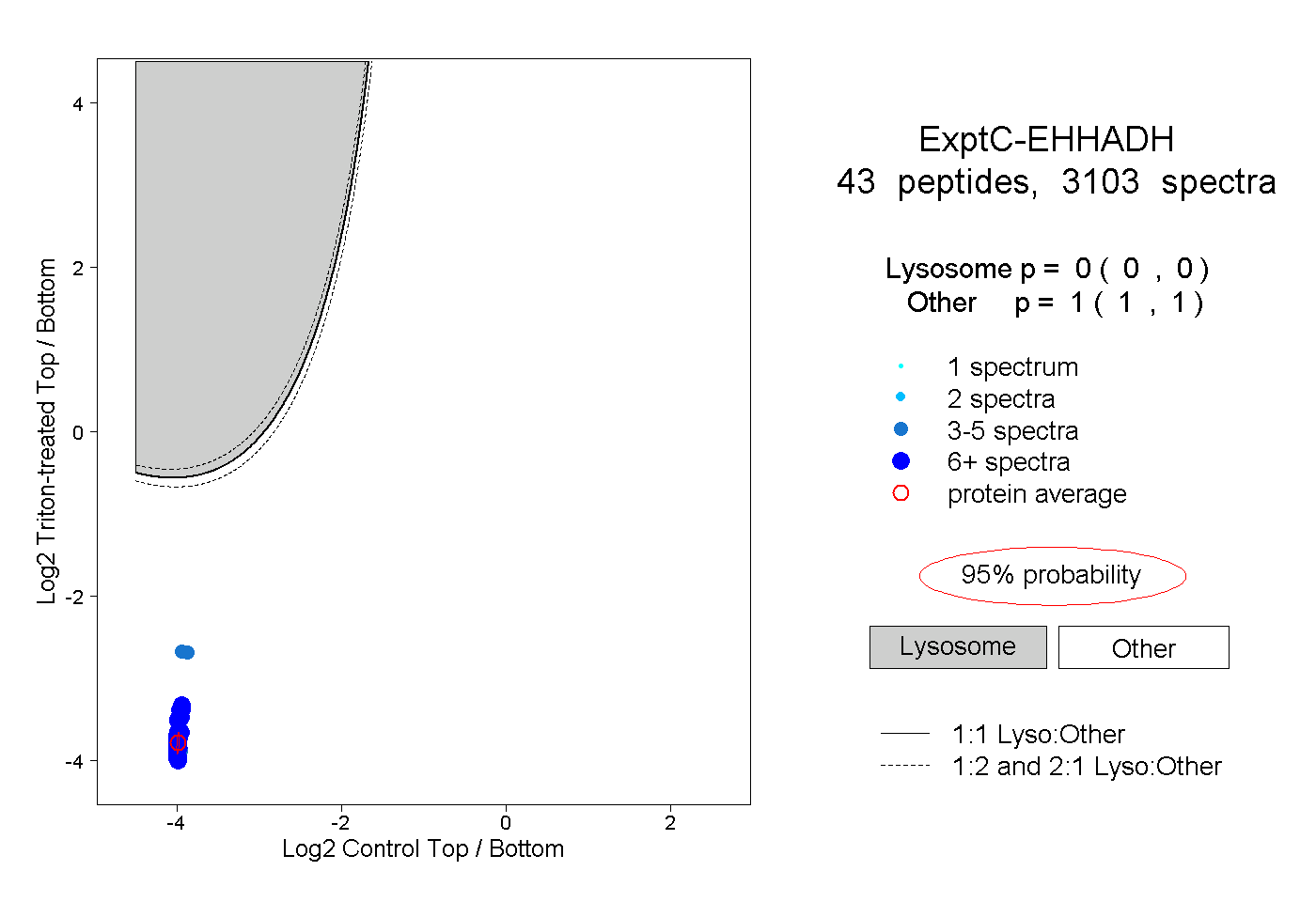 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
182 spectra |
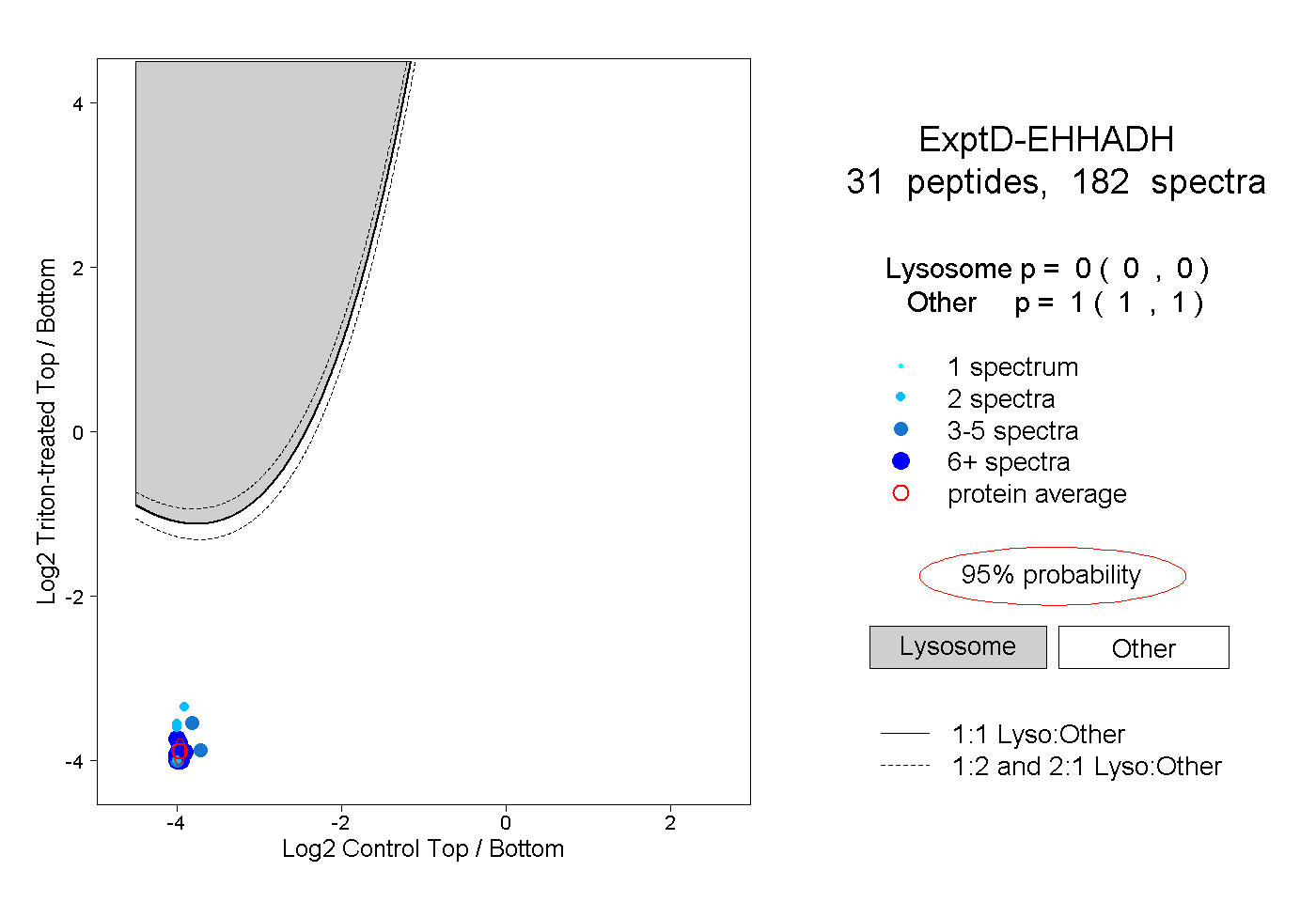 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |