peptides
spectra
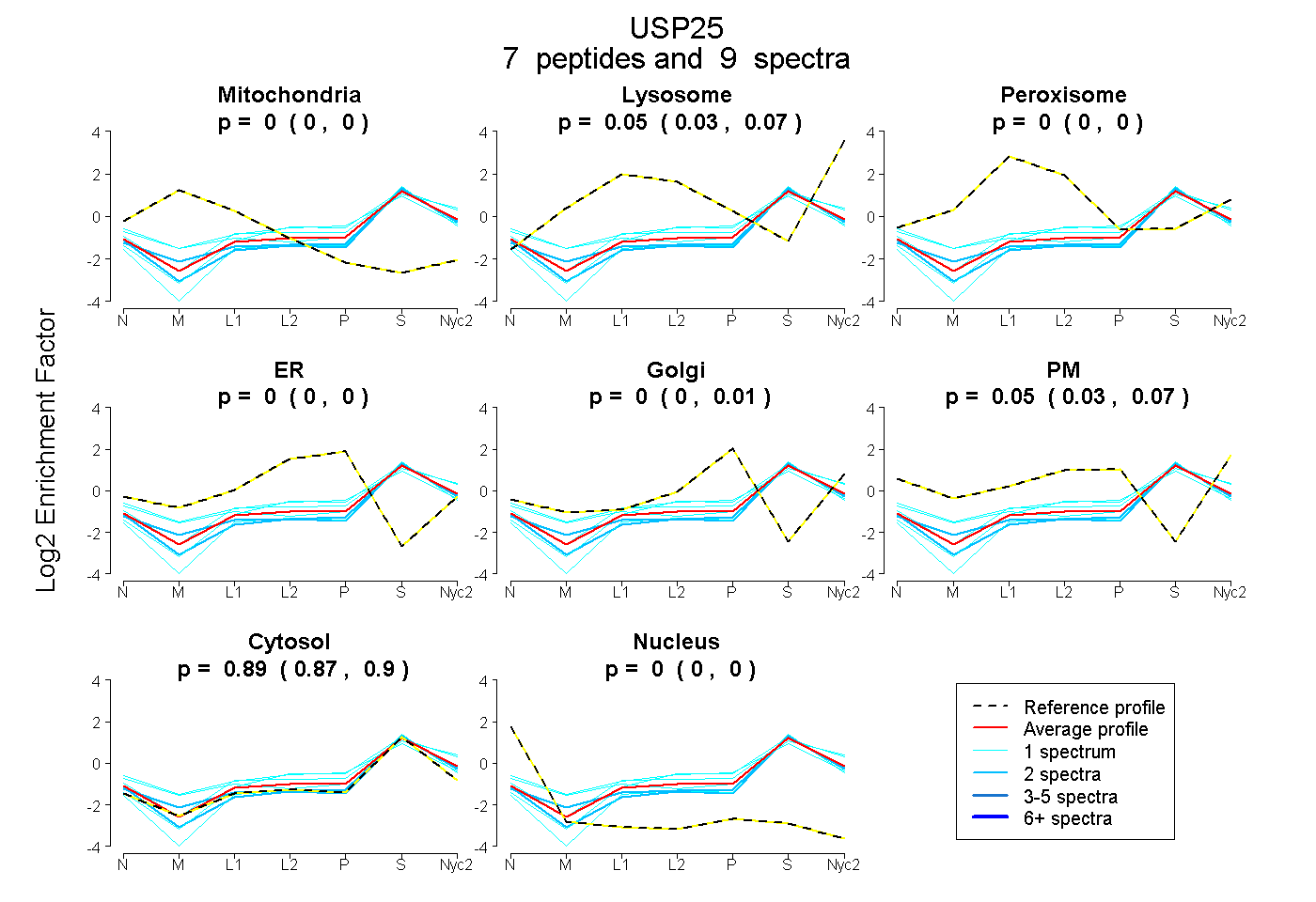
0.000 | 0.000
0.029 | 0.074
0.000 | 0.000
0.000 | 0.000
0.000 | 0.014
0.026 | 0.074
0.874 | 0.904
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
9 spectra |
 |
0.000 0.000 | 0.000 |
0.055 0.029 | 0.074 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.014 |
0.054 0.026 | 0.074 |
0.891 0.874 | 0.904 |
0.000 0.000 | 0.000 |
| 1 spectrum, ETGITDEEQAISR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, DFVEEDNQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.001 | 0.999 | 0.000 | ||
| 2 spectra, NLPFMR | 0.000 | 0.065 | 0.000 | 0.000 | 0.000 | 0.006 | 0.929 | 0.000 | ||
| 1 spectrum, TLLEQFGDR | 0.000 | 0.126 | 0.000 | 0.000 | 0.000 | 0.091 | 0.783 | 0.000 | ||
| 1 spectrum, AIALSLAESNR | 0.000 | 0.134 | 0.000 | 0.000 | 0.000 | 0.050 | 0.816 | 0.000 | ||
| 1 spectrum, LNEQAAELFESGEDR | 0.000 | 0.055 | 0.000 | 0.055 | 0.018 | 0.000 | 0.872 | 0.000 | ||
| 1 spectrum, ELEDWDTQLAQR | 0.000 | 0.000 | 0.096 | 0.016 | 0.000 | 0.169 | 0.719 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
2 spectra |
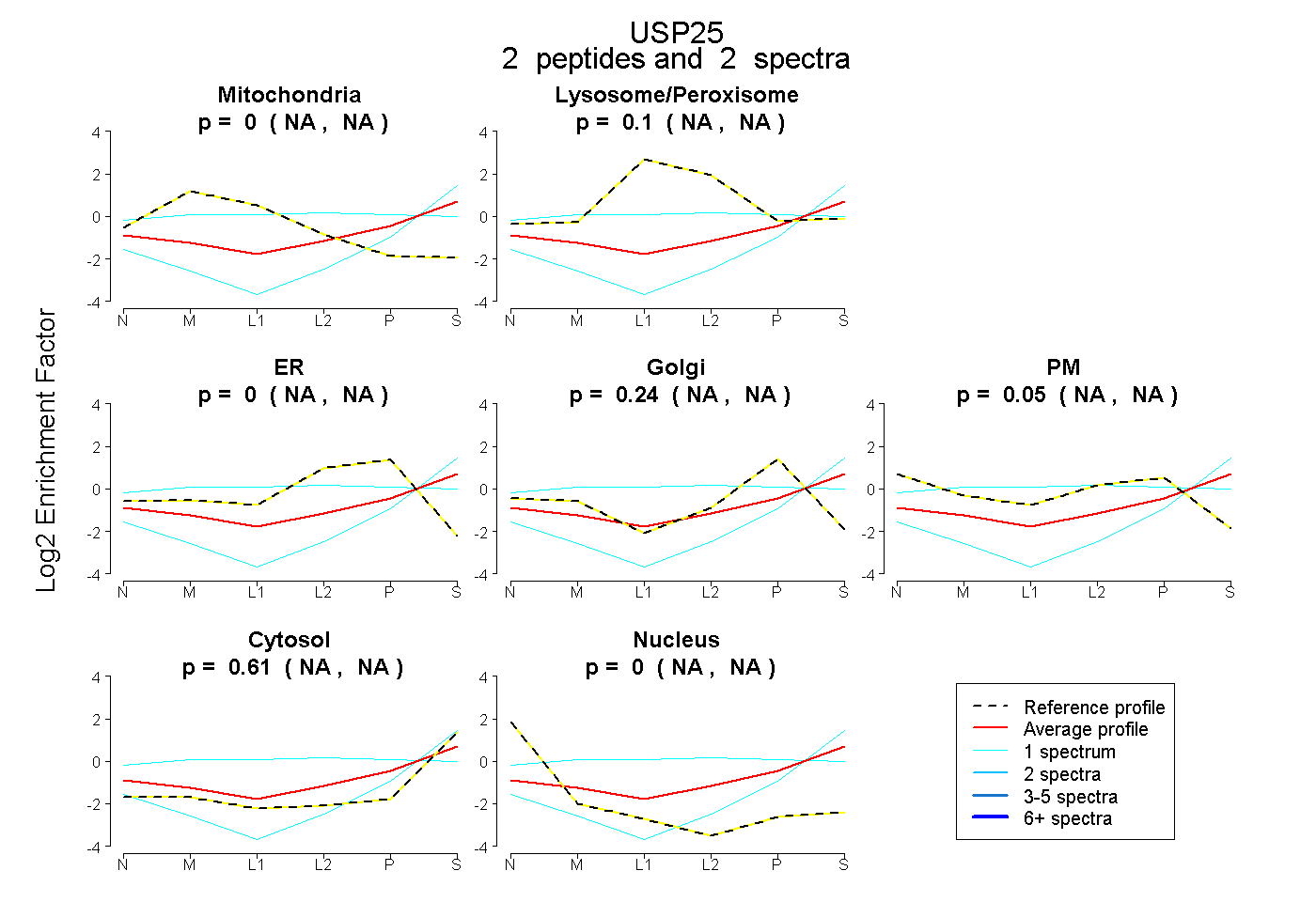 |
0.000 NA | NA |
0.095 NA | NA |
0.000 NA | NA |
0.238 NA | NA |
0.053 NA | NA |
0.613 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
2 spectra |
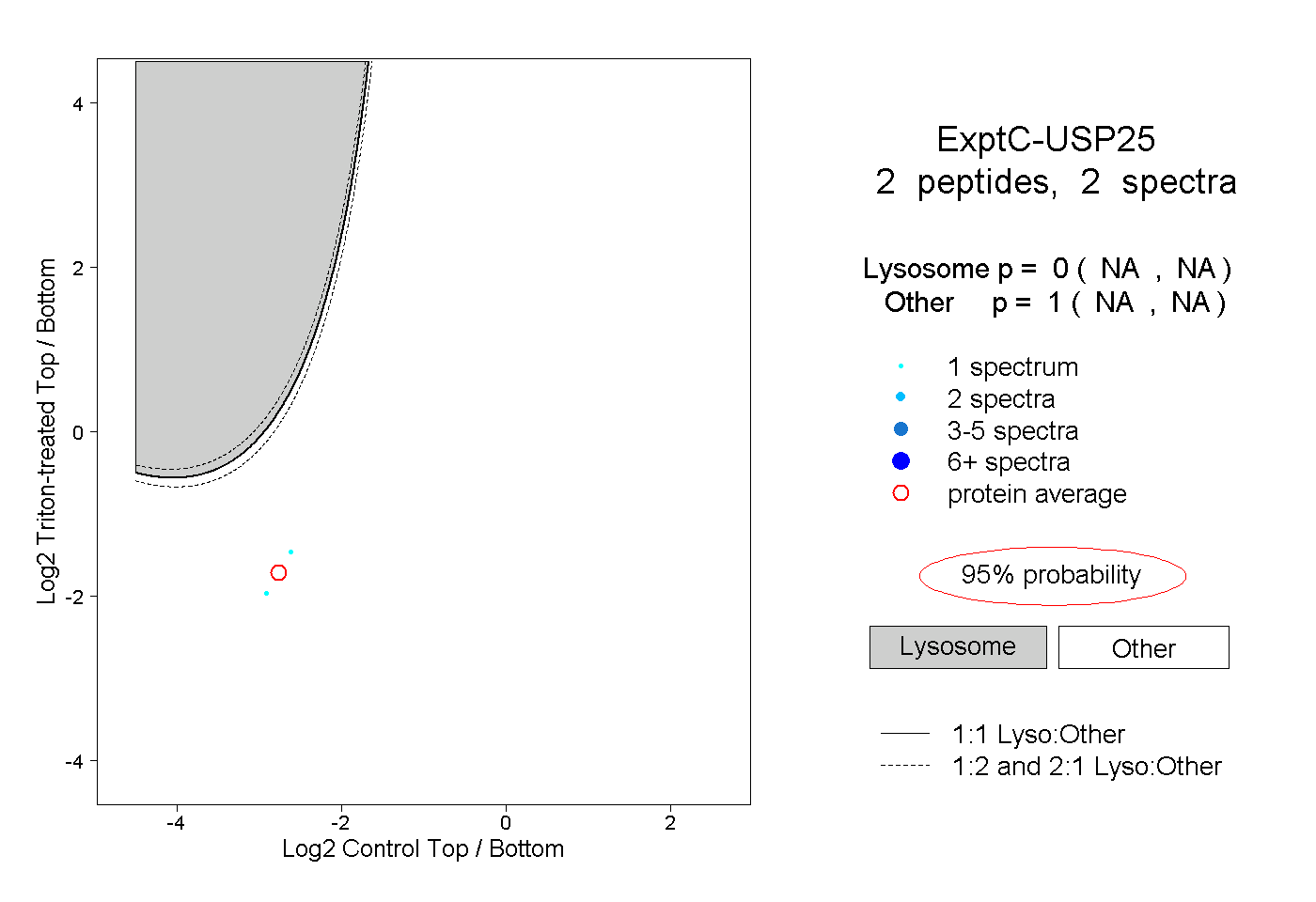 |
0.000 NA | NA |
1.000 NA | NA |