peptides
spectra
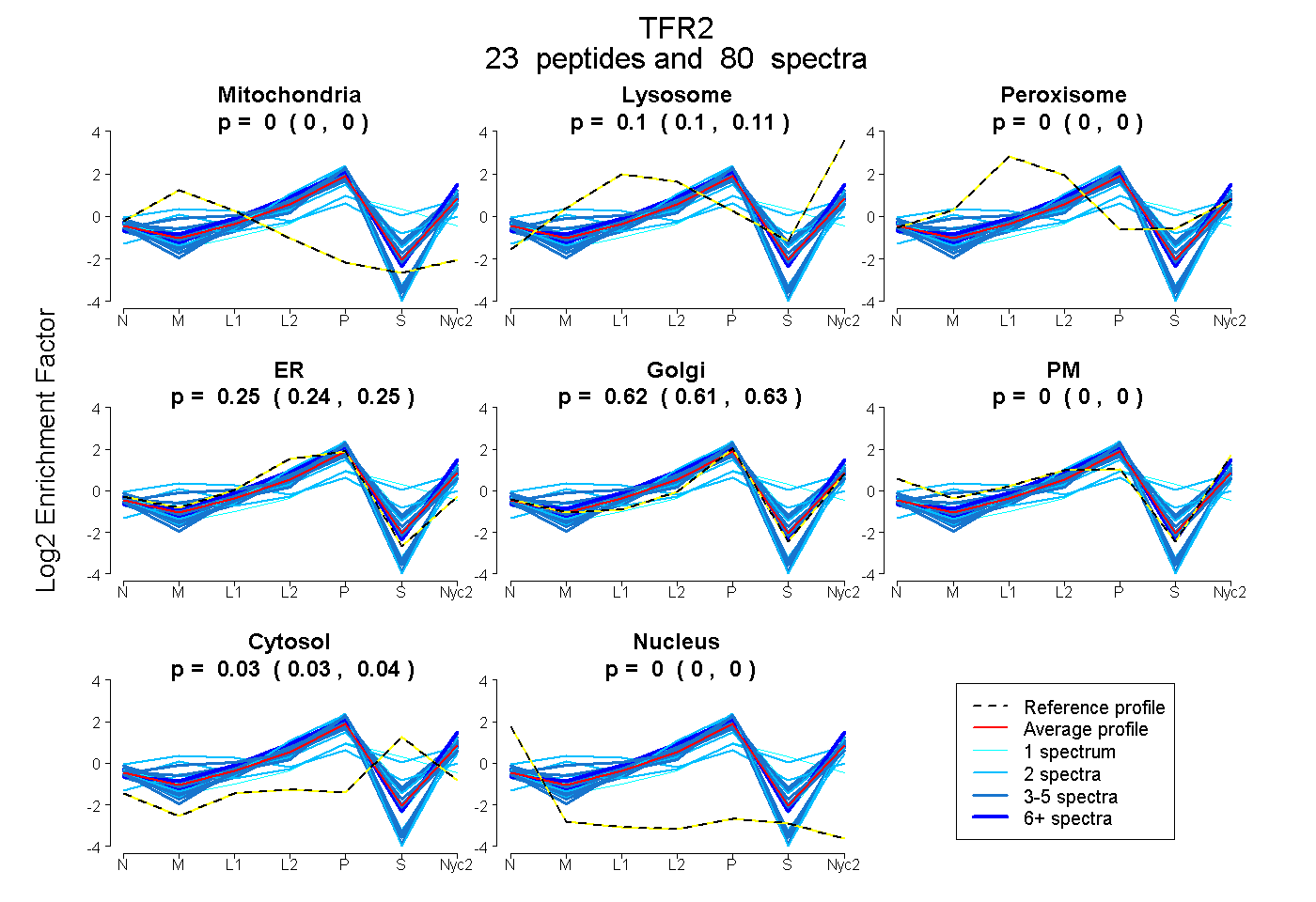
0.000 | 0.000
0.100 | 0.107
0.000 | 0.000
0.239 | 0.253
0.607 | 0.626
0.000 | 0.000
0.025 | 0.037
0.000 | 0.000
peptides
spectra
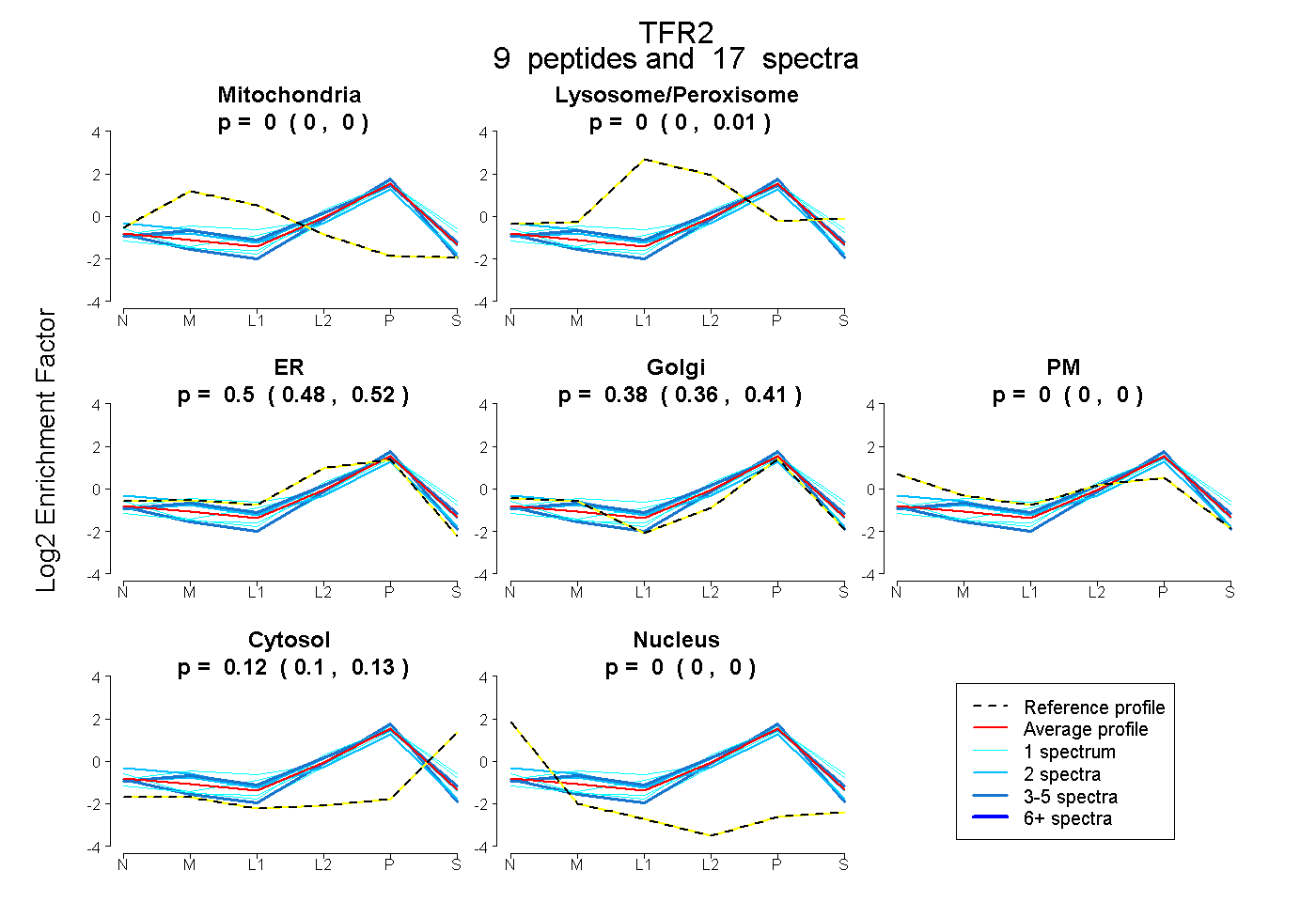
0.000 | 0.000
0.000 | 0.006
0.475 | 0.517
0.356 | 0.406
0.000 | 0.000
0.105 | 0.127
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
80 spectra |
 |
0.000 0.000 | 0.000 |
0.104 0.100 | 0.107 |
0.000 0.000 | 0.000 |
0.247 0.239 | 0.253 |
0.617 0.607 | 0.626 |
0.000 0.000 | 0.000 |
0.032 0.025 | 0.037 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
17 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.006 |
0.501 0.475 | 0.517 |
0.382 0.356 | 0.406 |
0.000 0.000 | 0.000 |
0.117 0.105 | 0.127 |
0.000 0.000 | 0.000 |
| 1 spectrum, MATLVQDILDK | 0.000 | 0.000 | 0.565 | 0.189 | 0.000 | 0.246 | 0.000 | |||
| 1 spectrum, HIGNLNEFSGDLK | 0.000 | 0.133 | 0.311 | 0.406 | 0.000 | 0.150 | 0.000 | |||
| 4 spectra, LGPGPGLR | 0.000 | 0.000 | 0.299 | 0.687 | 0.000 | 0.014 | 0.000 | |||
| 1 spectrum, HIFLGQGDHTLGALVEHLR | 0.000 | 0.278 | 0.009 | 0.714 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, MEDTIR | 0.000 | 0.008 | 0.578 | 0.309 | 0.000 | 0.105 | 0.000 | |||
| 4 spectra, TFSSMVSSGFRPR | 0.000 | 0.065 | 0.502 | 0.327 | 0.000 | 0.106 | 0.000 | |||
| 2 spectra, LSDSPYR | 0.000 | 0.105 | 0.137 | 0.692 | 0.066 | 0.000 | 0.000 | |||
| 1 spectrum, EDTYENLHK | 0.000 | 0.000 | 0.408 | 0.545 | 0.000 | 0.047 | 0.000 | |||
| 1 spectrum, GLTLQWVYSAR | 0.000 | 0.000 | 0.272 | 0.601 | 0.000 | 0.127 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
112 spectra |
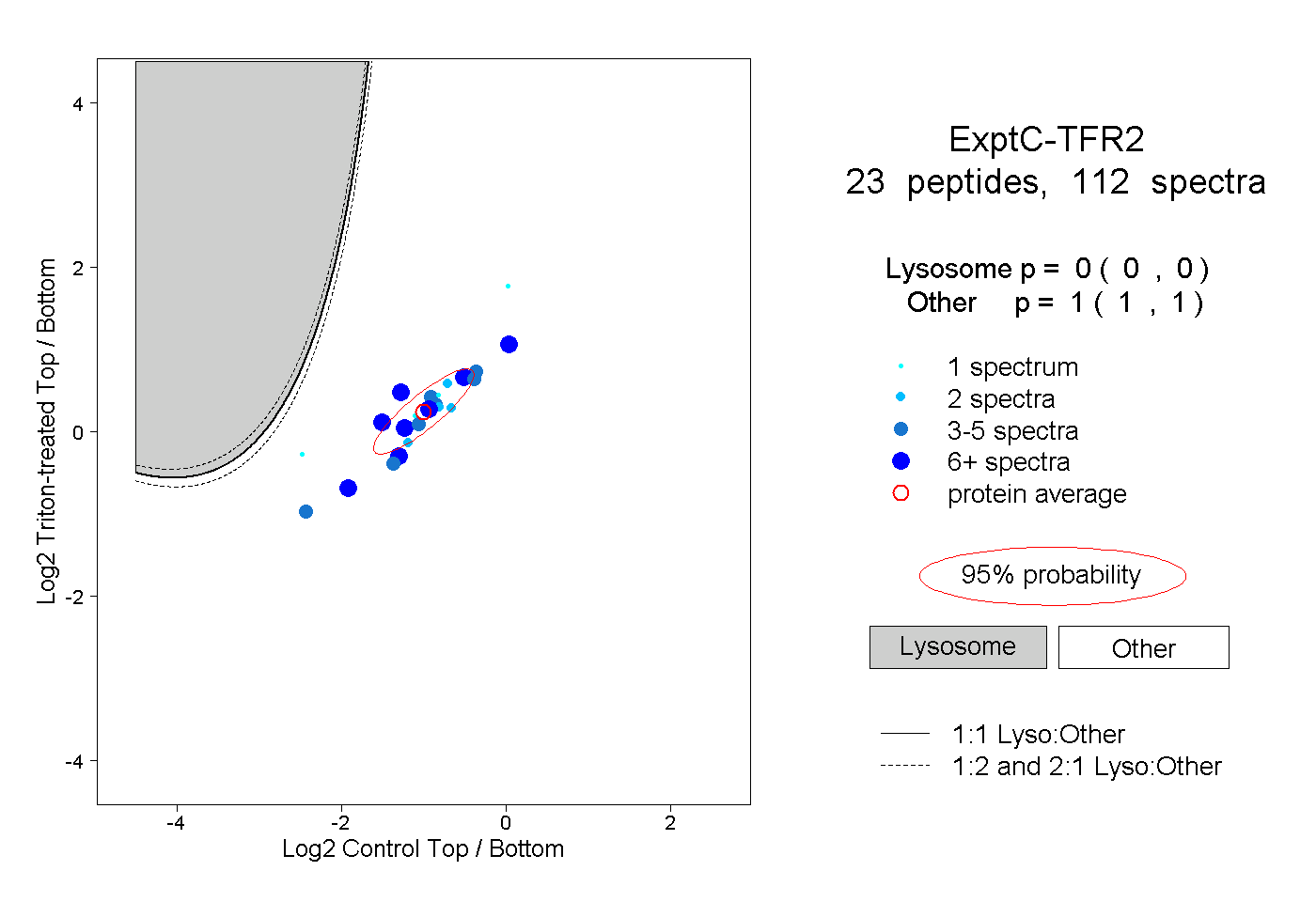 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
13 spectra |
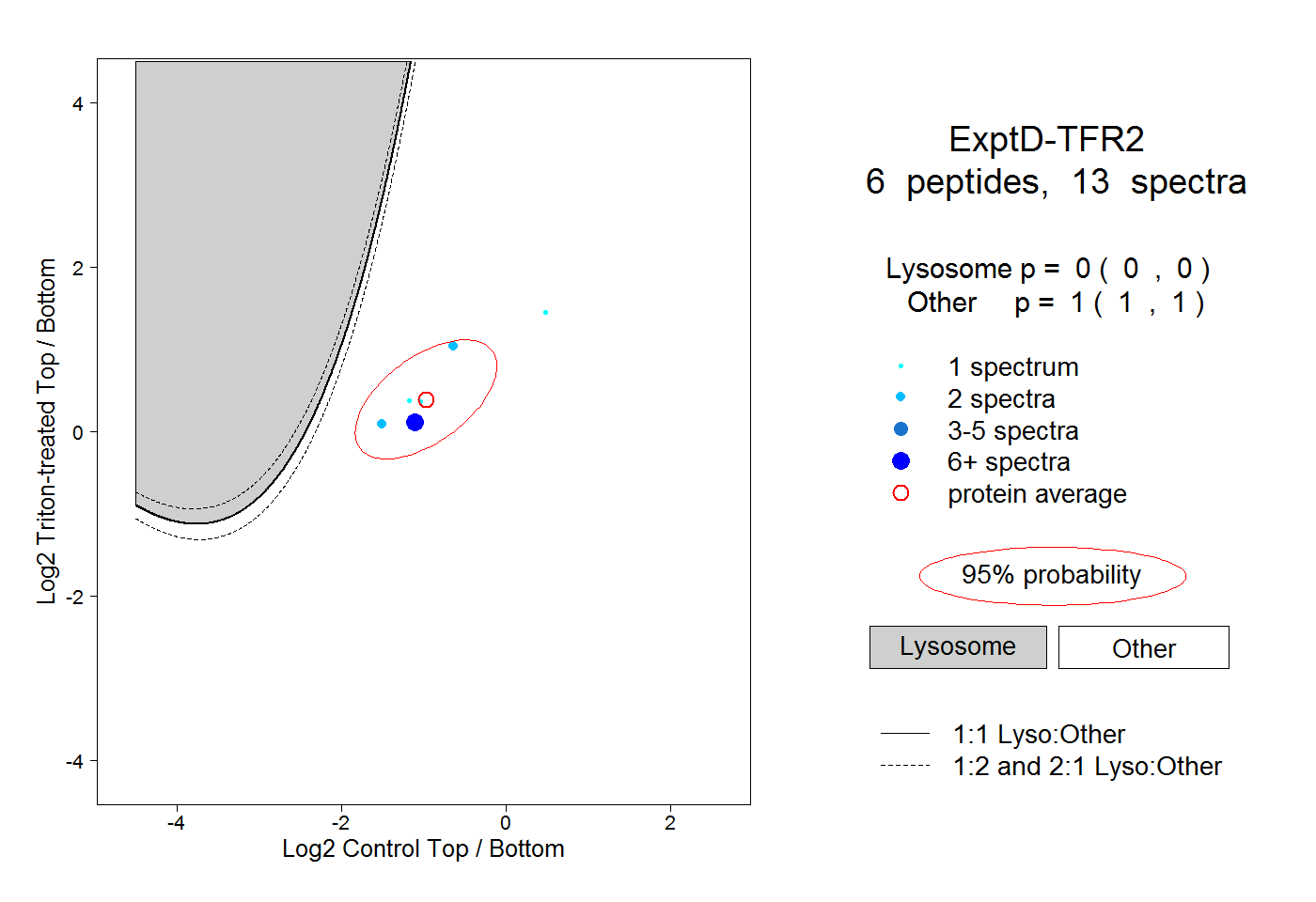 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |