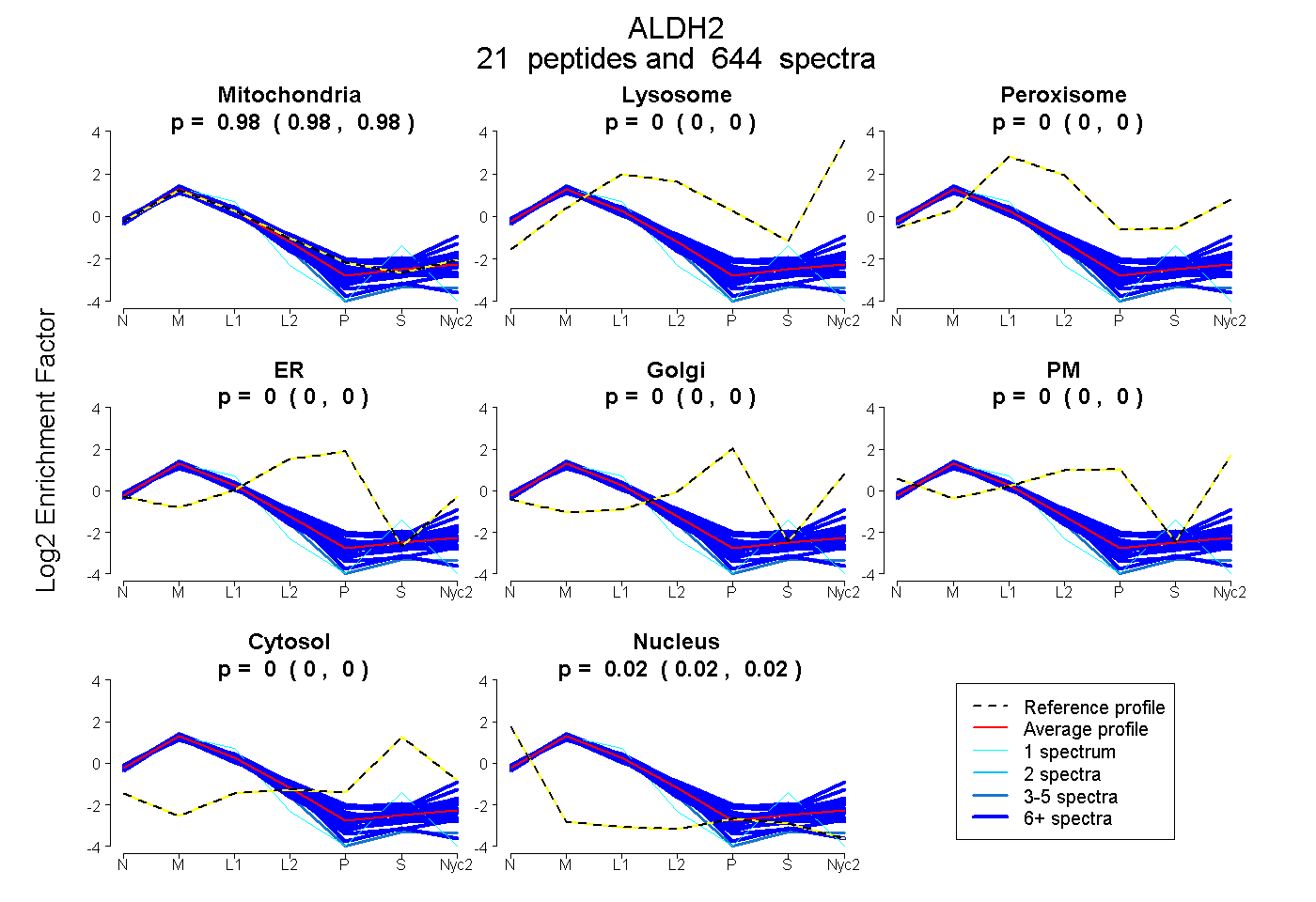
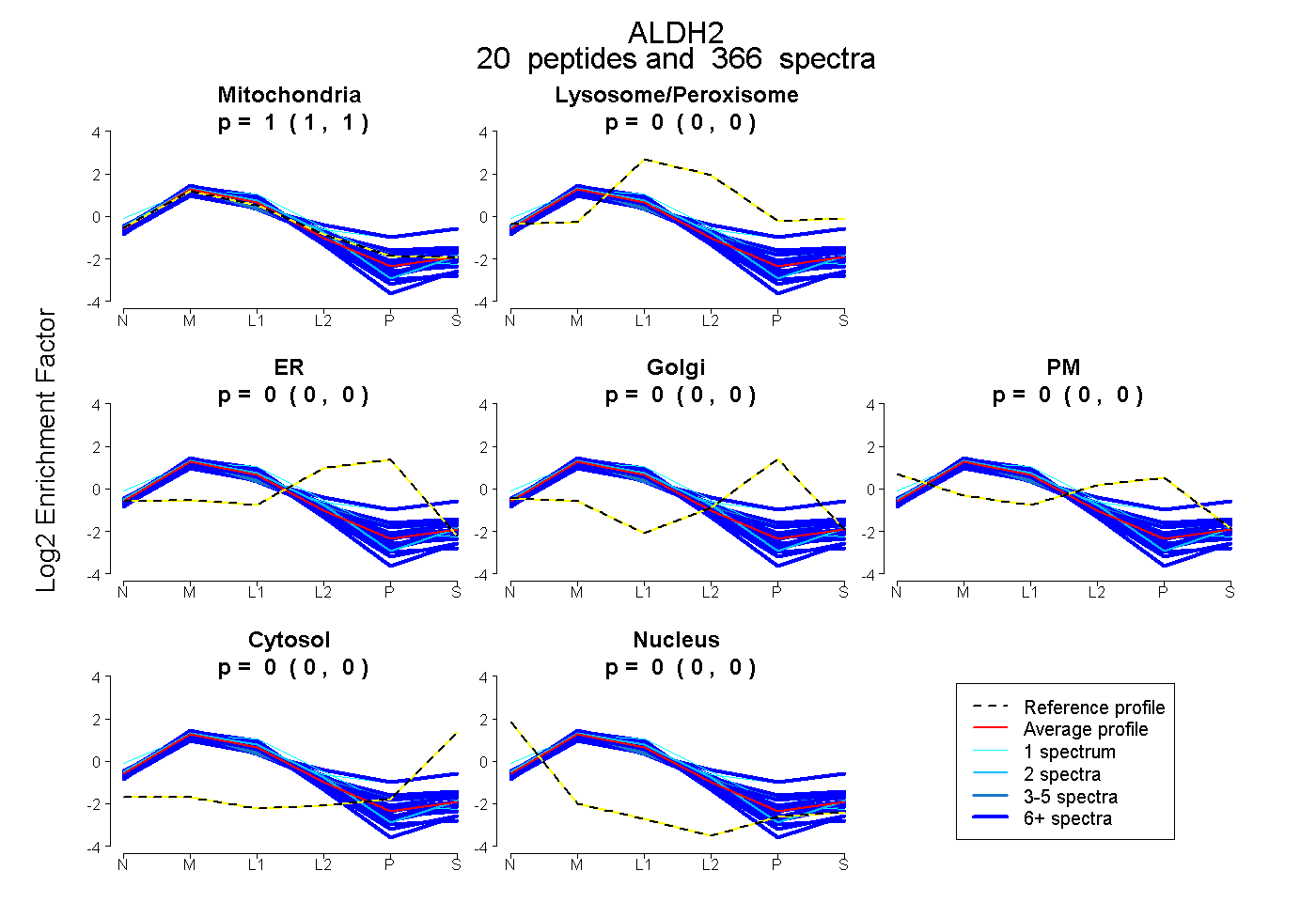
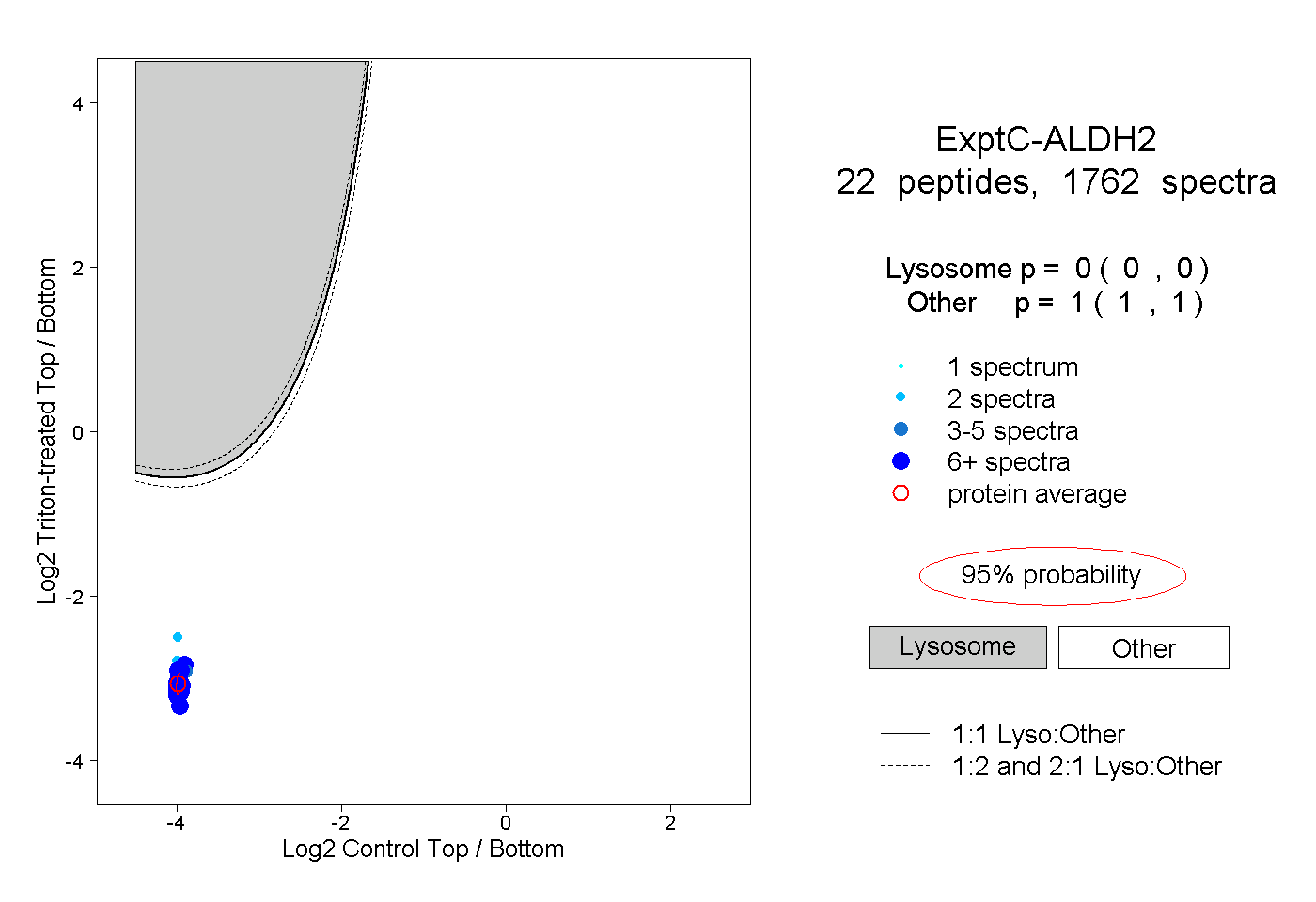
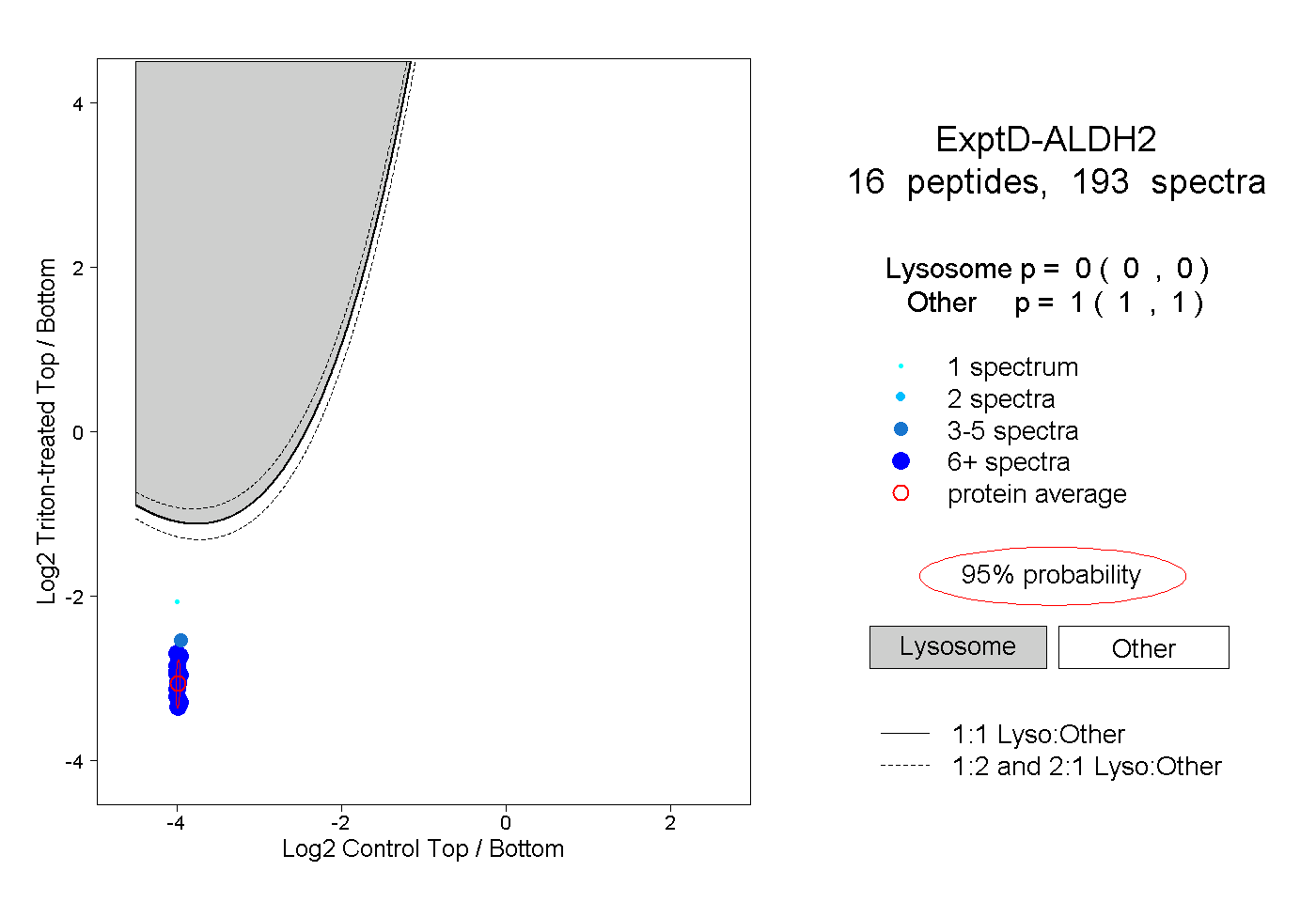
| 2 spectra, VAFTGSTEVGHLIQVAAGSSNLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 275 spectra, SGQQEGAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, TFPTVNPSTGEVICQVAEGNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 24 spectra, GYFIQPTVFGDVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 118 spectra, TIEEVVGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 87 spectra, YGLAAAVFTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 39 spectra, EEIFGPVMQILK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 129 spectra, LADLIER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 36 spectra, LGPALATGNVVVMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 147 spectra, TIPIDGDFFSYTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 129 spectra, DGMTIAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, ELGEYGLQAYTEVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 153 spectra, VVGNPFDSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 24 spectra, TEQGPQVDETQFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 119 spectra, VTLELGGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 58 spectra, YYAGWADK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, TFVQEDVYDEFVER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, VAEQTPLTALYVANLIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 175 spectra, LLGYLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 74 spectra, AAFQLGSPWR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 129 spectra, LLCGGGAAADR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EEIFGPVQQIMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |