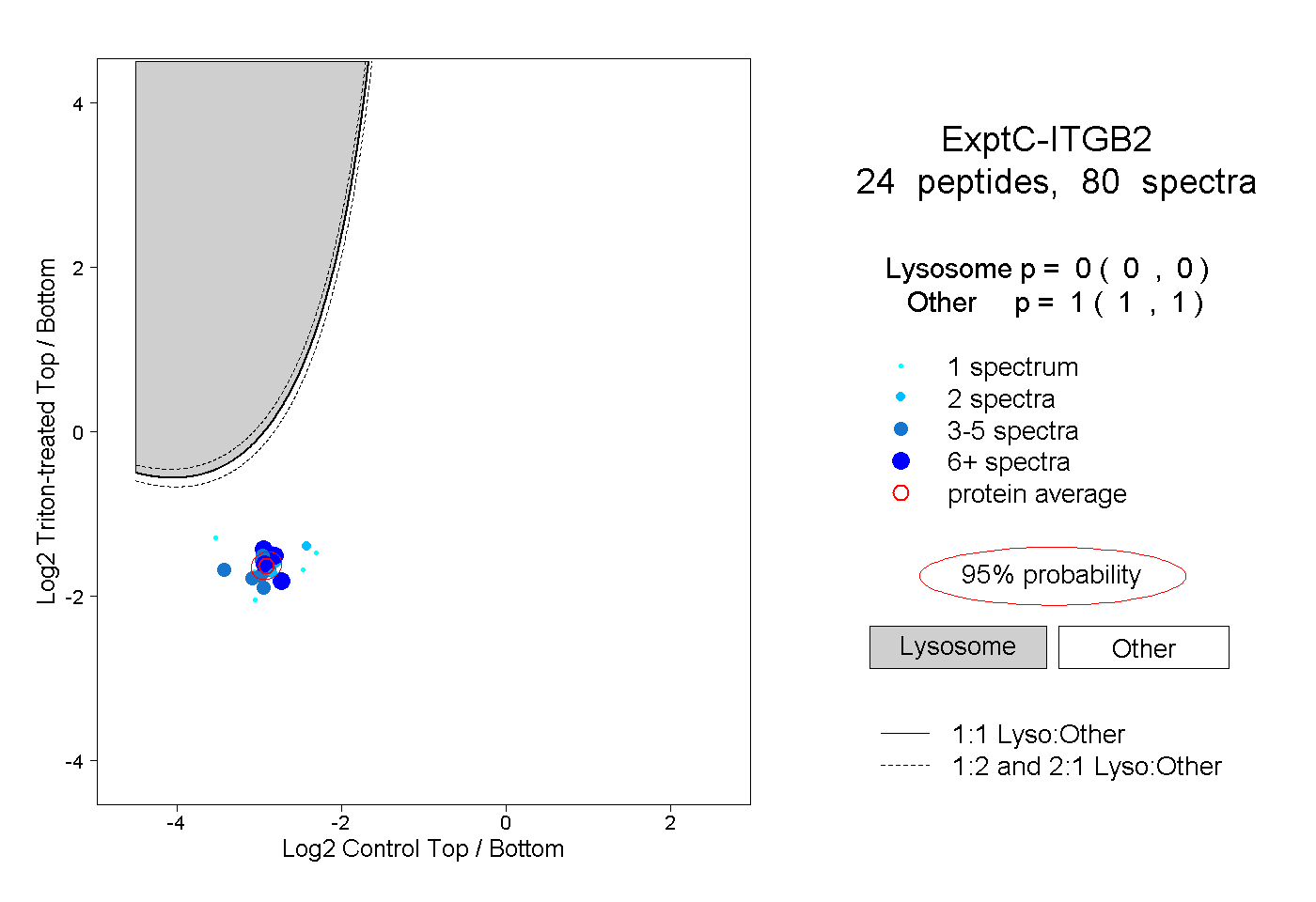
| 9 spectra, VSSLGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, VTYDSFCNNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, NPCPNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, NLCGGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GVMECGICR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, SATTTVMNPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LTEIIPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LVECSGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, TVLPFVNTHPEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, DGNAYNIHVDDDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, SQLSPQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, AQLILK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, CESGYIGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, SSQELEGNCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SNEFDYPSVGQLAHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GCPADDIMDPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LSESNIQPIFAVTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, YDGQVCGGLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VTASECIQEQSFVIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, EGFEGSACQCQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, STTGCLNAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LTDNSNQFQTEVGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, SFADLHPQYQVQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, IGFGSFVDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |