peptides
spectra

0.000 | 0.000
0.404 | 0.425
0.000 | 0.000
0.076 | 0.107
0.057 | 0.090
0.397 | 0.436
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
45 spectra |
 |
0.000 0.000 | 0.000 |
0.416 0.404 | 0.425 |
0.000 0.000 | 0.000 |
0.092 0.076 | 0.107 |
0.075 0.057 | 0.090 |
0.417 0.397 | 0.436 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, GSCSCGQCNCK | 0.000 | 0.570 | 0.000 | 0.332 | 0.000 | 0.098 | 0.000 | 0.000 | ||
| 1 spectrum, LGGDLLQALNEITESGR | 0.000 | 0.482 | 0.000 | 0.000 | 0.000 | 0.518 | 0.000 | 0.000 | ||
| 2 spectra, VTYDSFCNNR | 0.000 | 0.559 | 0.000 | 0.166 | 0.081 | 0.167 | 0.027 | 0.000 | ||
| 2 spectra, NLCGGK | 0.000 | 0.308 | 0.000 | 0.000 | 0.000 | 0.692 | 0.000 | 0.000 | ||
| 2 spectra, ACQPPFAFR | 0.000 | 0.497 | 0.000 | 0.081 | 0.000 | 0.422 | 0.000 | 0.000 | ||
| 3 spectra, GVMECGICR | 0.000 | 0.437 | 0.000 | 0.000 | 0.093 | 0.450 | 0.019 | 0.000 | ||
| 1 spectrum, SATTTVMNPK | 0.000 | 0.258 | 0.000 | 0.219 | 0.147 | 0.375 | 0.000 | 0.000 | ||
| 2 spectra, LTEIIPK | 0.000 | 0.530 | 0.000 | 0.000 | 0.103 | 0.000 | 0.366 | 0.000 | ||
| 2 spectra, LGAILTPNDGR | 0.000 | 0.507 | 0.000 | 0.000 | 0.000 | 0.493 | 0.000 | 0.000 | ||
| 1 spectrum, TVLPFVNTHPEK | 0.000 | 0.380 | 0.000 | 0.000 | 0.000 | 0.620 | 0.000 | 0.000 | ||
| 2 spectra, DGNAYNIHVDDDR | 0.000 | 0.656 | 0.000 | 0.000 | 0.199 | 0.000 | 0.146 | 0.000 | ||
| 1 spectrum, VIFGQYCECDNFNCER | 0.069 | 0.372 | 0.059 | 0.000 | 0.076 | 0.158 | 0.266 | 0.000 | ||
| 1 spectrum, AQLILK | 0.000 | 0.273 | 0.118 | 0.085 | 0.000 | 0.524 | 0.000 | 0.000 | ||
| 2 spectra, SSQELEGNCR | 0.000 | 0.049 | 0.000 | 0.000 | 0.000 | 0.951 | 0.000 | 0.000 | ||
| 1 spectrum, SAVGELSDDSSNVVQLIK | 0.000 | 0.199 | 0.000 | 0.445 | 0.000 | 0.356 | 0.000 | 0.000 | ||
| 2 spectra, GCPADDIMDPK | 0.000 | 0.435 | 0.000 | 0.268 | 0.000 | 0.298 | 0.000 | 0.000 | ||
| 1 spectrum, GDCDGVQINNPVTFQVK | 0.000 | 0.290 | 0.000 | 0.000 | 0.000 | 0.421 | 0.289 | 0.000 | ||
| 2 spectra, LSESNIQPIFAVTK | 0.000 | 0.465 | 0.000 | 0.013 | 0.041 | 0.481 | 0.000 | 0.000 | ||
| 1 spectrum, CHLEDNMYK | 0.000 | 0.603 | 0.000 | 0.000 | 0.215 | 0.000 | 0.182 | 0.000 | ||
| 2 spectra, SQWNNDNPLFK | 0.000 | 0.228 | 0.000 | 0.089 | 0.000 | 0.683 | 0.000 | 0.000 | ||
| 2 spectra, YDGQVCGGLK | 0.000 | 0.261 | 0.054 | 0.000 | 0.000 | 0.322 | 0.363 | 0.000 | ||
| 2 spectra, VTASECIQEQSFVIR | 0.000 | 0.341 | 0.000 | 0.310 | 0.000 | 0.349 | 0.000 | 0.000 | ||
| 2 spectra, EGFEGSACQCQR | 0.000 | 0.189 | 0.142 | 0.049 | 0.000 | 0.397 | 0.224 | 0.000 | ||
| 4 spectra, STTGCLNAR | 0.000 | 0.535 | 0.000 | 0.119 | 0.000 | 0.345 | 0.000 | 0.000 | ||
| 3 spectra, SFADLHPQYQVQR | 0.000 | 0.343 | 0.144 | 0.000 | 0.227 | 0.245 | 0.042 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
 |
0.000 NA | NA |
0.363 NA | NA |
0.000 NA | NA |
0.133 NA | NA |
0.412 NA | NA |
0.092 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
80 spectra |
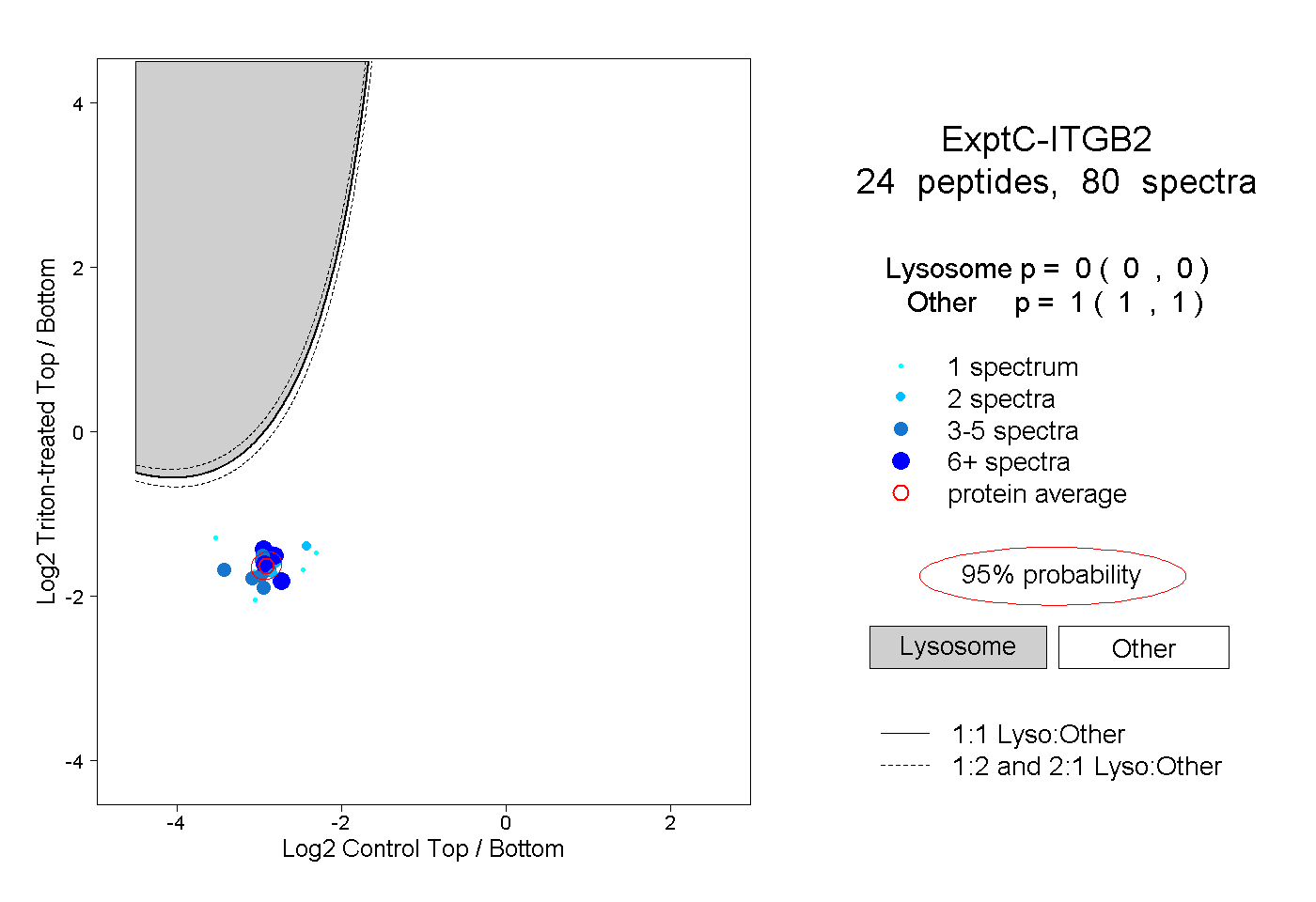 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
5 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |