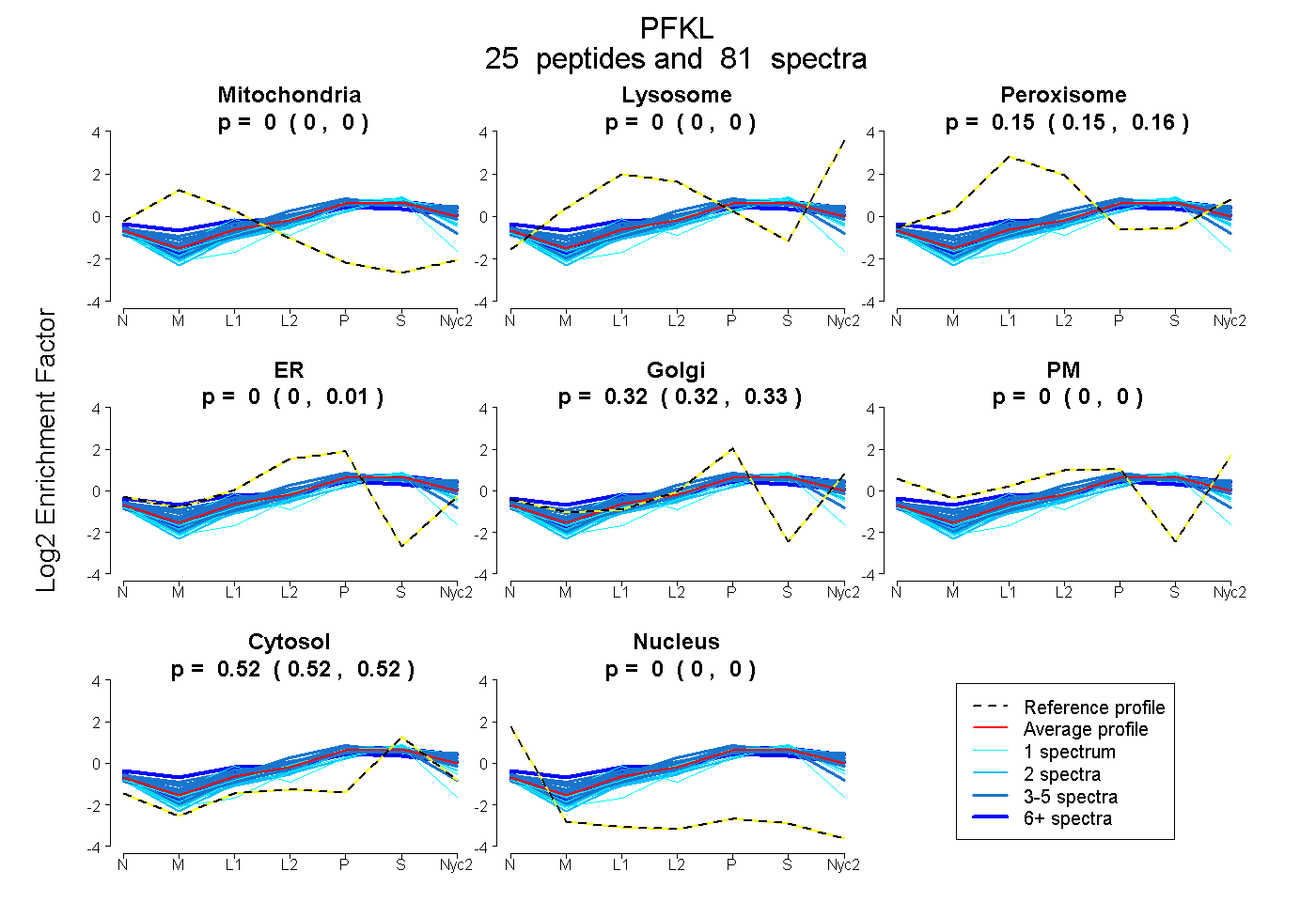
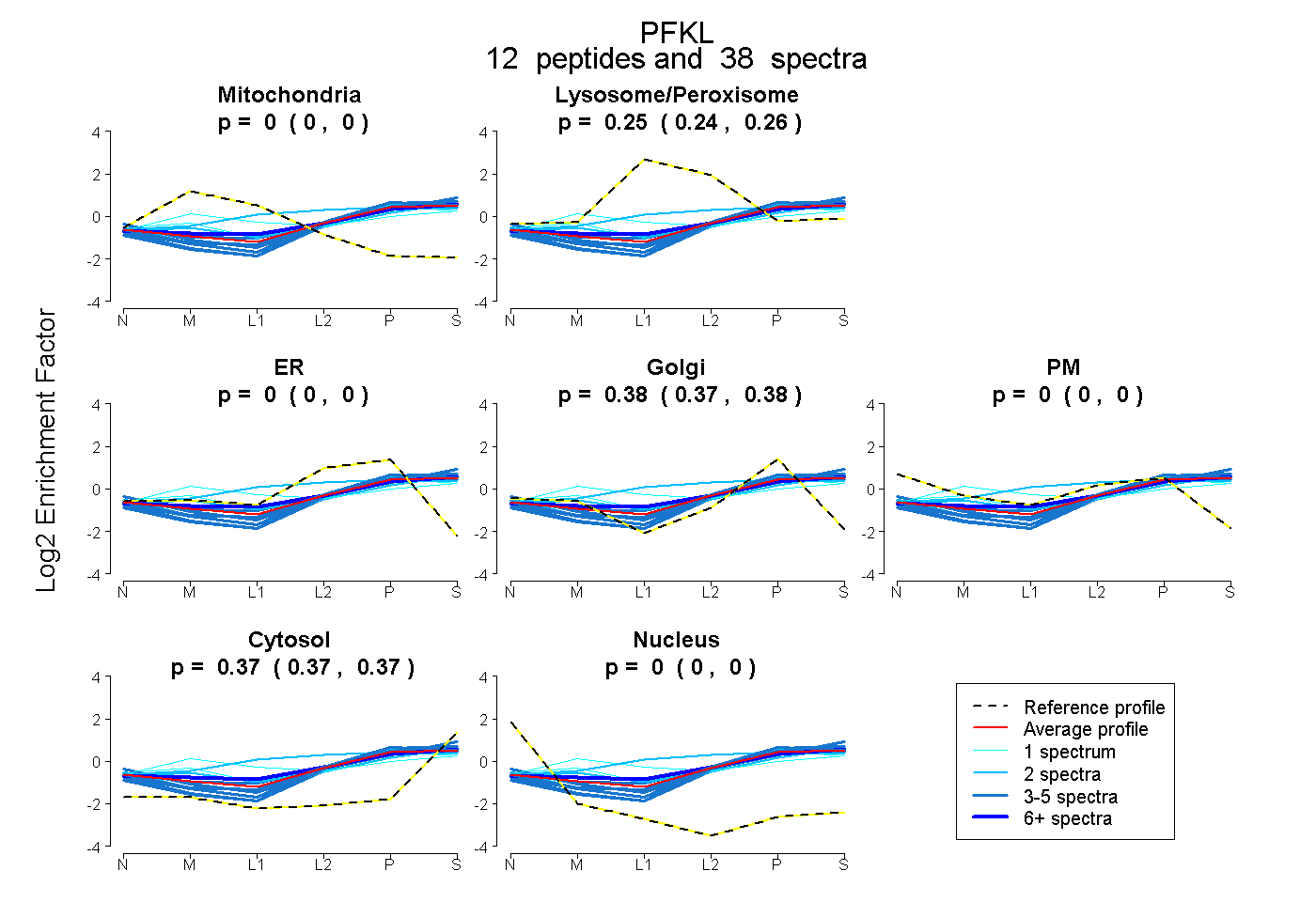
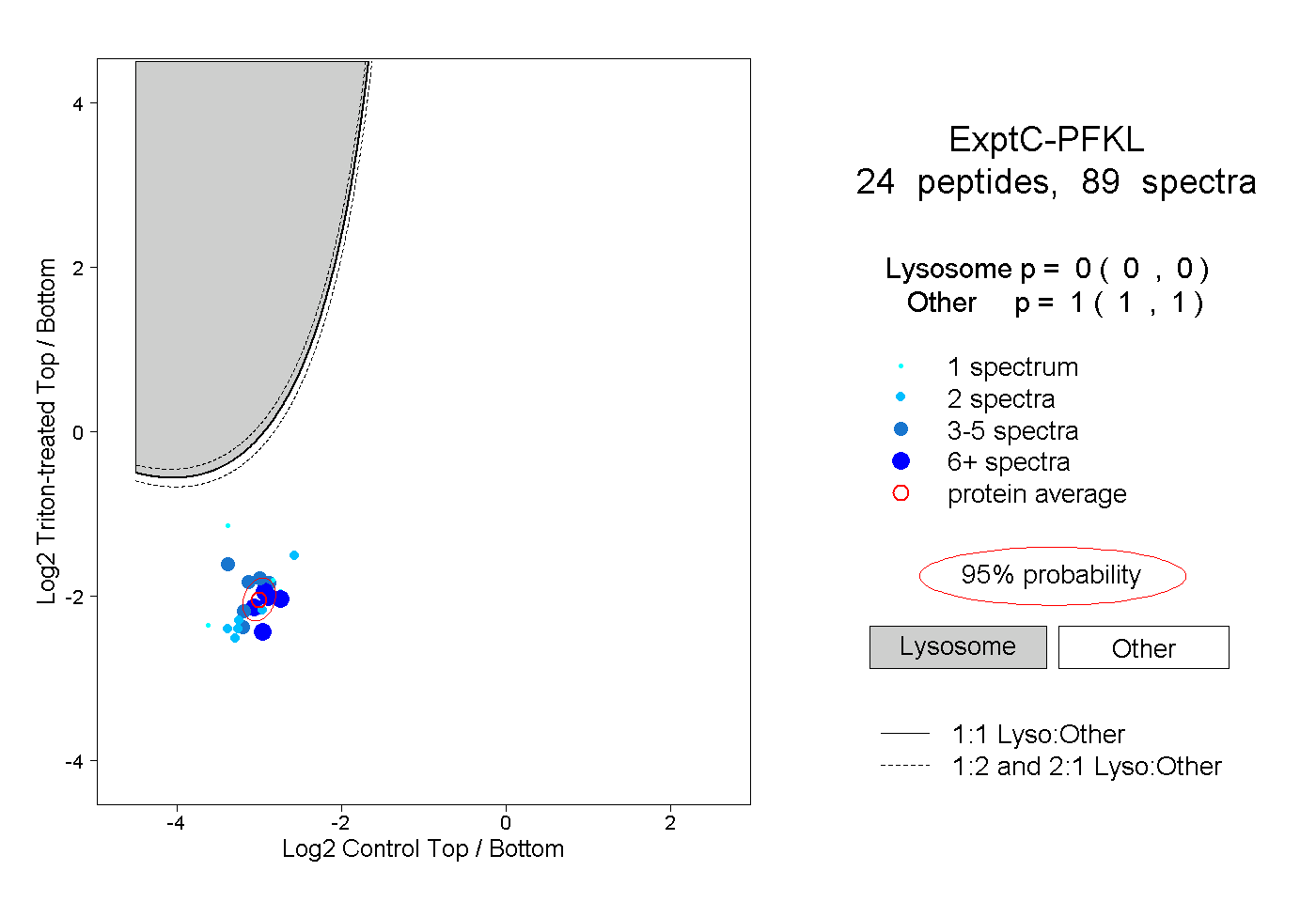
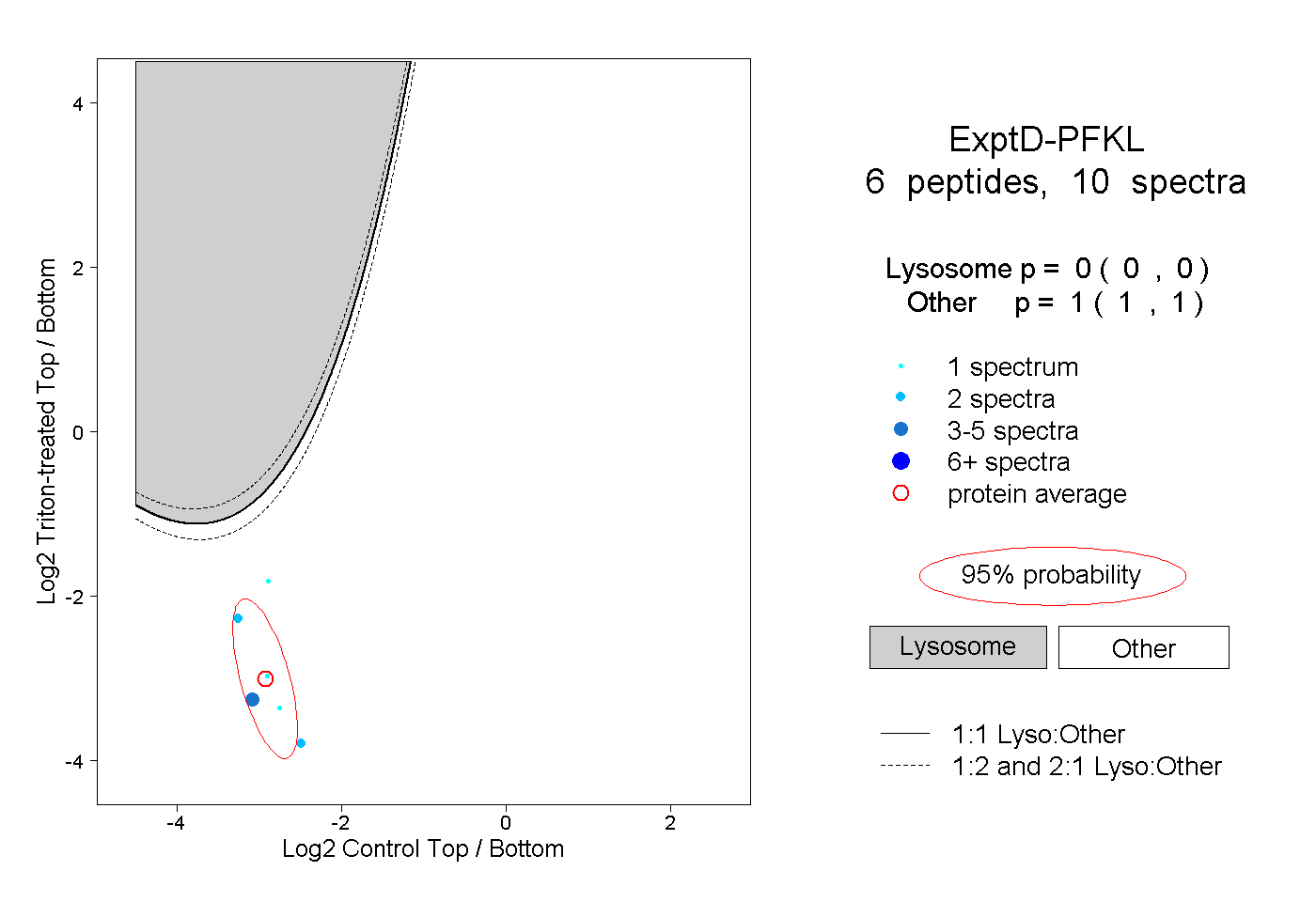
| 2 spectra, EQWWLNLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VVAFSSVTELK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TGISEGHTVYVVHDGFEGLAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, NEWGSLLEELVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, GGTPSAFDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, ETDFEHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, DLVVQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, TFVLEVMGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, AMLWMSEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, GVFDCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SFENNWK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, FDEAIQLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, HGKPISSSYVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, VTVLGHVQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, QSASGTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, TLPKPHLEAIVENLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, IMEVIDAITTTAQSHQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, MSGAGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, MGIYVGAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ANVEHMTEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, TNVLGHLQQGGAPTPFDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, LPLMECVQVTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, GGSMLGTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, LIAHQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |