peptides
spectra
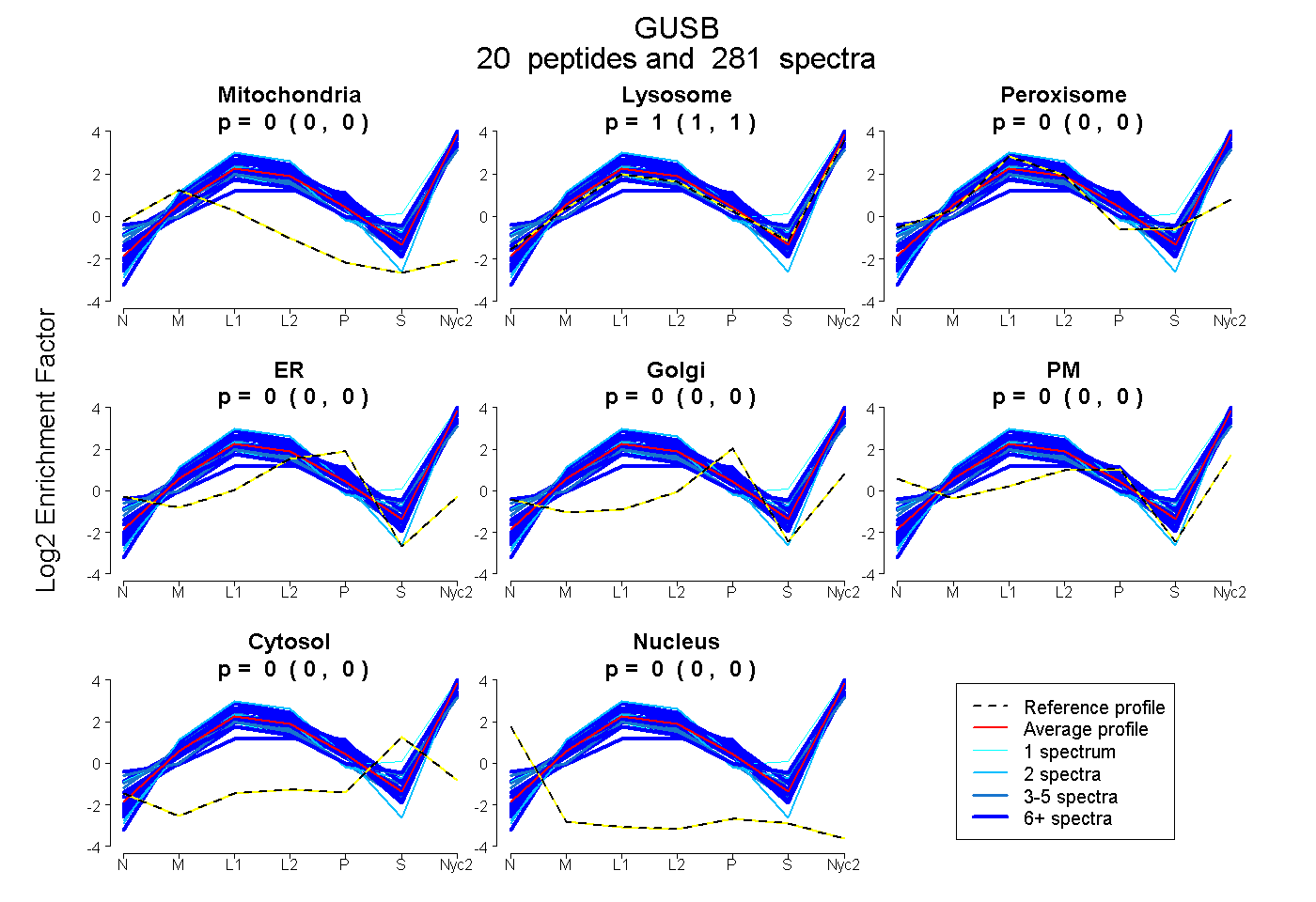
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
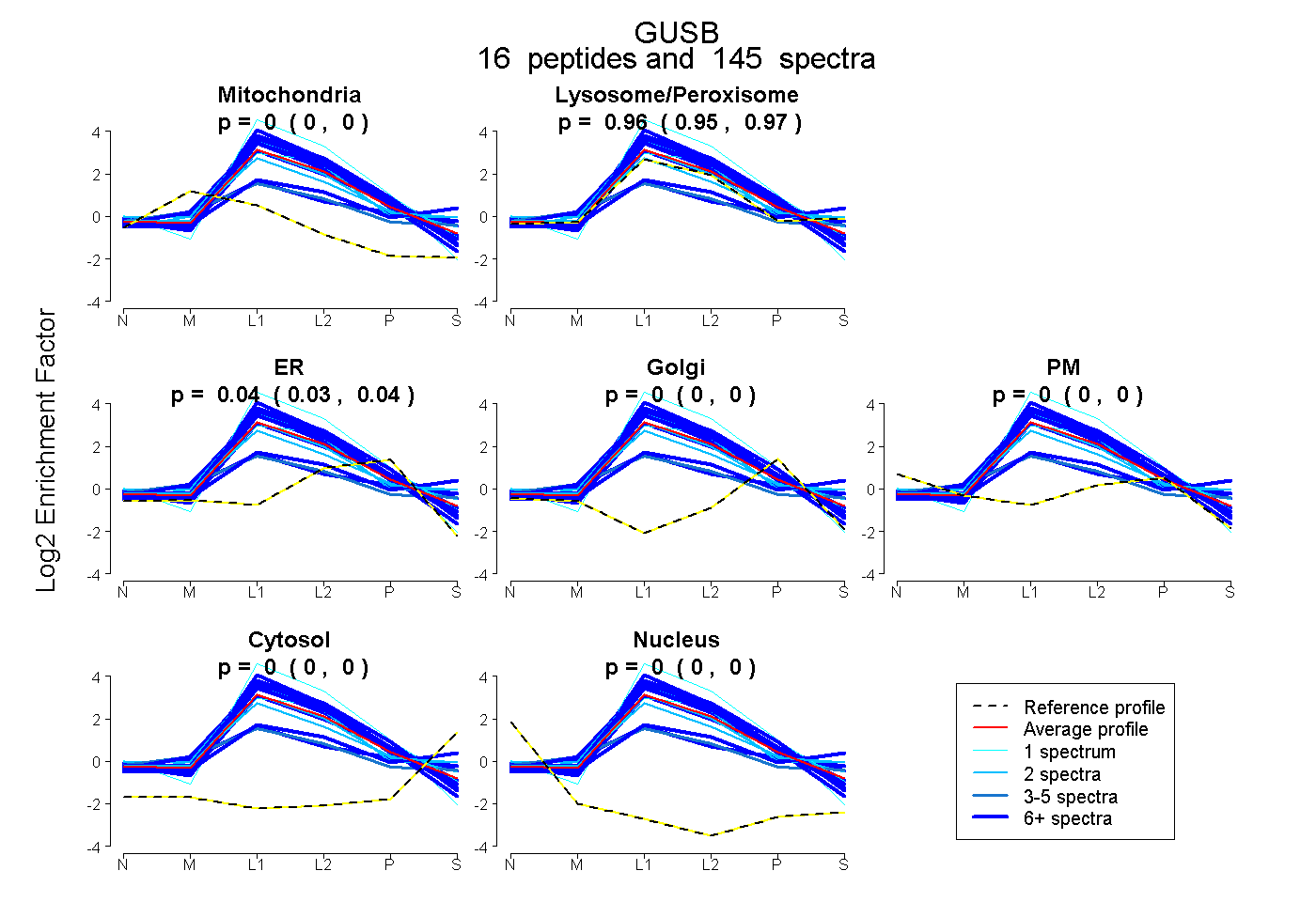
0.000 | 0.000
0.954 | 0.968
0.032 | 0.044
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
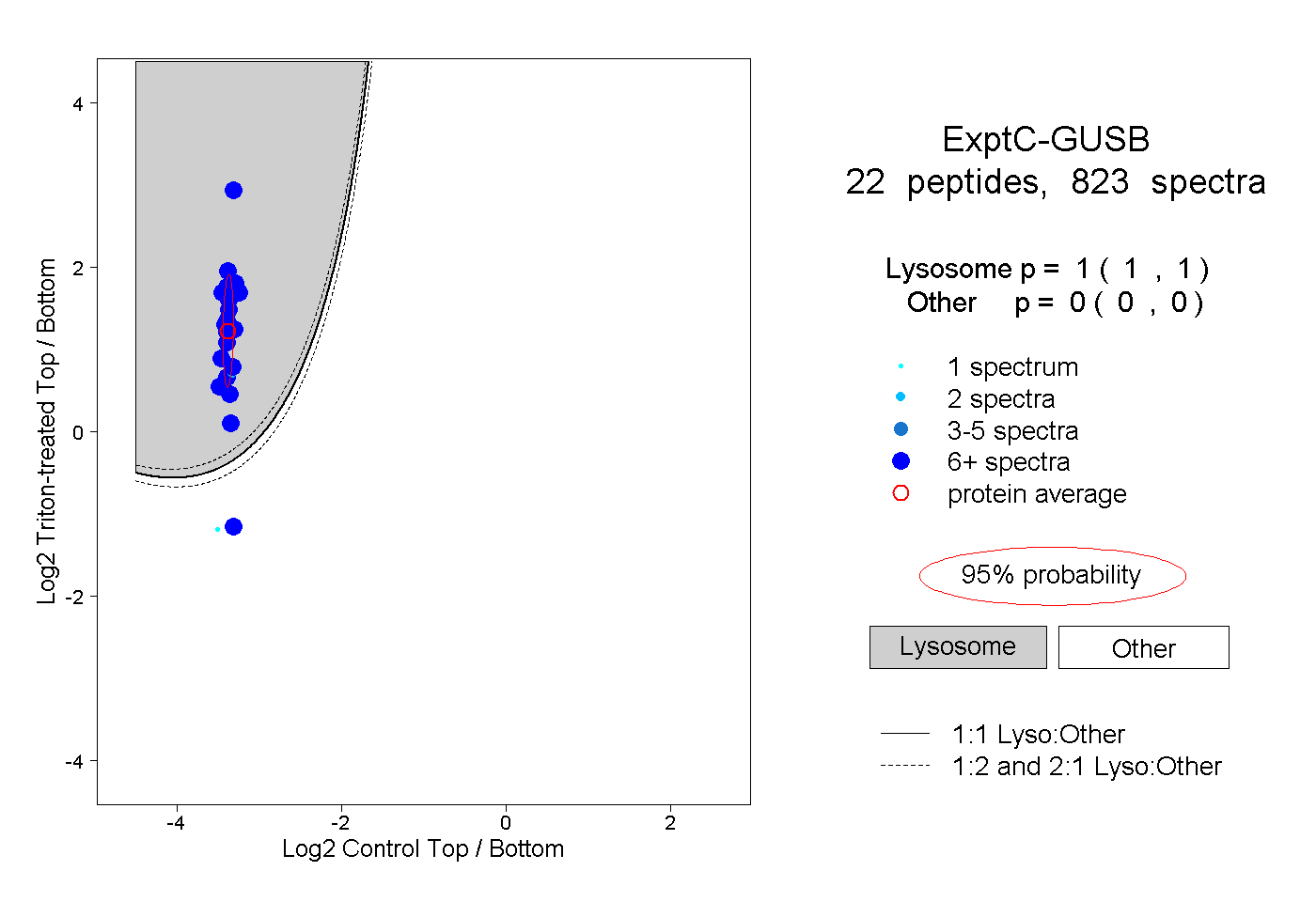
1.000 | 1.000
0.000 | 0.000
peptides
spectra
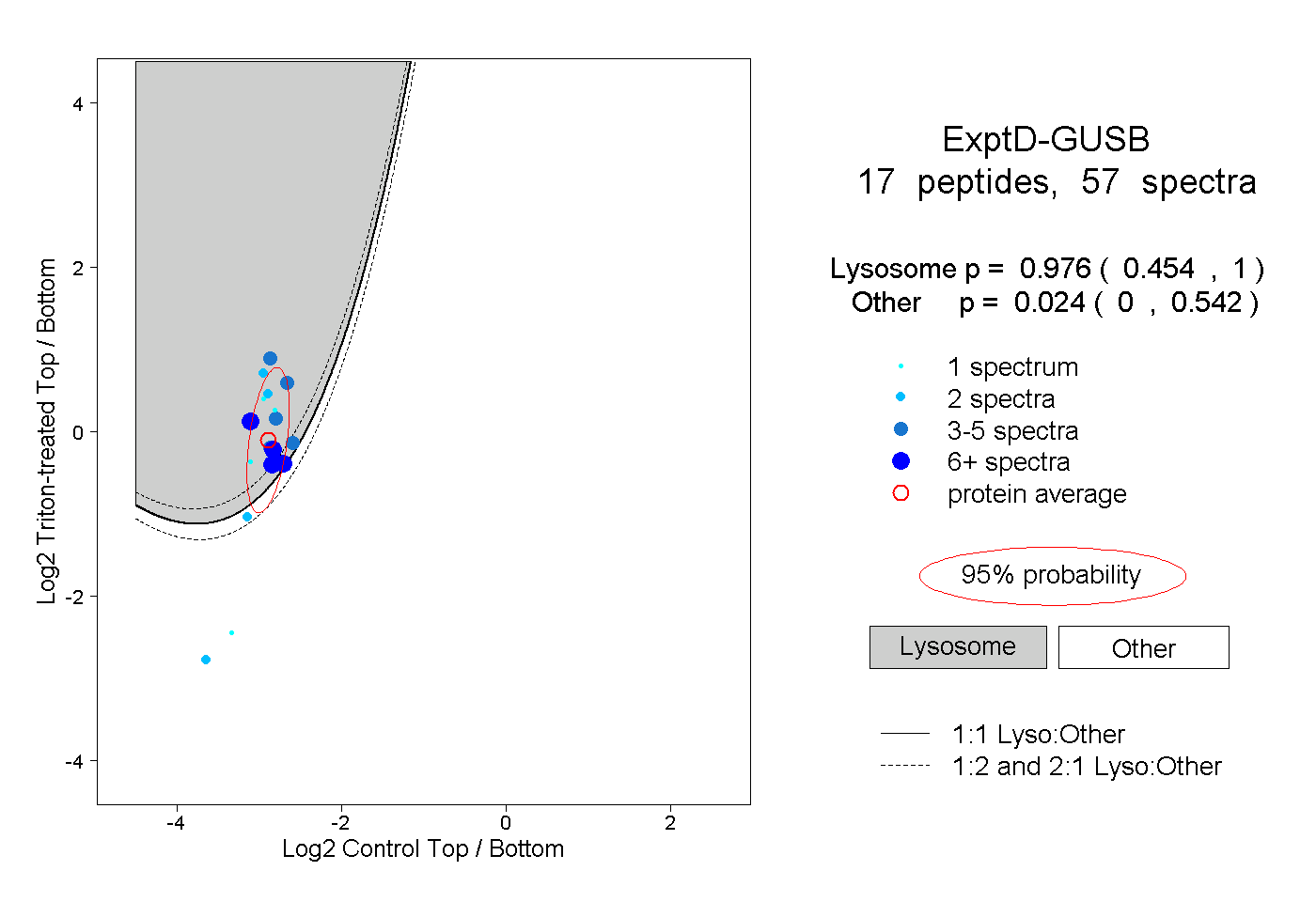
0.454 | 1.000
0.000 | 0.542