peptides
spectra
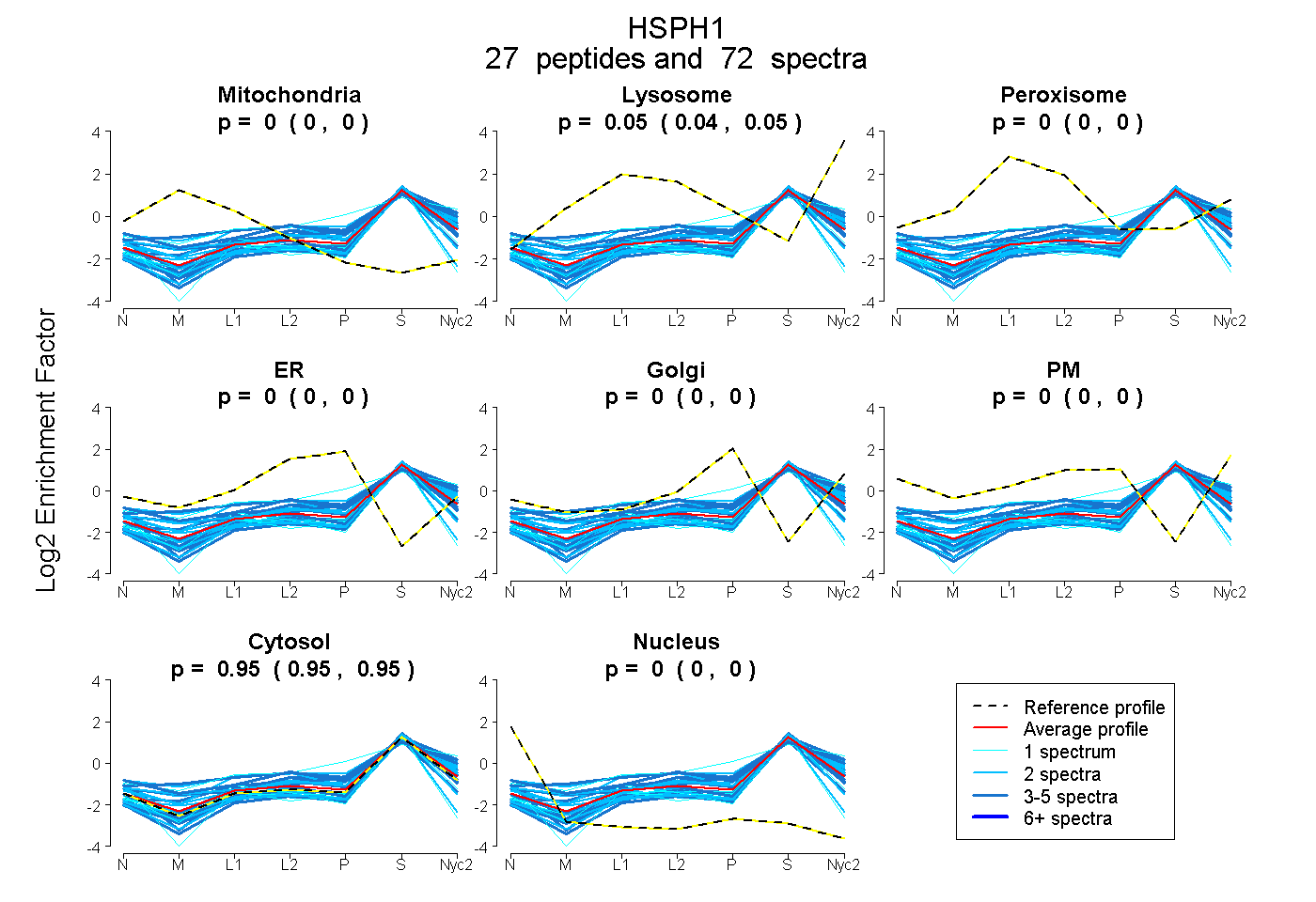
0.000 | 0.000
0.042 | 0.050
0.000 | 0.004
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.949 | 0.955
0.000 | 0.000
peptides
spectra
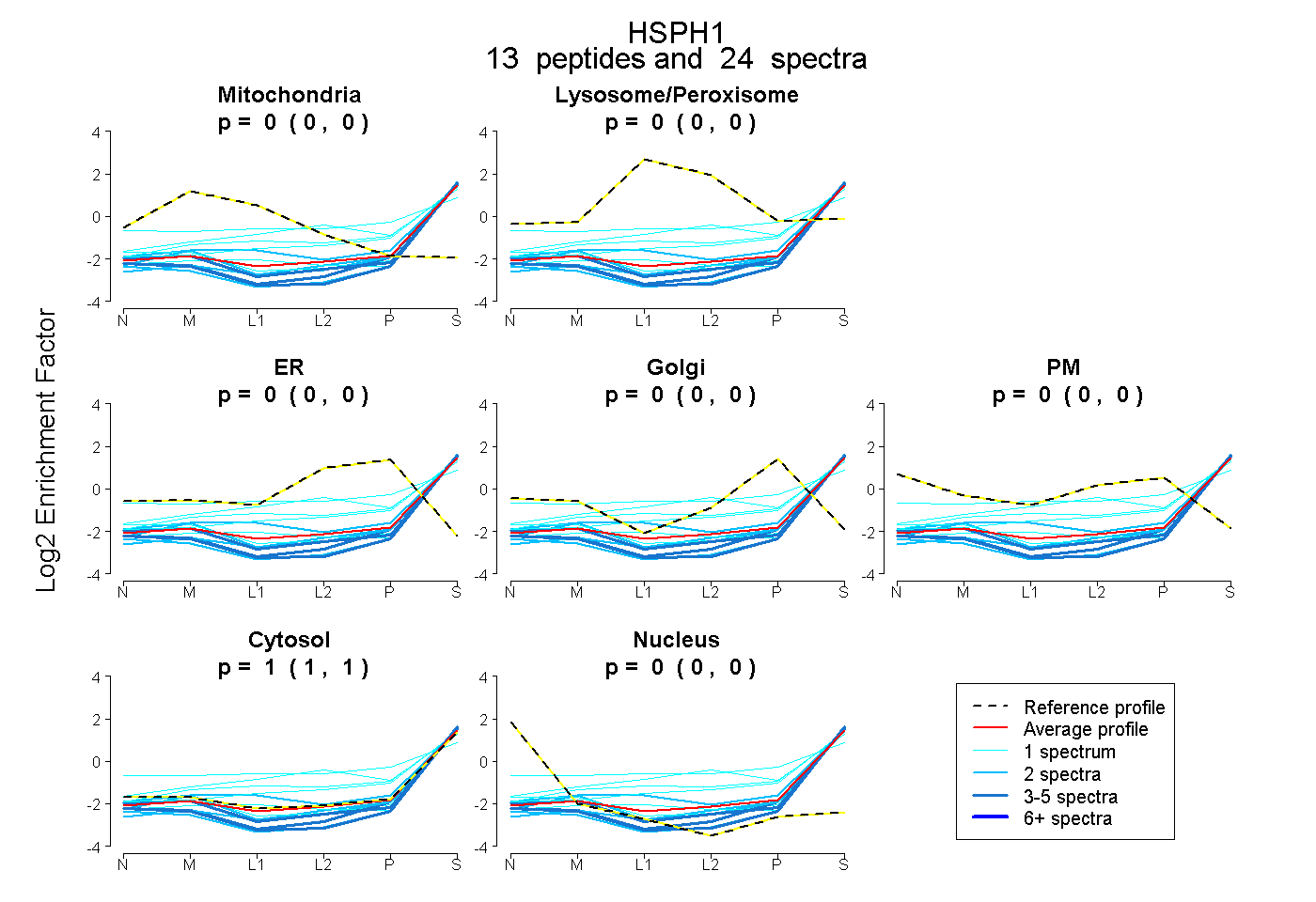
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
72 spectra |
 |
0.000 0.000 | 0.000 |
0.048 0.042 | 0.050 |
0.000 0.000 | 0.004 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.952 0.949 | 0.955 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
24 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
| 3 spectra, VLEELGQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.999 | 0.001 | |||
| 1 spectrum, THEISAK | 0.000 | 0.134 | 0.017 | 0.000 | 0.000 | 0.849 | 0.000 | |||
| 2 spectra, TEEVSAIEIVGGATR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, LVEHFCAEFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, DVSTTLNADEAVAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.981 | 0.019 | |||
| 4 spectra, FQEAEERPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 3 spectra, SQFEELCAELLQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, KPVTDCVISVPSFFTDAER | 0.000 | 0.203 | 0.011 | 0.000 | 0.000 | 0.787 | 0.000 | |||
| 1 spectrum, LAADFR | 0.000 | 0.307 | 0.018 | 0.000 | 0.000 | 0.675 | 0.000 | |||
| 2 spectra, LHQECEK | 0.000 | 0.055 | 0.000 | 0.000 | 0.000 | 0.945 | 0.000 | |||
| 2 spectra, LQHYAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, AFNDPFIQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, SVLDAAQIVGLNCLR | 0.000 | 0.340 | 0.000 | 0.180 | 0.000 | 0.480 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
87 spectra |
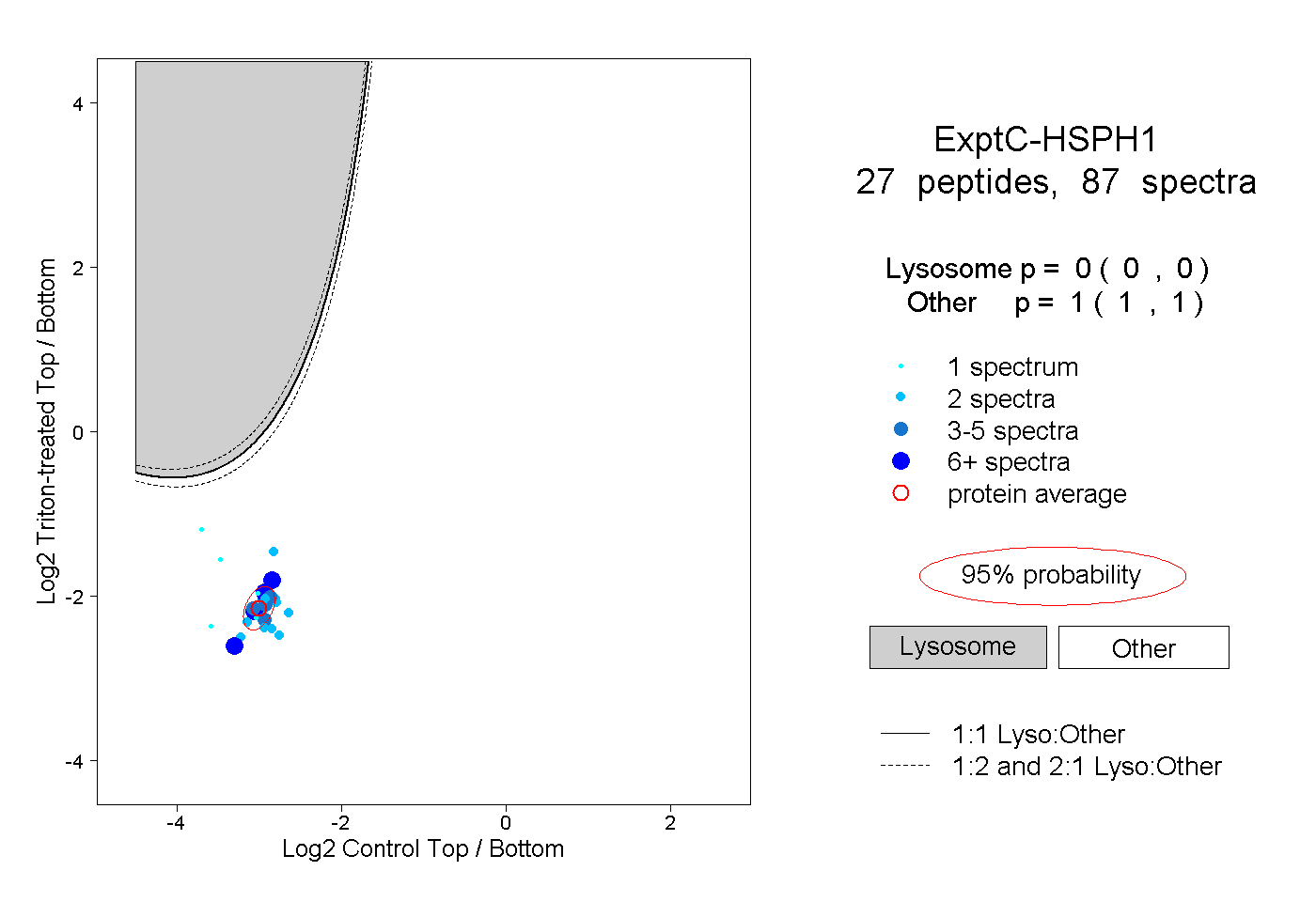 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
13 spectra |
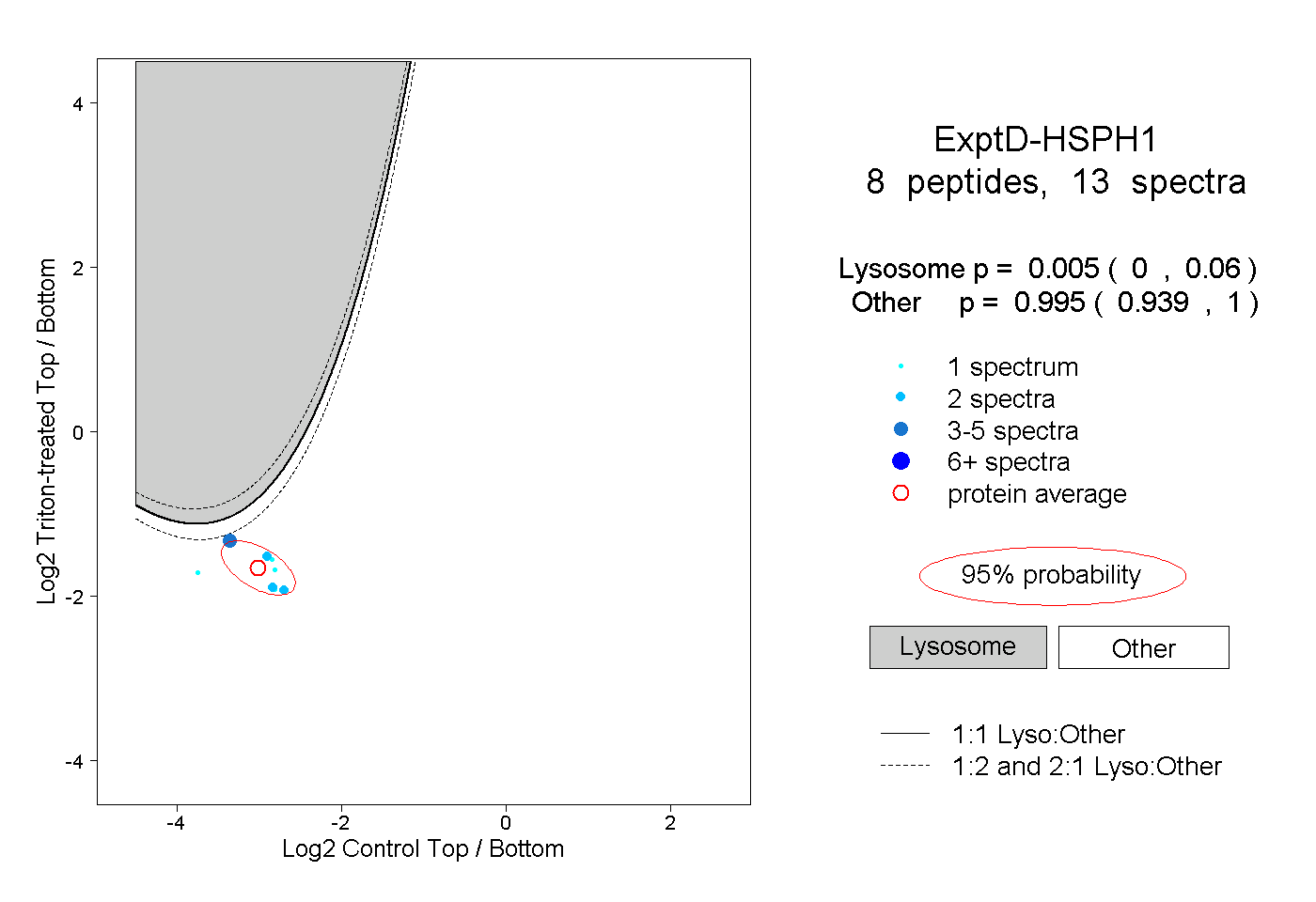 |
0.005 0.000 | 0.060 |
0.995 0.939 | 1.000 |