peptides
spectra
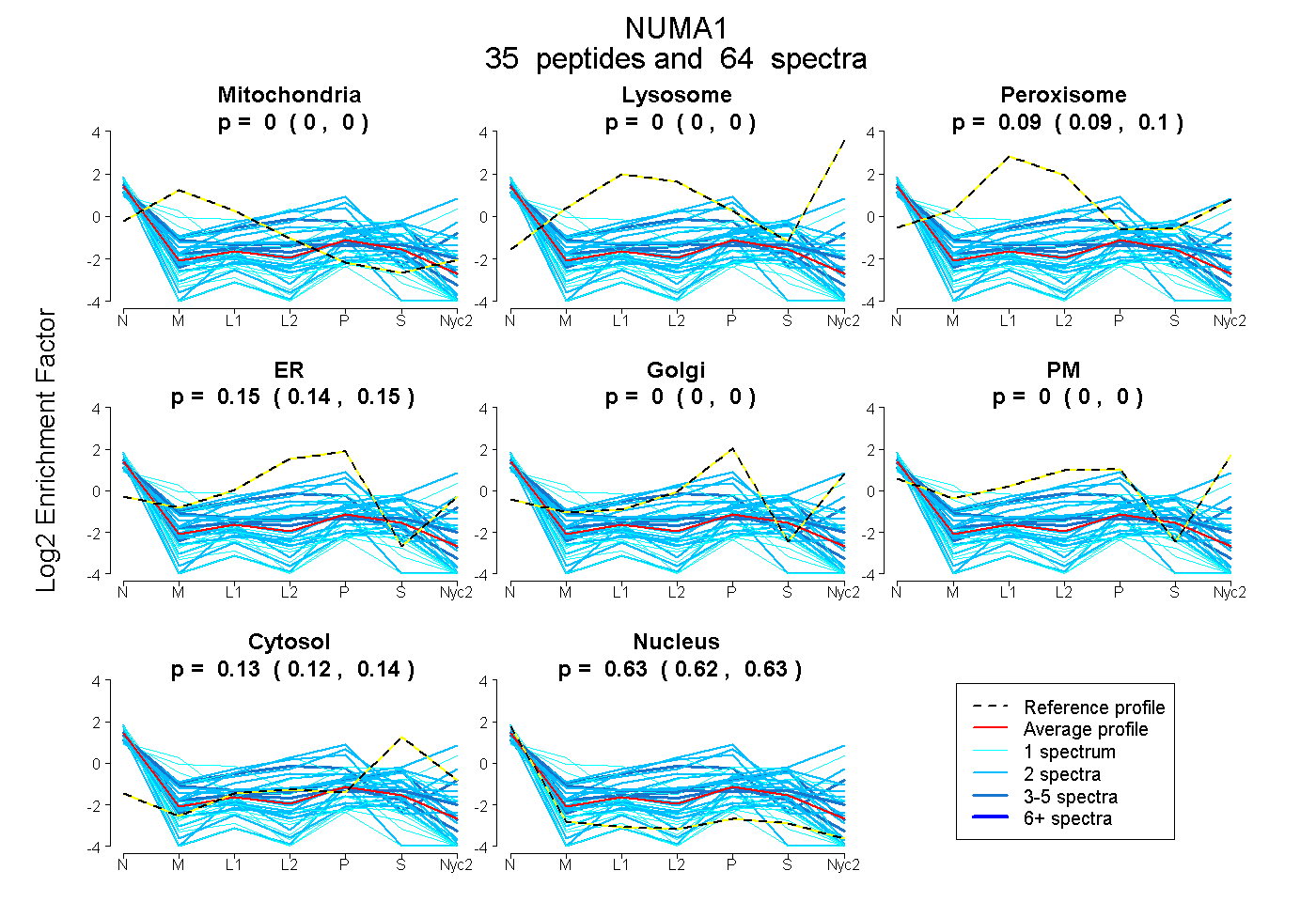
0.000 | 0.000
0.000 | 0.000
0.086 | 0.102
0.137 | 0.155
0.000 | 0.000
0.000 | 0.000
0.122 | 0.139
0.621 | 0.633
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
64 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.095 0.086 | 0.102 |
0.147 0.137 | 0.155 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.131 0.122 | 0.139 |
0.627 0.621 | 0.633 |
| 3 spectra, AELEMR | 0.000 | 0.000 | 0.032 | 0.155 | 0.000 | 0.000 | 0.364 | 0.449 | ||
| 1 spectrum, EAEQMGGELER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.018 | 0.982 | ||
| 2 spectra, QDHAQQLATIVEAR | 0.000 | 0.000 | 0.181 | 0.101 | 0.000 | 0.018 | 0.275 | 0.425 | ||
| 5 spectra, TEAPGPEVEALR | 0.071 | 0.000 | 0.198 | 0.000 | 0.000 | 0.113 | 0.106 | 0.512 | ||
| 4 spectra, AALMQSQGQQQEVR | 0.011 | 0.000 | 0.130 | 0.131 | 0.000 | 0.379 | 0.000 | 0.349 | ||
| 2 spectra, ISQLEDR | 0.000 | 0.000 | 0.142 | 0.055 | 0.000 | 0.000 | 0.208 | 0.595 | ||
| 2 spectra, GQAQADLAQEK | 0.082 | 0.000 | 0.083 | 0.000 | 0.000 | 0.000 | 0.046 | 0.789 | ||
| 2 spectra, VMEGSEMELAK | 0.015 | 0.000 | 0.060 | 0.000 | 0.000 | 0.267 | 0.360 | 0.297 | ||
| 1 spectrum, QFLEVELDQAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.334 | 0.666 | ||
| 1 spectrum, LQNTLNEQR | 0.104 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.040 | 0.856 | ||
| 1 spectrum, THYDAK | 0.000 | 0.000 | 0.000 | 0.272 | 0.000 | 0.000 | 0.415 | 0.313 | ||
| 2 spectra, ELGELGSLR | 0.000 | 0.000 | 0.039 | 0.006 | 0.000 | 0.000 | 0.132 | 0.822 | ||
| 1 spectrum, ELGHNQAASASAQR | 0.248 | 0.000 | 0.000 | 0.008 | 0.266 | 0.078 | 0.084 | 0.317 | ||
| 2 spectra, ATSSTQSLAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.268 | 0.732 | ||
| 2 spectra, QAASPQEPSELEELR | 0.000 | 0.000 | 0.000 | 0.359 | 0.000 | 0.366 | 0.094 | 0.182 | ||
| 2 spectra, SLEAQVAHADQQLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.163 | 0.000 | 0.277 | 0.560 | ||
| 2 spectra, AEESGQELK | 0.000 | 0.000 | 0.084 | 0.468 | 0.000 | 0.055 | 0.134 | 0.259 | ||
| 1 spectrum, ASYAEQLSMLK | 0.314 | 0.000 | 0.167 | 0.000 | 0.000 | 0.138 | 0.194 | 0.188 | ||
| 1 spectrum, LVVAESEK | 0.493 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.057 | 0.450 | ||
| 1 spectrum, GSLEEEK | 0.000 | 0.000 | 0.182 | 0.000 | 0.000 | 0.455 | 0.189 | 0.174 | ||
| 1 spectrum, LGSPDDSNSALLSLPGYRPTTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.022 | 0.000 | 0.000 | 0.978 | ||
| 3 spectra, LLQVETASSSAR | 0.010 | 0.000 | 0.142 | 0.141 | 0.000 | 0.000 | 0.027 | 0.679 | ||
| 2 spectra, QQVEQLSSSLK | 0.121 | 0.000 | 0.030 | 0.562 | 0.000 | 0.000 | 0.000 | 0.287 | ||
| 2 spectra, HELAGATAAQHGAESER | 0.000 | 0.000 | 0.115 | 0.095 | 0.000 | 0.152 | 0.107 | 0.531 | ||
| 2 spectra, AGEQQAAASHELK | 0.000 | 0.000 | 0.078 | 0.180 | 0.000 | 0.177 | 0.129 | 0.436 | ||
| 2 spectra, LLDDLSALR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.067 | 0.933 | ||
| 1 spectrum, QCQNLK | 0.000 | 0.000 | 0.053 | 0.068 | 0.000 | 0.000 | 0.044 | 0.835 | ||
| 2 spectra, TDAETHLAEMR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.476 | 0.440 | 0.084 | ||
| 2 spectra, IDHLALLNEK | 0.000 | 0.000 | 0.000 | 0.105 | 0.000 | 0.000 | 0.000 | 0.895 | ||
| 1 spectrum, DTAQTSVTQAQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 2 spectra, EIQALR | 0.000 | 0.000 | 0.075 | 0.092 | 0.000 | 0.000 | 0.163 | 0.670 | ||
| 2 spectra, LATDNTELQAR | 0.063 | 0.000 | 0.073 | 0.007 | 0.000 | 0.000 | 0.022 | 0.835 | ||
| 1 spectrum, LQQLEEAHQAETEALR | 0.142 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.858 | ||
| 1 spectrum, VEFAALQEALTHAMTEK | 0.000 | 0.000 | 0.000 | 0.061 | 0.000 | 0.000 | 0.017 | 0.922 | ||
| 2 spectra, QAAGGLQAELMR | 0.000 | 0.000 | 0.092 | 0.039 | 0.000 | 0.000 | 0.080 | 0.788 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
2 spectra |
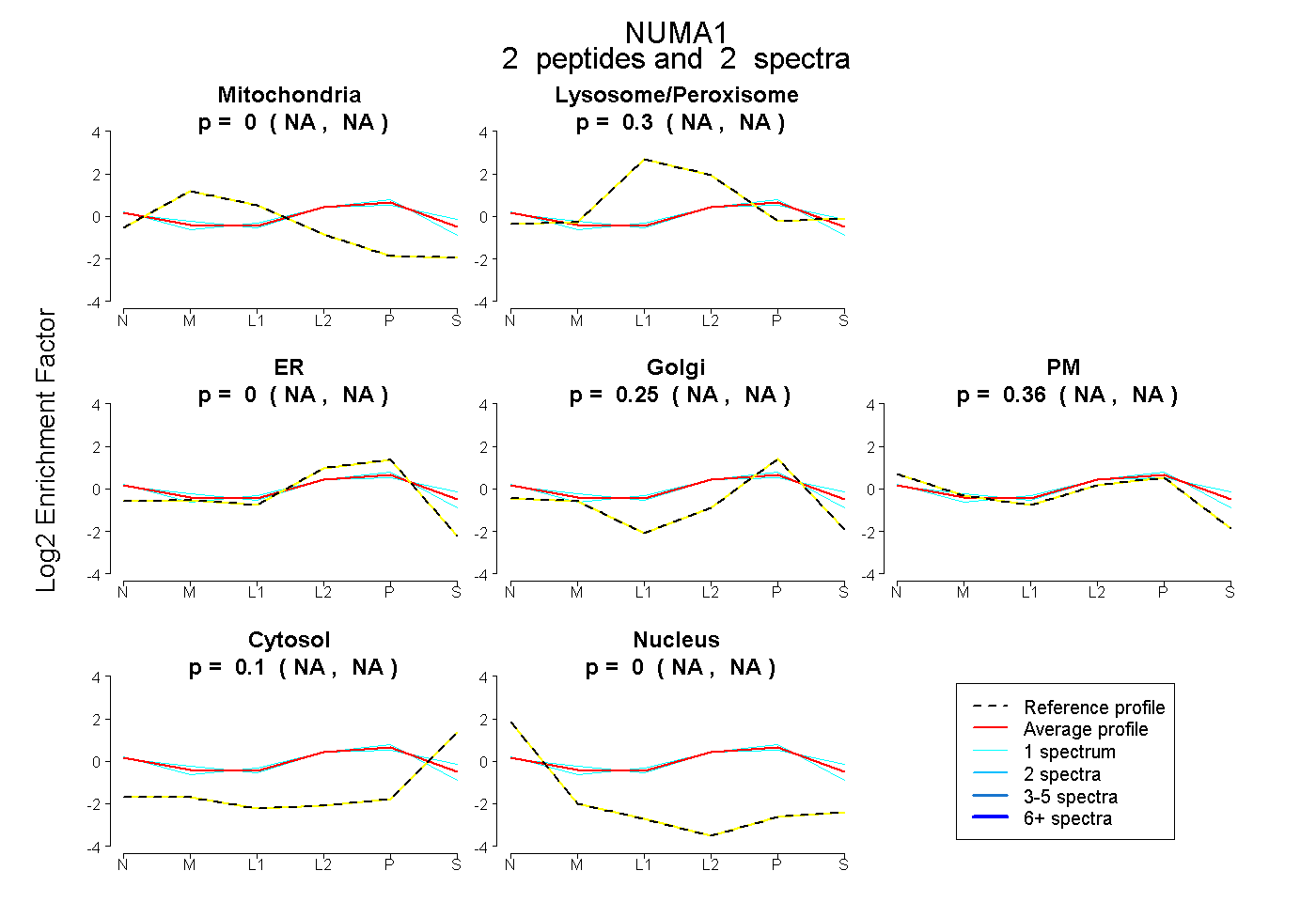 |
0.000 NA | NA |
0.295 NA | NA |
0.000 NA | NA |
0.247 NA | NA |
0.361 NA | NA |
0.097 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
26 spectra |
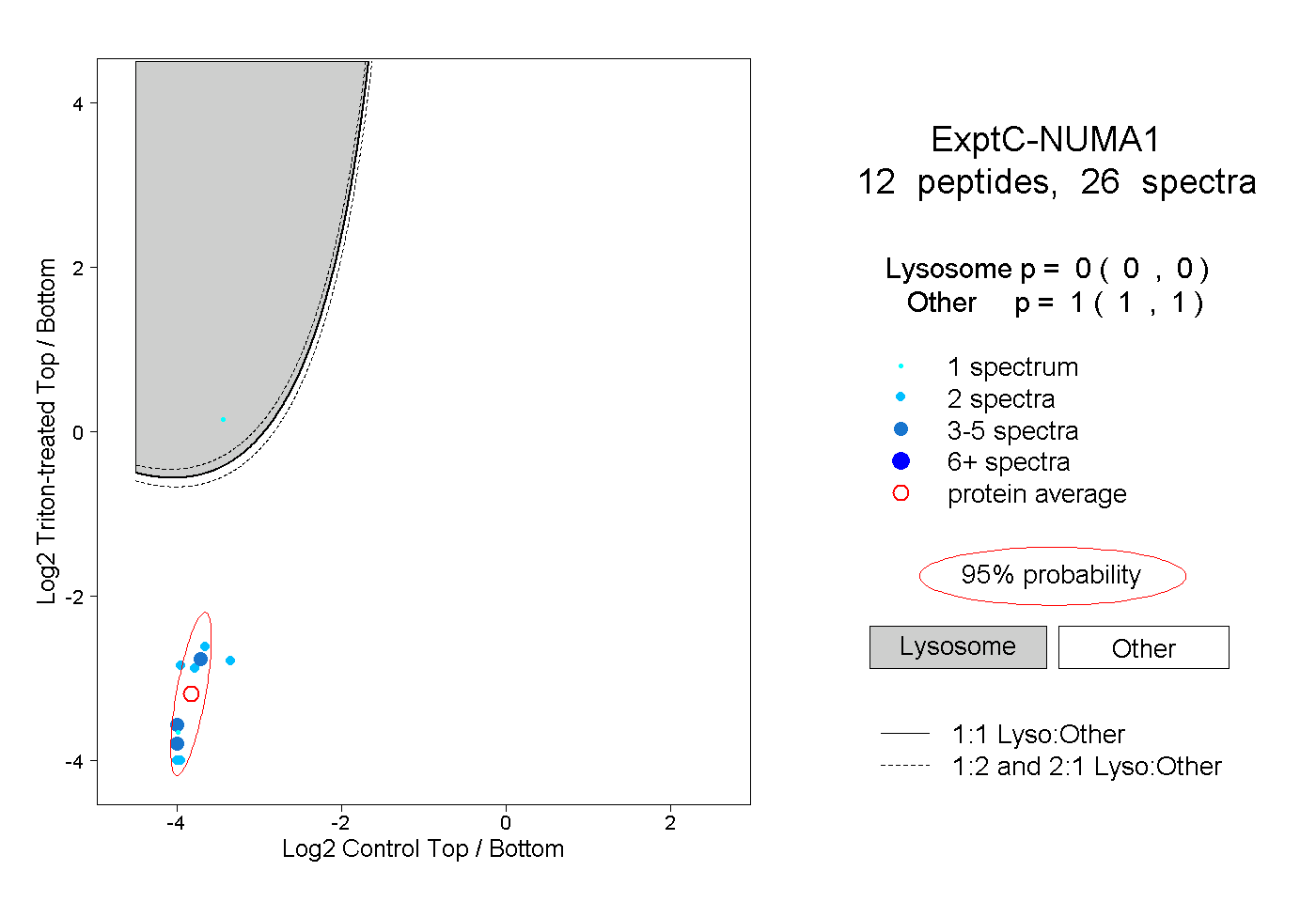 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
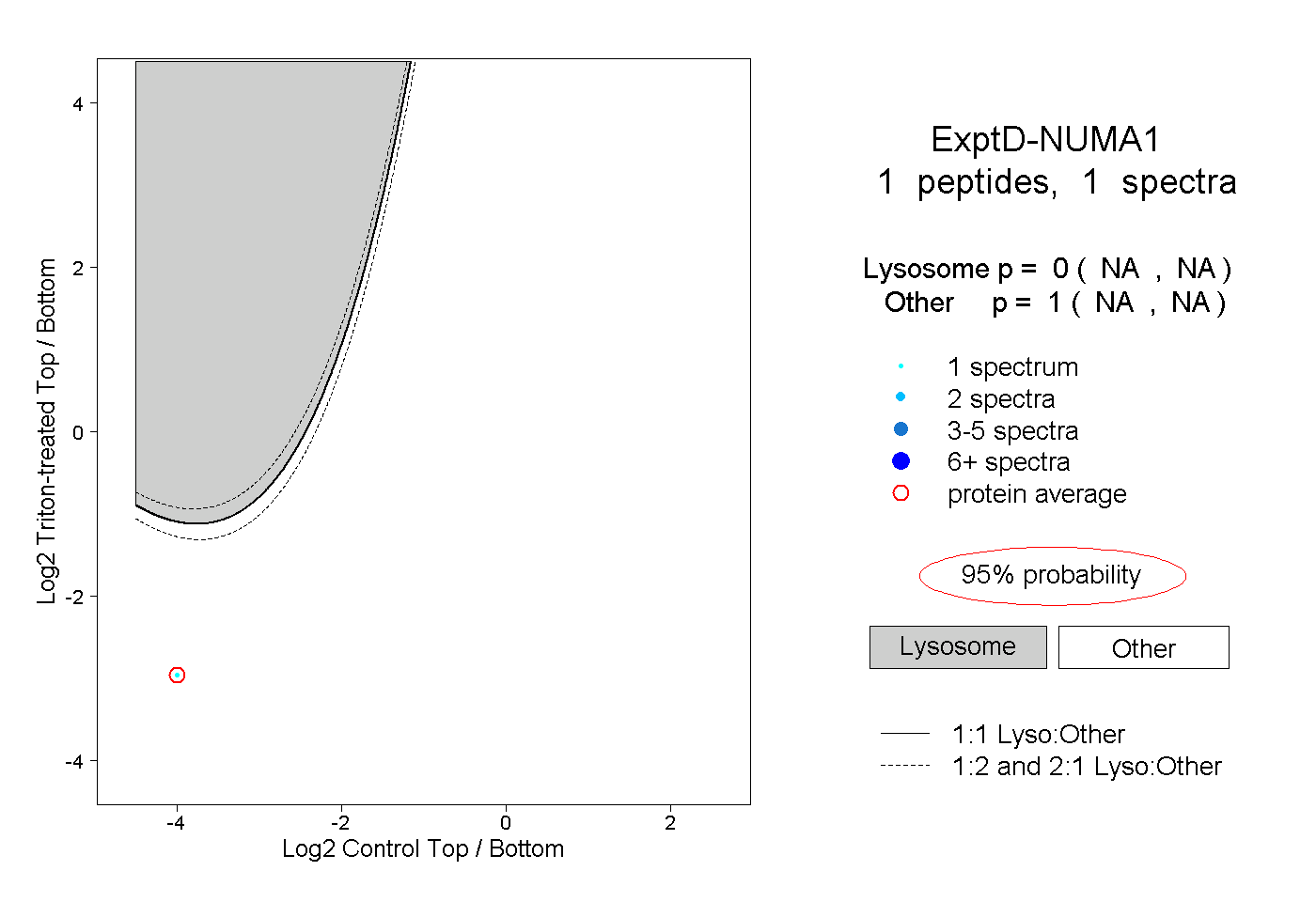 |
0.000 NA | NA |
1.000 NA | NA |