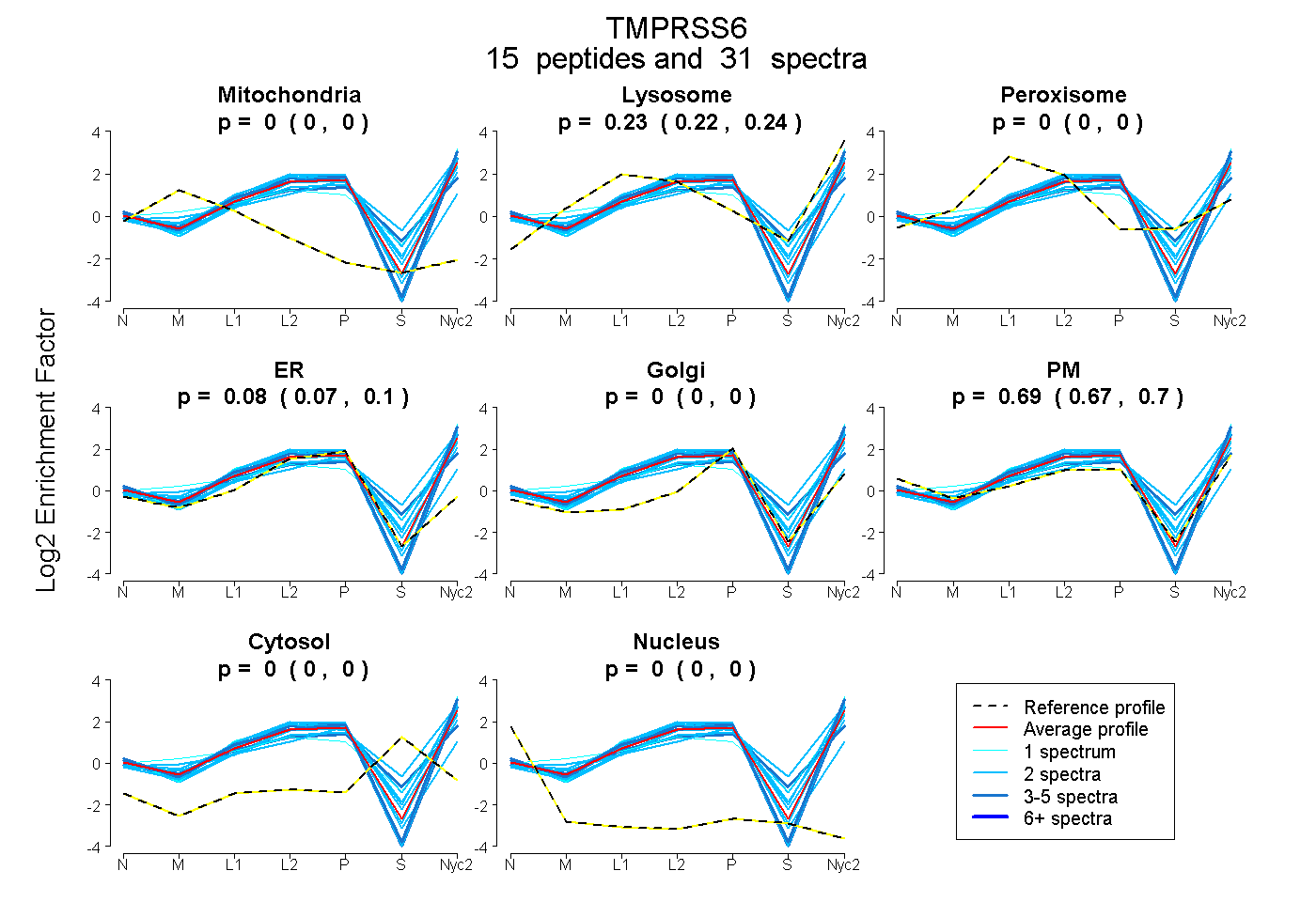
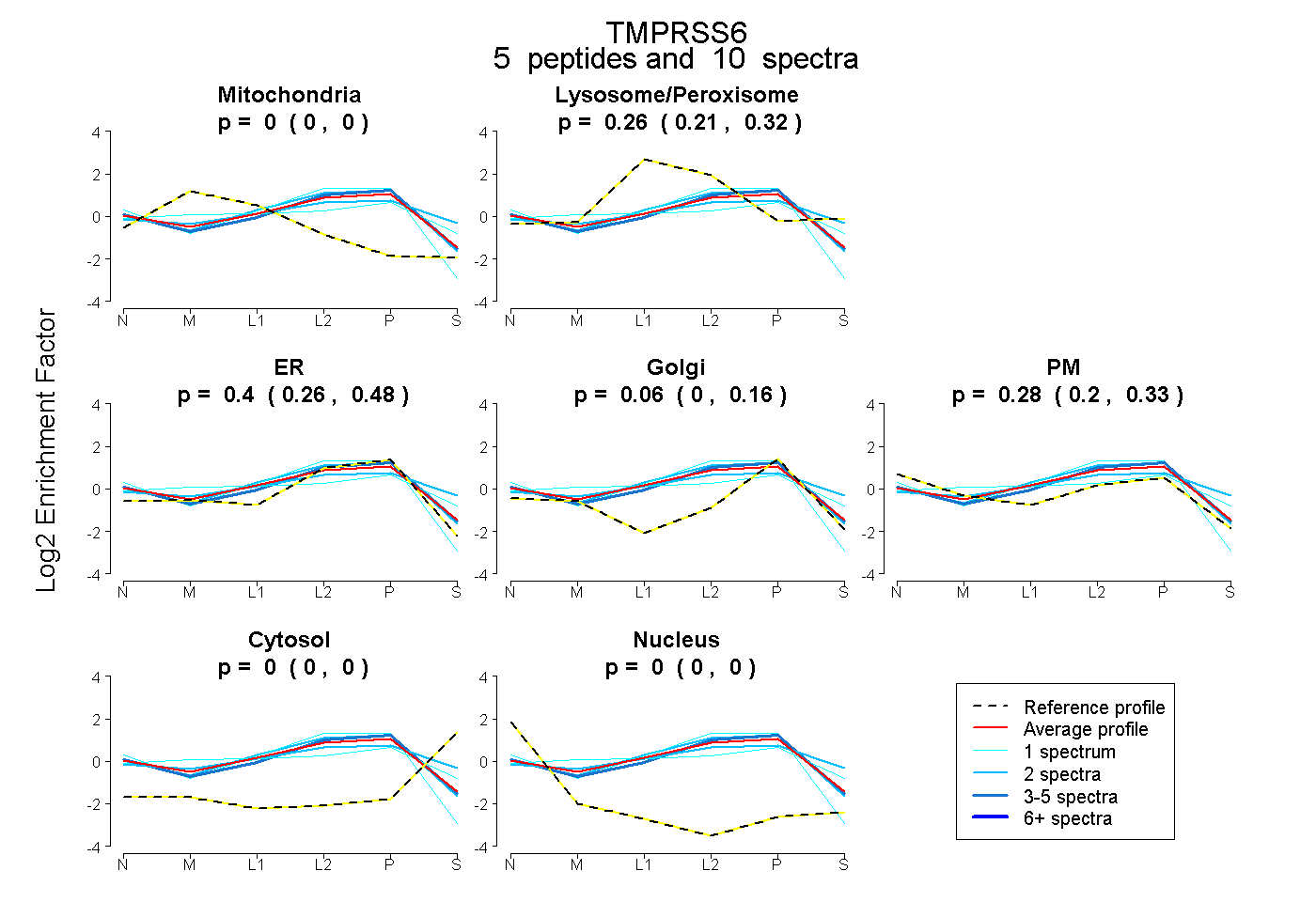
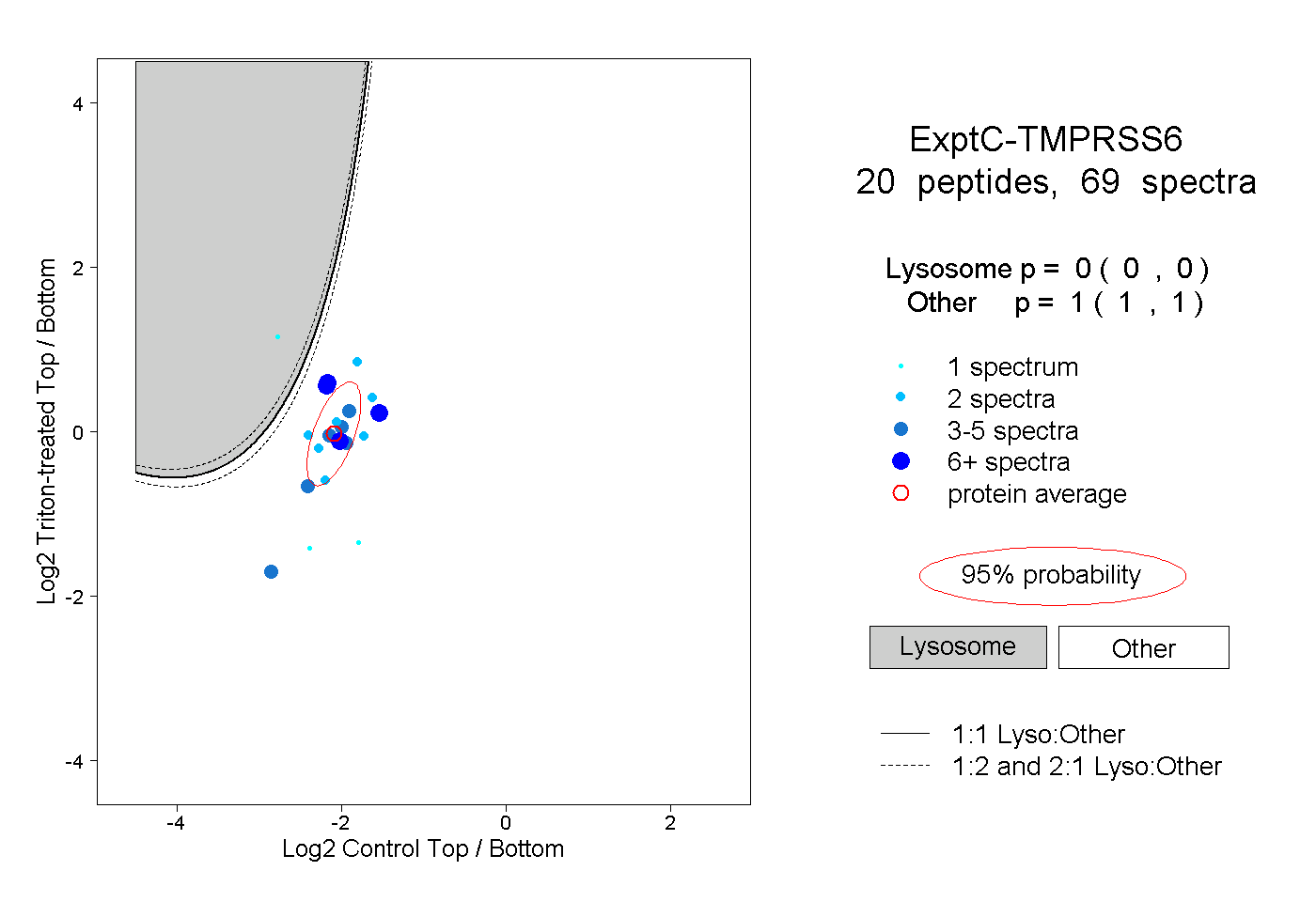
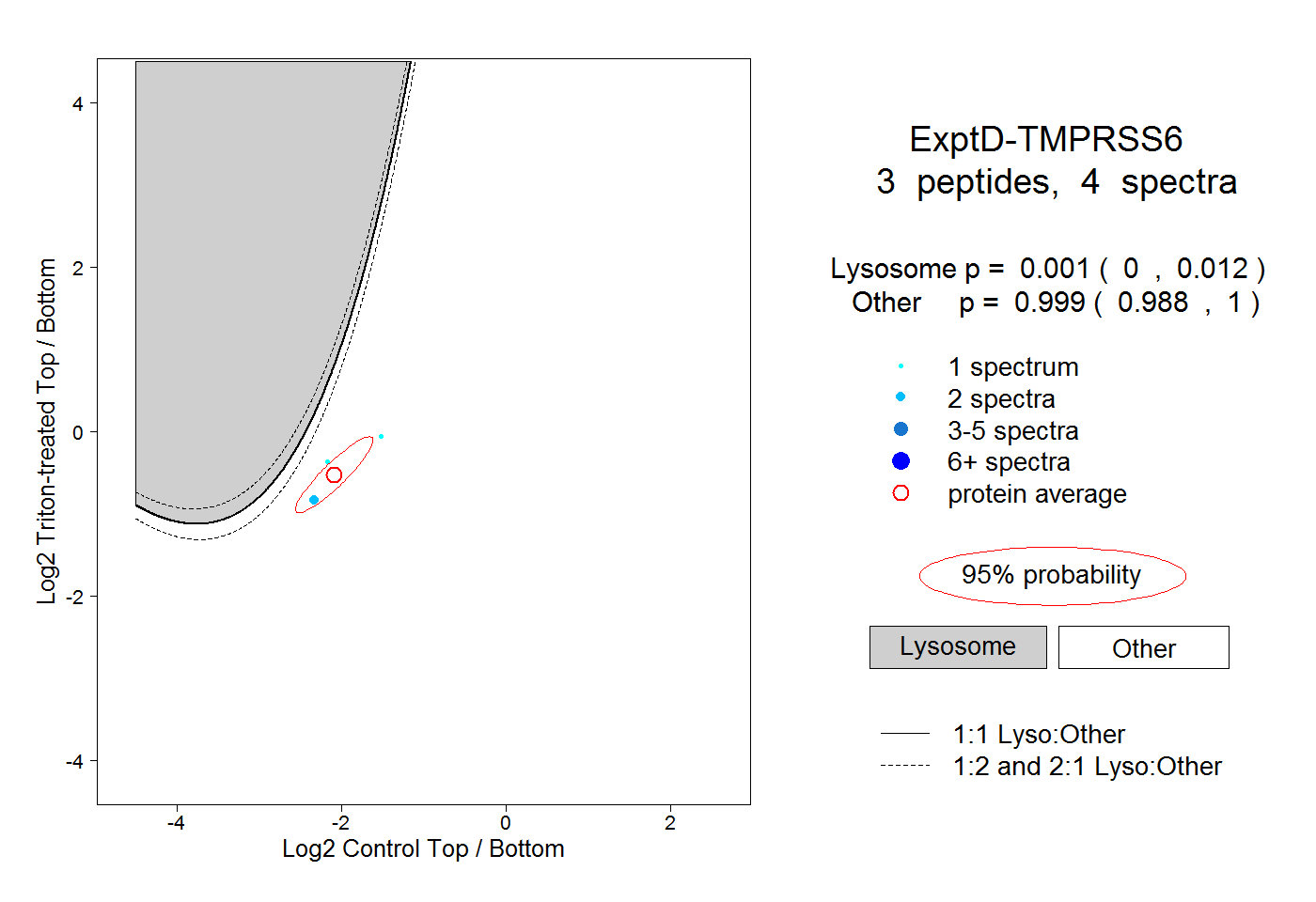
| 2 spectra, MLCAGYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, HFSQDLAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, YQVTPR |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 5 spectra, HICGGALIADR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, DACQGDSGGPLVCK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, WPGEVSFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VQLEWTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, EGGPGSSTLQK |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 2 spectra, GLHSFYDPFLLSVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, VAMYDAAGPLEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, TLQPYAER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ESIAFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, DCPNGLDER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VDVQLIPQDLCNEAYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, KPNPECDGQADCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LITSVYGCSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, MFQELVASTR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 4 spectra, LDPQGFLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, YSYVNPGQVLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LTLSPEVVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |