peptides
spectra
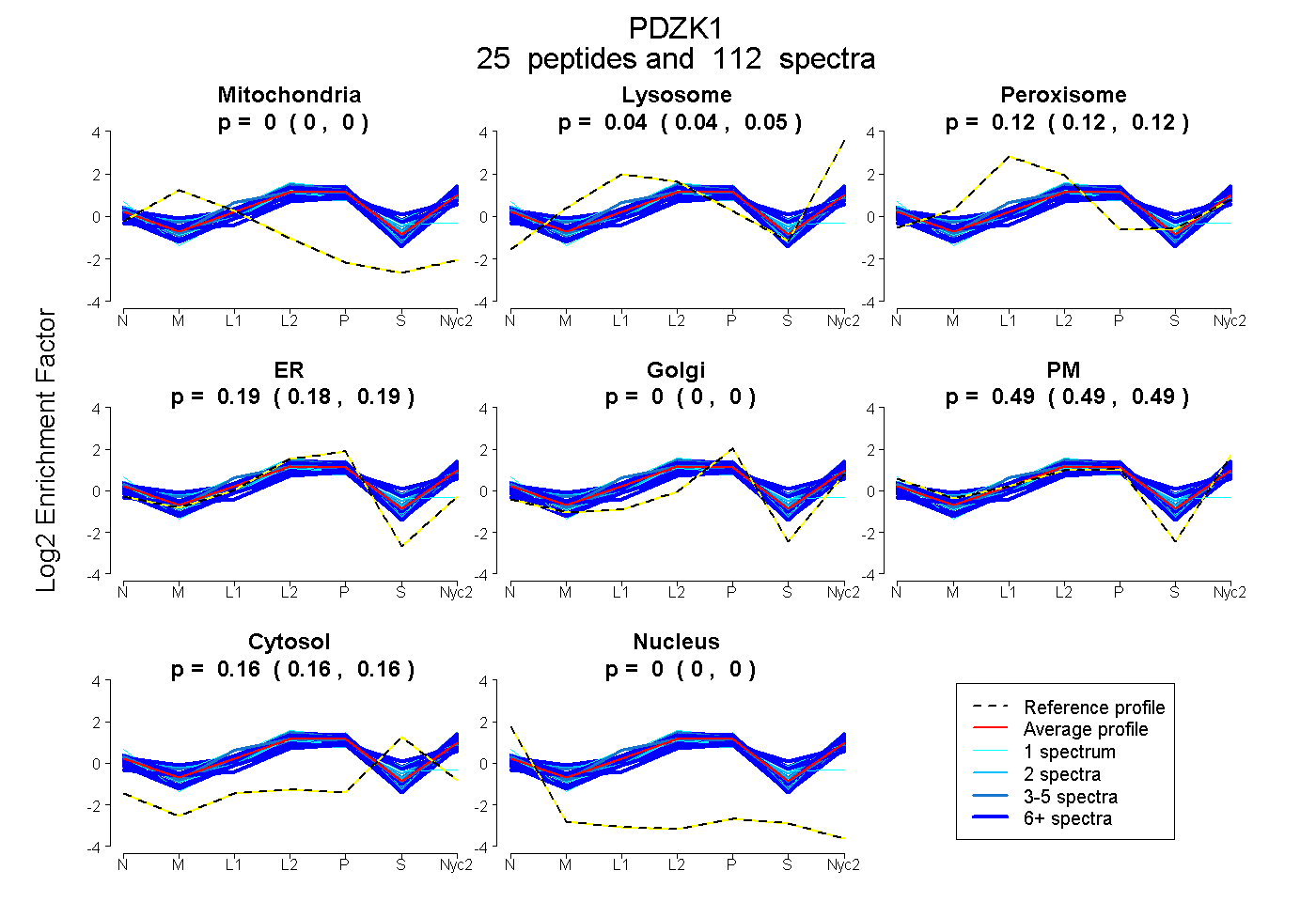
0.000 | 0.000
0.041 | 0.048
0.116 | 0.122
0.182 | 0.189
0.000 | 0.000
0.485 | 0.495
0.158 | 0.161
0.000 | 0.000
peptides
spectra
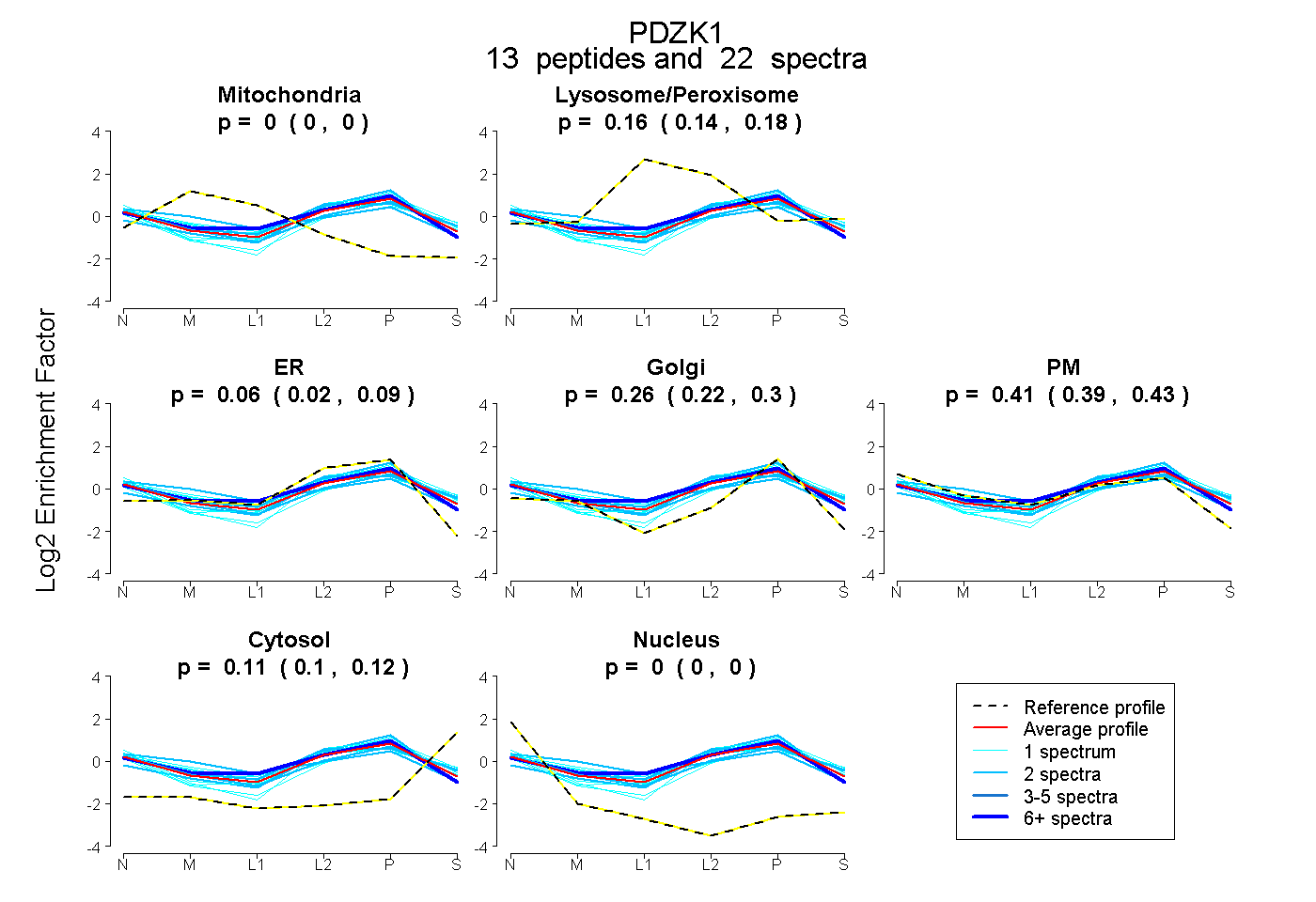
0.000 | 0.000
0.141 | 0.178
0.021 | 0.087
0.223 | 0.297
0.390 | 0.432
0.095 | 0.117
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
112 spectra |
 |
0.000 0.000 | 0.000 |
0.045 0.041 | 0.048 |
0.119 0.116 | 0.122 |
0.186 0.182 | 0.189 |
0.000 0.000 | 0.000 |
0.491 0.485 | 0.495 |
0.160 0.158 | 0.161 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
22 spectra |
 |
0.000 0.000 | 0.000 |
0.161 0.141 | 0.178 |
0.057 0.021 | 0.087 |
0.262 0.223 | 0.297 |
0.413 0.390 | 0.432 |
0.107 0.095 | 0.117 |
0.000 0.000 | 0.000 |
| 6 spectra, LLPHQPR | 0.000 | 0.262 | 0.000 | 0.423 | 0.301 | 0.015 | 0.000 | |||
| 1 spectrum, DIEPGSPAEAAGLK | 0.000 | 0.034 | 0.279 | 0.084 | 0.499 | 0.103 | 0.000 | |||
| 1 spectrum, IMFLLVDK | 0.000 | 0.000 | 0.357 | 0.081 | 0.365 | 0.196 | 0.000 | |||
| 1 spectrum, HQVDLK | 0.000 | 0.120 | 0.208 | 0.282 | 0.309 | 0.081 | 0.000 | |||
| 1 spectrum, EPALNEK | 0.000 | 0.207 | 0.000 | 0.172 | 0.515 | 0.106 | 0.000 | |||
| 1 spectrum, DTDGHLVR | 0.000 | 0.122 | 0.000 | 0.115 | 0.544 | 0.219 | 0.000 | |||
| 1 spectrum, AGPEQK | 0.000 | 0.079 | 0.085 | 0.364 | 0.258 | 0.213 | 0.000 | |||
| 2 spectra, EGQNYGFFLR | 0.000 | 0.067 | 0.470 | 0.242 | 0.114 | 0.108 | 0.000 | |||
| 1 spectrum, ELDQSPR | 0.000 | 0.197 | 0.025 | 0.362 | 0.375 | 0.040 | 0.000 | |||
| 2 spectra, VIEEGSPAEK | 0.000 | 0.129 | 0.000 | 0.246 | 0.456 | 0.169 | 0.000 | |||
| 1 spectrum, GQPGSFVK | 0.000 | 0.169 | 0.000 | 0.045 | 0.641 | 0.145 | 0.000 | |||
| 2 spectra, IYSLAR | 0.000 | 0.154 | 0.157 | 0.011 | 0.508 | 0.170 | 0.000 | |||
| 2 spectra, EGNSFGFSLK | 0.009 | 0.144 | 0.000 | 0.103 | 0.642 | 0.102 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
169 spectra |
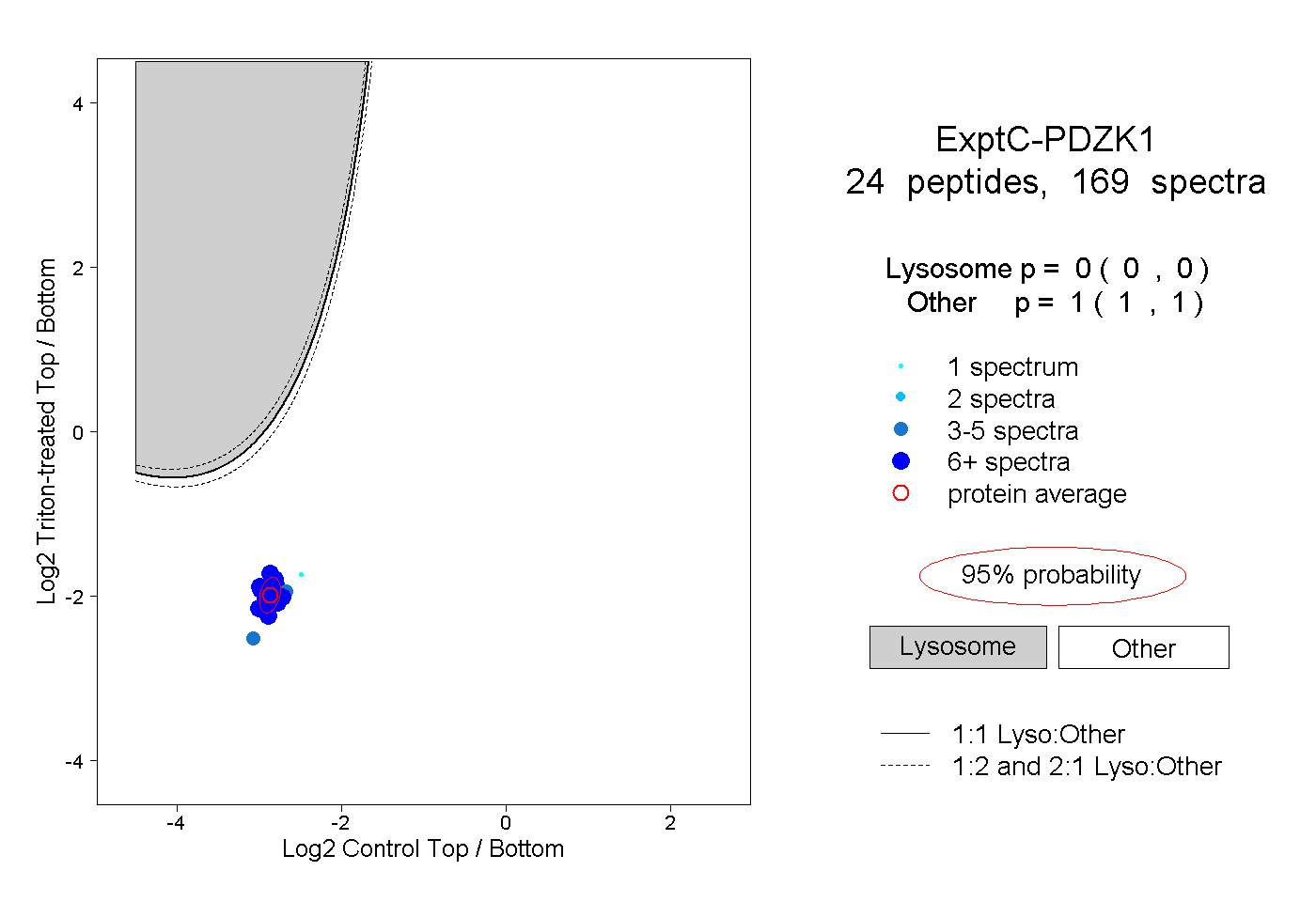 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
23 spectra |
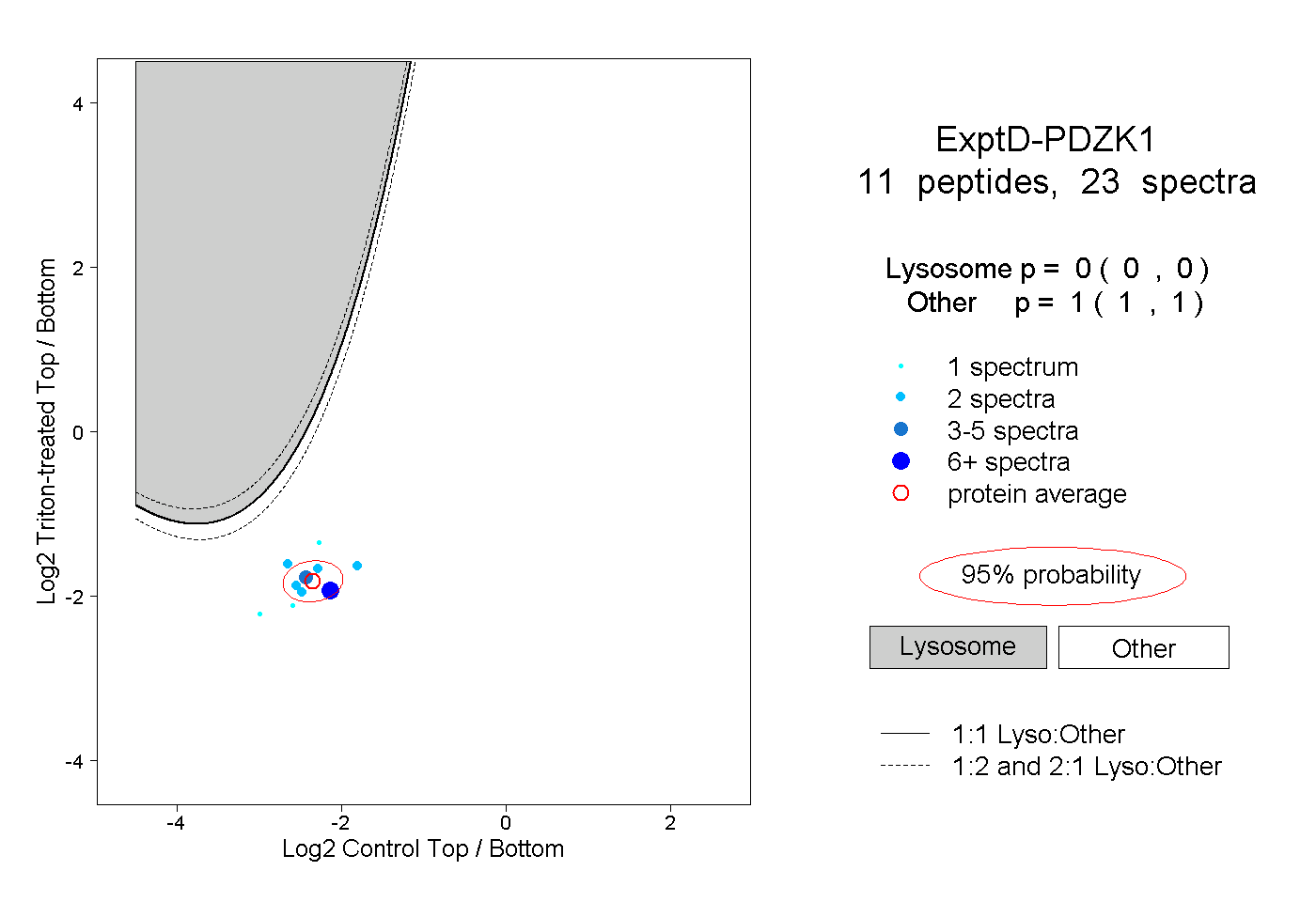 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |