peptides
spectra
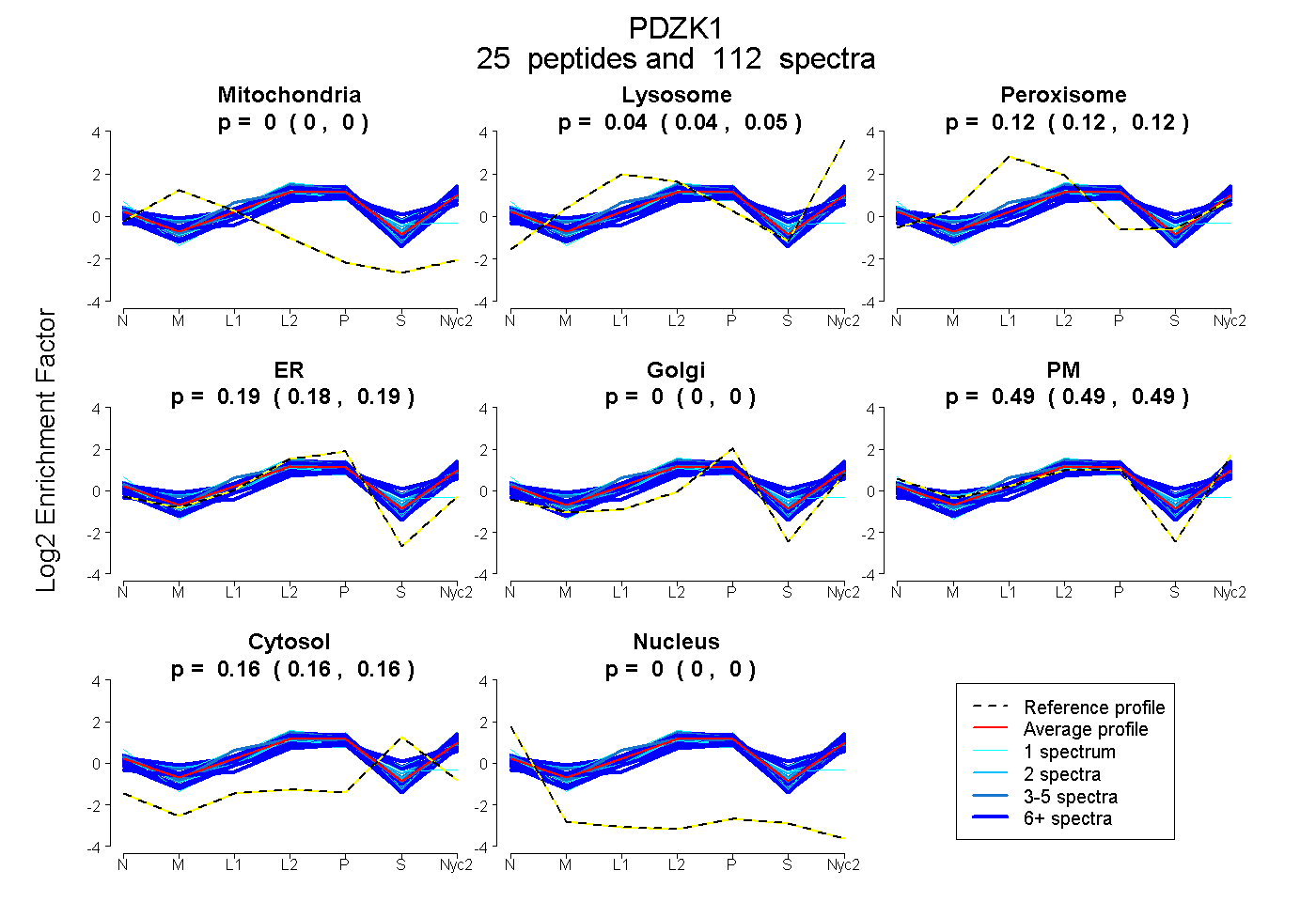
0.000 | 0.000
0.041 | 0.048
0.116 | 0.122
0.182 | 0.189
0.000 | 0.000
0.485 | 0.495
0.158 | 0.161
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
112 spectra |
 |
0.000 0.000 | 0.000 |
0.045 0.041 | 0.048 |
0.119 0.116 | 0.122 |
0.186 0.182 | 0.189 |
0.000 0.000 | 0.000 |
0.491 0.485 | 0.495 |
0.160 0.158 | 0.161 |
0.000 0.000 | 0.000 |
| 6 spectra, VVVIK | 0.000 | 0.096 | 0.095 | 0.183 | 0.175 | 0.167 | 0.285 | 0.000 | ||
| 5 spectra, GVFLTDITPQGVAMK | 0.000 | 0.138 | 0.047 | 0.125 | 0.000 | 0.543 | 0.147 | 0.000 | ||
| 7 spectra, IMFLLVDK | 0.000 | 0.215 | 0.000 | 0.263 | 0.000 | 0.406 | 0.117 | 0.000 | ||
| 1 spectrum, FSPLLYCQSQELPNGSVK | 0.000 | 0.000 | 0.169 | 0.310 | 0.000 | 0.434 | 0.087 | 0.000 | ||
| 1 spectrum, GETEHDSAESTK | 0.000 | 0.000 | 0.037 | 0.236 | 0.000 | 0.546 | 0.180 | 0.000 | ||
| 3 spectra, CHSEQK | 0.000 | 0.128 | 0.095 | 0.260 | 0.000 | 0.382 | 0.135 | 0.000 | ||
| 8 spectra, EPALNEK | 0.000 | 0.125 | 0.041 | 0.170 | 0.000 | 0.376 | 0.289 | 0.000 | ||
| 6 spectra, EVQQGGPADK | 0.000 | 0.005 | 0.085 | 0.270 | 0.000 | 0.504 | 0.136 | 0.000 | ||
| 6 spectra, ELDQSPR | 0.026 | 0.000 | 0.172 | 0.138 | 0.073 | 0.494 | 0.097 | 0.000 | ||
| 6 spectra, VIEEGSPAEK | 0.000 | 0.114 | 0.062 | 0.161 | 0.000 | 0.300 | 0.363 | 0.000 | ||
| 2 spectra, GQPGSFVK | 0.000 | 0.101 | 0.051 | 0.244 | 0.000 | 0.529 | 0.074 | 0.000 | ||
| 2 spectra, EDDSYGFHLNAIR | 0.000 | 0.000 | 0.251 | 0.002 | 0.163 | 0.445 | 0.138 | 0.000 | ||
| 2 spectra, EEHAQVVDLVR | 0.000 | 0.000 | 0.223 | 0.000 | 0.141 | 0.426 | 0.210 | 0.000 | ||
| 1 spectrum, LCYLVK | 0.000 | 0.000 | 0.338 | 0.452 | 0.000 | 0.000 | 0.210 | 0.000 | ||
| 5 spectra, VAYSYFQAK | 0.000 | 0.000 | 0.229 | 0.203 | 0.000 | 0.433 | 0.135 | 0.000 | ||
| 13 spectra, LLPHQPR | 0.000 | 0.083 | 0.144 | 0.220 | 0.000 | 0.439 | 0.114 | 0.000 | ||
| 3 spectra, DIEPGSPAEAAGLK | 0.000 | 0.000 | 0.082 | 0.137 | 0.000 | 0.635 | 0.145 | 0.000 | ||
| 2 spectra, HQVDLK | 0.000 | 0.000 | 0.075 | 0.207 | 0.000 | 0.598 | 0.120 | 0.000 | ||
| 1 spectrum, NGGDQTTLLVLDK | 0.000 | 0.043 | 0.136 | 0.092 | 0.000 | 0.459 | 0.269 | 0.000 | ||
| 6 spectra, AGLLDGDR | 0.000 | 0.042 | 0.139 | 0.089 | 0.000 | 0.623 | 0.107 | 0.000 | ||
| 5 spectra, DTDGHLVR | 0.000 | 0.016 | 0.193 | 0.089 | 0.000 | 0.535 | 0.167 | 0.000 | ||
| 4 spectra, EGQNYGFFLR | 0.000 | 0.064 | 0.071 | 0.236 | 0.000 | 0.530 | 0.099 | 0.000 | ||
| 4 spectra, KPDLGMNGGVETCAQPR | 0.000 | 0.066 | 0.117 | 0.252 | 0.000 | 0.436 | 0.129 | 0.000 | ||
| 8 spectra, IYSLAR | 0.000 | 0.034 | 0.102 | 0.175 | 0.000 | 0.614 | 0.075 | 0.000 | ||
| 5 spectra, EGNSFGFSLK | 0.000 | 0.052 | 0.130 | 0.188 | 0.000 | 0.519 | 0.111 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
22 spectra |
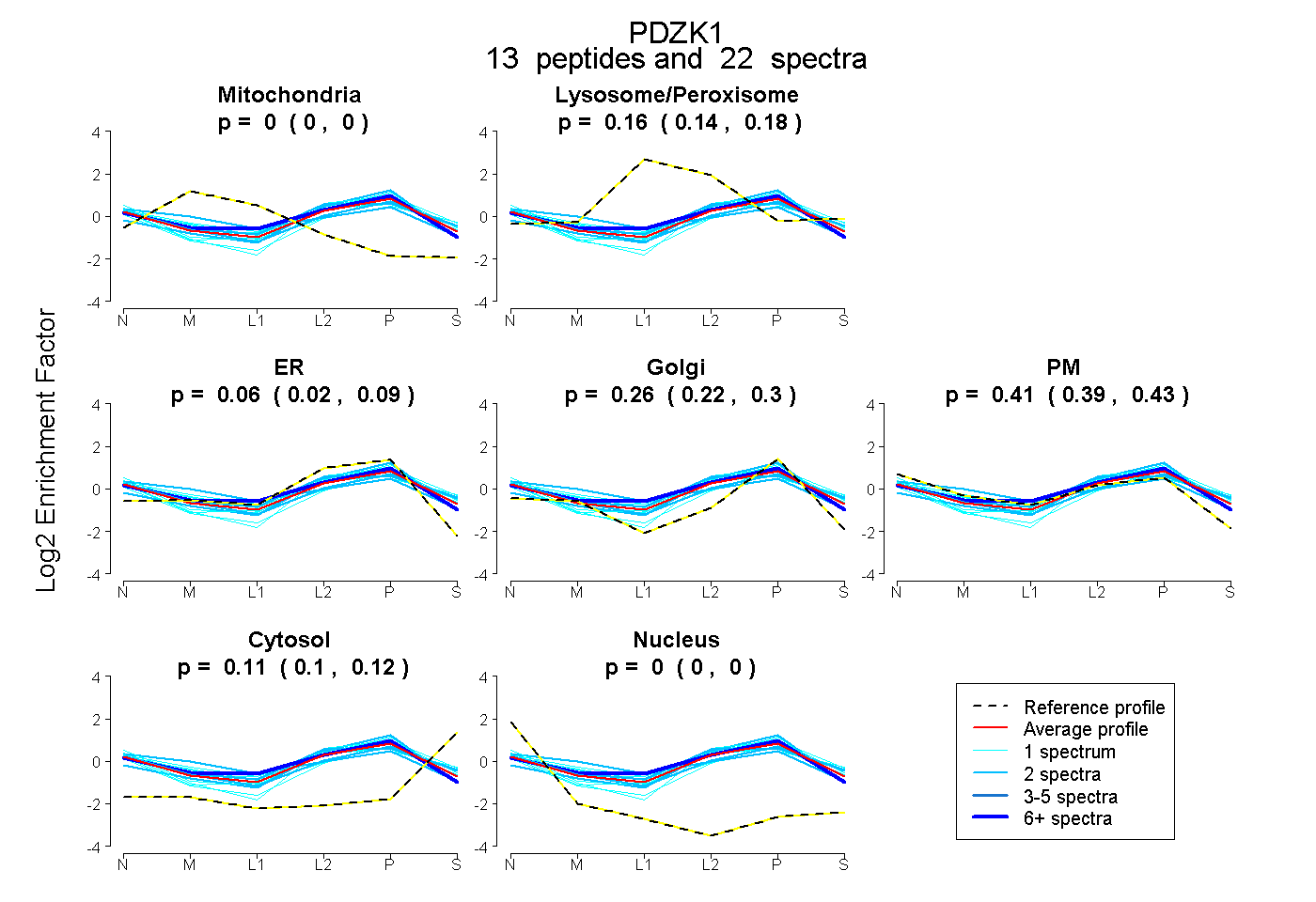 |
0.000 0.000 | 0.000 |
0.161 0.141 | 0.178 |
0.057 0.021 | 0.087 |
0.262 0.223 | 0.297 |
0.413 0.390 | 0.432 |
0.107 0.095 | 0.117 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
169 spectra |
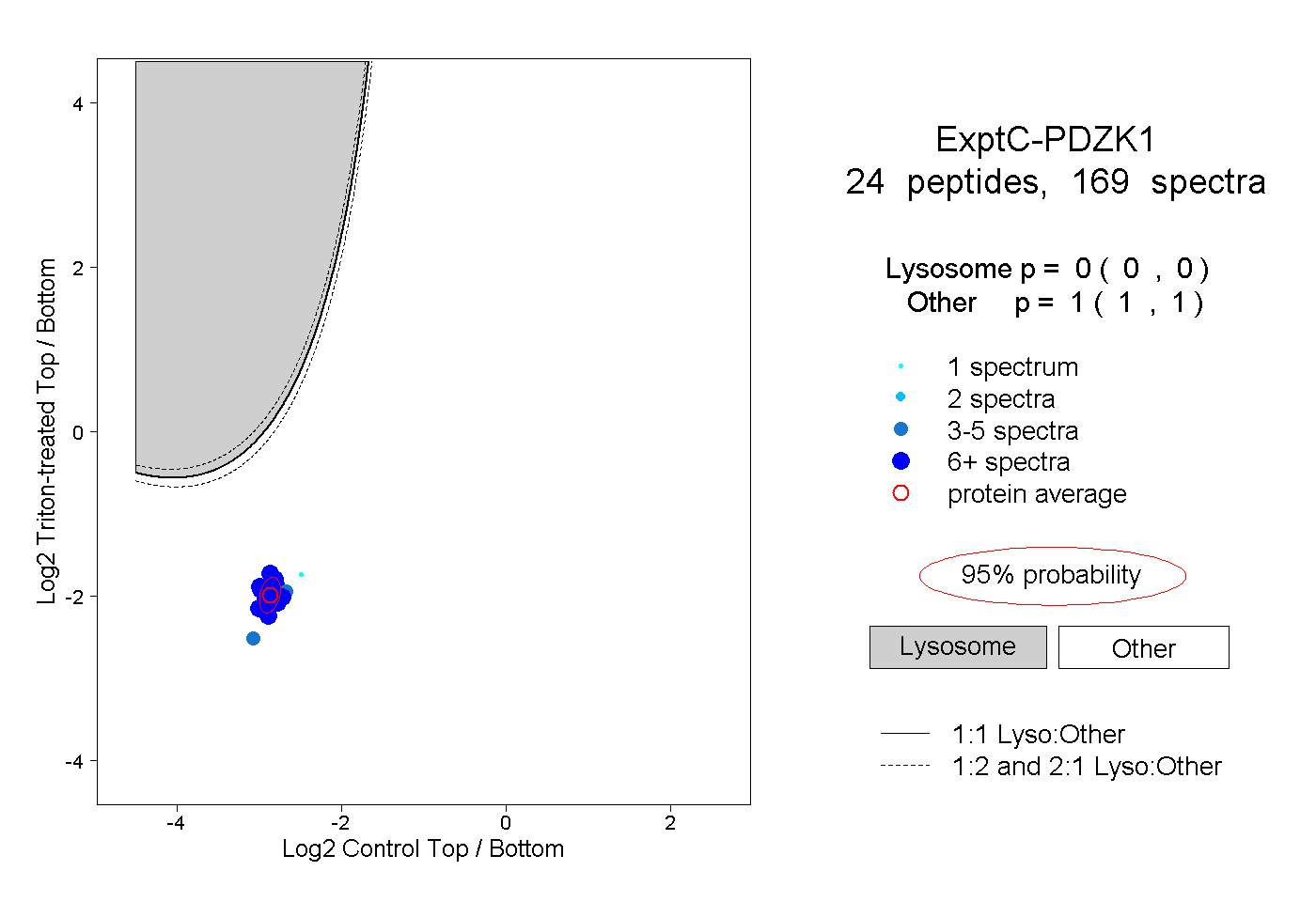 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
23 spectra |
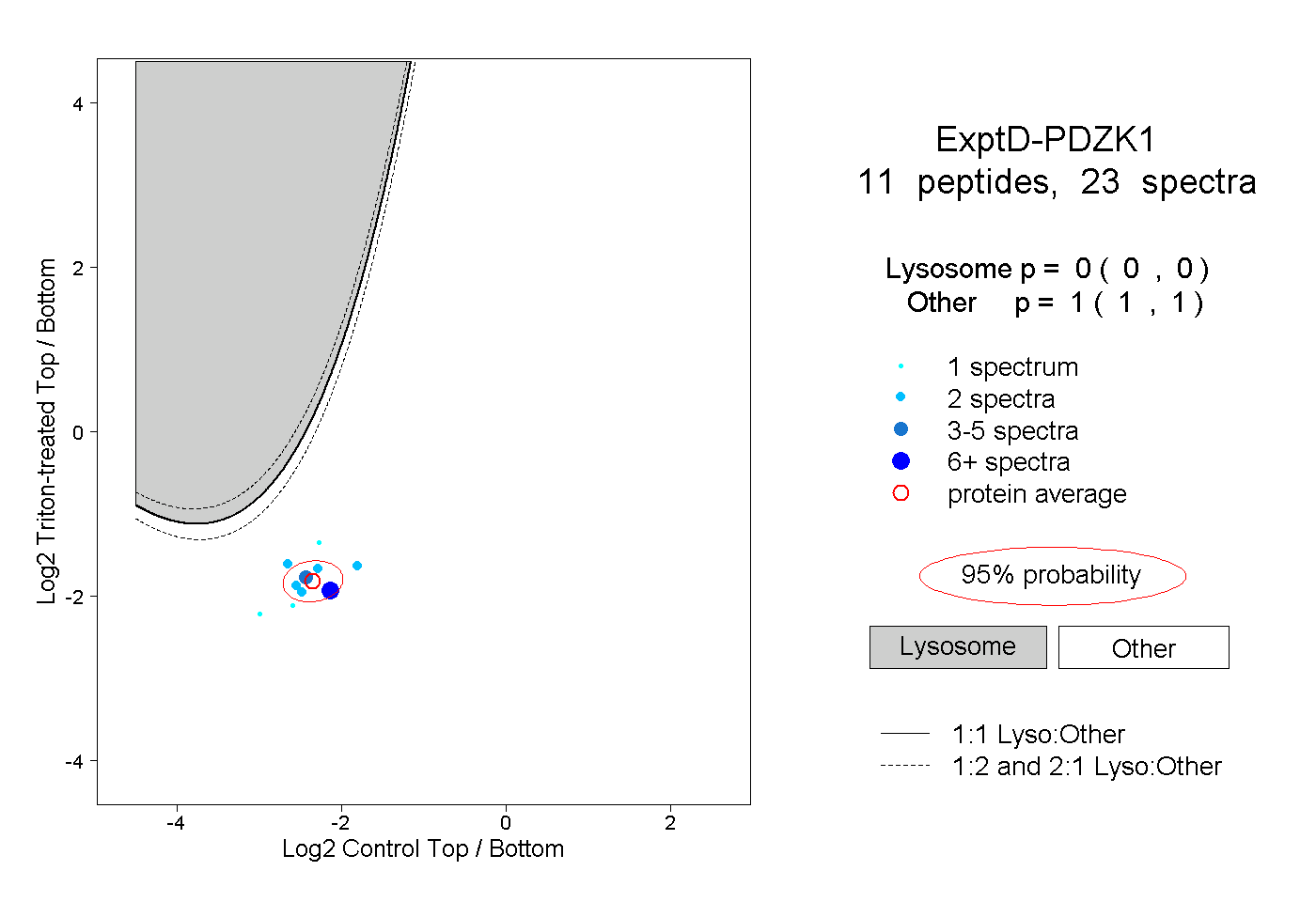 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |