peptides
spectra
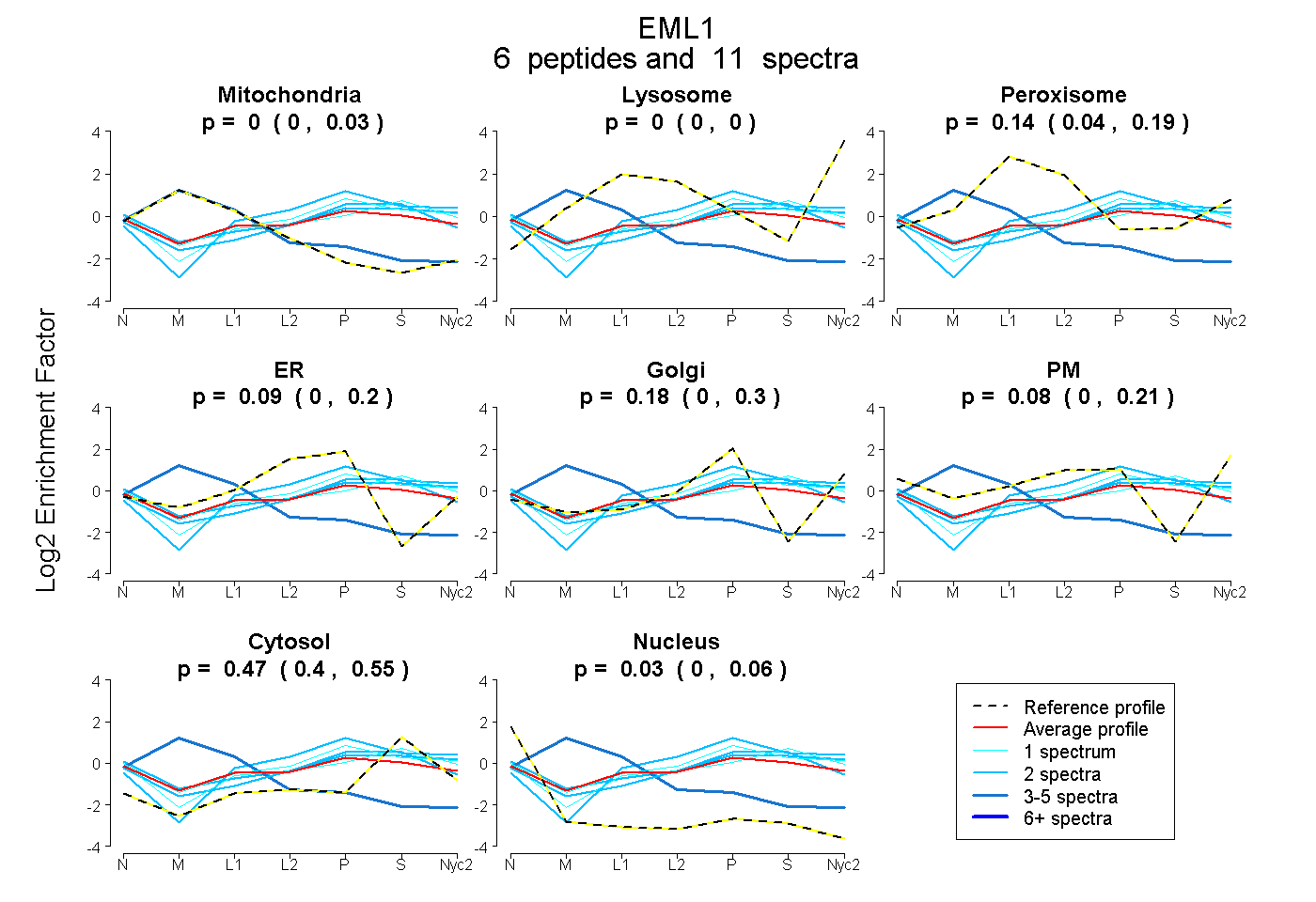
0.000 | 0.030
0.000 | 0.000
0.042 | 0.193
0.000 | 0.201
0.000 | 0.300
0.000 | 0.213
0.402 | 0.546
0.000 | 0.059
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
11 spectra |
 |
0.000 0.000 | 0.030 |
0.000 0.000 | 0.000 |
0.136 0.042 | 0.193 |
0.092 0.000 | 0.201 |
0.185 0.000 | 0.300 |
0.084 0.000 | 0.213 |
0.473 0.402 | 0.546 |
0.030 0.000 | 0.059 |
| 1 spectrum, KPSASLPSPSGSR | 0.000 | 0.000 | 0.097 | 0.028 | 0.263 | 0.166 | 0.447 | 0.000 | ||
| 2 spectra, ARPLGQTLPLR | 0.000 | 0.095 | 0.000 | 0.259 | 0.146 | 0.000 | 0.500 | 0.000 | ||
| 2 spectra, HYAGHNDDVK | 0.000 | 0.000 | 0.000 | 0.206 | 0.156 | 0.037 | 0.601 | 0.000 | ||
| 3 spectra, EEGYVK | 0.890 | 0.000 | 0.000 | 0.006 | 0.059 | 0.000 | 0.045 | 0.000 | ||
| 1 spectrum, ITIATGQVAGTSK | 0.000 | 0.000 | 0.028 | 0.002 | 0.000 | 0.316 | 0.653 | 0.000 | ||
| 2 spectra, AEIPEQFGPIR | 0.000 | 0.000 | 0.007 | 0.000 | 0.050 | 0.408 | 0.535 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
2 spectra |
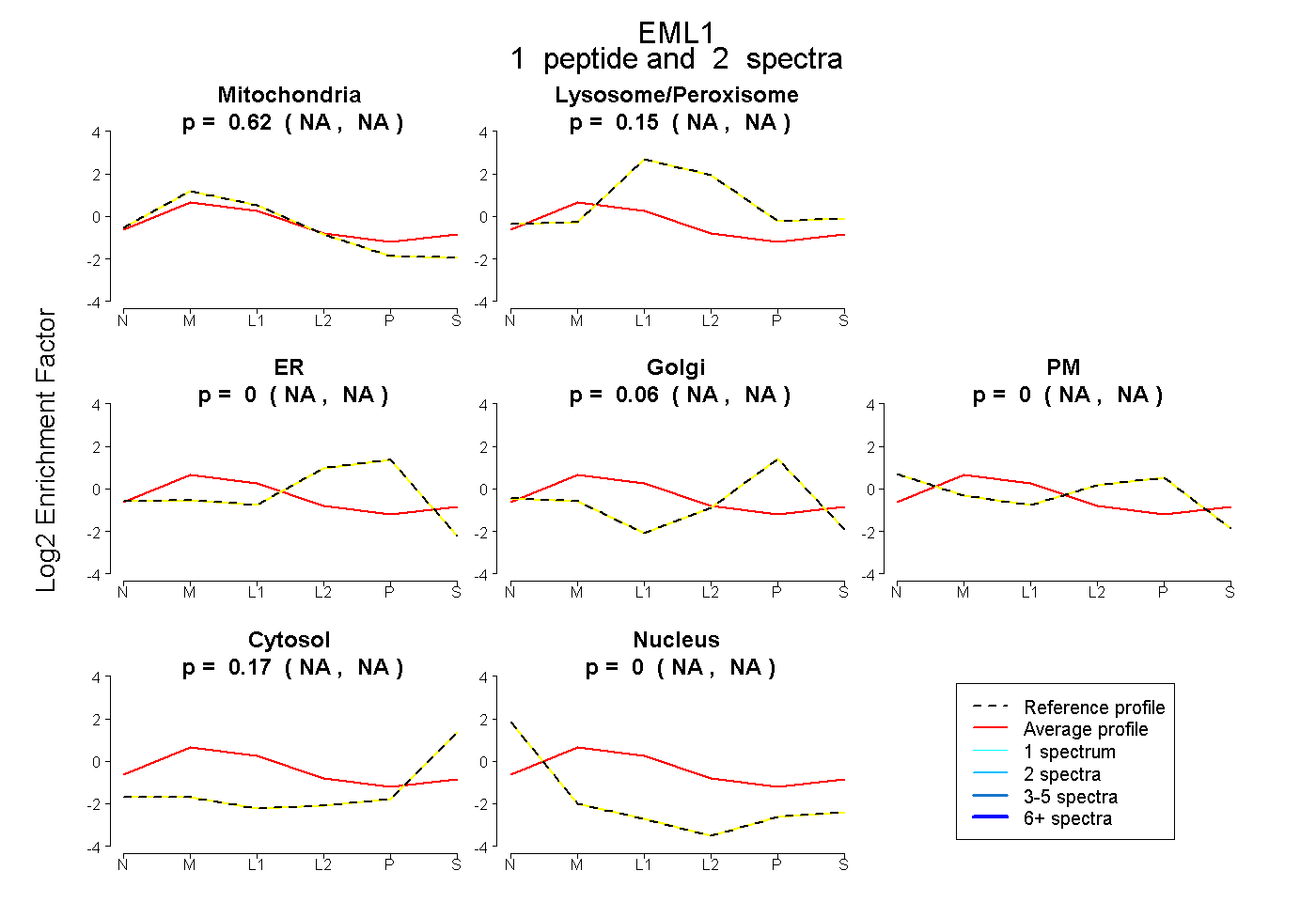 |
0.616 NA | NA |
0.150 NA | NA |
0.000 NA | NA |
0.060 NA | NA |
0.000 NA | NA |
0.173 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
9 spectra |
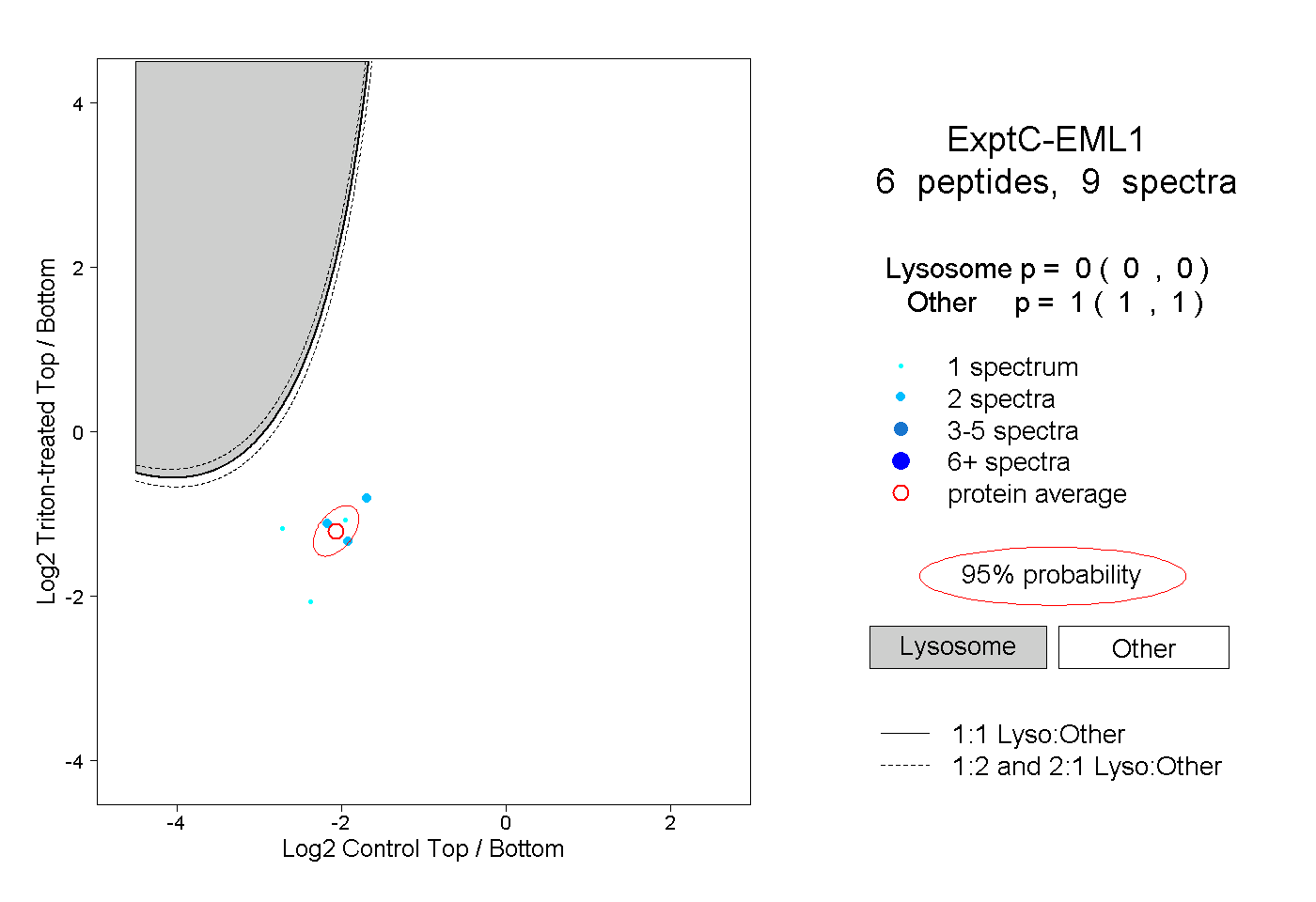 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
3 spectra |
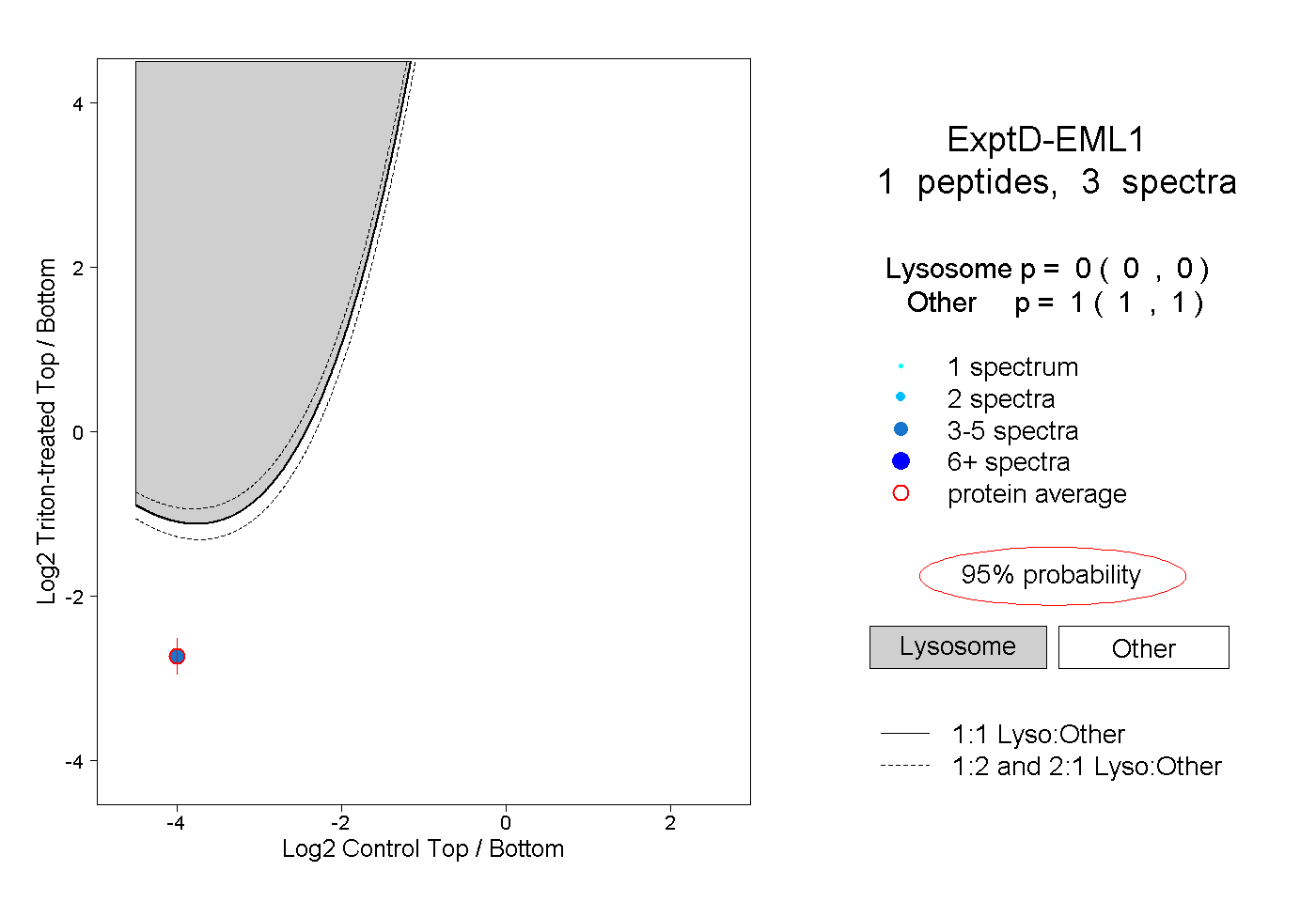 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |