peptides
spectra
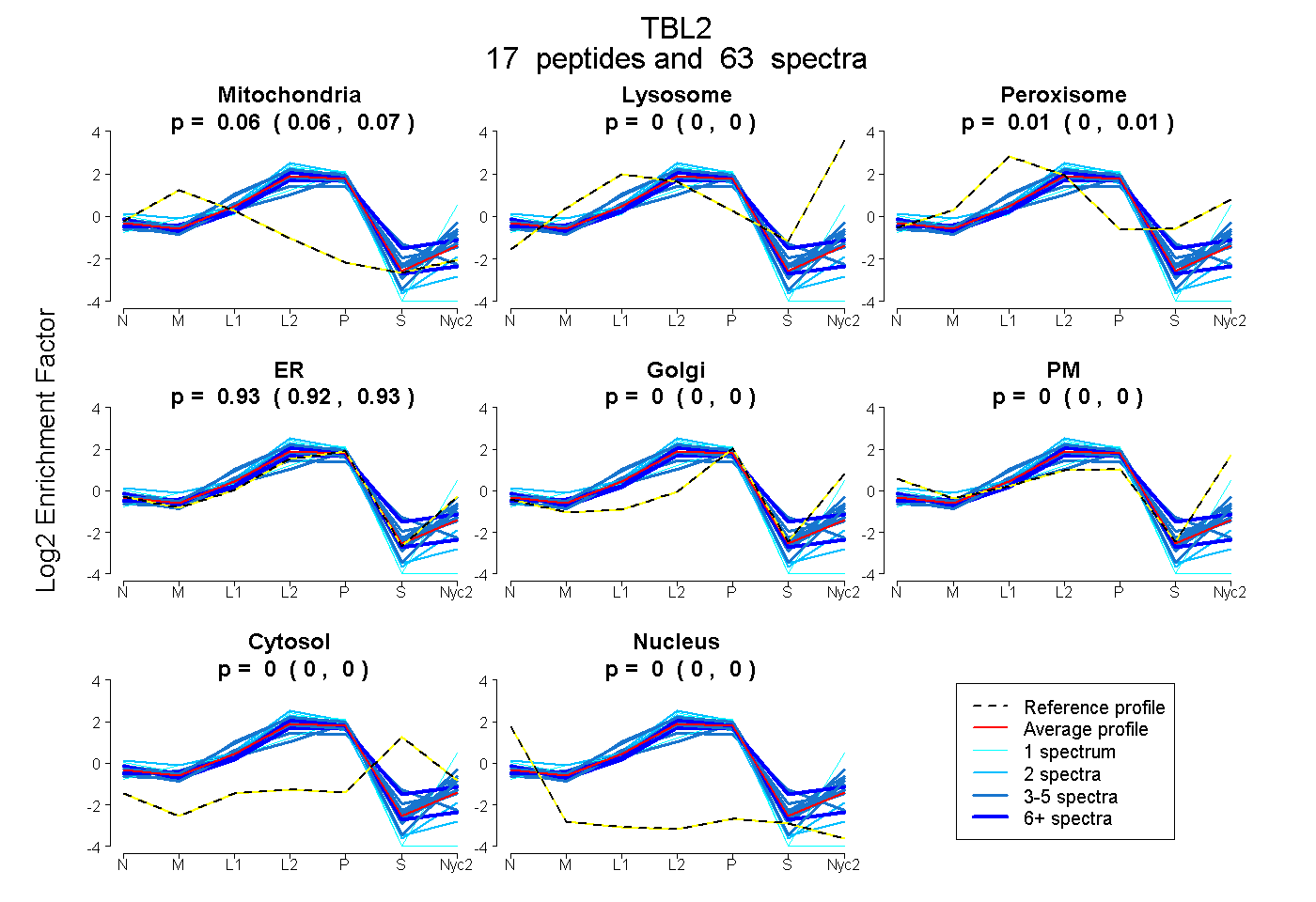
0.059 | 0.069
0.000 | 0.000
0.000 | 0.015
0.923 | 0.932
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
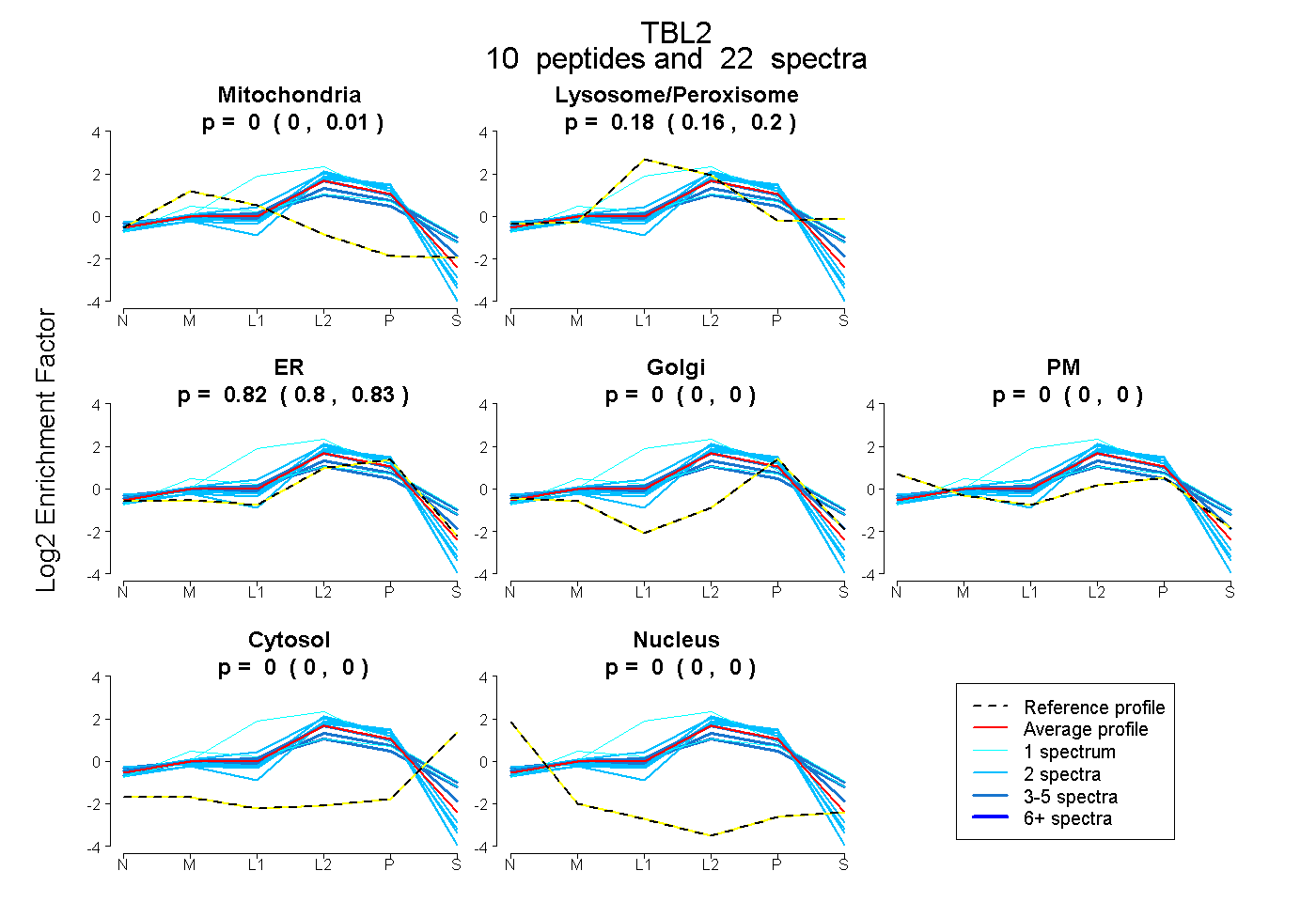
0.000 | 0.012
0.156 | 0.199
0.797 | 0.834
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
63 spectra |
 |
0.064 0.059 | 0.069 |
0.000 0.000 | 0.000 |
0.008 0.000 | 0.015 |
0.928 0.923 | 0.932 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
22 spectra |
 |
0.000 0.000 | 0.012 |
0.182 0.156 | 0.199 |
0.818 0.797 | 0.834 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, LQQQLTQAQEALK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, GEFQEVLR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, FVGSCGFTPDVK | 0.000 | 0.176 | 0.824 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, YLATCADDR | 0.000 | 0.261 | 0.739 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, APIINIGIADTGK | 0.000 | 0.297 | 0.513 | 0.000 | 0.147 | 0.043 | 0.000 | |||
| 2 spectra, QQDPYLLR | 0.000 | 0.038 | 0.962 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LFHNTPGHR | 0.000 | 0.703 | 0.297 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, FLASCGDR | 0.000 | 0.034 | 0.966 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, AVVEEMQGLLK | 0.113 | 0.280 | 0.558 | 0.000 | 0.000 | 0.049 | 0.000 | |||
| 1 spectrum, VWEVCFGK | 0.151 | 0.281 | 0.536 | 0.031 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
93 spectra |
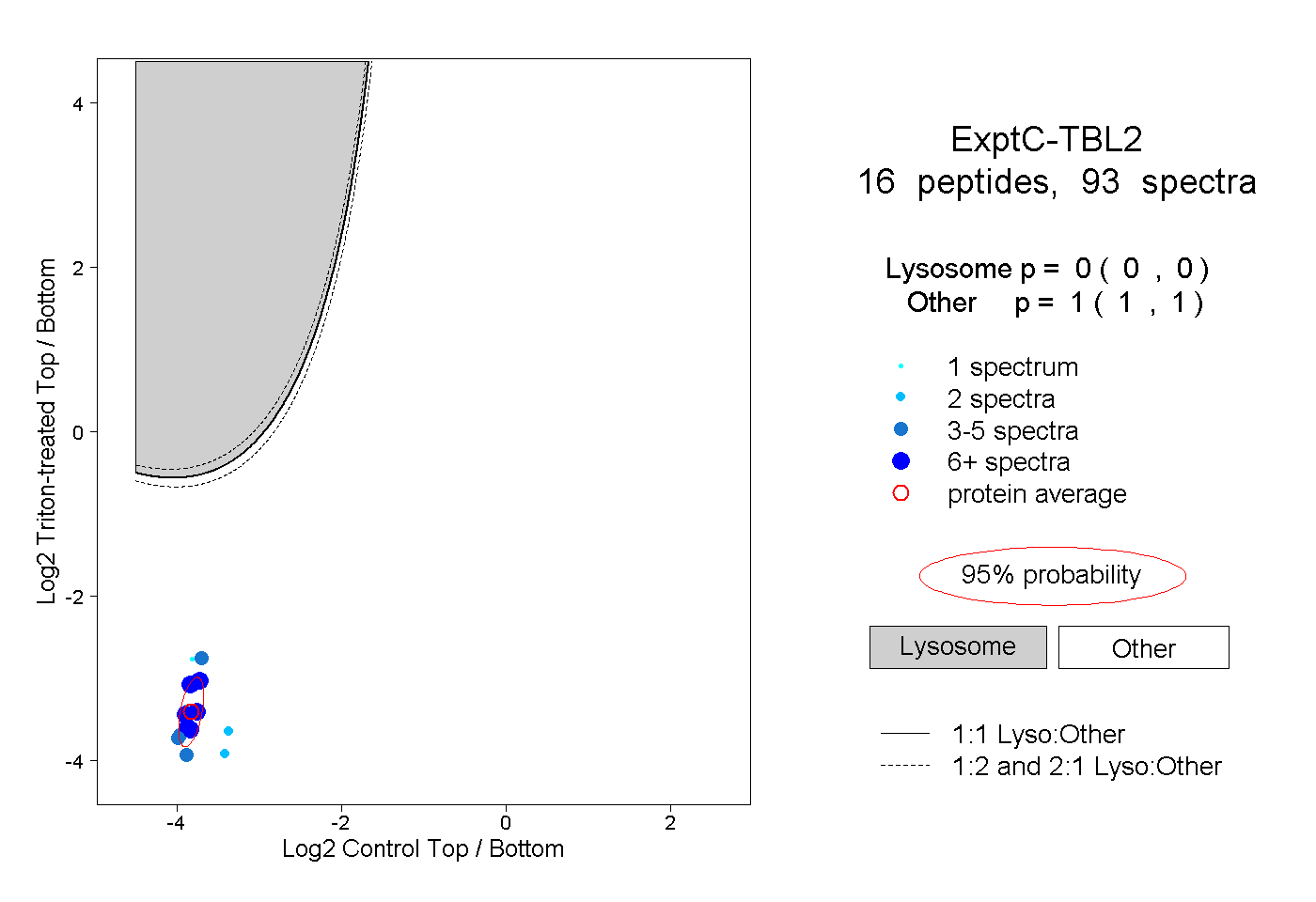 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
14 spectra |
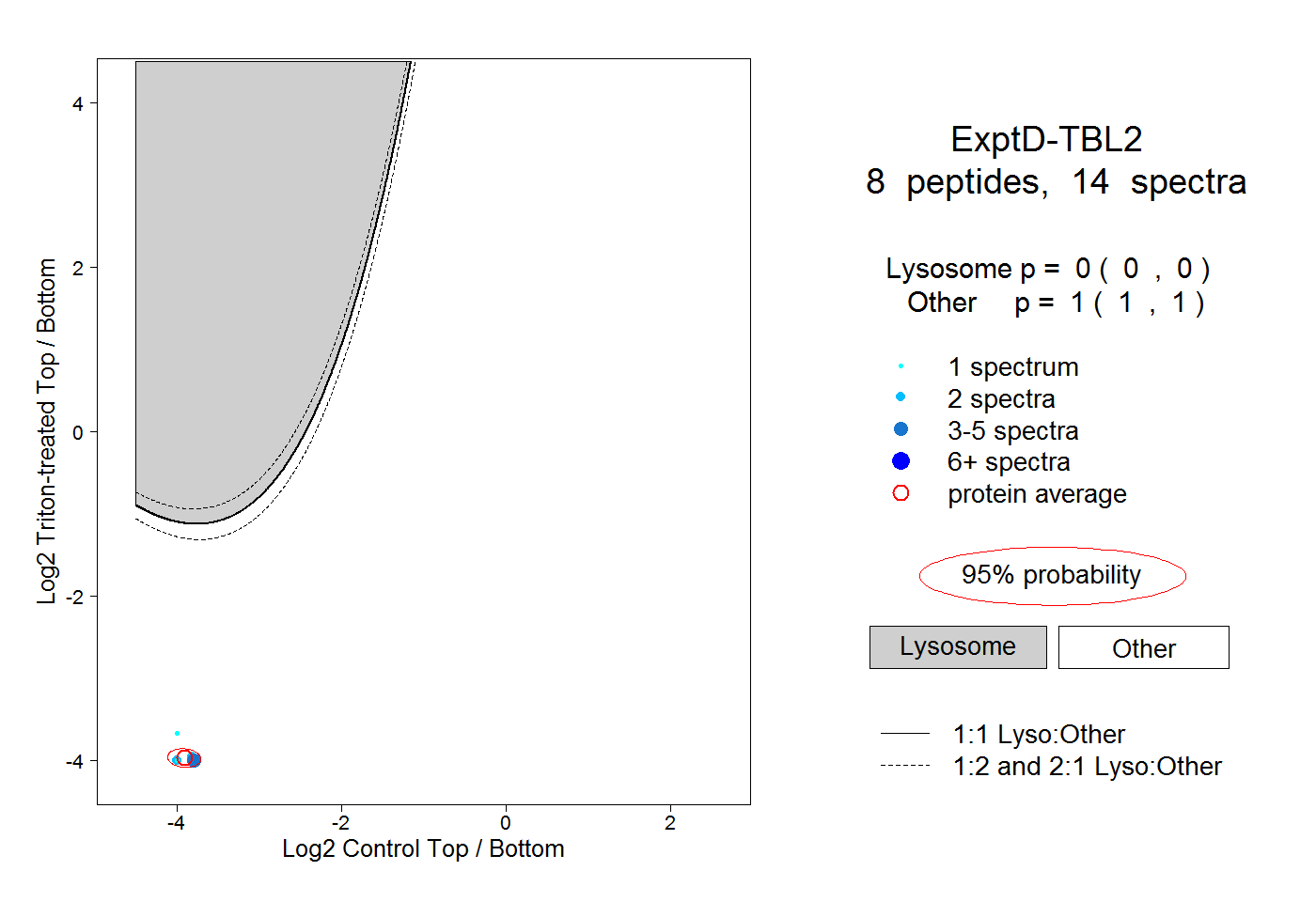 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |