peptides
spectra
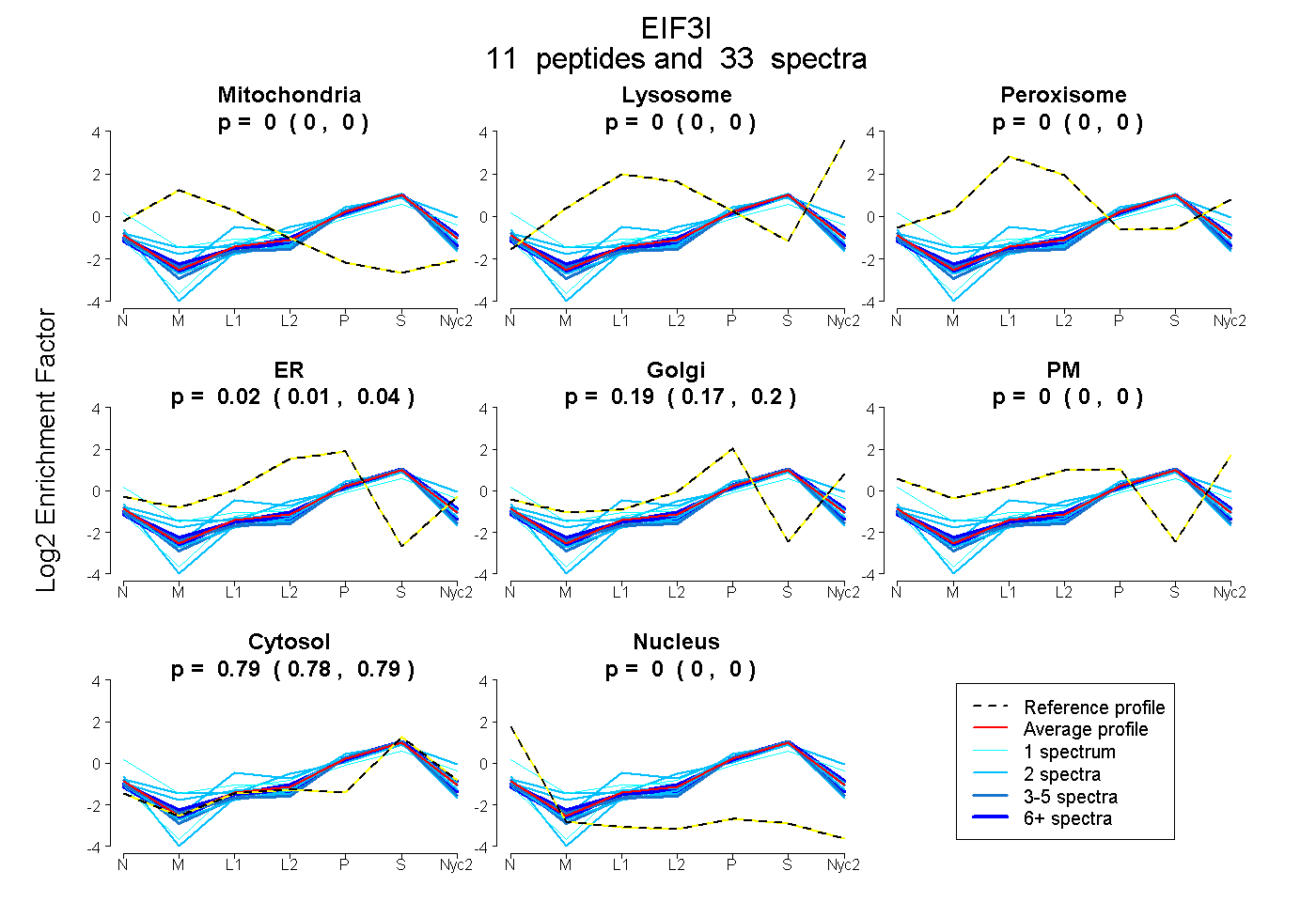
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.007 | 0.040
0.167 | 0.203
0.000 | 0.000
0.784 | 0.793
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
33 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.024 0.007 | 0.040 |
0.187 0.167 | 0.203 |
0.000 0.000 | 0.000 |
0.789 0.784 | 0.793 |
0.000 0.000 | 0.000 |
| 2 spectra, QINDIQLSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.169 | 0.000 | 0.812 | 0.019 | ||
| 2 spectra, LFDSTSLEHQK | 0.000 | 0.000 | 0.007 | 0.236 | 0.000 | 0.000 | 0.758 | 0.000 | ||
| 2 spectra, EGDLLFTVAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.096 | 0.000 | 0.804 | 0.100 | ||
| 4 spectra, SYSSGGEDGYVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.155 | 0.000 | 0.800 | 0.045 | ||
| 3 spectra, DPIVNVWYSVNGER | 0.000 | 0.000 | 0.000 | 0.000 | 0.189 | 0.000 | 0.796 | 0.015 | ||
| 1 spectrum, GHFGPINSVAFHPDGK | 0.000 | 0.000 | 0.000 | 0.101 | 0.063 | 0.000 | 0.837 | 0.000 | ||
| 2 spectra, SITQIK | 0.000 | 0.000 | 0.000 | 0.035 | 0.240 | 0.000 | 0.724 | 0.000 | ||
| 2 spectra, DMTMFVTASK | 0.000 | 0.046 | 0.000 | 0.000 | 0.198 | 0.076 | 0.680 | 0.000 | ||
| 6 spectra, LWDCETGK | 0.000 | 0.000 | 0.000 | 0.120 | 0.072 | 0.000 | 0.803 | 0.006 | ||
| 1 spectrum, HVLTGSADNSCR | 0.000 | 0.000 | 0.000 | 0.000 | 0.026 | 0.294 | 0.626 | 0.053 | ||
| 8 spectra, FFHLAFEEEFGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.199 | 0.000 | 0.801 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
6 spectra |
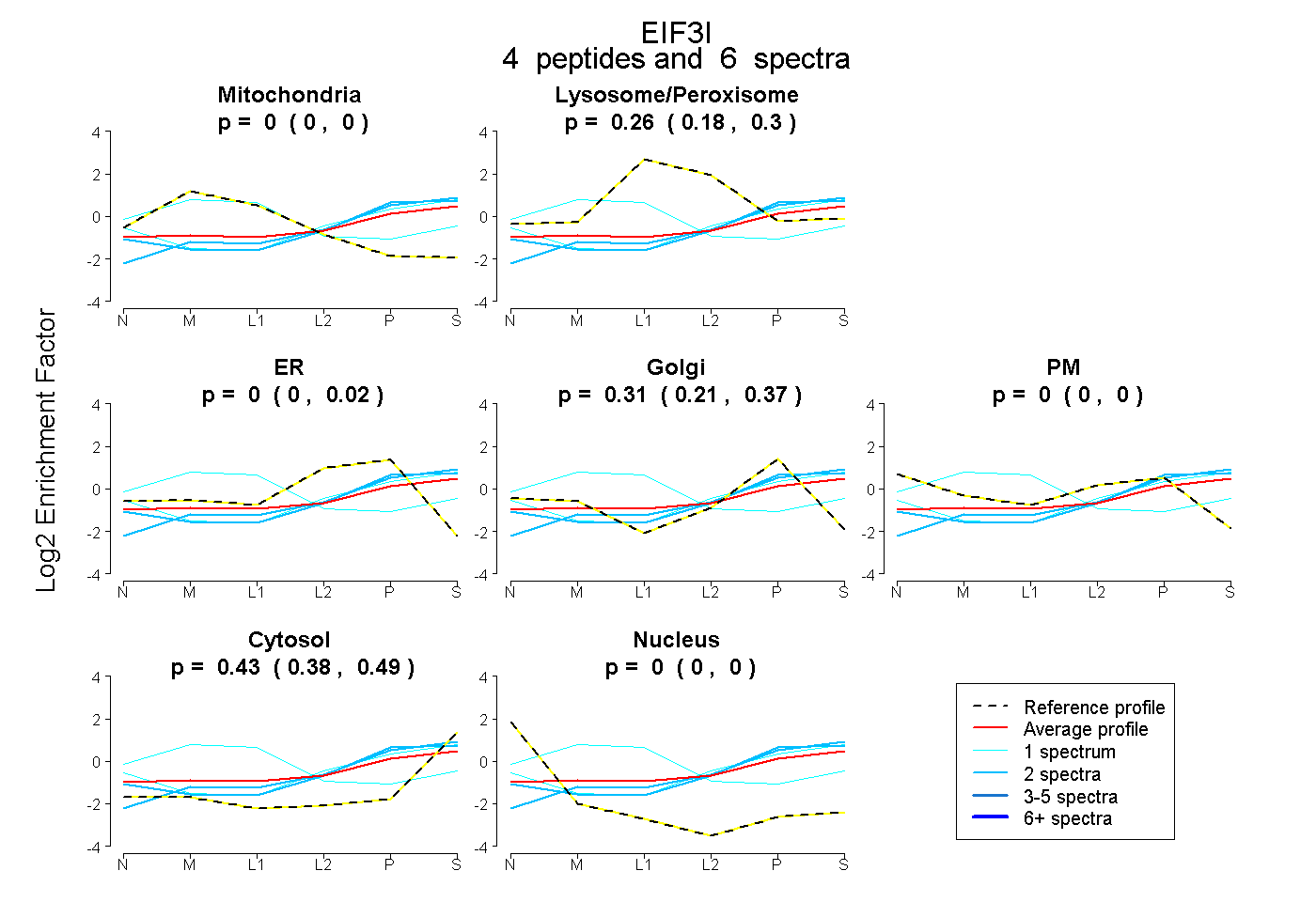 |
0.000 0.000 | 0.000 |
0.256 0.179 | 0.304 |
0.000 0.000 | 0.023 |
0.310 0.209 | 0.369 |
0.000 0.000 | 0.000 |
0.434 0.378 | 0.489 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
20 spectra |
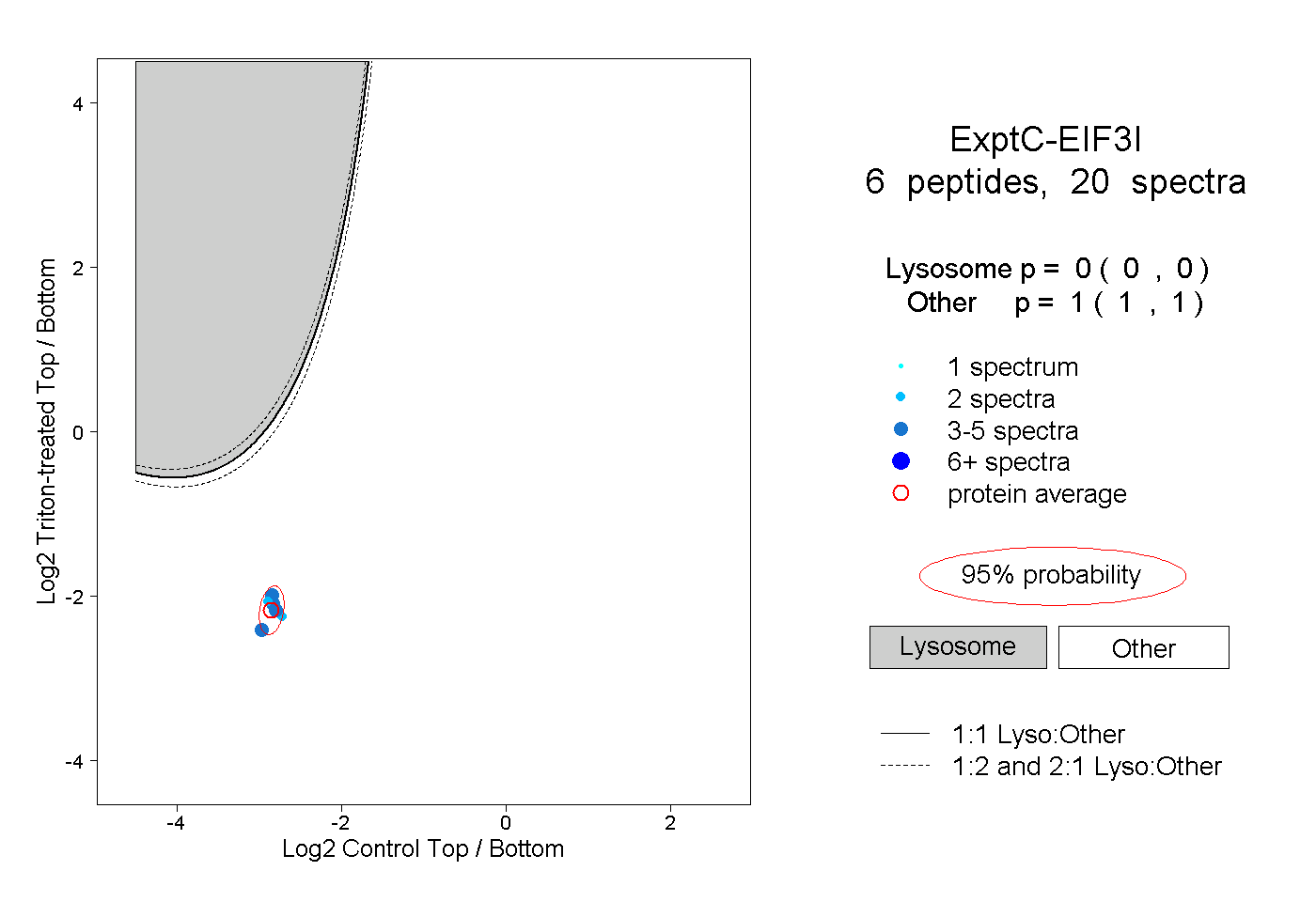 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
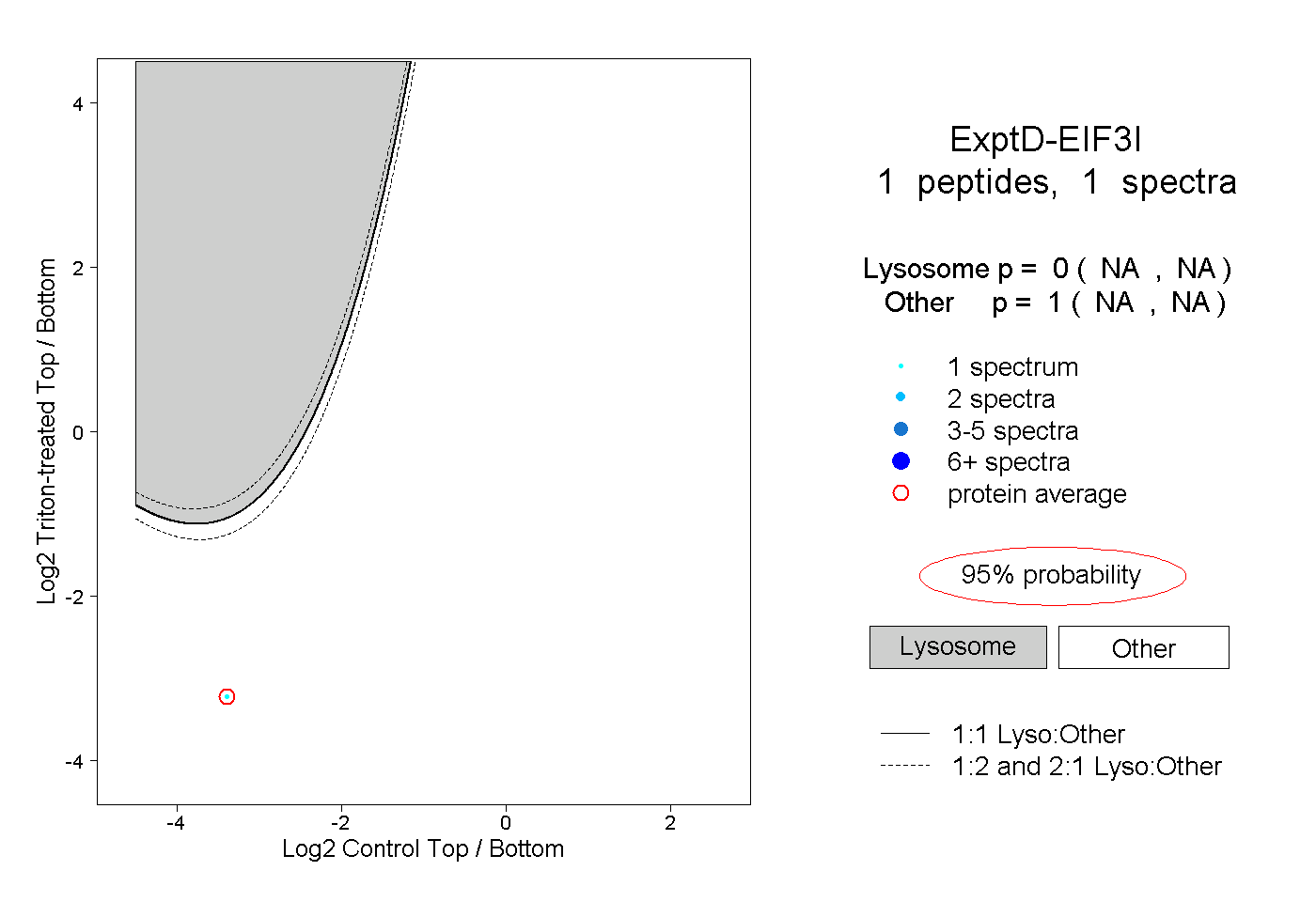 |
0.000 NA | NA |
1.000 NA | NA |