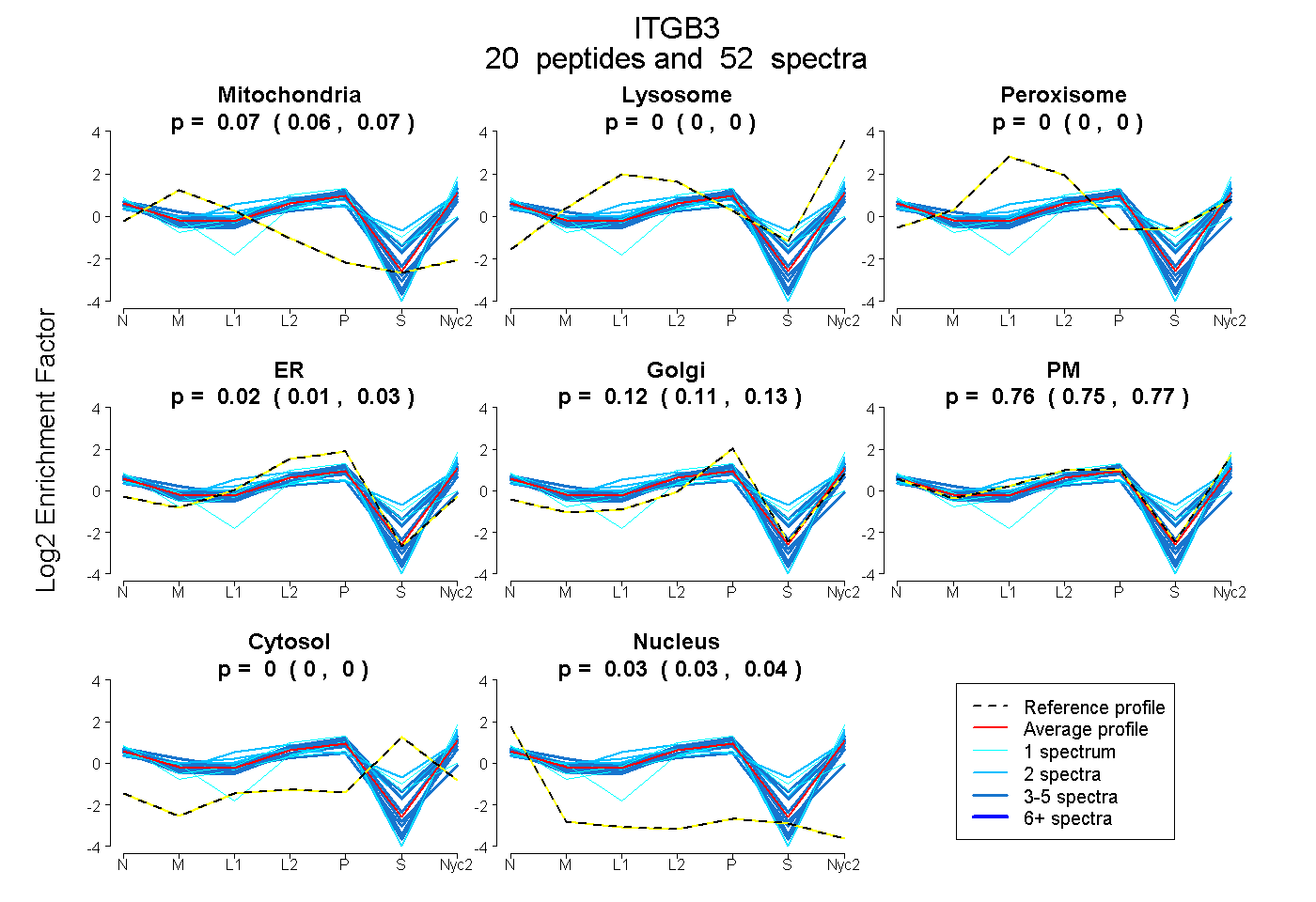
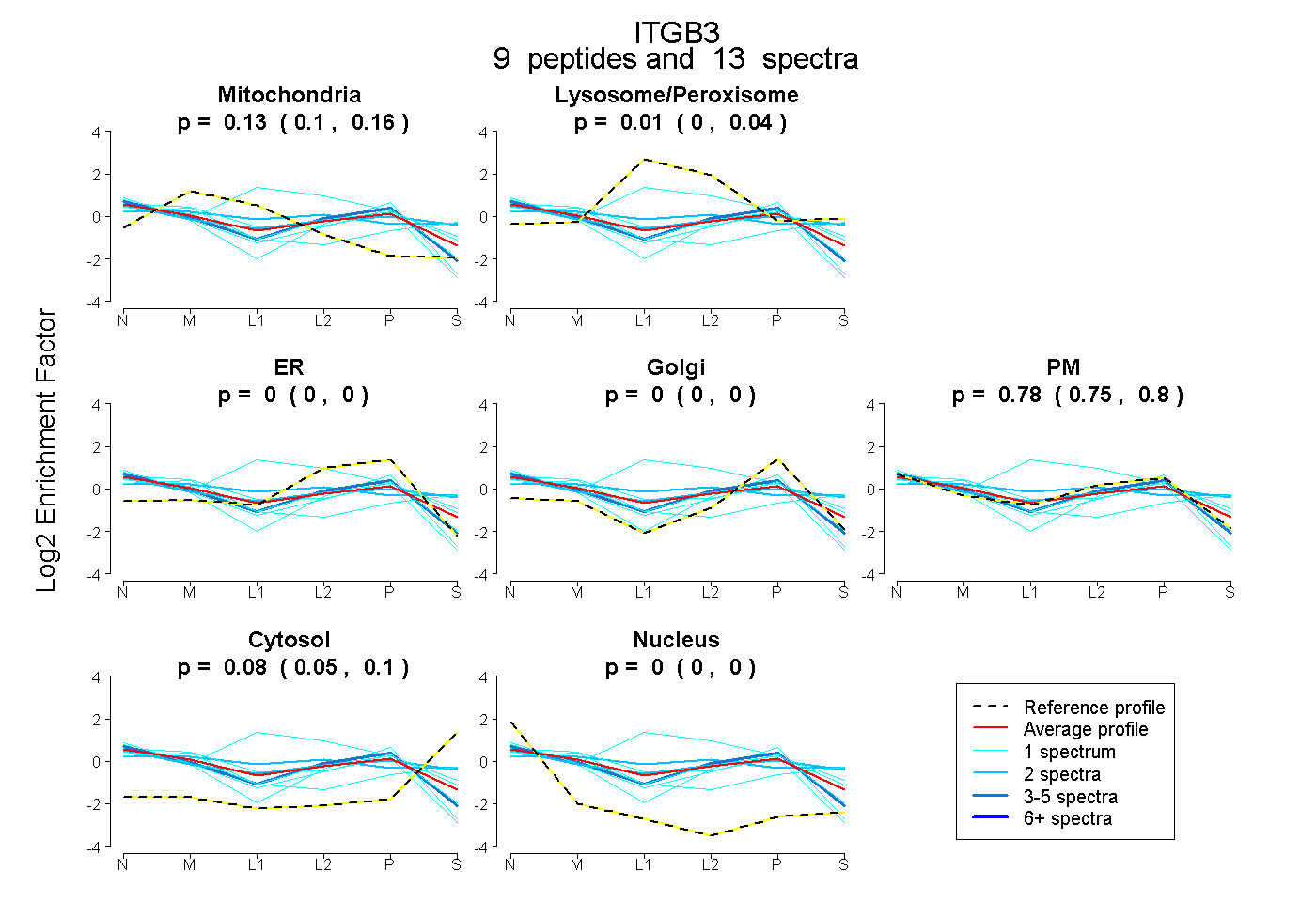
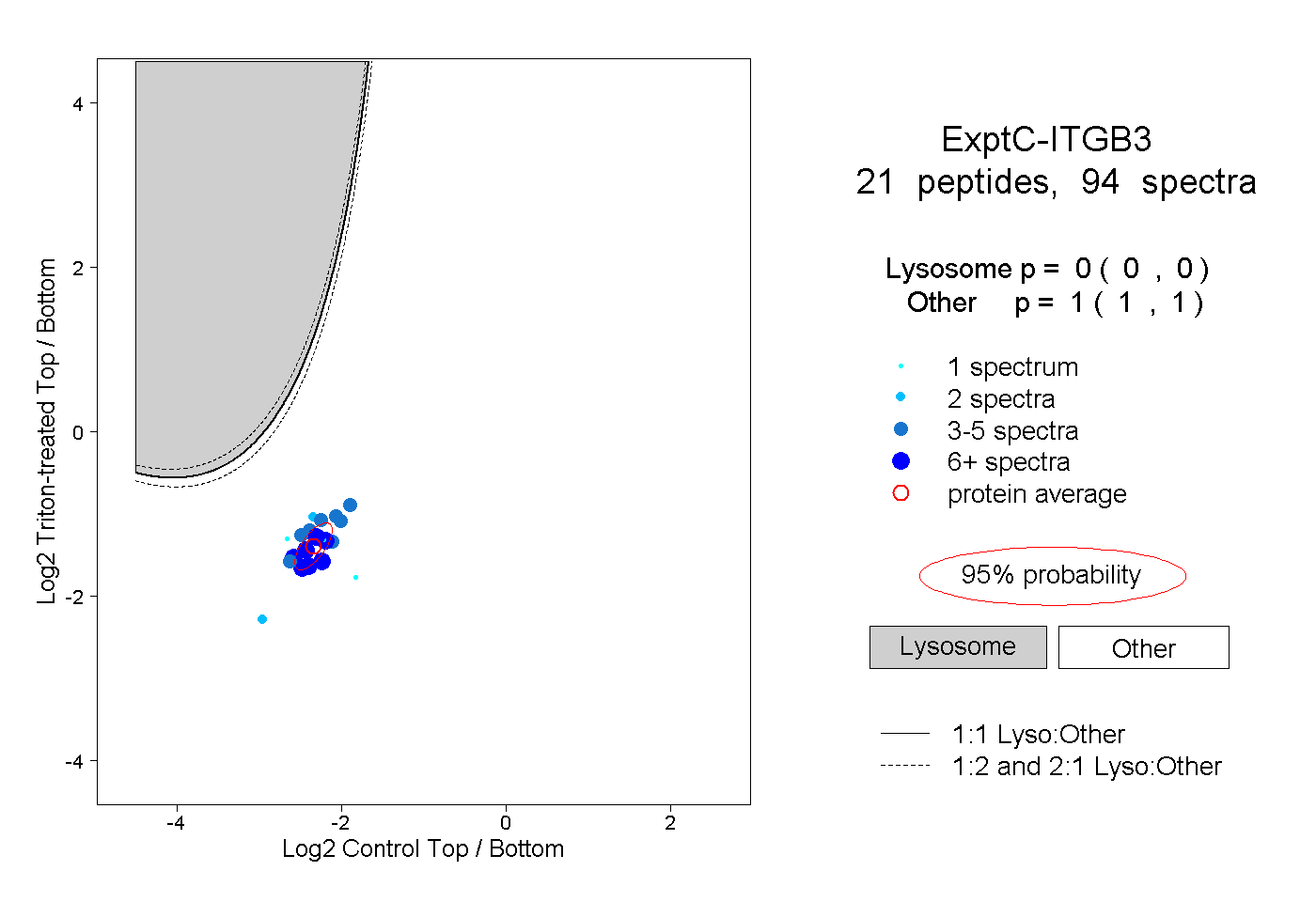
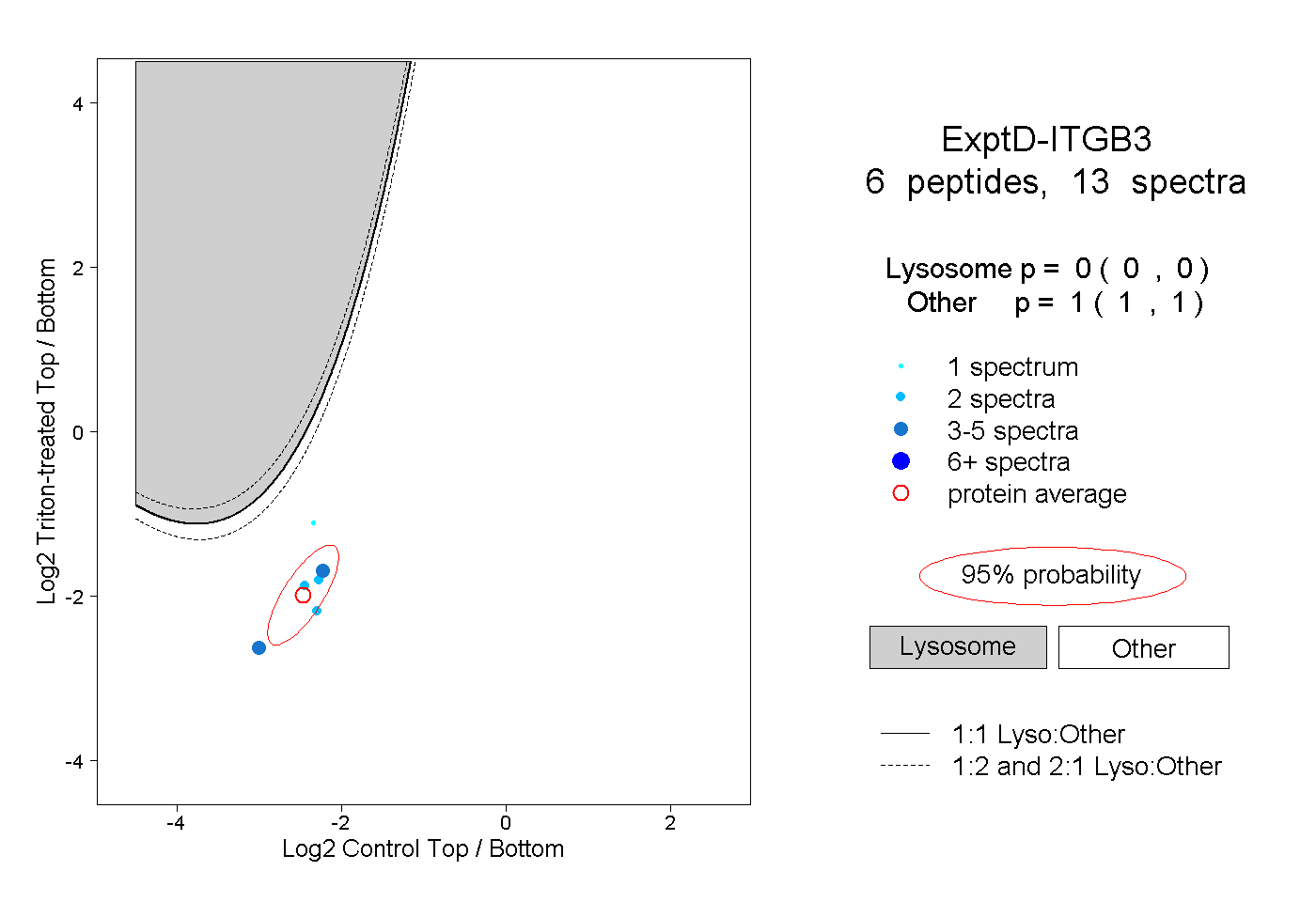
| 3 spectra, LTSNLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, IFSLQVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GCGAPQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, EATSTFTNITYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, NDASHLLVFTTDAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, EGQPICSQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, SCVGLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, NEDDCVVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, IGDTVSFSIEAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, STCLPMFGYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, THIALDGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, LAGIVLPNDGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, AVLYVVEEPECPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, GCPQQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LASQMR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, FQYYEDSSGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, EQSFTIKPVGFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, LRPDDSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, HVLTLTDQVTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, NPCYTMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, GSGDSAQITQVSPQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |