peptides
spectra
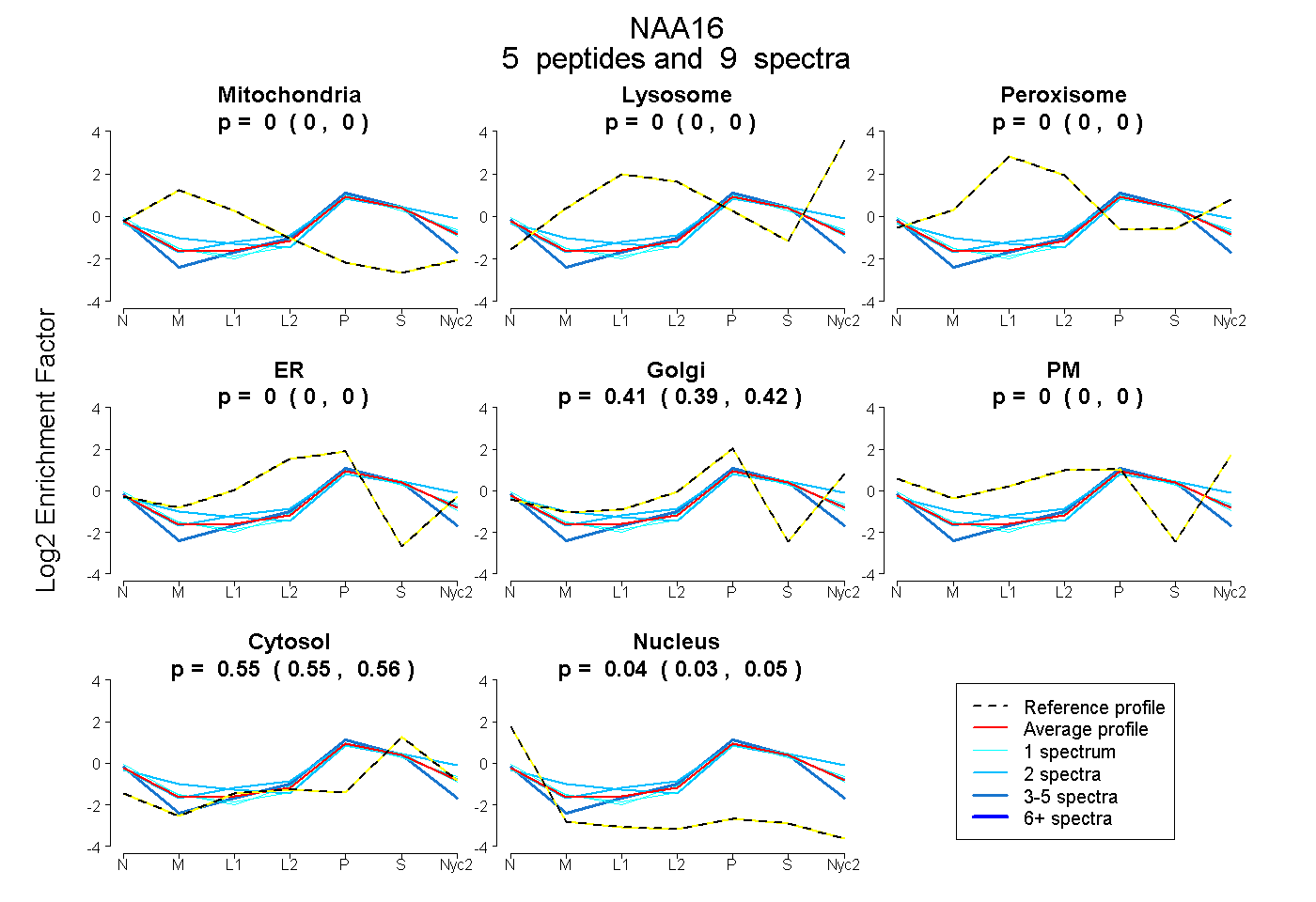
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.394 | 0.420
0.000 | 0.000
0.545 | 0.560
0.025 | 0.051
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
9 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.409 0.394 | 0.420 |
0.000 0.000 | 0.000 |
0.553 0.545 | 0.560 |
0.038 0.025 | 0.051 |
| 1 spectrum, YQLLQLRPTQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.380 | 0.000 | 0.568 | 0.052 | ||
| 1 spectrum, FQELMDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.430 | 0.000 | 0.500 | 0.069 | ||
| 3 spectra, AIATATR | 0.000 | 0.000 | 0.000 | 0.131 | 0.202 | 0.000 | 0.562 | 0.105 | ||
| 2 spectra, EEAYEFVR | 0.039 | 0.000 | 0.000 | 0.000 | 0.406 | 0.000 | 0.541 | 0.014 | ||
| 2 spectra, ESALFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.460 | 0.000 | 0.540 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
2 spectra |
 |
0.000 NA | NA |
0.303 NA | NA |
0.000 NA | NA |
0.480 NA | NA |
0.000 NA | NA |
0.217 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptide |
1 spectrum |
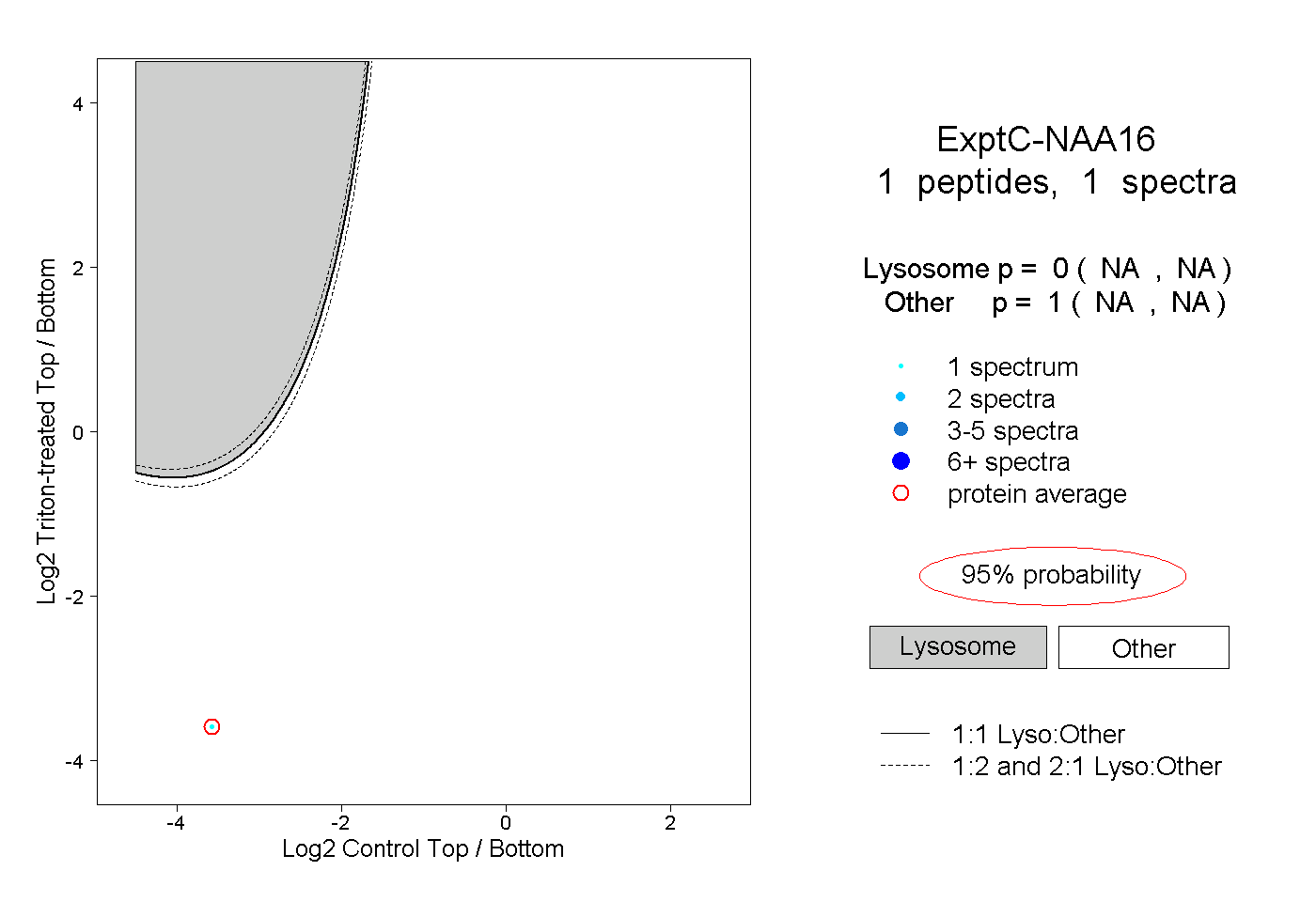 |
0.000 NA | NA |
1.000 NA | NA |