peptides
spectra
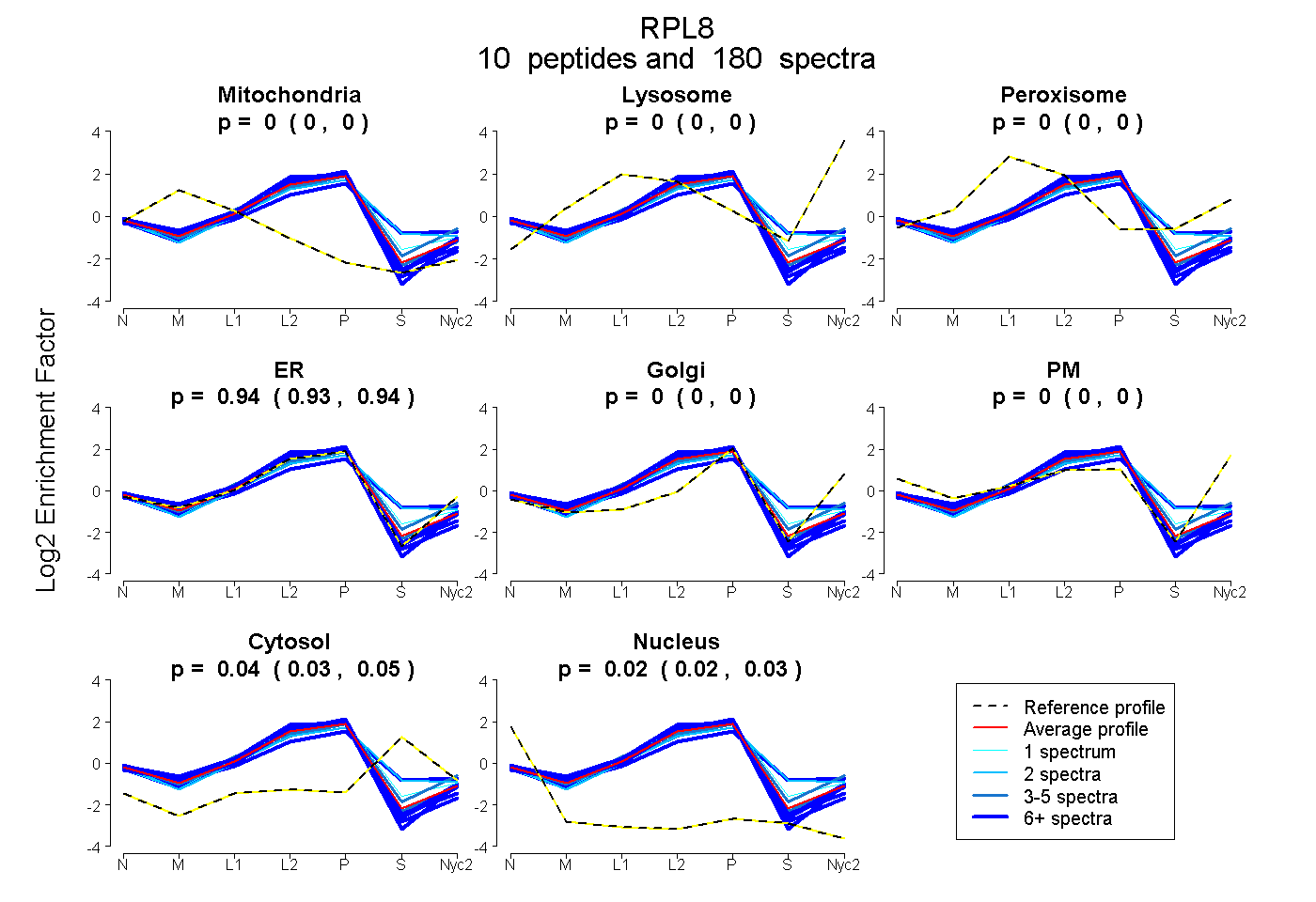
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.932 | 0.938
0.000 | 0.000
0.000 | 0.000
0.035 | 0.046
0.020 | 0.027
peptides
spectra
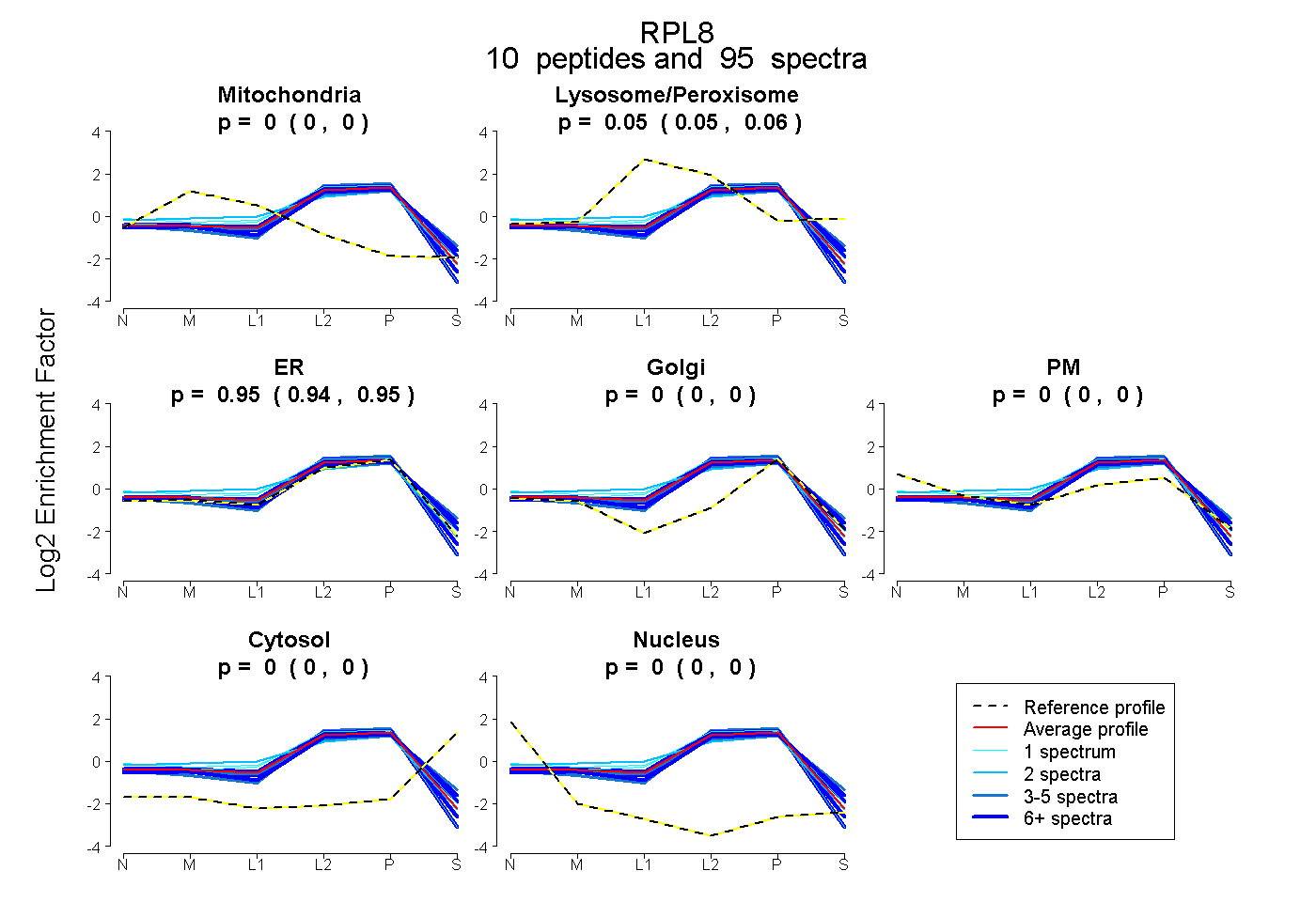
0.000 | 0.000
0.047 | 0.057
0.939 | 0.952
0.000 | 0.000
0.000 | 0.004
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
180 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.935 0.932 | 0.938 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.041 0.035 | 0.046 |
0.024 0.020 | 0.027 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
95 spectra |
 |
0.000 0.000 | 0.000 |
0.052 0.047 | 0.057 |
0.948 0.939 | 0.952 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.004 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 40 spectra, AVVGVVAGGGR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, ASGNYATVISHNPETK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, GAGSVFR | 0.000 | 0.053 | 0.935 | 0.000 | 0.012 | 0.000 | 0.000 | |||
| 11 spectra, DIIHDPGR | 0.000 | 0.095 | 0.905 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 26 spectra, VISSANR | 0.000 | 0.046 | 0.900 | 0.000 | 0.008 | 0.047 | 0.000 | |||
| 2 spectra, SAPLAK | 0.050 | 0.113 | 0.711 | 0.000 | 0.126 | 0.000 | 0.000 | |||
| 1 spectrum, DAPAGR | 0.000 | 0.169 | 0.649 | 0.000 | 0.182 | 0.000 | 0.000 | |||
| 4 spectra, VGLIAAR | 0.000 | 0.141 | 0.733 | 0.048 | 0.029 | 0.050 | 0.000 | |||
| 6 spectra, AVDFAER | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, IDKPILK | 0.000 | 0.012 | 0.988 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
347 spectra |
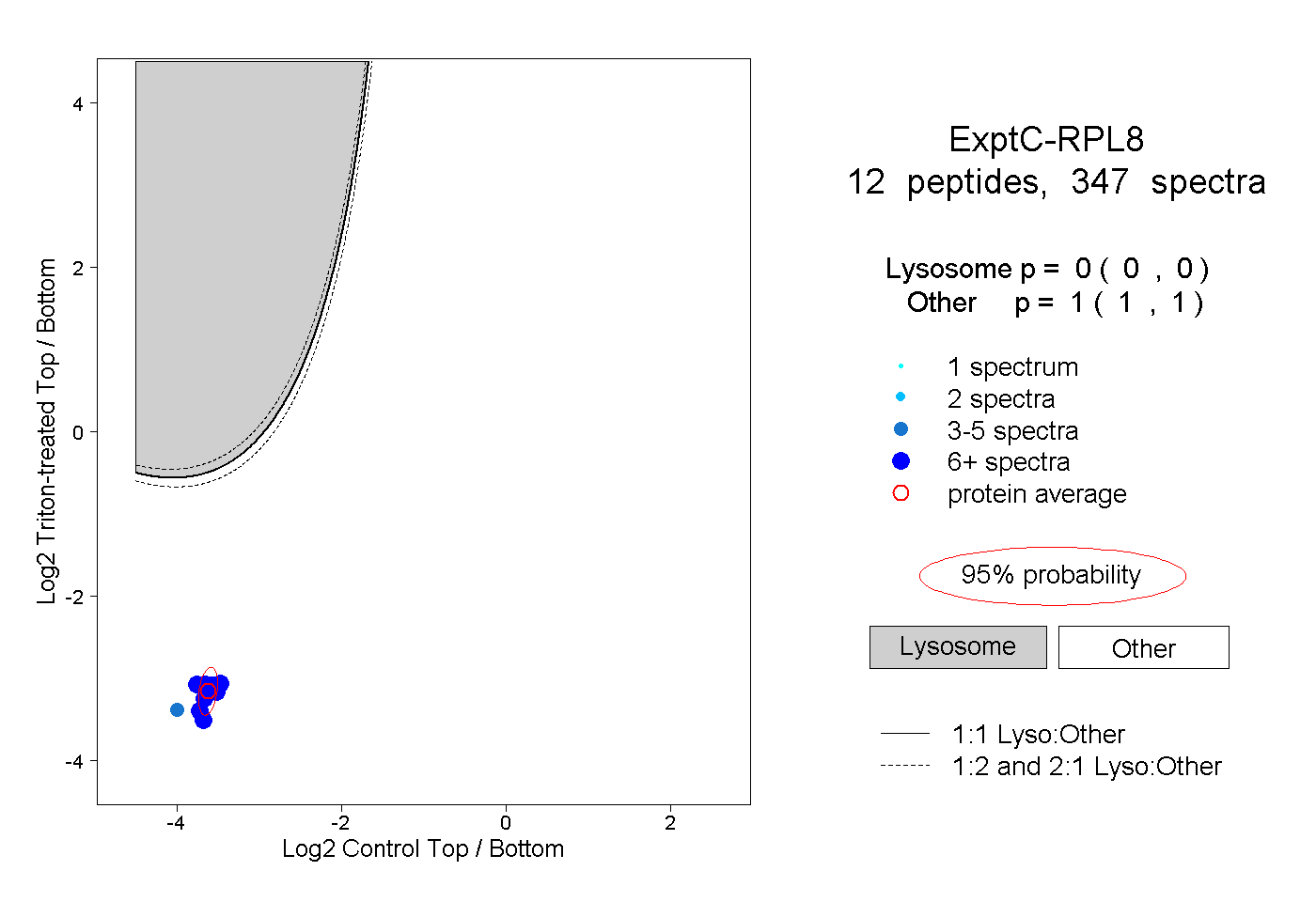 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
48 spectra |
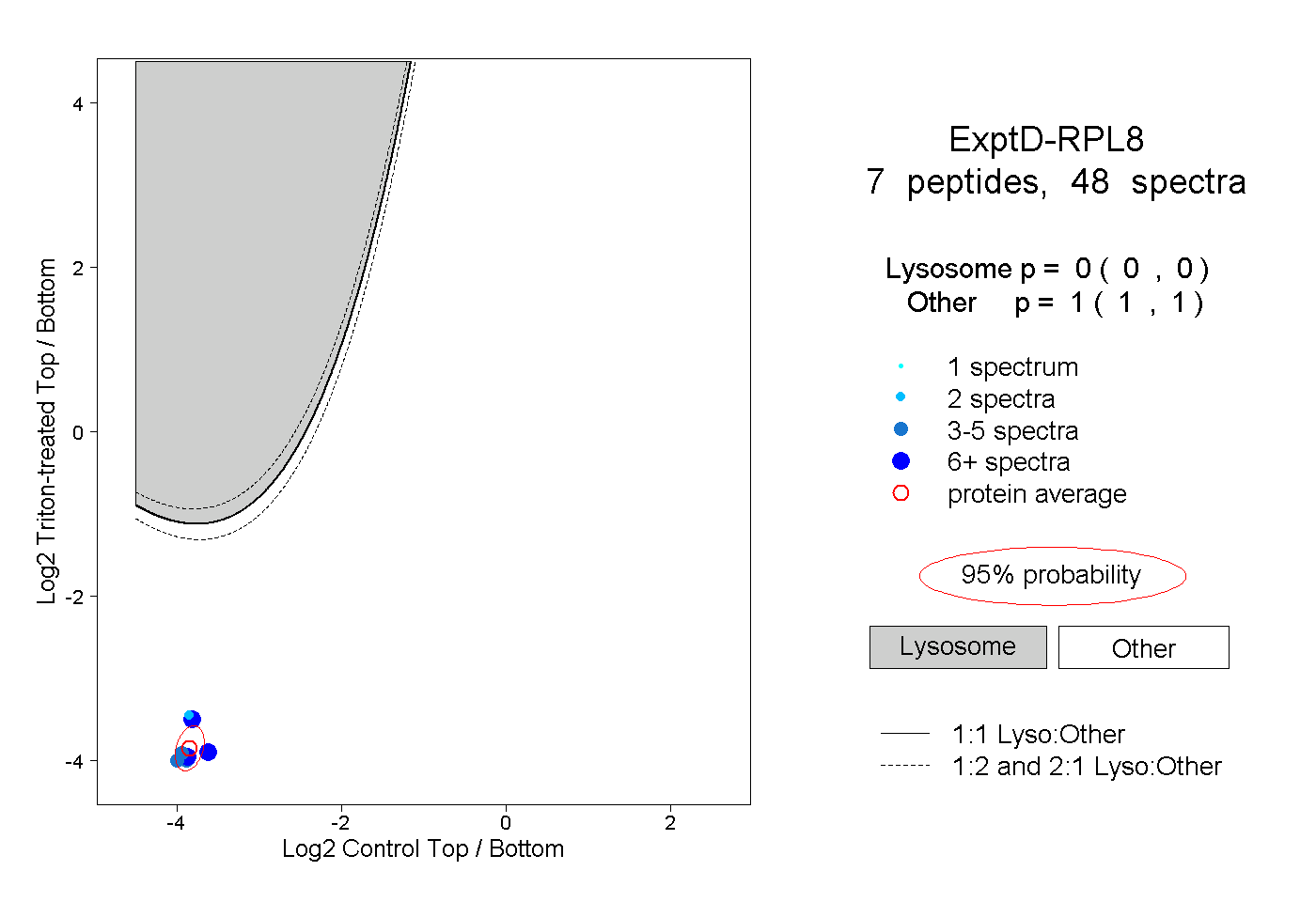 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |