peptides
spectra
0.019 | 0.043
0.069 | 0.094
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.876 | 0.893
0.000 | 0.000
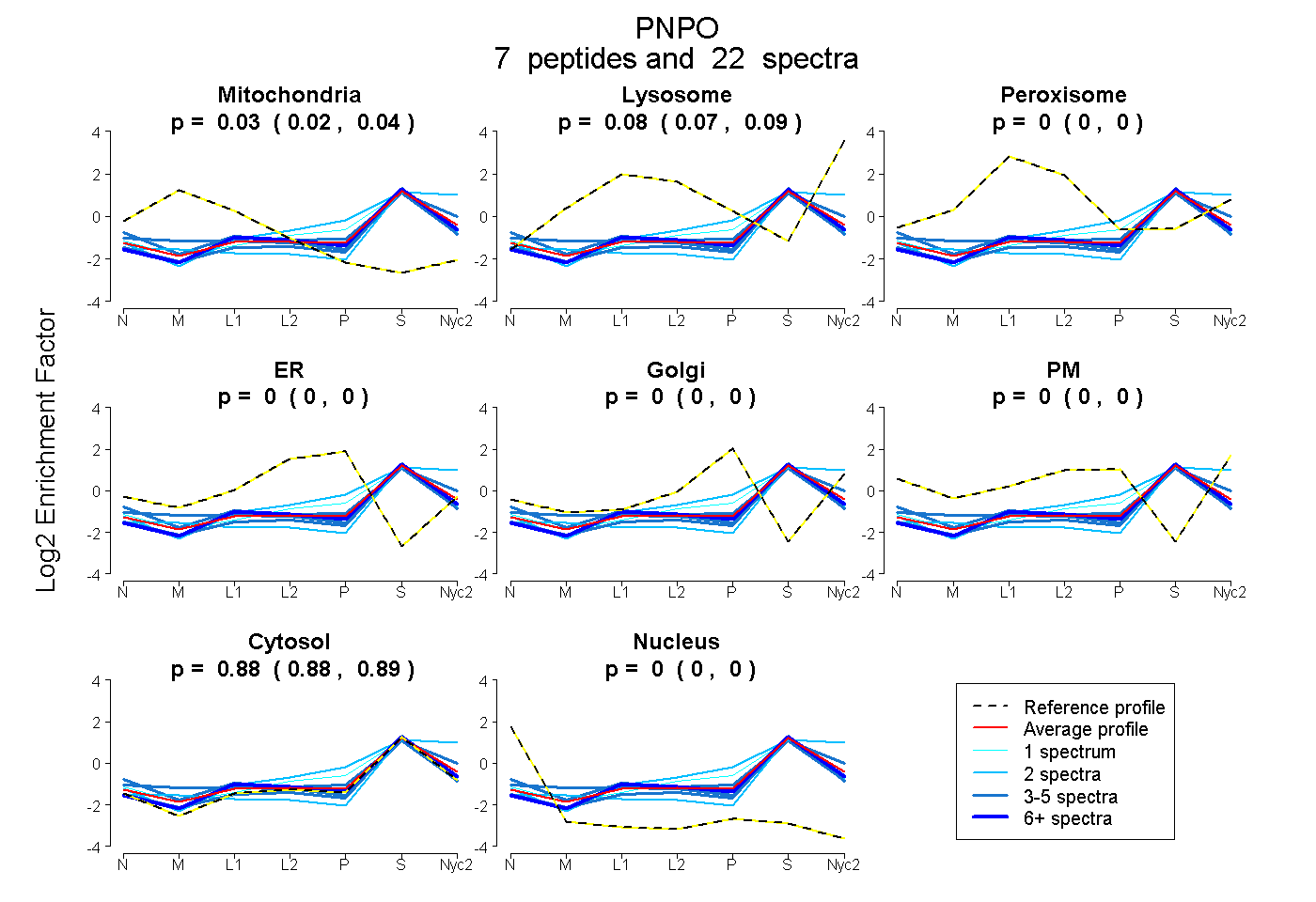
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
22 spectra |
 |
0.032 0.019 | 0.043 |
0.083 0.069 | 0.094 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.885 0.876 | 0.893 |
0.000 0.000 | 0.000 |
| 2 spectra, QSSVIPDR | 0.094 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.906 | 0.000 | ||
| 4 spectra, SSQIGAVVSR | 0.041 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.959 | 0.000 | ||
| 2 spectra, NEELGQLYR | 0.000 | 0.202 | 0.000 | 0.000 | 0.081 | 0.000 | 0.718 | 0.000 | ||
| 1 spectrum, DGKPSAR | 0.000 | 0.000 | 0.020 | 0.075 | 0.061 | 0.000 | 0.844 | 0.000 | ||
| 6 spectra, VEGPVK | 0.000 | 0.016 | 0.068 | 0.000 | 0.000 | 0.000 | 0.916 | 0.000 | ||
| 4 spectra, FFTNYESR | 0.093 | 0.124 | 0.000 | 0.000 | 0.000 | 0.000 | 0.782 | 0.000 | ||
| 3 spectra, EAENYFHSRPK | 0.050 | 0.000 | 0.084 | 0.000 | 0.000 | 0.033 | 0.820 | 0.013 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
13 spectra |
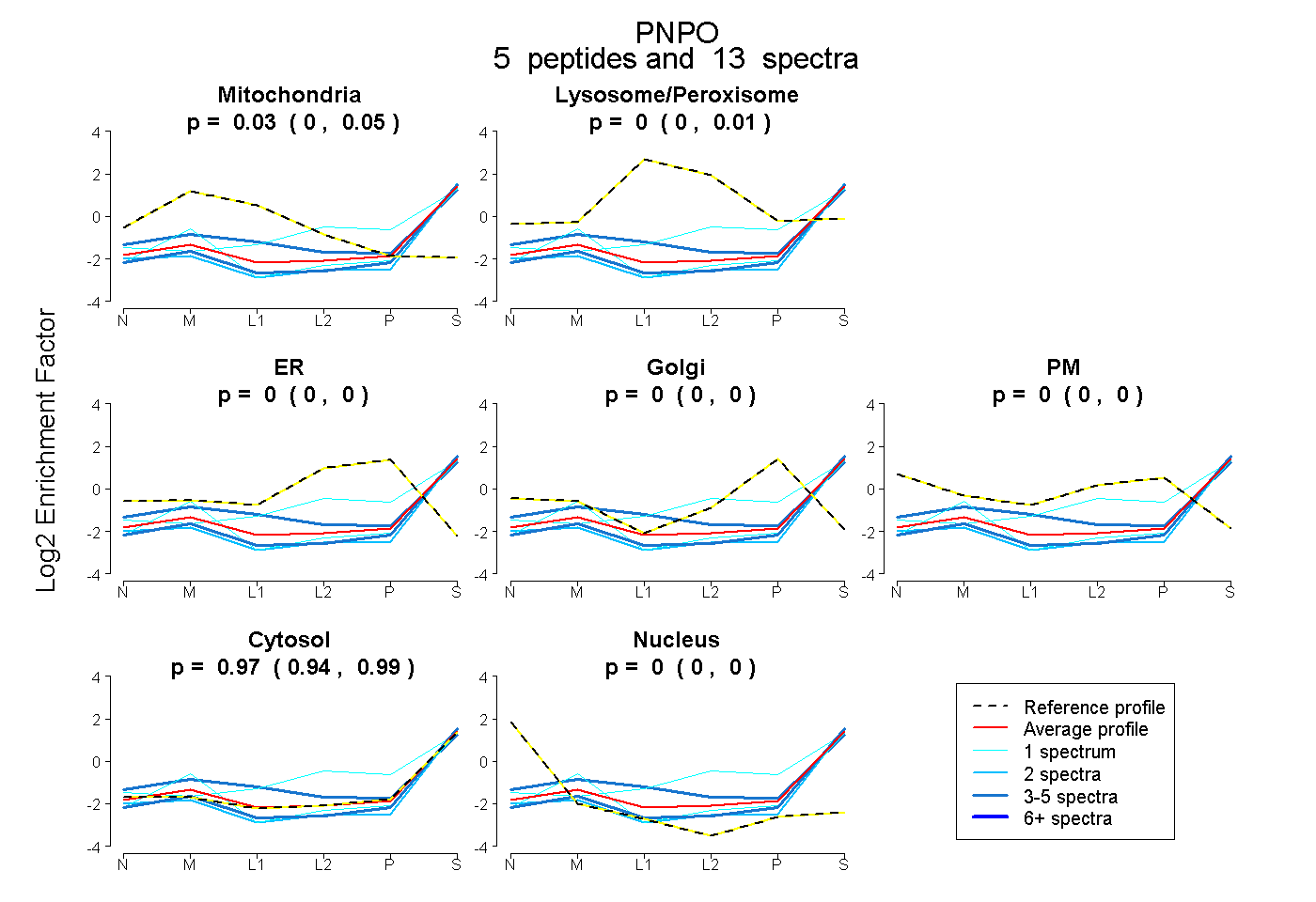 |
0.031 0.003 | 0.051 |
0.000 0.000 | 0.008 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.969 0.942 | 0.991 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
31 spectra |
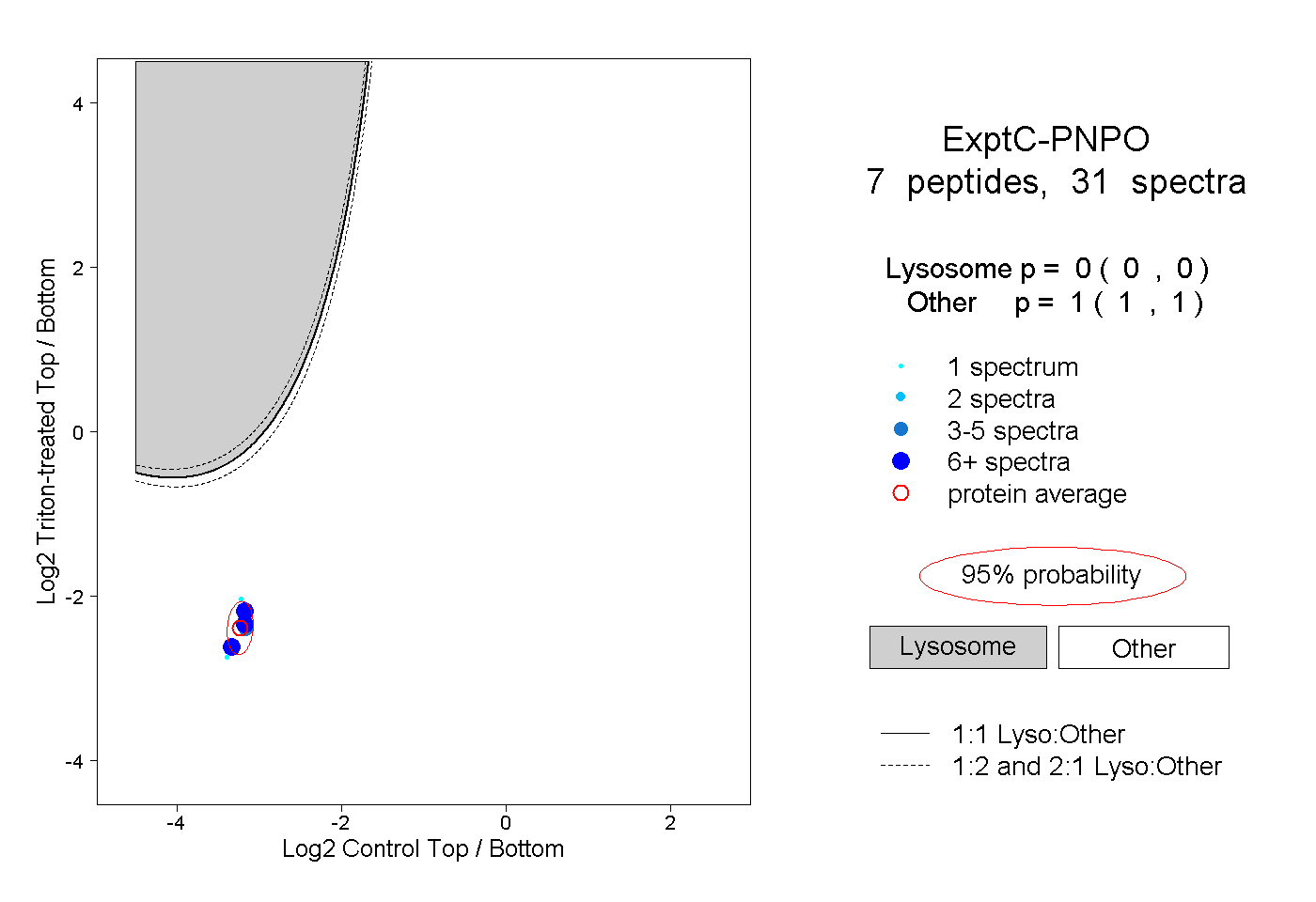 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
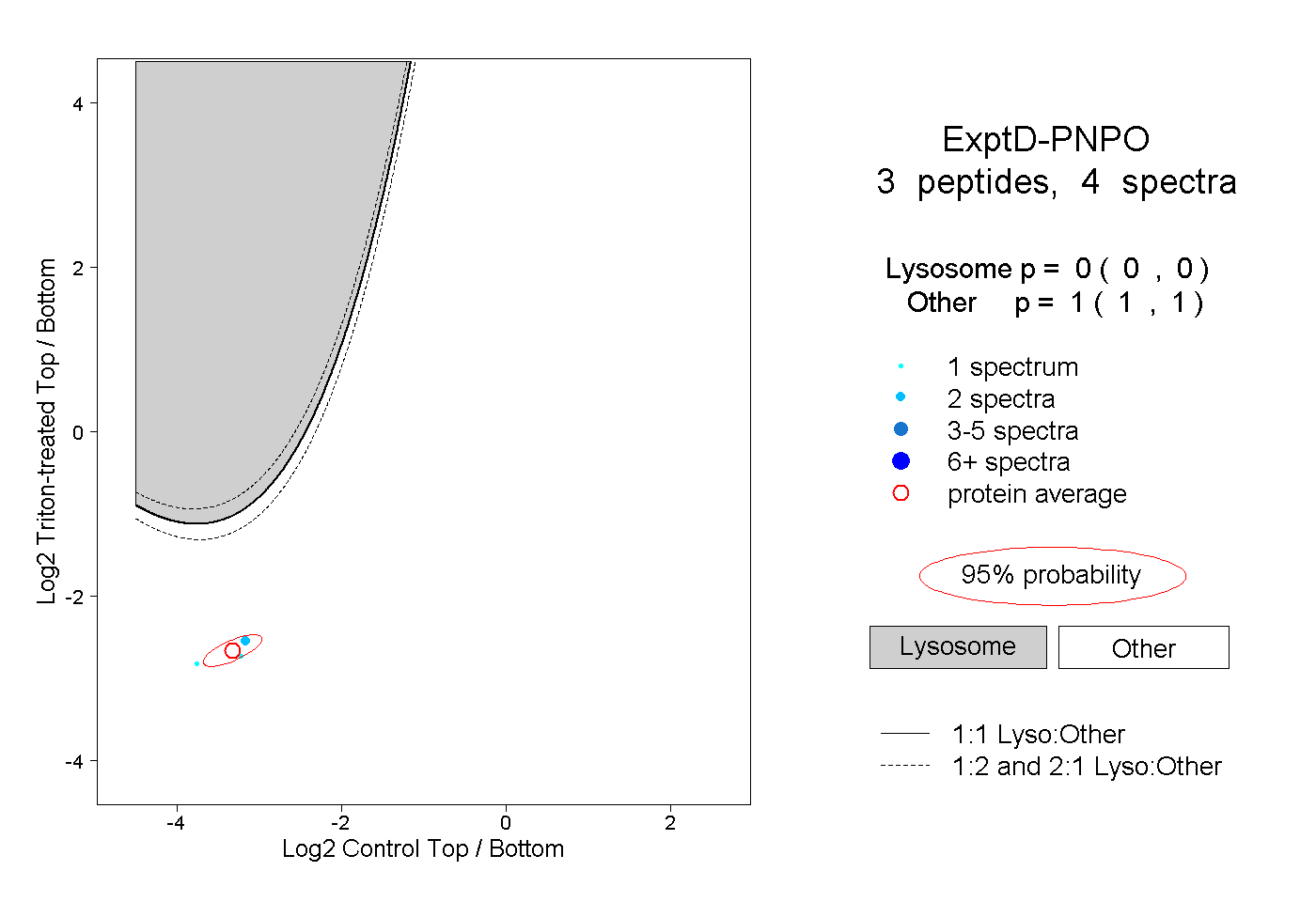 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |