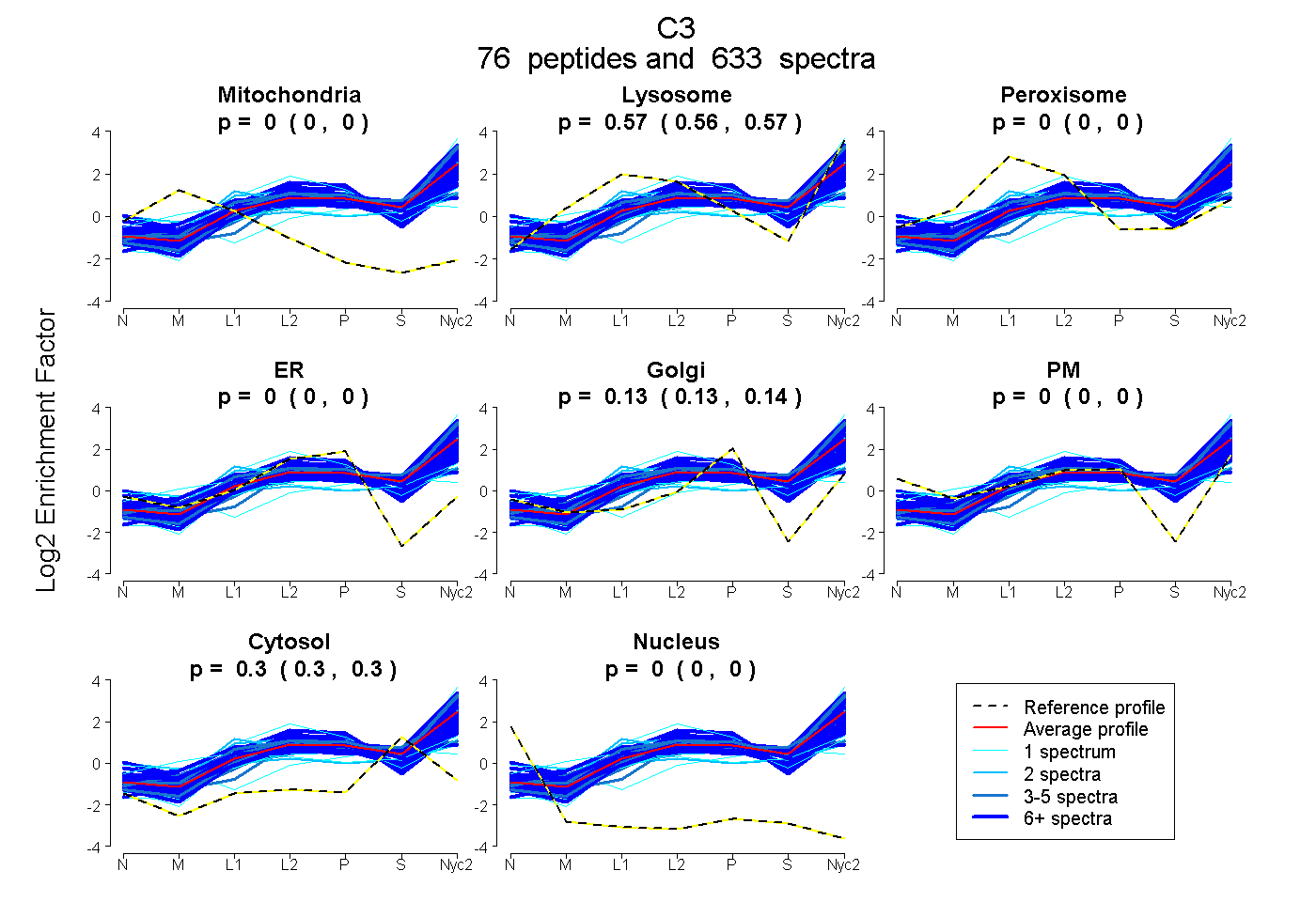
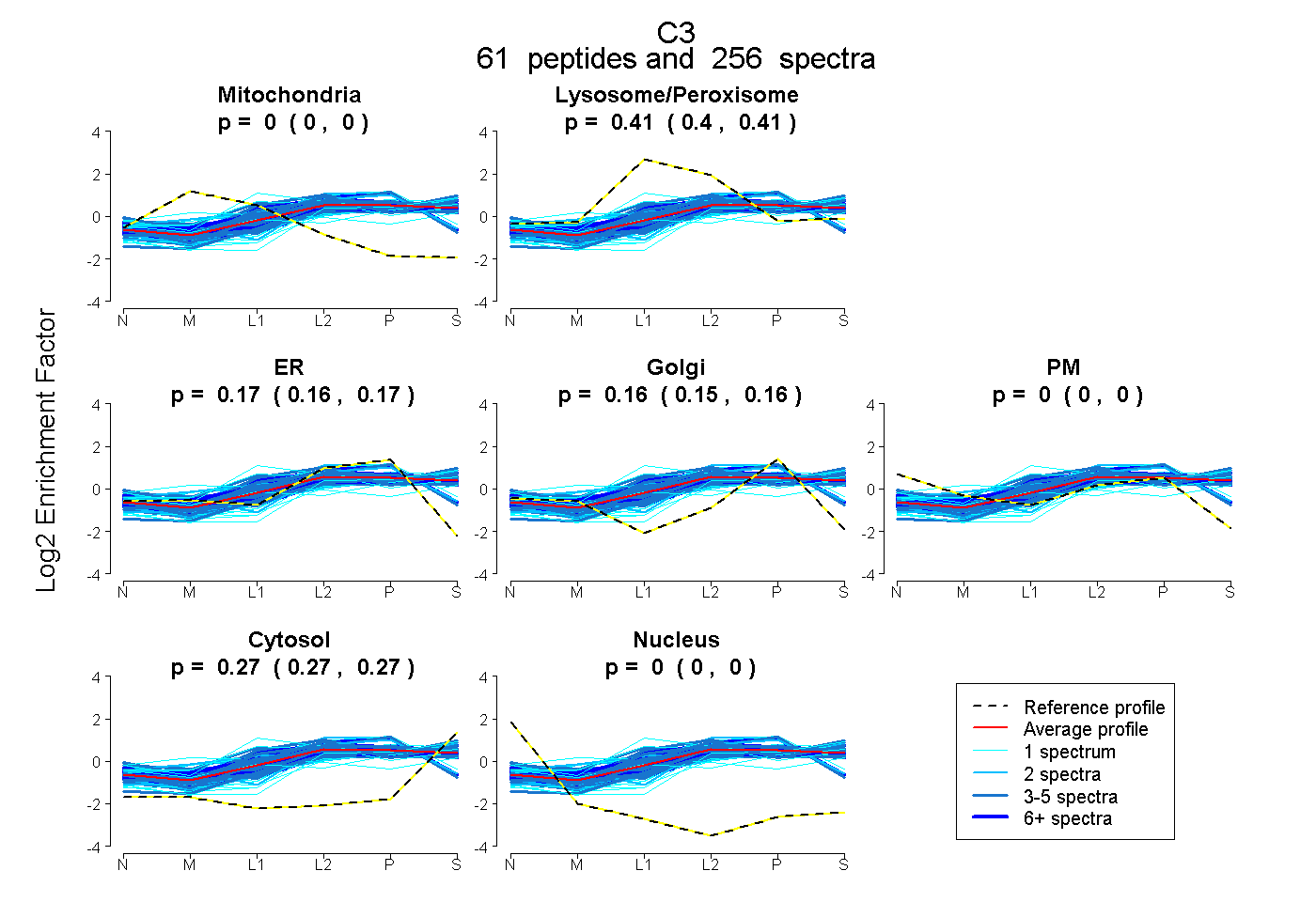
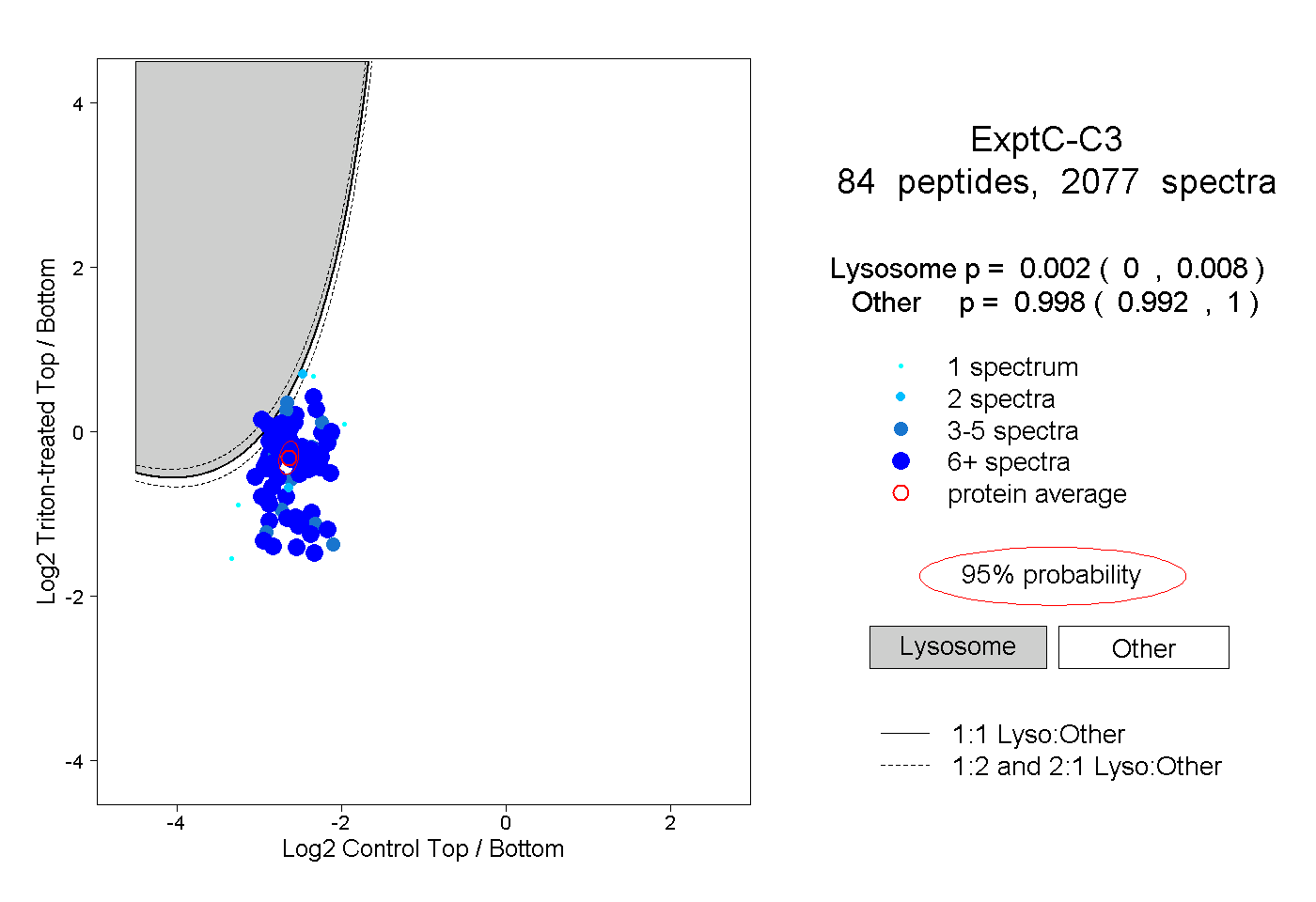
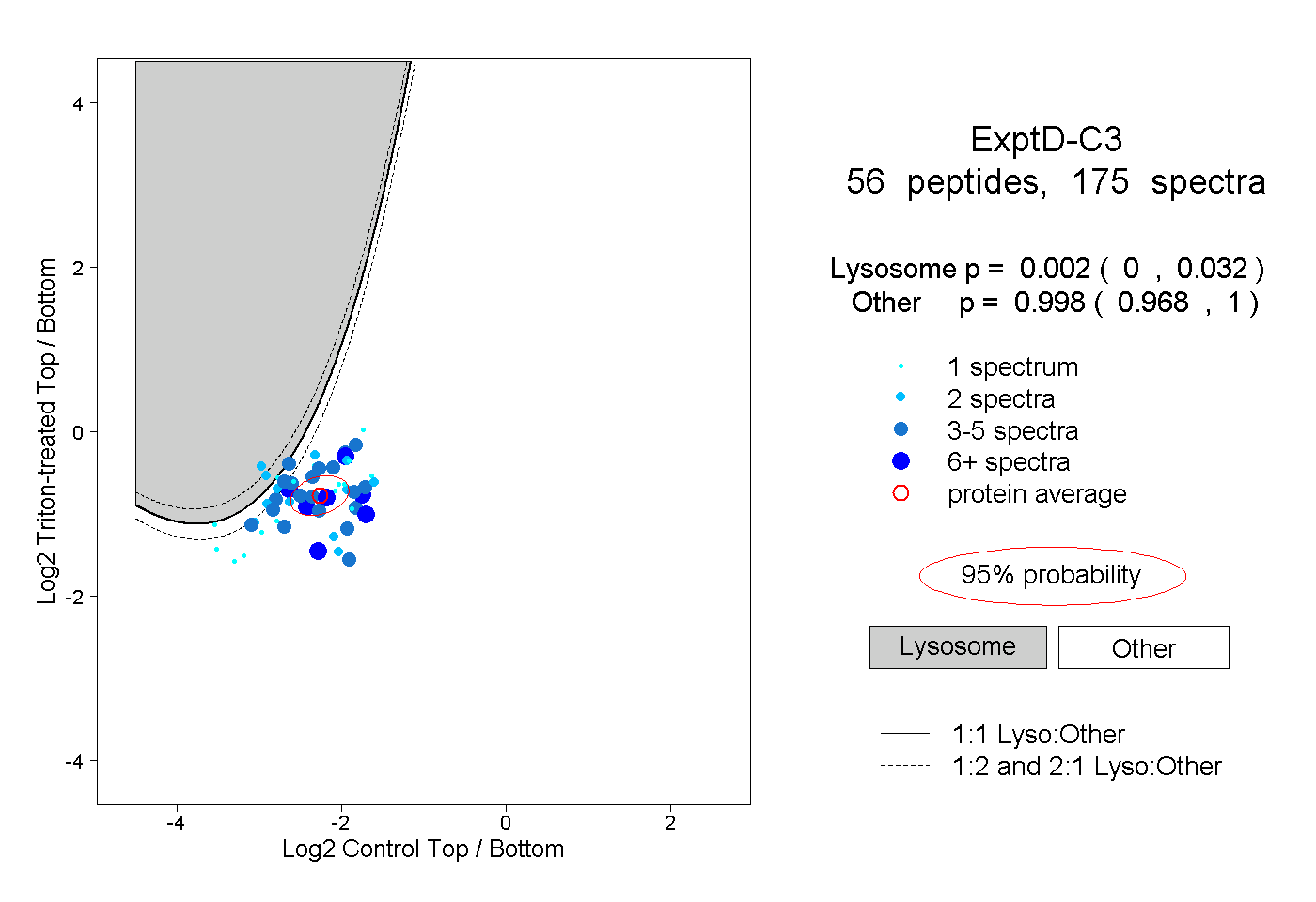
| 2 spectra, VMNIFLK |
|
0.042 |
|
|
|
|
|
|
|
0.958 |
| 6 spectra, LITQGESCLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, EDVPAADLSDQVPDTDSETR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, SGSDEVQAGQER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ADIGCTPGSGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VLIEDGSGEAVLSR |
|
0.287 |
|
|
|
|
|
|
|
0.713 |
| 1 spectrum, SSVAVPYVIVPLK |
|
0.021 |
|
|
|
|
|
|
|
0.979 |
| 1 spectrum, GVFVLNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, QPLTITVR |
|
0.124 |
|
|
|
|
|
|
|
0.876 |
| 6 spectra, EFNADK |
|
0.005 |
|
|
|
|
|
|
|
0.995 |
| 1 spectrum, VYSYYNLEESCTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VHQFFNVGLIQPGSVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SVQLMER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, QVLTSEK |
|
0.088 |
|
|
|
|
|
|
|
0.912 |
| 4 spectra, DFDSVPPVVR |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 11 spectra, VGLVAVDK |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 5 spectra, GYTQQLAFK |
|
0.005 |
|
|
|
|
|
|
|
0.995 |
| 2 spectra, KPQDAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, NTLIIYLEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LPYSVVR |
|
0.430 |
|
|
|
|
|
|
|
0.570 |
| 4 spectra, FISHVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, IFTVDNNLLPVGK |
|
0.037 |
|
|
|
|
|
|
|
0.963 |
| 1 spectrum, VVPEGMR |
|
0.115 |
|
|
|
|
|
|
|
0.885 |
| 2 spectra, QEALELIK |
|
0.050 |
|
|
|
|
|
|
|
0.950 |
| 1 spectrum, FGLEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VLMDGVRPSSPEALVGK |
|
0.901 |
|
|
|
|
|
|
|
0.099 |
| 3 spectra, SSMILDICTR |
|
0.002 |
|
|
|
|
|
|
|
0.998 |
| 4 spectra, GLEVSITAR |
|
0.013 |
|
|
|
|
|
|
|
0.987 |
| 3 spectra, TVLTGATGHLNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, CCEDGMR |
|
0.028 |
|
|
|
|
|
|
|
0.972 |
| 3 spectra, AGQYTDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, QTFSAEFEVK |
|
0.112 |
|
|
|
|
|
|
|
0.888 |
| 6 spectra, WLNEQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, EGIPDAR |
|
0.170 |
|
|
|
|
|
|
|
0.830 |
| 3 spectra, TNQGLQTDQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, NEQVEIR |
|
0.022 |
|
|
|
|
|
|
|
0.978 |
| 1 spectrum, NYAGVFMDAGLTFK |
|
0.462 |
|
|
|
|
|
|
|
0.538 |
| 1 spectrum, LEEPYLTK |
|
0.023 |
|
|
|
|
|
|
|
0.977 |
| 5 spectra, LLWESGSLLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, AFYEHAPK |
|
0.150 |
|
|
|
|
|
|
|
0.850 |
| 2 spectra, SDVDEDIIPEEDIISR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, AFMDCCNYITK |
|
0.450 |
|
|
|
|
|
|
|
0.550 |
| 3 spectra, EVVADSVWVDVK |
|
0.018 |
|
|
|
|
|
|
|
0.982 |
| 1 spectrum, QPAPGHQTTLR |
|
0.052 |
|
|
|
|
|
|
|
0.948 |
| 1 spectrum, ACEPGVDYVYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, LSVNTPNNR |
|
0.114 |
|
|
|
|
|
|
|
0.886 |
| 2 spectra, TLDPEHLGQGGVQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, SSPTVFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, FYYIDDPK |
|
0.739 |
|
|
|
|
|
|
|
0.261 |
| 3 spectra, IGLQEVEVK |
|
0.168 |
|
|
|
|
|
|
|
0.832 |
| 1 spectrum, QKPDGVFQEDGPVIHQEMIGGFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, FYHPEK |
|
0.239 |
|
|
|
|
|
|
|
0.761 |
| 4 spectra, TDAGQEAK |
|
0.014 |
|
|
|
|
|
|
|
0.986 |
| 3 spectra, ISLAQSLTR |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 17 spectra, IWDVVEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, YYQTIEIPPK |
|
0.267 |
|
|
|
|
|
|
|
0.733 |