peptides
spectra
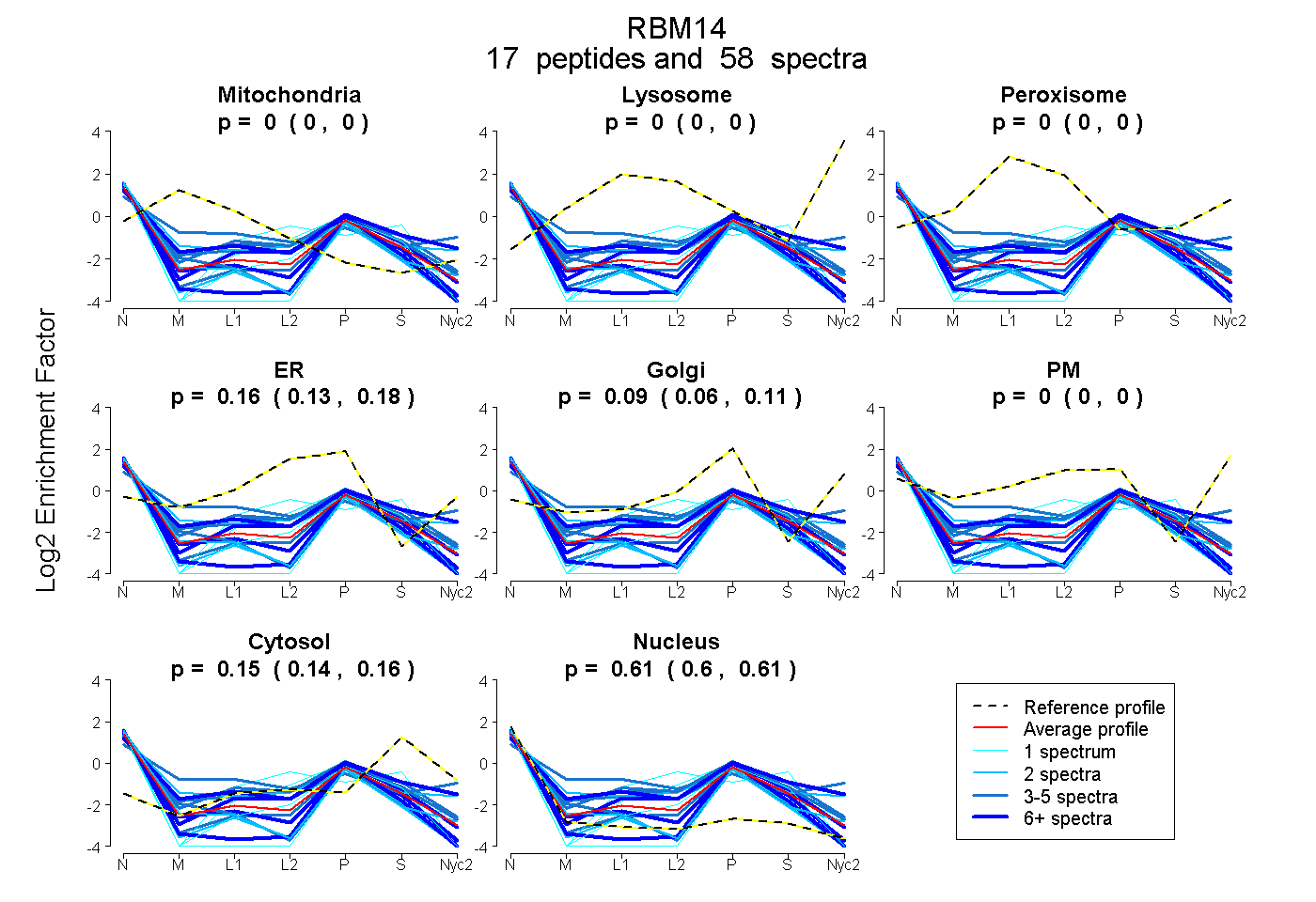
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.128 | 0.180
0.058 | 0.111
0.000 | 0.000
0.144 | 0.155
0.602 | 0.613
peptides
spectra
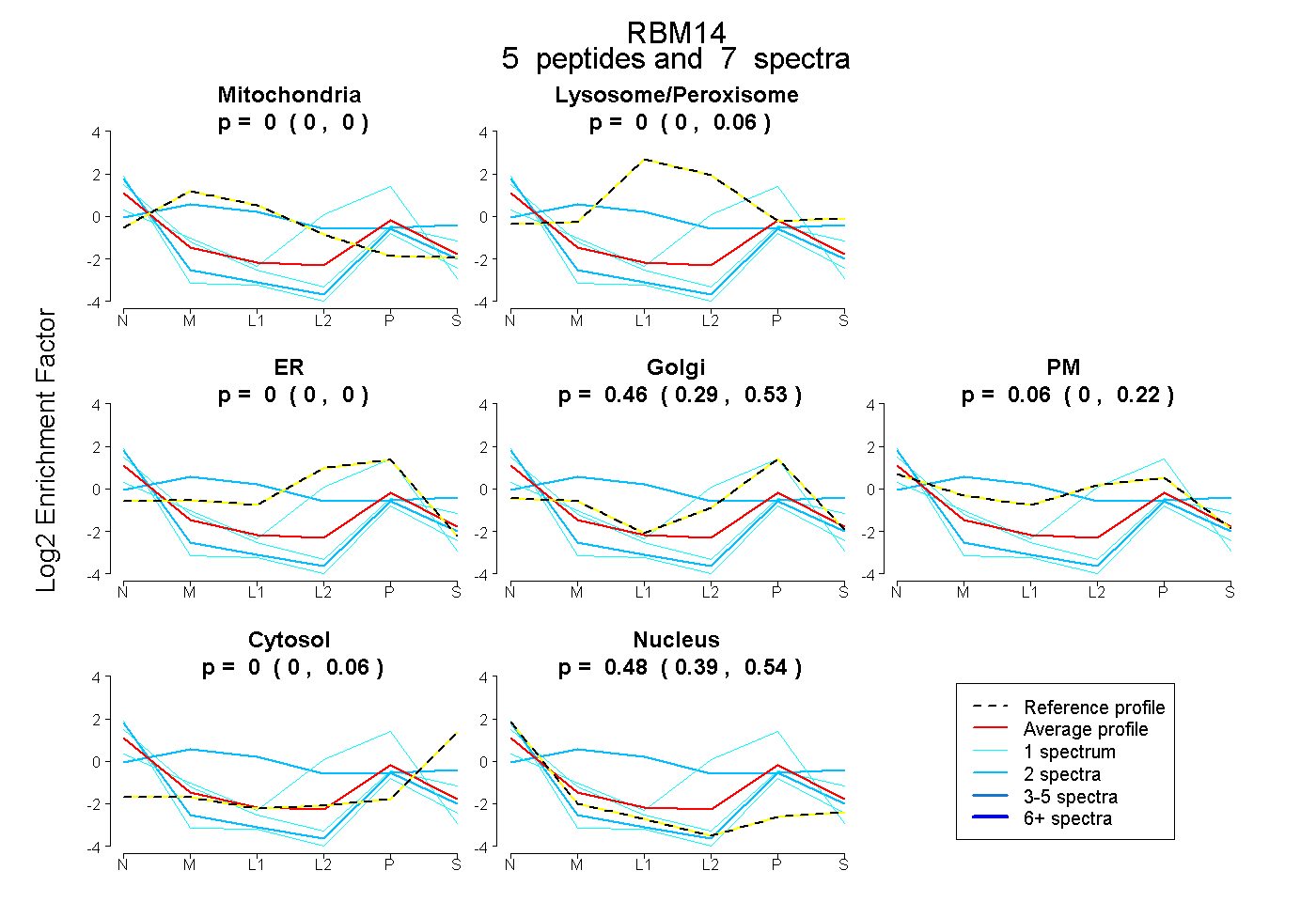
0.000 | 0.000
0.000 | 0.056
0.000 | 0.000
0.287 | 0.535
0.000 | 0.219
0.000 | 0.064
0.388 | 0.540
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
58 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.156 0.128 | 0.180 |
0.087 0.058 | 0.111 |
0.000 0.000 | 0.000 |
0.150 0.144 | 0.155 |
0.607 0.602 | 0.613 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
7 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.056 |
0.000 0.000 | 0.000 |
0.461 0.287 | 0.535 |
0.058 0.000 | 0.219 |
0.005 0.000 | 0.064 |
0.476 0.388 | 0.540 |
| 2 spectra, LSESQLSFR | 0.000 | 0.000 | 0.000 | 0.231 | 0.000 | 0.000 | 0.769 | |||
| 1 spectrum, AQPSVSLGAPYR | 0.000 | 0.000 | 0.000 | 0.123 | 0.000 | 0.000 | 0.877 | |||
| 1 spectrum, SLFER | 0.000 | 0.000 | 0.407 | 0.501 | 0.000 | 0.000 | 0.092 | |||
| 1 spectrum, AQPSASLGVGYR | 0.000 | 0.000 | 0.000 | 0.336 | 0.000 | 0.080 | 0.584 | |||
| 2 spectra, IFVGNVSAACTSQELR | 0.359 | 0.212 | 0.000 | 0.014 | 0.235 | 0.180 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
9 spectra |
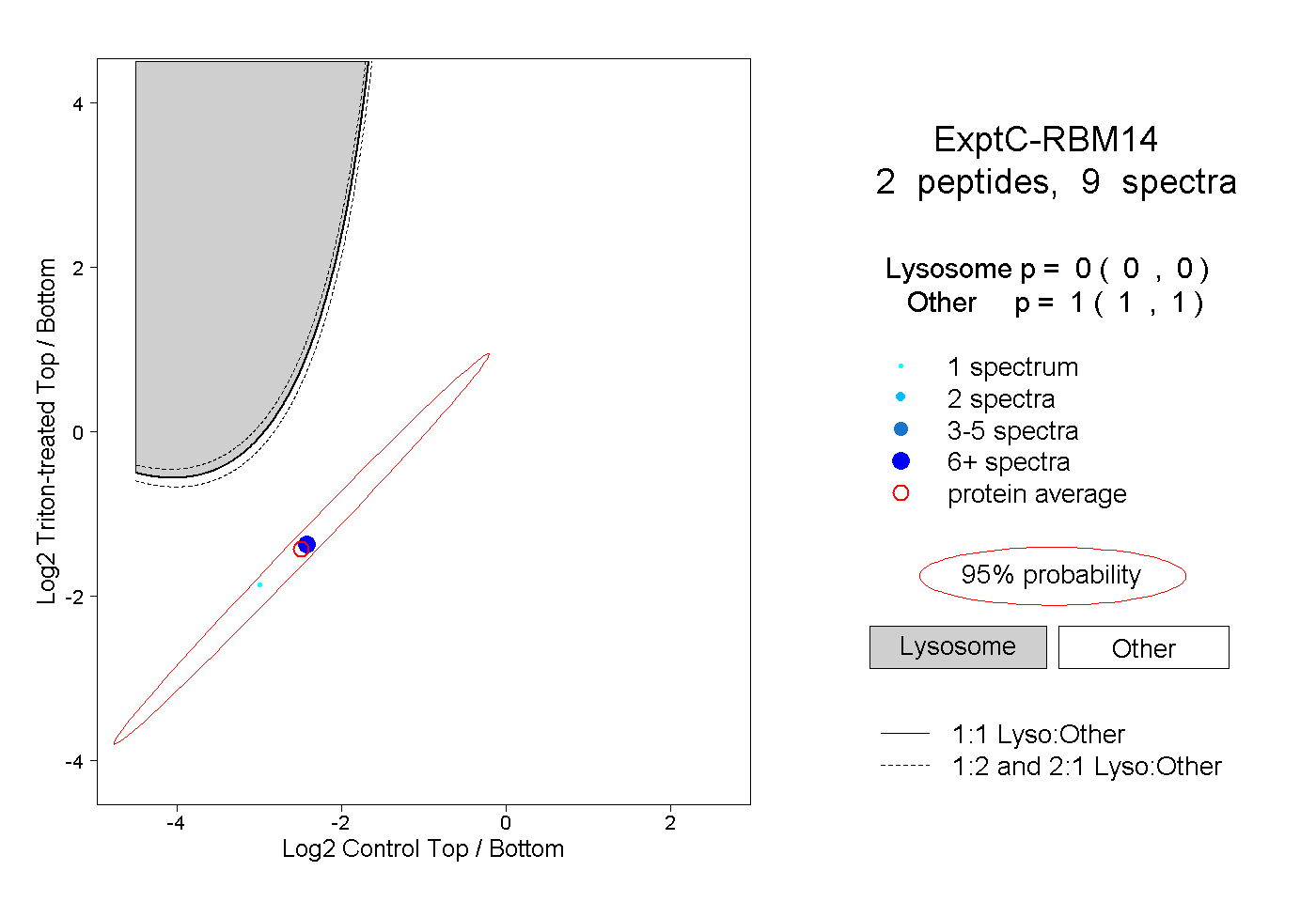 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
2 spectra |
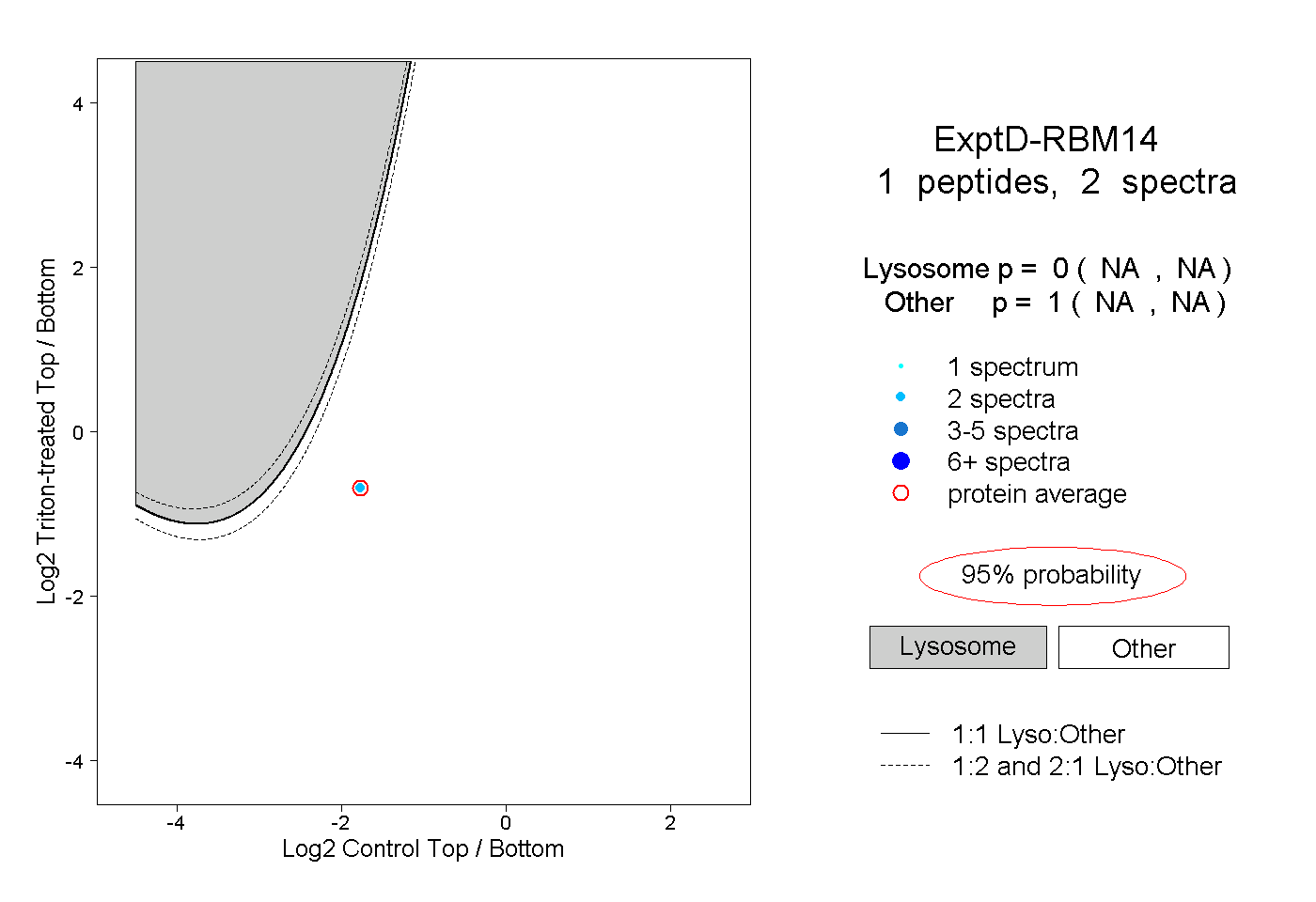 |
0.000 NA | NA |
1.000 NA | NA |