peptides
spectra
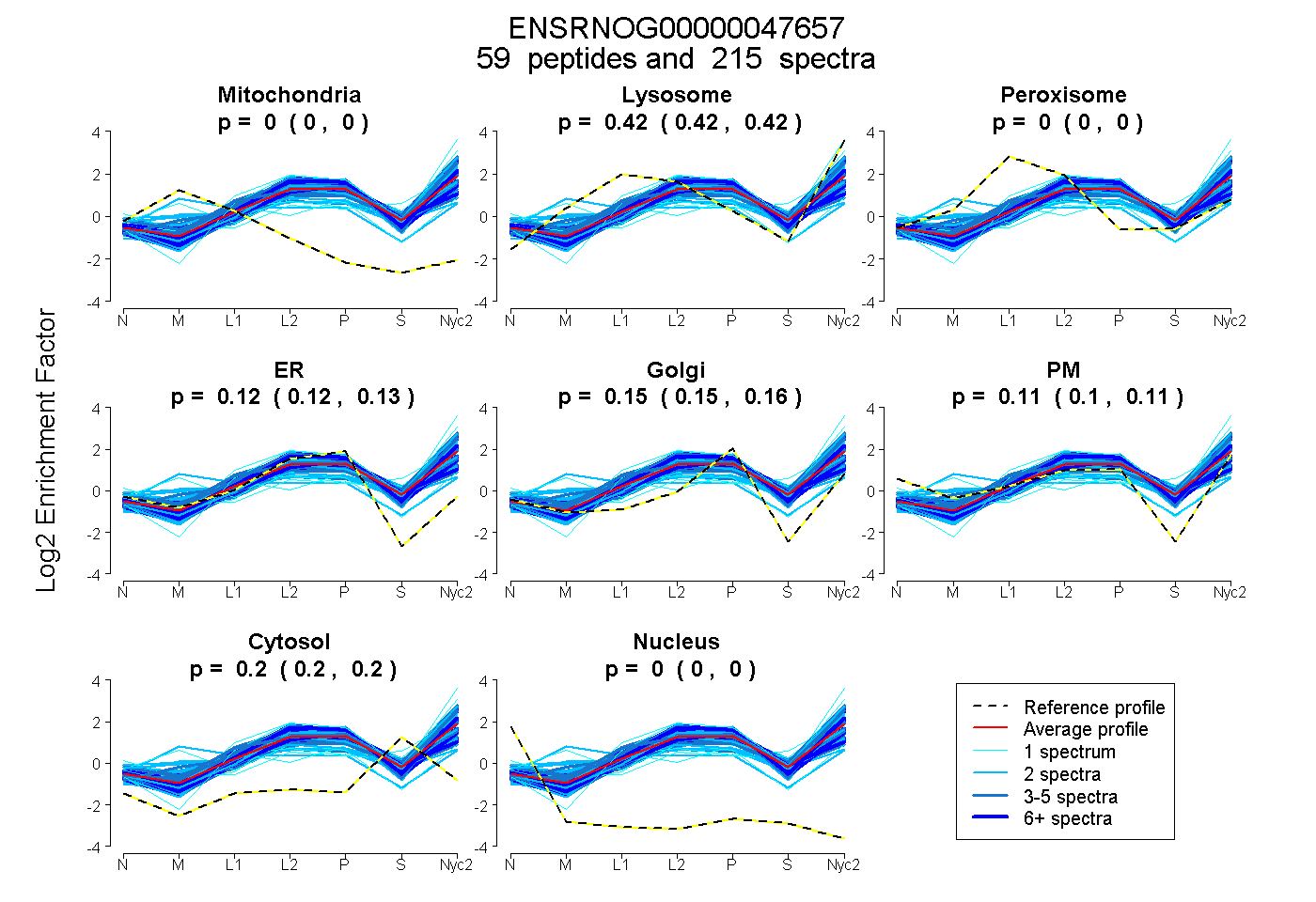
0.000 | 0.000
0.419 | 0.422
0.000 | 0.000
0.118 | 0.126
0.150 | 0.157
0.104 | 0.109
0.196 | 0.198
0.000 | 0.000
peptides
spectra
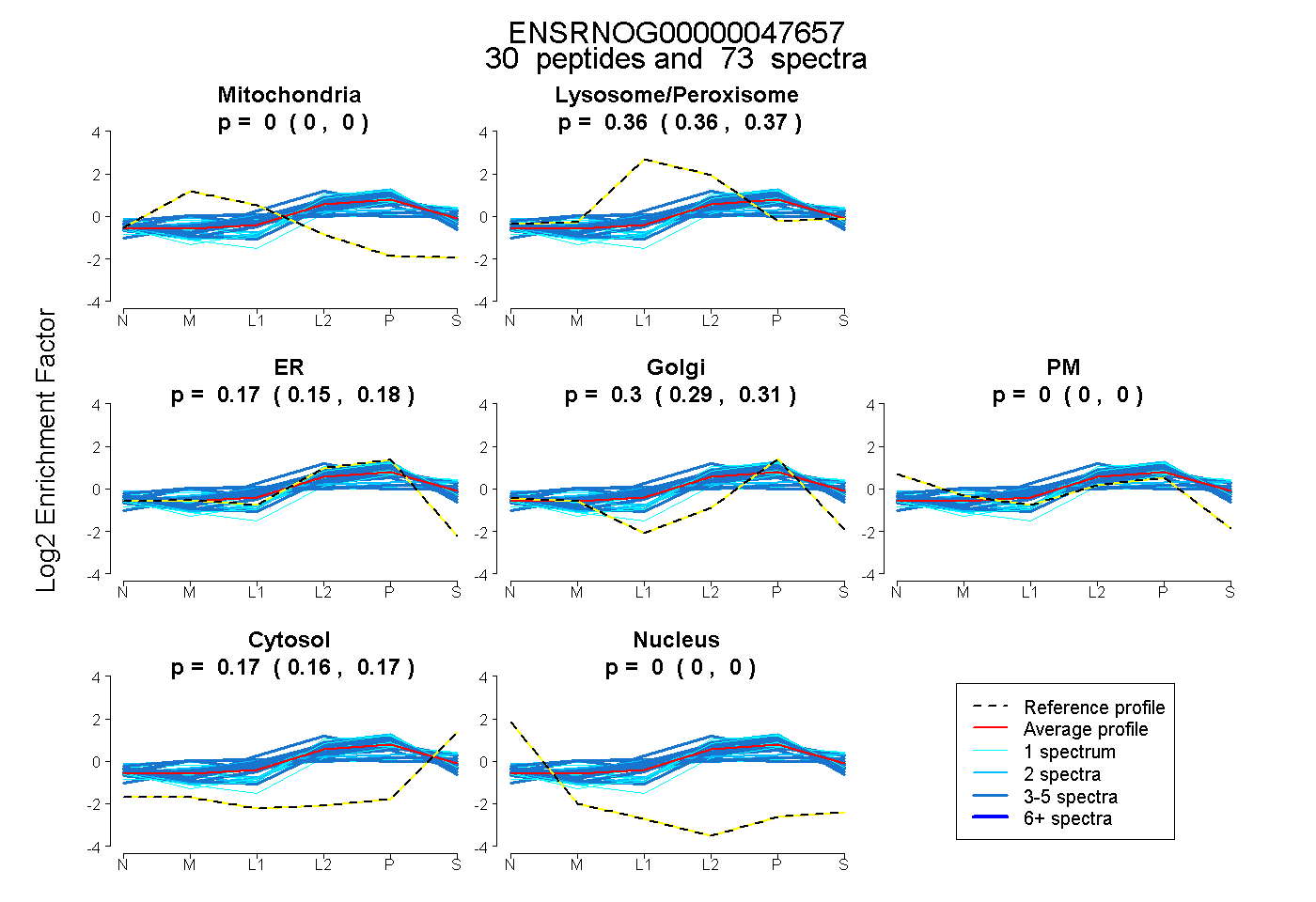
0.000 | 0.000
0.359 | 0.369
0.150 | 0.178
0.288 | 0.312
0.000 | 0.000
0.164 | 0.172
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
215 spectra |
 |
0.000 0.000 | 0.000 |
0.420 0.419 | 0.422 |
0.000 0.000 | 0.000 |
0.122 0.118 | 0.126 |
0.154 0.150 | 0.157 |
0.107 0.104 | 0.109 |
0.197 0.196 | 0.198 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
73 spectra |
 |
0.000 0.000 | 0.000 |
0.365 0.359 | 0.369 |
0.166 0.150 | 0.178 |
0.301 0.288 | 0.312 |
0.000 0.000 | 0.000 |
0.169 0.164 | 0.172 |
0.000 0.000 | 0.000 |
| 1 spectrum, YVYGKPVQGVAYTR | 0.000 | 0.151 | 0.630 | 0.000 | 0.000 | 0.220 | 0.000 | |||
| 3 spectra, GHIFVQTDQPIYNPGQR | 0.016 | 0.324 | 0.000 | 0.118 | 0.294 | 0.248 | 0.000 | |||
| 2 spectra, ANSFLGQK | 0.000 | 0.312 | 0.141 | 0.333 | 0.000 | 0.214 | 0.000 | |||
| 1 spectrum, VATWLTHQGSFQGGFR | 0.000 | 0.318 | 0.387 | 0.000 | 0.000 | 0.295 | 0.000 | |||
| 2 spectra, SCGLFGLR | 0.000 | 0.134 | 0.685 | 0.000 | 0.000 | 0.181 | 0.000 | |||
| 3 spectra, VNTEIGDLEGLR | 0.000 | 0.293 | 0.424 | 0.194 | 0.000 | 0.089 | 0.000 | |||
| 3 spectra, GLCVAKPTR | 0.000 | 0.332 | 0.207 | 0.206 | 0.000 | 0.255 | 0.000 | |||
| 1 spectrum, DHAVDLIQK | 0.000 | 0.357 | 0.174 | 0.316 | 0.000 | 0.152 | 0.000 | |||
| 2 spectra, LSSGNDFVLLR | 0.000 | 0.131 | 0.659 | 0.000 | 0.000 | 0.210 | 0.000 | |||
| 1 spectrum, GSFTIGDAVSK | 0.000 | 0.181 | 0.494 | 0.183 | 0.000 | 0.142 | 0.000 | |||
| 5 spectra, EFHLHLR | 0.000 | 0.387 | 0.172 | 0.187 | 0.000 | 0.254 | 0.000 | |||
| 5 spectra, VFALDQK | 0.000 | 0.436 | 0.113 | 0.361 | 0.000 | 0.089 | 0.000 | |||
| 3 spectra, YVLPNFEVK | 0.000 | 0.363 | 0.275 | 0.219 | 0.000 | 0.143 | 0.000 | |||
| 2 spectra, DQFQAALGK | 0.000 | 0.331 | 0.000 | 0.165 | 0.285 | 0.219 | 0.000 | |||
| 3 spectra, DGSFGAWLHR | 0.000 | 0.453 | 0.024 | 0.404 | 0.000 | 0.120 | 0.000 | |||
| 1 spectrum, ENLSCPK | 0.000 | 0.302 | 0.161 | 0.323 | 0.000 | 0.214 | 0.000 | |||
| 1 spectrum, LTVQAPPSR | 0.000 | 0.369 | 0.138 | 0.340 | 0.000 | 0.153 | 0.000 | |||
| 3 spectra, ATETQGVNLLFSSR | 0.000 | 0.216 | 0.560 | 0.037 | 0.000 | 0.186 | 0.000 | |||
| 2 spectra, DSSTWLTAFVLK | 0.000 | 0.195 | 0.363 | 0.209 | 0.000 | 0.232 | 0.000 | |||
| 3 spectra, VPQPACR | 0.000 | 0.197 | 0.329 | 0.258 | 0.000 | 0.216 | 0.000 | |||
| 2 spectra, SHLLQLNNHQVK | 0.000 | 0.474 | 0.000 | 0.273 | 0.000 | 0.253 | 0.000 | |||
| 1 spectrum, VSATLLSGSDSK | 0.000 | 0.137 | 0.648 | 0.000 | 0.000 | 0.215 | 0.000 | |||
| 4 spectra, ITQVLHFTK | 0.000 | 0.469 | 0.324 | 0.000 | 0.000 | 0.207 | 0.000 | |||
| 5 spectra, VGDTFVLSLR | 0.000 | 0.403 | 0.205 | 0.335 | 0.000 | 0.057 | 0.000 | |||
| 1 spectrum, FACYYPR | 0.000 | 0.389 | 0.000 | 0.165 | 0.161 | 0.286 | 0.000 | |||
| 3 spectra, LLVSAGSLYPAVAK | 0.000 | 0.399 | 0.117 | 0.383 | 0.000 | 0.101 | 0.000 | |||
| 1 spectrum, NVNFQK | 0.000 | 0.135 | 0.310 | 0.178 | 0.000 | 0.377 | 0.000 | |||
| 2 spectra, FSLGSTINVK | 0.000 | 0.474 | 0.000 | 0.428 | 0.000 | 0.098 | 0.000 | |||
| 4 spectra, APHIQLVAHSPWLK | 0.009 | 0.465 | 0.000 | 0.417 | 0.000 | 0.108 | 0.000 | |||
| 3 spectra, QHLVPGAPFLLQALVR | 0.040 | 0.450 | 0.000 | 0.295 | 0.000 | 0.215 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
534 spectra |
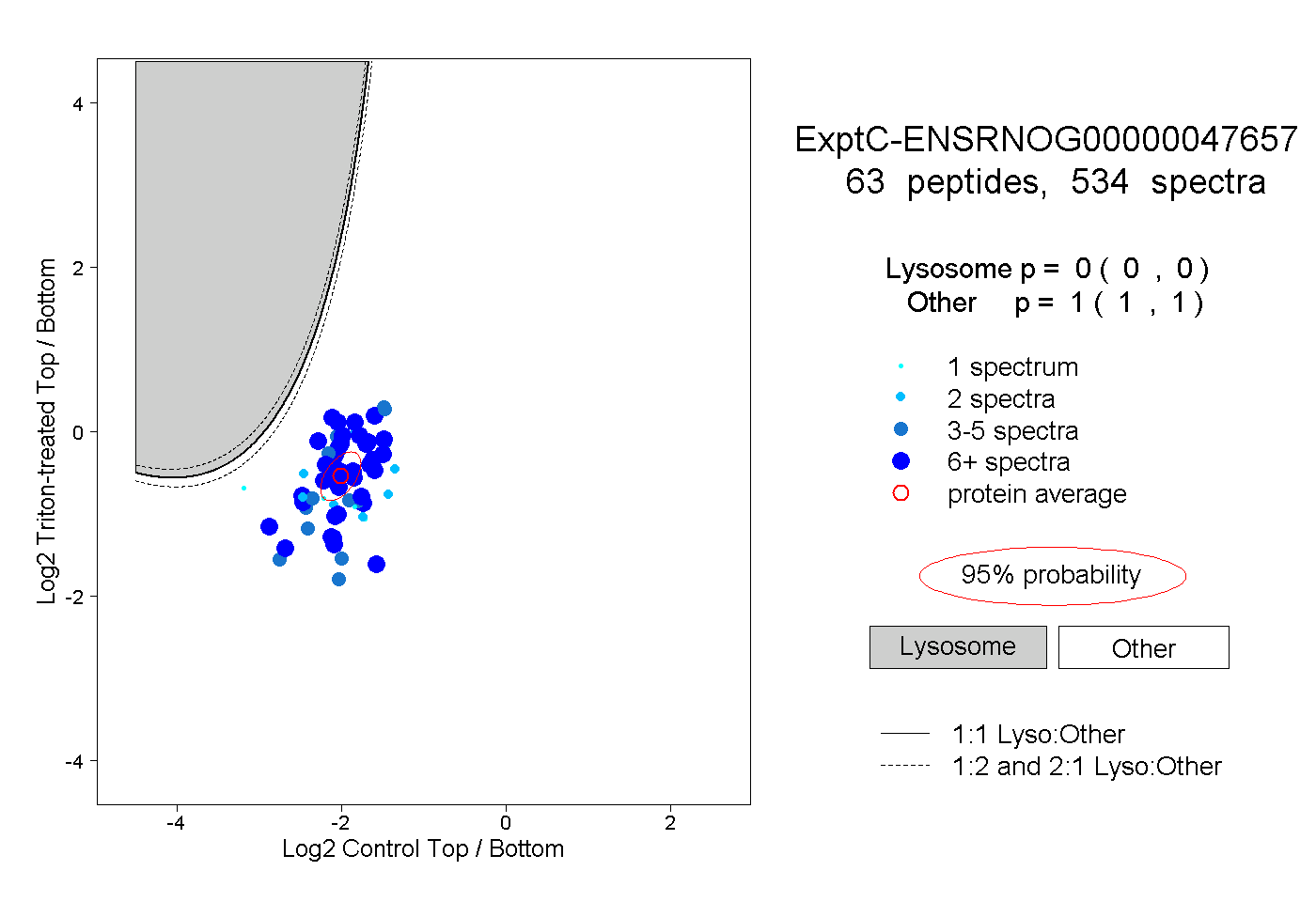 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
52 spectra |
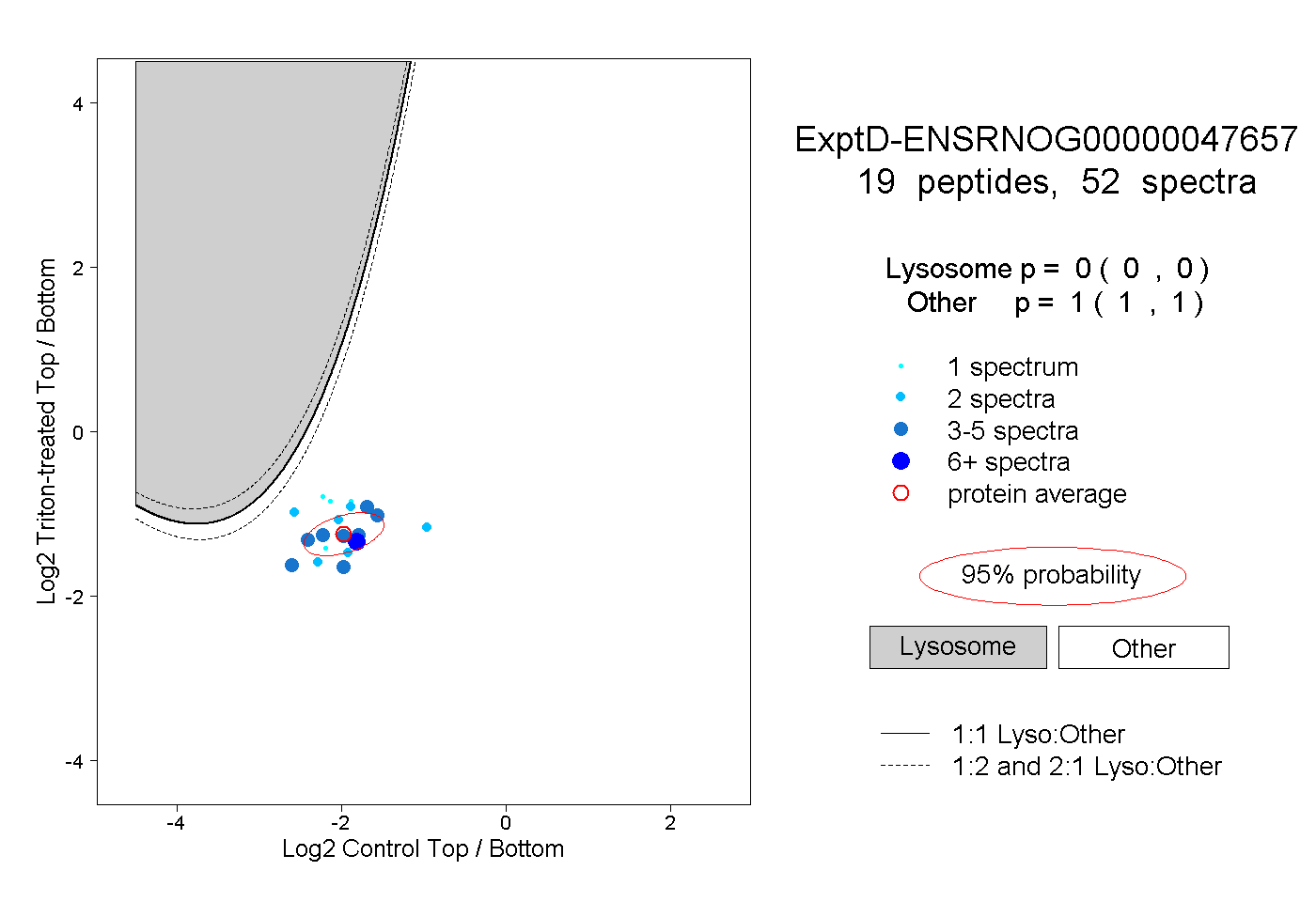 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |