peptides
spectra
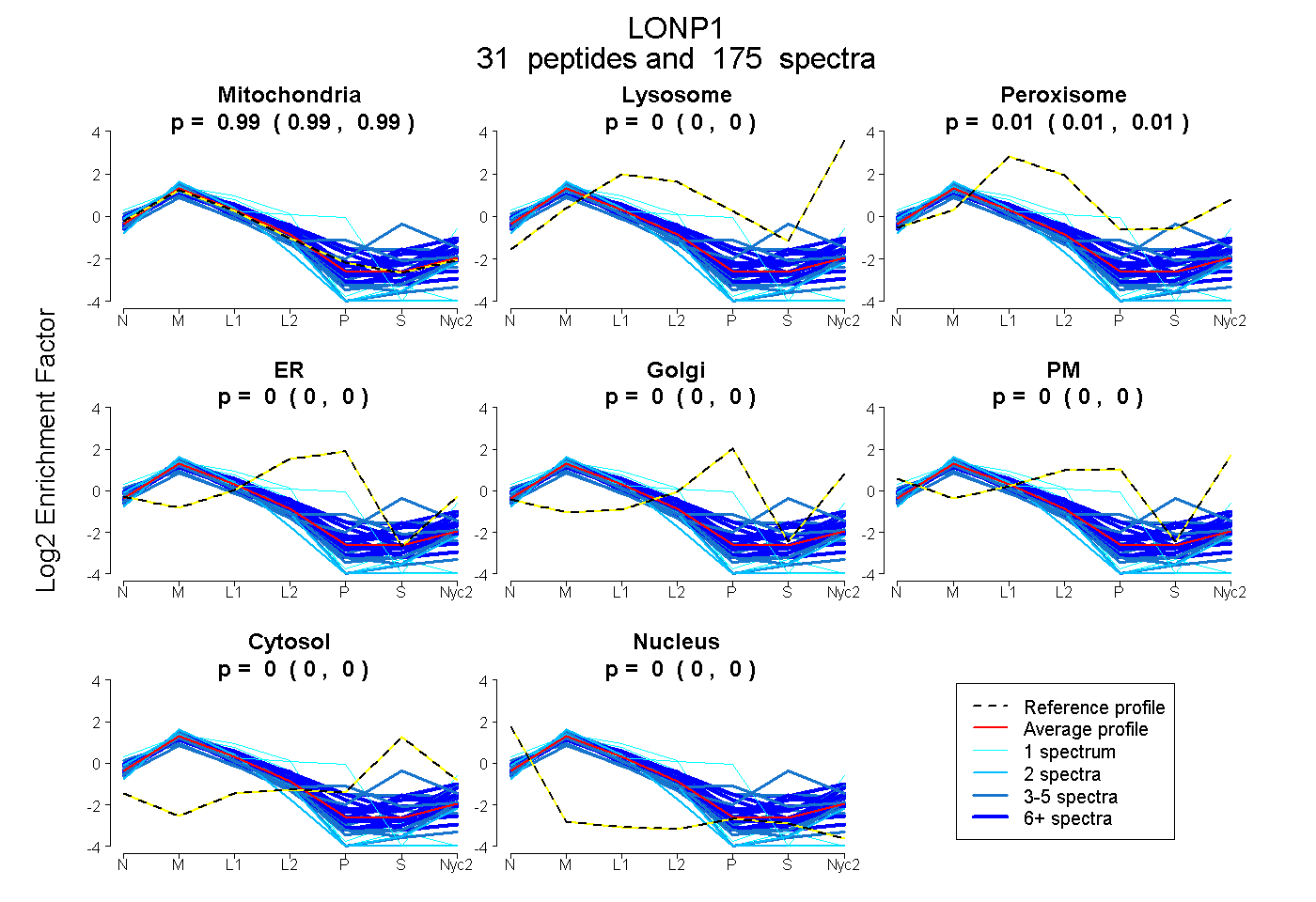
0.989 | 0.994
0.000 | 0.000
0.005 | 0.010
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
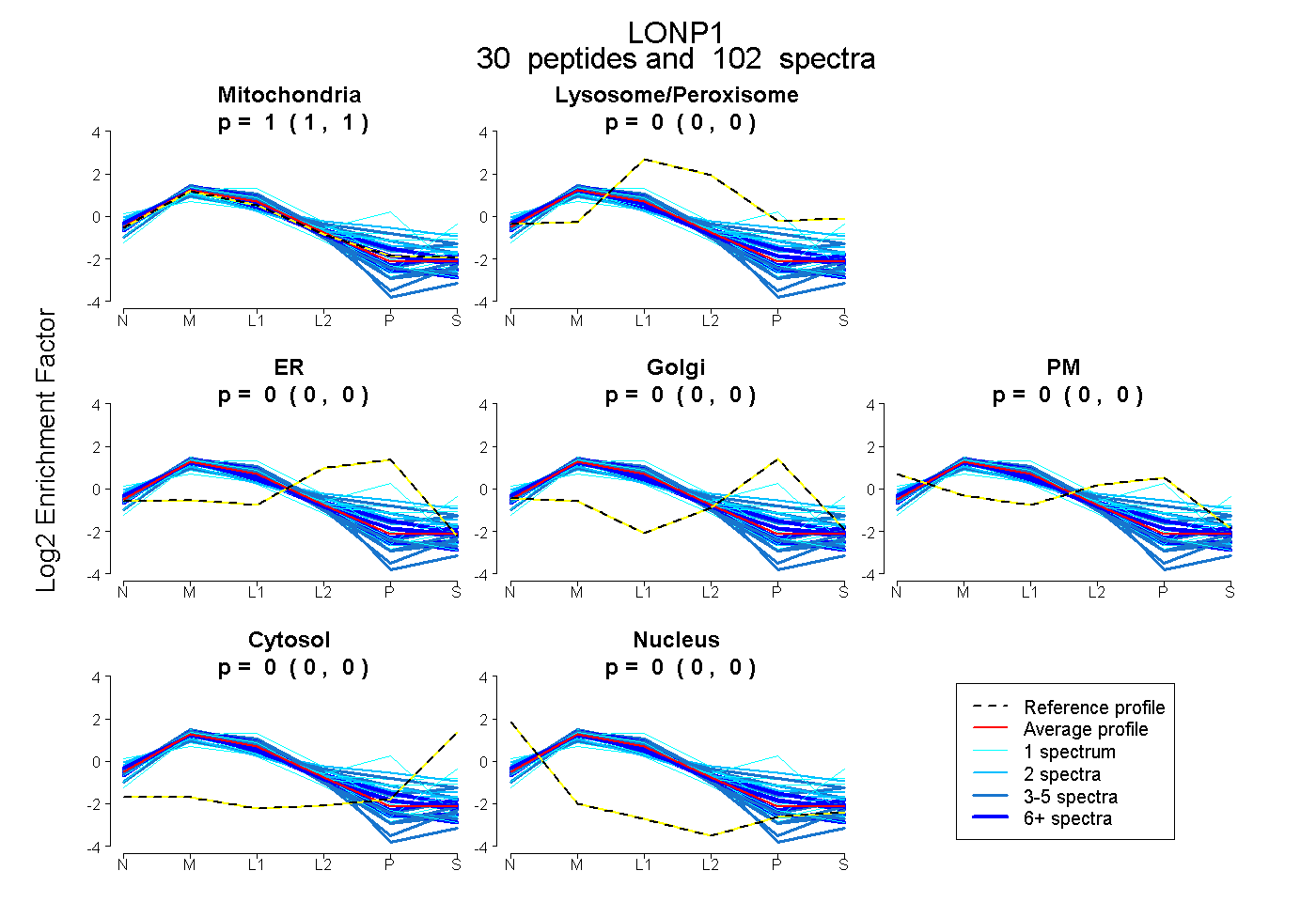
1.000 | 1.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
175 spectra |
 |
0.992 0.989 | 0.994 |
0.000 0.000 | 0.000 |
0.008 0.005 | 0.010 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
102 spectra |
 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, AQSVLEEDHYGMEDVK | 0.821 | 0.129 | 0.027 | 0.000 | 0.000 | 0.023 | 0.000 | |||
| 11 spectra, LVELIR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LALLDNHSSEFNVTR | 0.843 | 0.157 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, MIVTGHR | 0.725 | 0.062 | 0.000 | 0.000 | 0.000 | 0.213 | 0.000 | |||
| 1 spectrum, HVMDVVDEELSK | 0.976 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.024 | |||
| 1 spectrum, ESVLQMMQAGQR | 0.549 | 0.153 | 0.000 | 0.020 | 0.163 | 0.115 | 0.000 | |||
| 3 spectra, TLCGLDESK | 0.990 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.010 | |||
| 2 spectra, AQLSATVLTLLIK | 0.934 | 0.055 | 0.000 | 0.001 | 0.000 | 0.010 | 0.000 | |||
| 3 spectra, EHQEALAVER | 0.821 | 0.114 | 0.000 | 0.000 | 0.000 | 0.064 | 0.000 | |||
| 3 spectra, VLPVGGIK | 0.997 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.003 | |||
| 7 spectra, QSDENLDLAR | 0.996 | 0.000 | 0.000 | 0.004 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, QLEVEPEGLEPEAENK | 0.448 | 0.000 | 0.189 | 0.018 | 0.345 | 0.000 | 0.000 | |||
| 4 spectra, NPVFPR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, EFELSK | 0.999 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.001 | |||
| 3 spectra, ALTAEIVK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, YLVPQAR | 0.980 | 0.000 | 0.000 | 0.000 | 0.008 | 0.000 | 0.012 | |||
| 2 spectra, FSVGGMTDVAEIK | 0.507 | 0.254 | 0.000 | 0.202 | 0.000 | 0.037 | 0.000 | |||
| 2 spectra, RPQPSGSK | 0.753 | 0.000 | 0.000 | 0.000 | 0.247 | 0.000 | 0.000 | |||
| 7 spectra, ILCFHGPPGVGK | 0.901 | 0.065 | 0.034 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, YLLQEQLK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, IAFPLR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, IAYTFAR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, DIIALNPLYR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, AGVTCIILPAENR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, TYVGAMPGK | 0.727 | 0.123 | 0.000 | 0.068 | 0.000 | 0.082 | 0.000 | |||
| 2 spectra, LLQCLK | 0.985 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.015 | |||
| 3 spectra, ALSLLK | 0.774 | 0.112 | 0.040 | 0.000 | 0.074 | 0.000 | 0.000 | |||
| 4 spectra, LAQPYVGVFLK | 0.967 | 0.033 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, VLEFIAVSQLR | 0.989 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.011 | |||
| 3 spectra, MEMINVSGYVAQEK | 0.619 | 0.189 | 0.000 | 0.176 | 0.010 | 0.007 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
698 spectra |
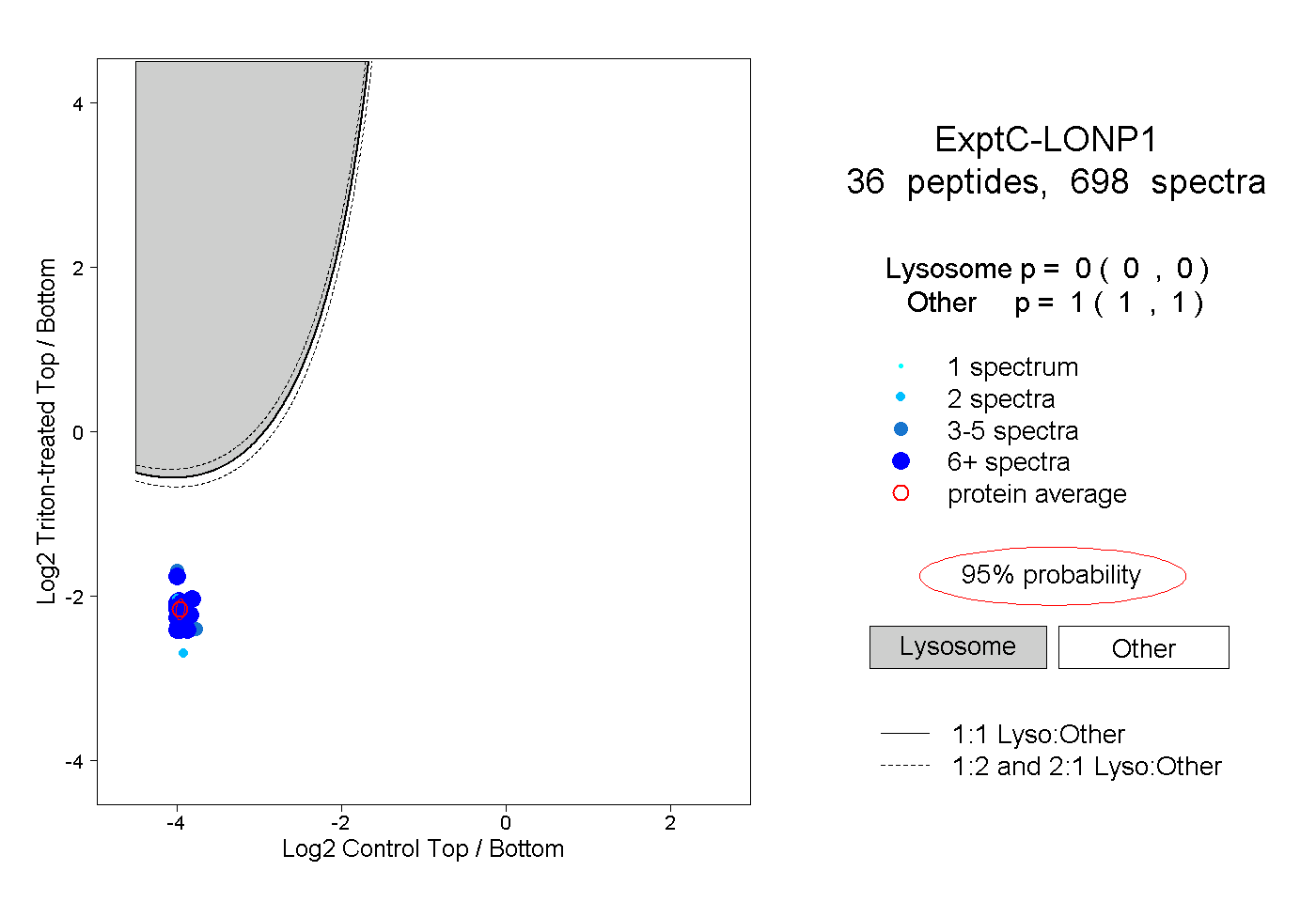 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
54 spectra |
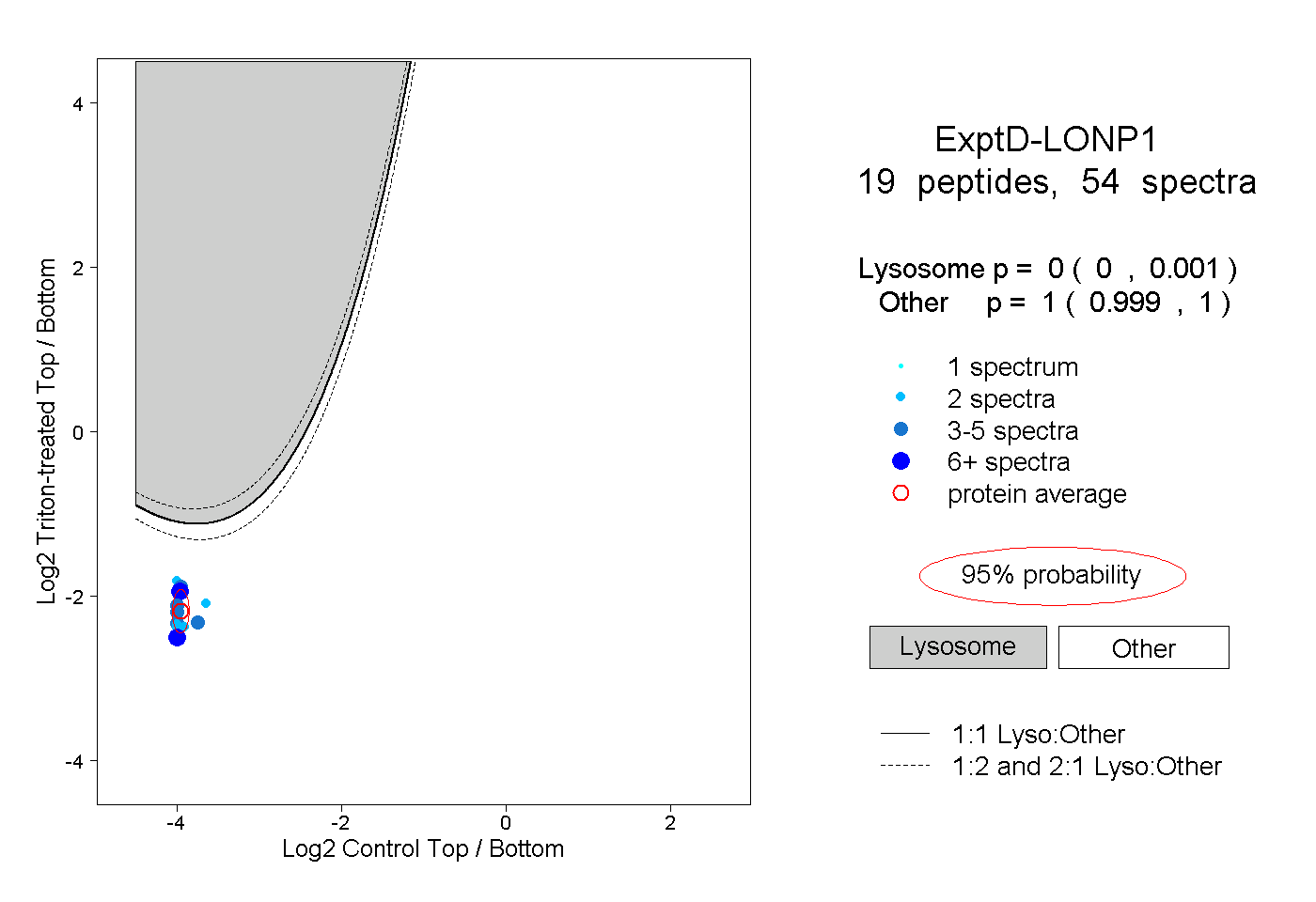 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |