peptides
spectra
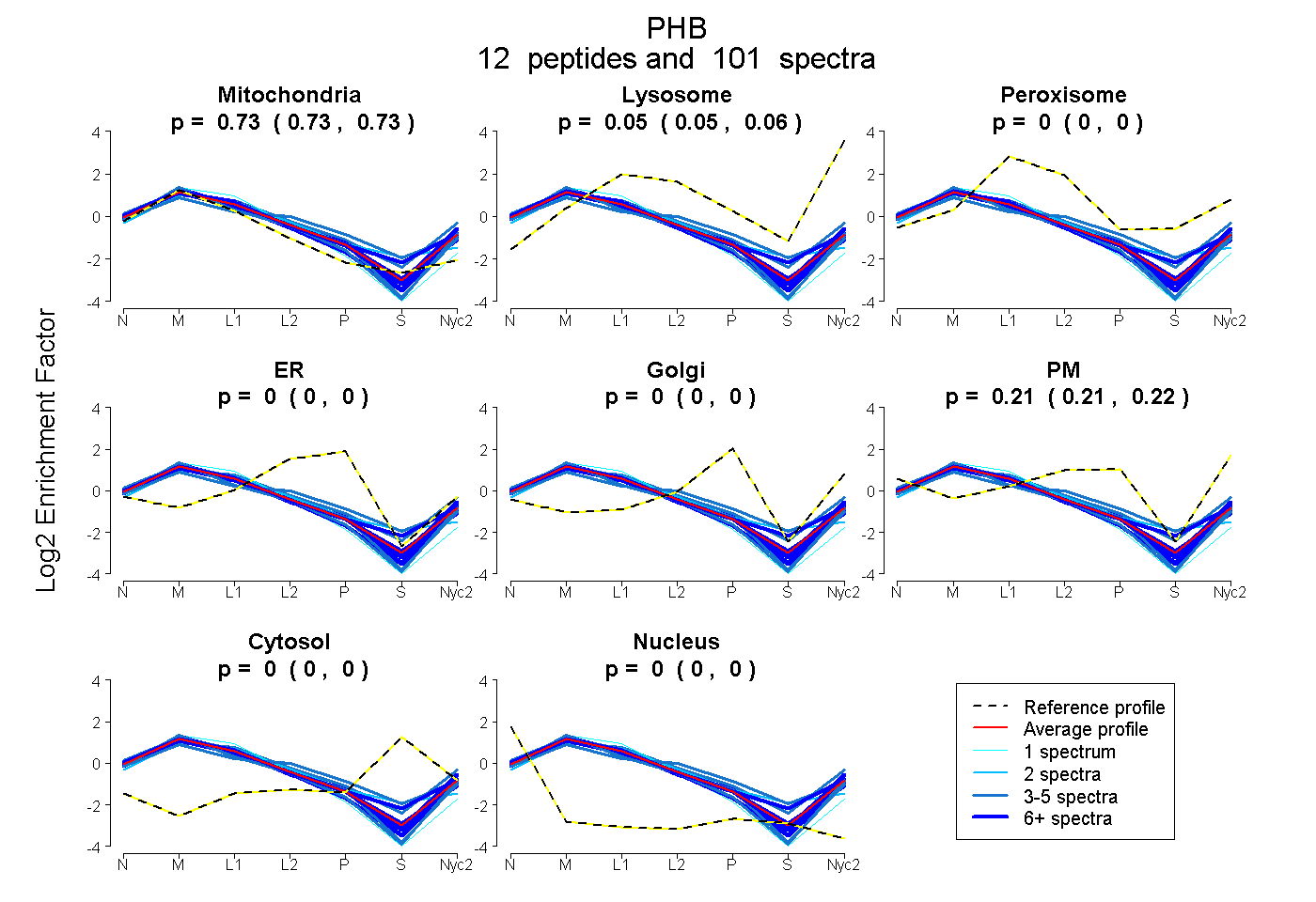
0.731 | 0.735
0.051 | 0.058
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.207 | 0.216
0.000 | 0.000
0.000 | 0.000
peptides
spectra
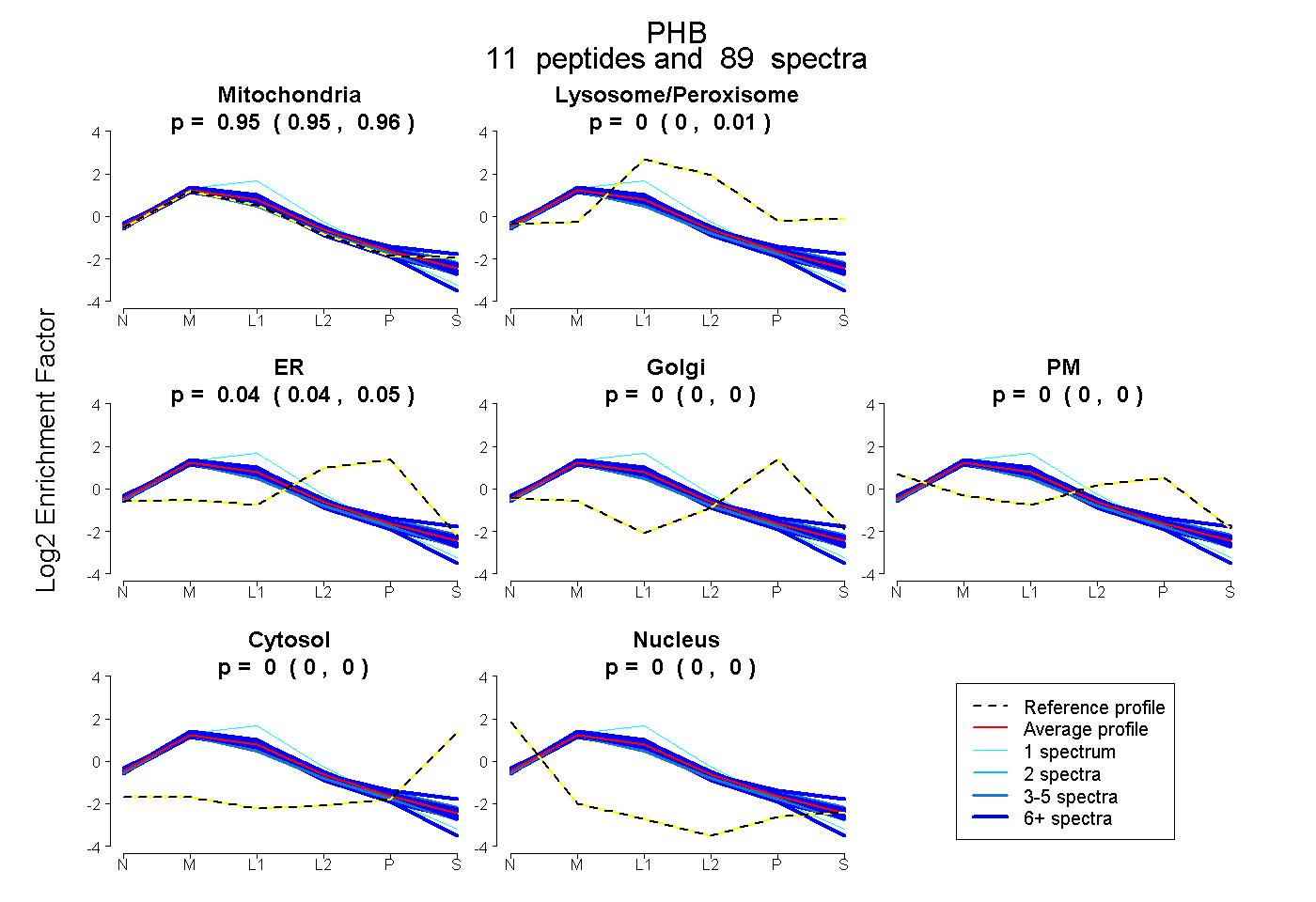
0.951 | 0.956
0.000 | 0.006
0.040 | 0.046
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
101 spectra |
 |
0.733 0.731 | 0.735 |
0.055 0.051 | 0.058 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.212 0.207 | 0.216 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
89 spectra |
 |
0.954 0.951 | 0.956 |
0.002 0.000 | 0.006 |
0.044 0.040 | 0.046 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 10 spectra, VLPSITTEILK | 0.924 | 0.000 | 0.076 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, EFTEAVEAK | 0.964 | 0.027 | 0.009 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, AATFGLILDDVSLTHLTFGK | 0.919 | 0.081 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, AVIFDR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, IYTSIGEDYDER | 0.931 | 0.032 | 0.037 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 18 spectra, QVSDDLTER | 0.923 | 0.035 | 0.027 | 0.000 | 0.016 | 0.000 | 0.000 | |||
| 19 spectra, DLQNVNITLR | 0.972 | 0.013 | 0.015 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, AAIISAEGDSK | 0.892 | 0.008 | 0.059 | 0.000 | 0.041 | 0.000 | 0.000 | |||
| 3 spectra, NVPVITGSK | 0.956 | 0.000 | 0.028 | 0.000 | 0.000 | 0.000 | 0.017 | |||
| 11 spectra, FDAGELITQR | 0.858 | 0.088 | 0.012 | 0.042 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, ILFRPVASQLPR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
540 spectra |
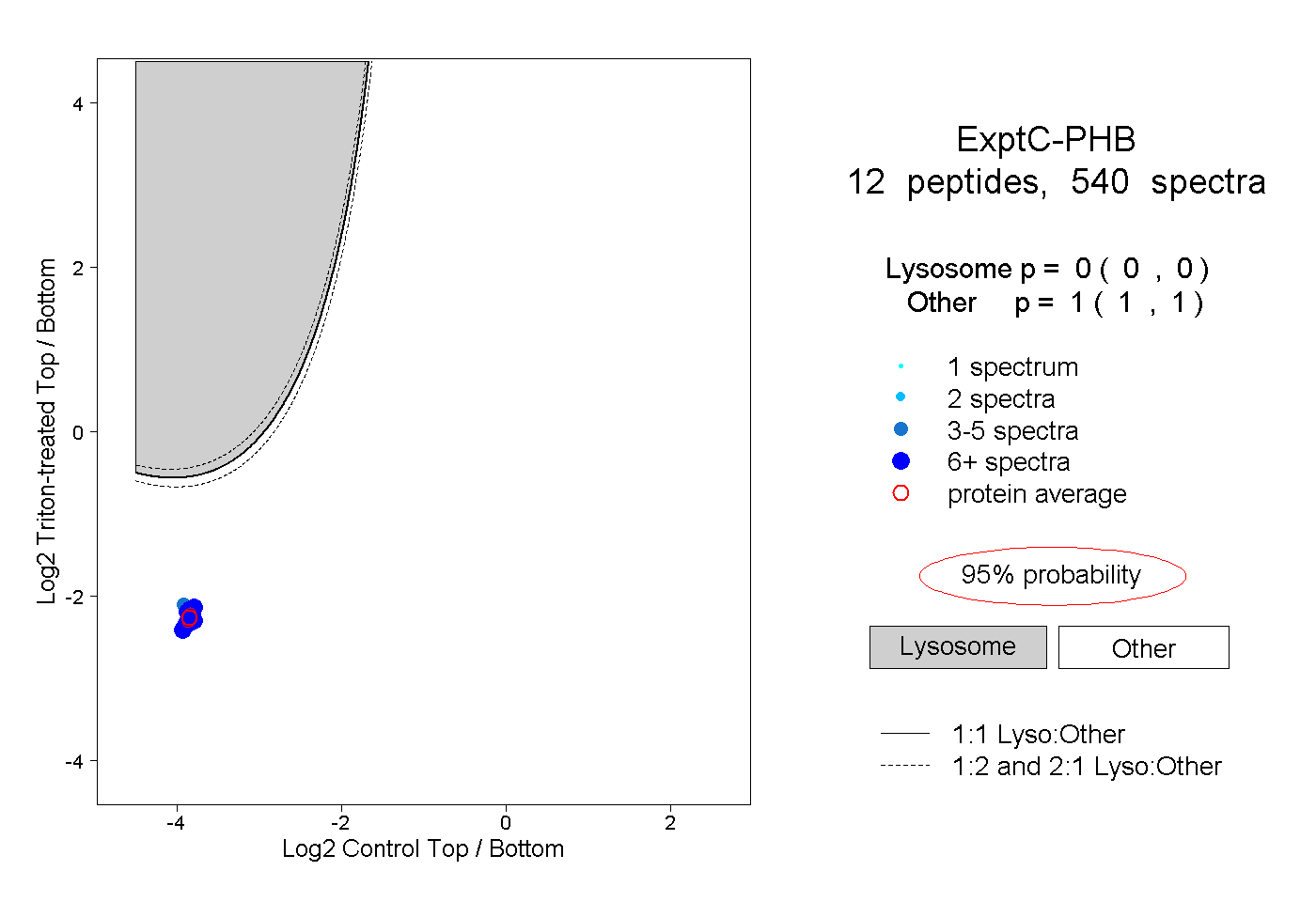 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
68 spectra |
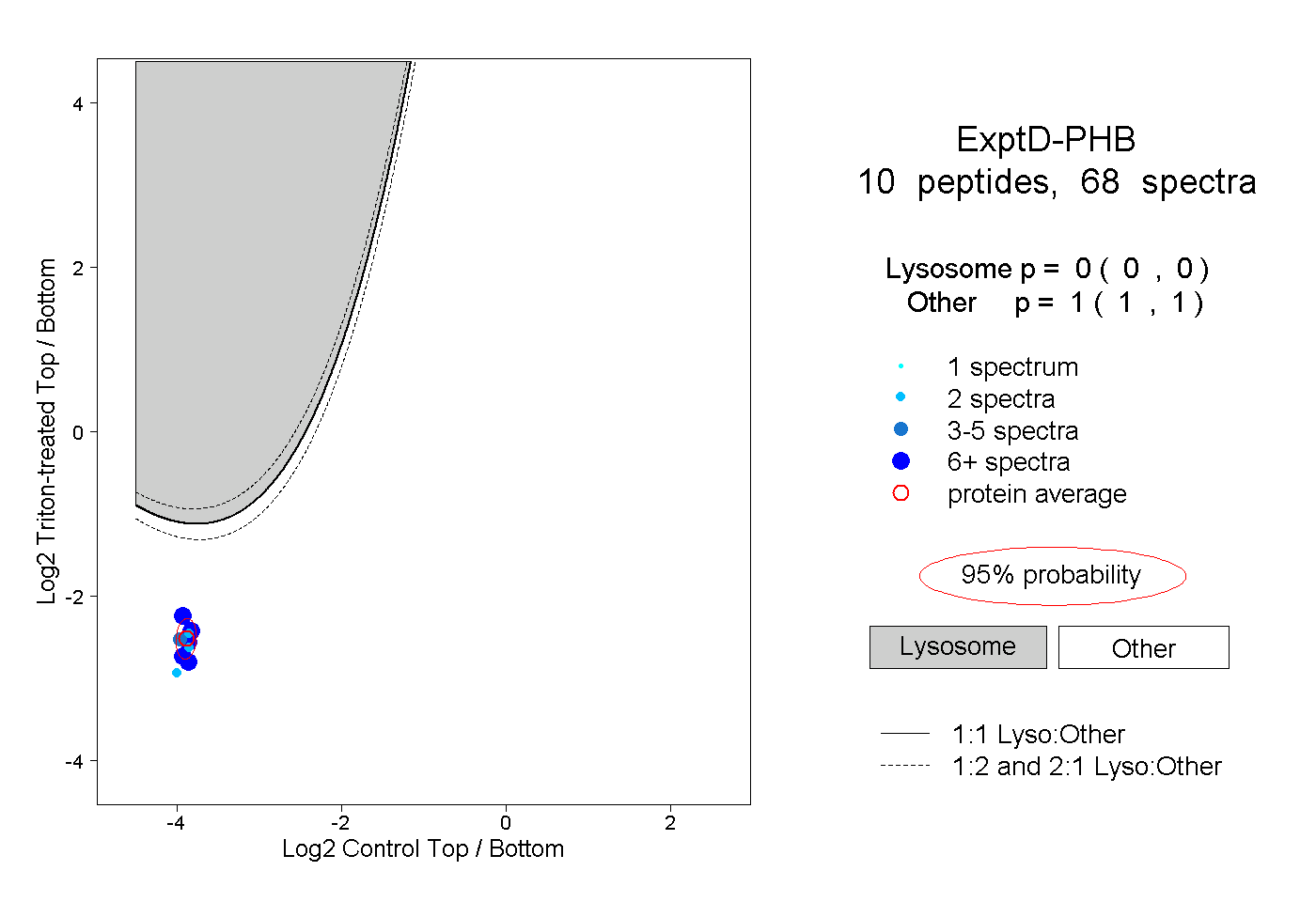 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |