peptides
spectra
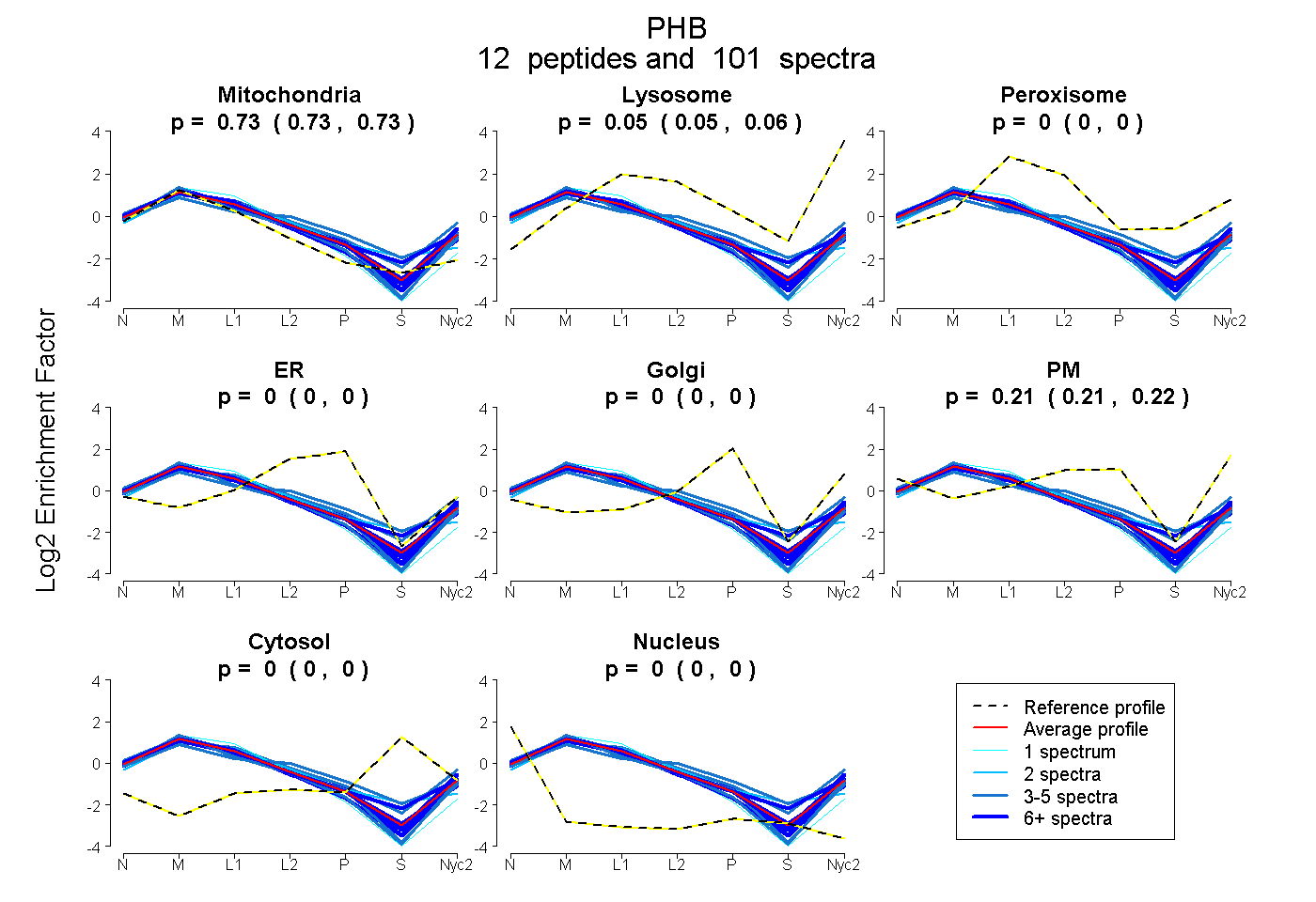
0.731 | 0.735
0.051 | 0.058
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.207 | 0.216
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
101 spectra |
 |
0.733 0.731 | 0.735 |
0.055 0.051 | 0.058 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.212 0.207 | 0.216 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 15 spectra, VLPSITTEILK | 0.708 | 0.068 | 0.000 | 0.000 | 0.000 | 0.225 | 0.000 | 0.000 | ||
| 1 spectrum, GVQDIVVGEGTHFLIPWVQKPIIFDCR | 0.895 | 0.000 | 0.000 | 0.067 | 0.000 | 0.038 | 0.000 | 0.000 | ||
| 2 spectra, EFTEAVEAK | 0.688 | 0.000 | 0.196 | 0.088 | 0.000 | 0.000 | 0.028 | 0.000 | ||
| 3 spectra, VFESIGK | 0.774 | 0.000 | 0.000 | 0.000 | 0.000 | 0.226 | 0.000 | 0.000 | ||
| 9 spectra, AVIFDR | 0.696 | 0.063 | 0.000 | 0.000 | 0.000 | 0.241 | 0.000 | 0.000 | ||
| 13 spectra, IYTSIGEDYDER | 0.798 | 0.032 | 0.000 | 0.000 | 0.000 | 0.171 | 0.000 | 0.000 | ||
| 5 spectra, LEAAEDIAYQLSR | 0.750 | 0.000 | 0.000 | 0.000 | 0.000 | 0.250 | 0.000 | 0.000 | ||
| 17 spectra, QVSDDLTER | 0.701 | 0.058 | 0.068 | 0.000 | 0.000 | 0.172 | 0.000 | 0.000 | ||
| 12 spectra, DLQNVNITLR | 0.765 | 0.017 | 0.005 | 0.000 | 0.000 | 0.212 | 0.000 | 0.000 | ||
| 4 spectra, AAIISAEGDSK | 0.620 | 0.123 | 0.045 | 0.000 | 0.000 | 0.212 | 0.000 | 0.000 | ||
| 5 spectra, NVPVITGSK | 0.579 | 0.000 | 0.123 | 0.100 | 0.032 | 0.134 | 0.032 | 0.000 | ||
| 15 spectra, FDAGELITQR | 0.728 | 0.009 | 0.000 | 0.000 | 0.000 | 0.263 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
89 spectra |
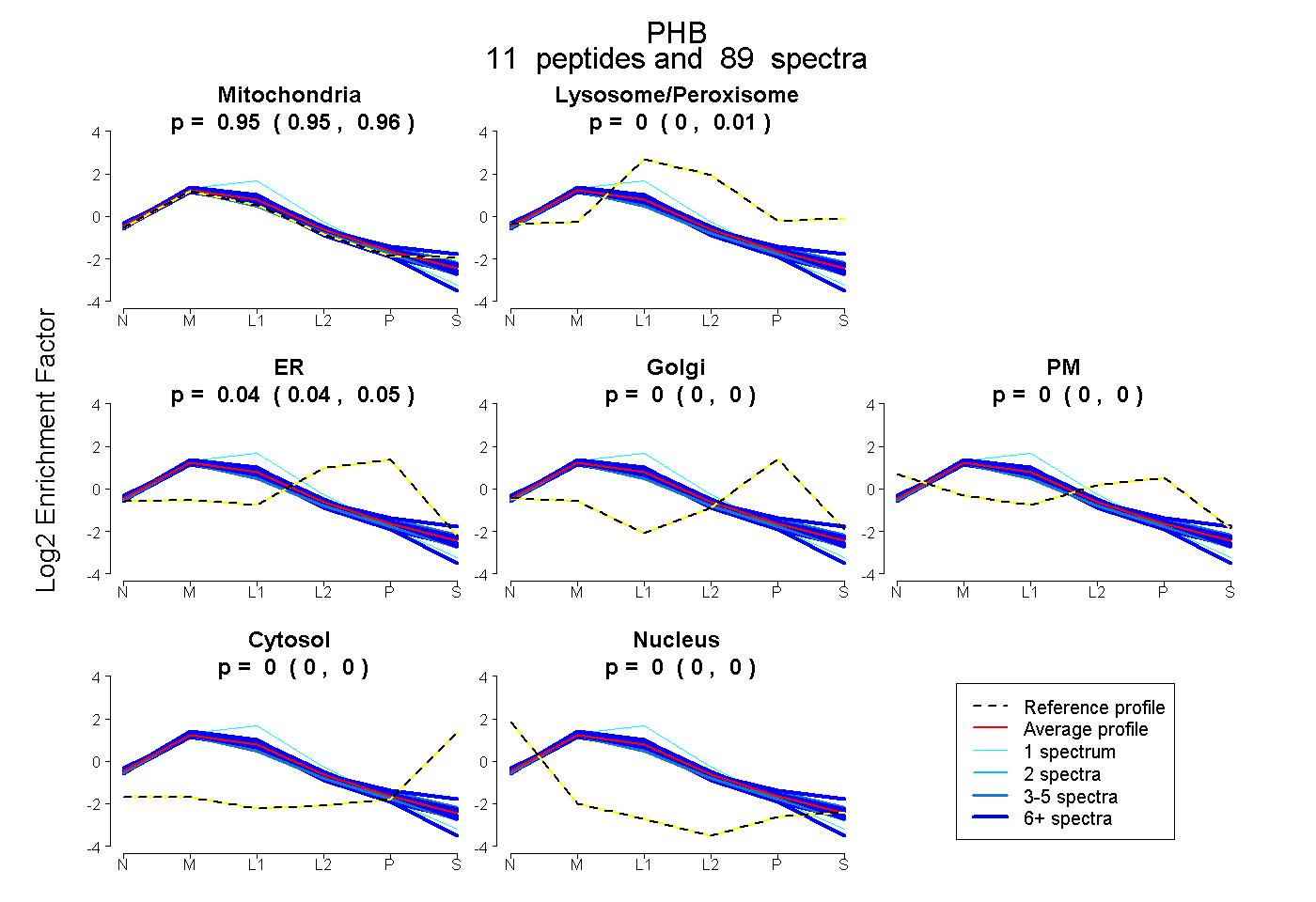 |
0.954 0.951 | 0.956 |
0.002 0.000 | 0.006 |
0.044 0.040 | 0.046 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
540 spectra |
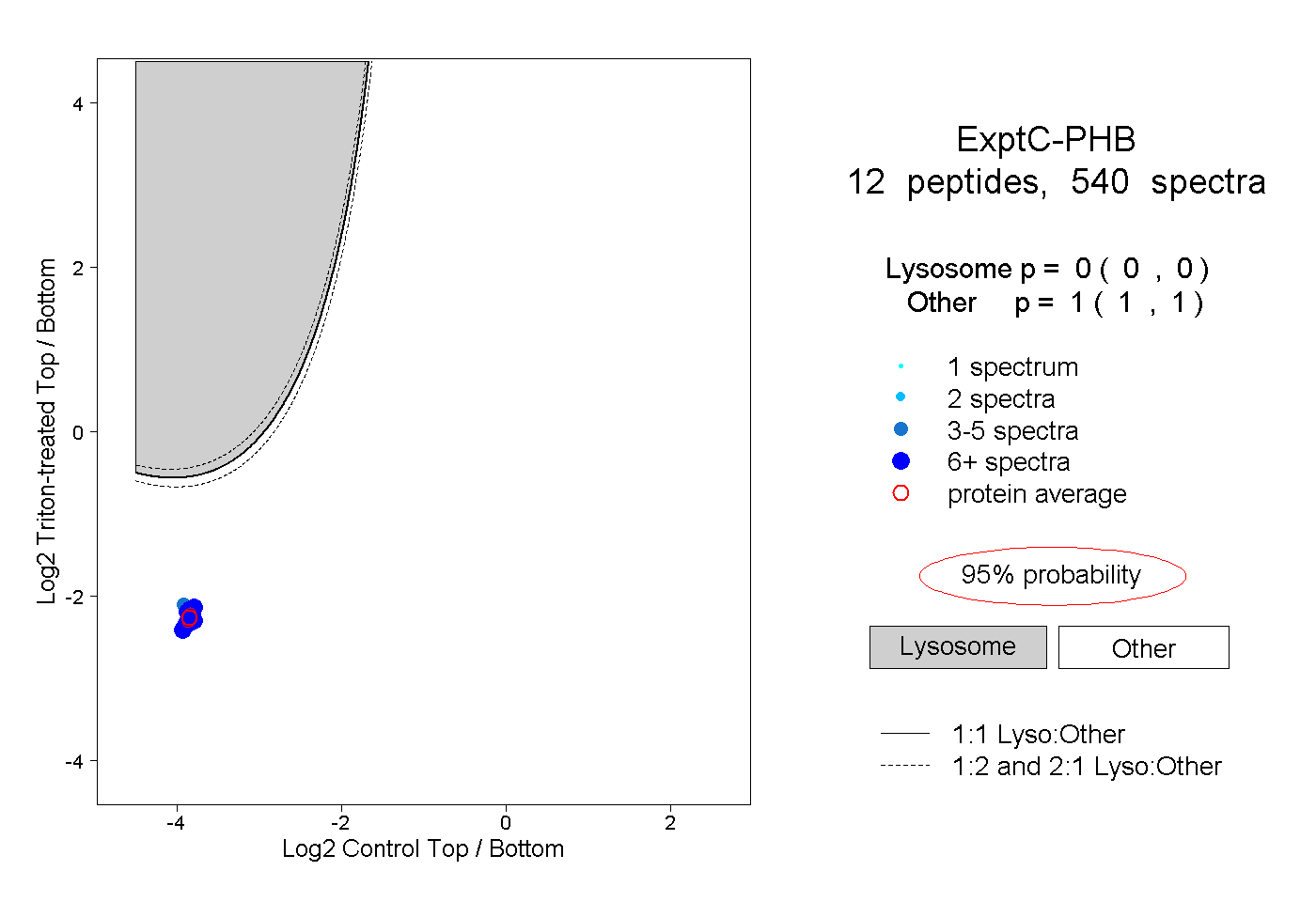 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
68 spectra |
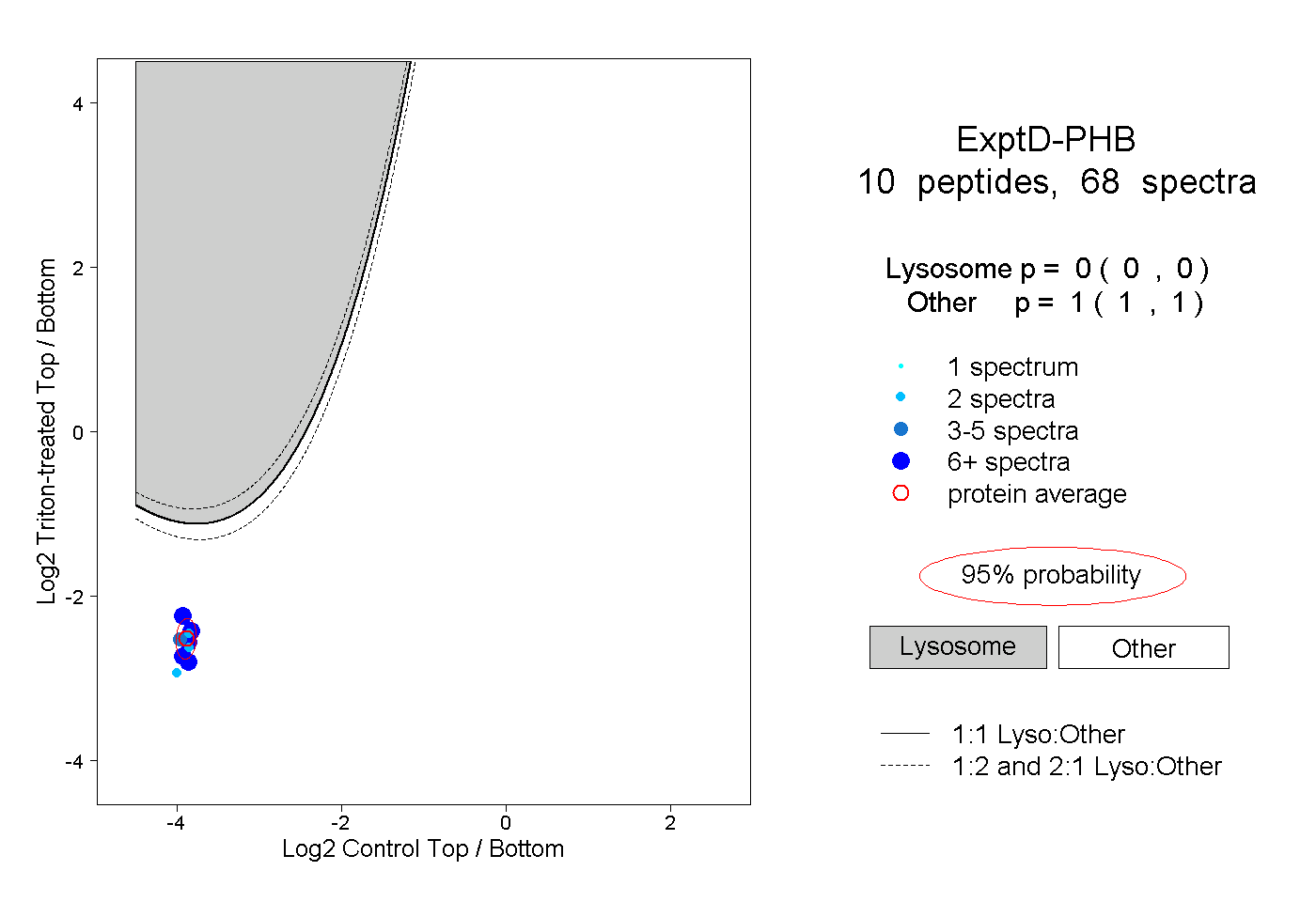 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |