peptides
spectra
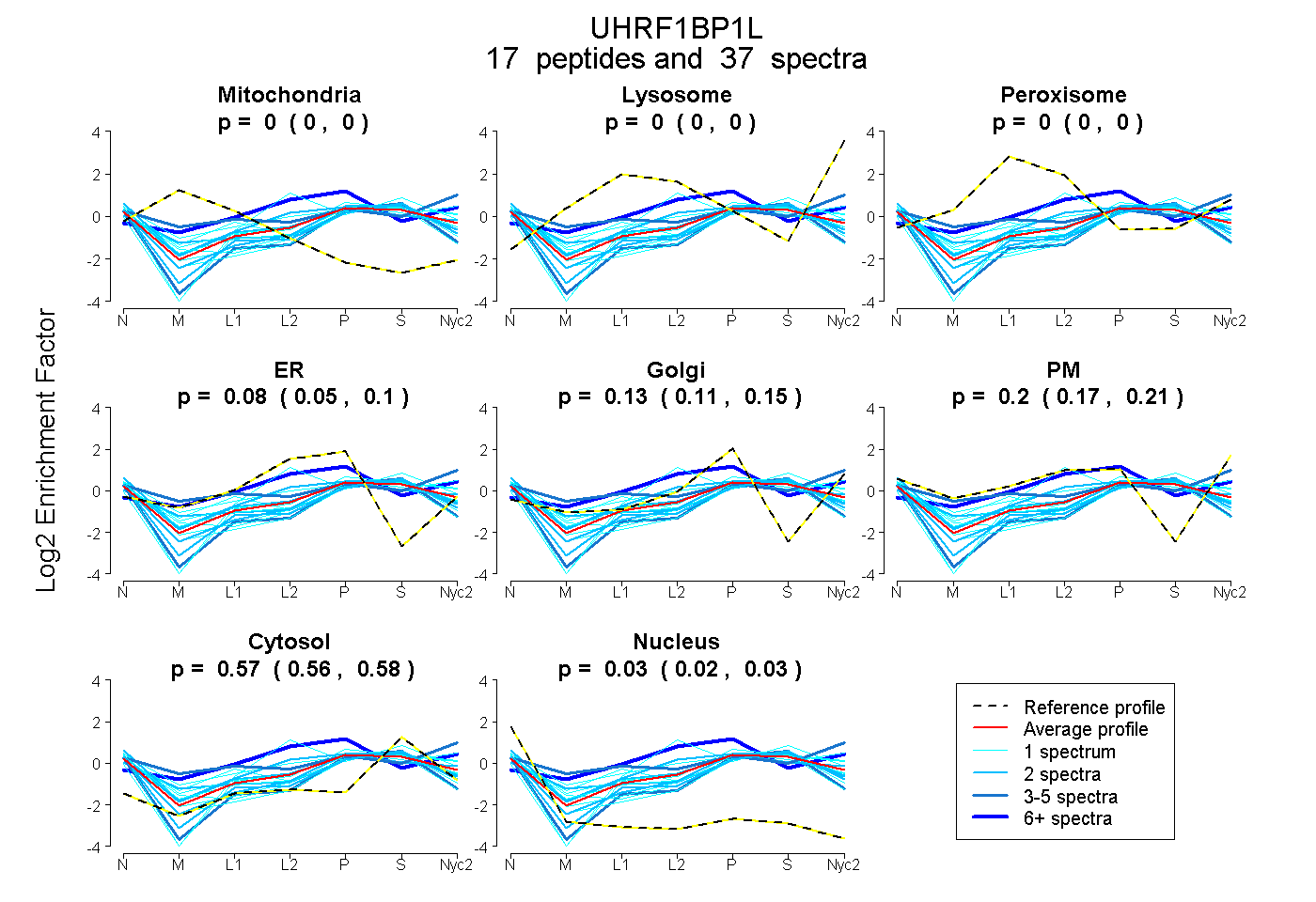
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.048 | 0.098
0.109 | 0.154
0.174 | 0.212
0.565 | 0.576
0.020 | 0.030
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
37 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.077 0.048 | 0.098 |
0.132 0.109 | 0.154 |
0.195 0.174 | 0.212 |
0.571 0.565 | 0.576 |
0.025 0.020 | 0.030 |
| 2 spectra, EINWQMIR | 0.027 | 0.000 | 0.029 | 0.000 | 0.196 | 0.133 | 0.580 | 0.036 | ||
| 2 spectra, SDEHVDIR | 0.000 | 0.000 | 0.000 | 0.034 | 0.224 | 0.000 | 0.650 | 0.092 | ||
| 4 spectra, QELAQAR | 0.000 | 0.064 | 0.056 | 0.000 | 0.000 | 0.495 | 0.386 | 0.000 | ||
| 2 spectra, NDDGSFHIR | 0.000 | 0.000 | 0.000 | 0.165 | 0.000 | 0.336 | 0.478 | 0.021 | ||
| 1 spectrum, LFNDFDVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.209 | 0.170 | 0.560 | 0.062 | ||
| 1 spectrum, LITNQSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.257 | 0.000 | 0.616 | 0.127 | ||
| 1 spectrum, LALGQLQRP | 0.000 | 0.000 | 0.000 | 0.000 | 0.330 | 0.047 | 0.618 | 0.004 | ||
| 1 spectrum, FVIPSEVKPGCHR | 0.000 | 0.000 | 0.020 | 0.320 | 0.000 | 0.000 | 0.660 | 0.000 | ||
| 1 spectrum, AMVQYAK | 0.000 | 0.000 | 0.177 | 0.000 | 0.296 | 0.000 | 0.489 | 0.038 | ||
| 2 spectra, GTCDVR | 0.000 | 0.000 | 0.000 | 0.204 | 0.000 | 0.187 | 0.565 | 0.044 | ||
| 1 spectrum, HAHEQDTK | 0.000 | 0.000 | 0.000 | 0.124 | 0.058 | 0.262 | 0.503 | 0.053 | ||
| 4 spectra, EQLMEENECLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.203 | 0.000 | 0.651 | 0.145 | ||
| 1 spectrum, SCDSFNLLHPIFQR | 0.000 | 0.000 | 0.000 | 0.054 | 0.162 | 0.169 | 0.545 | 0.070 | ||
| 10 spectra, AGIIK | 0.000 | 0.060 | 0.207 | 0.204 | 0.272 | 0.017 | 0.238 | 0.000 | ||
| 1 spectrum, MHEVYK | 0.000 | 0.000 | 0.032 | 0.000 | 0.000 | 0.518 | 0.450 | 0.000 | ||
| 1 spectrum, HSDLEALFQDFK | 0.000 | 0.000 | 0.000 | 0.115 | 0.187 | 0.000 | 0.551 | 0.147 | ||
| 2 spectra, SSPEISLR | 0.000 | 0.000 | 0.000 | 0.017 | 0.333 | 0.000 | 0.586 | 0.063 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
4 spectra |
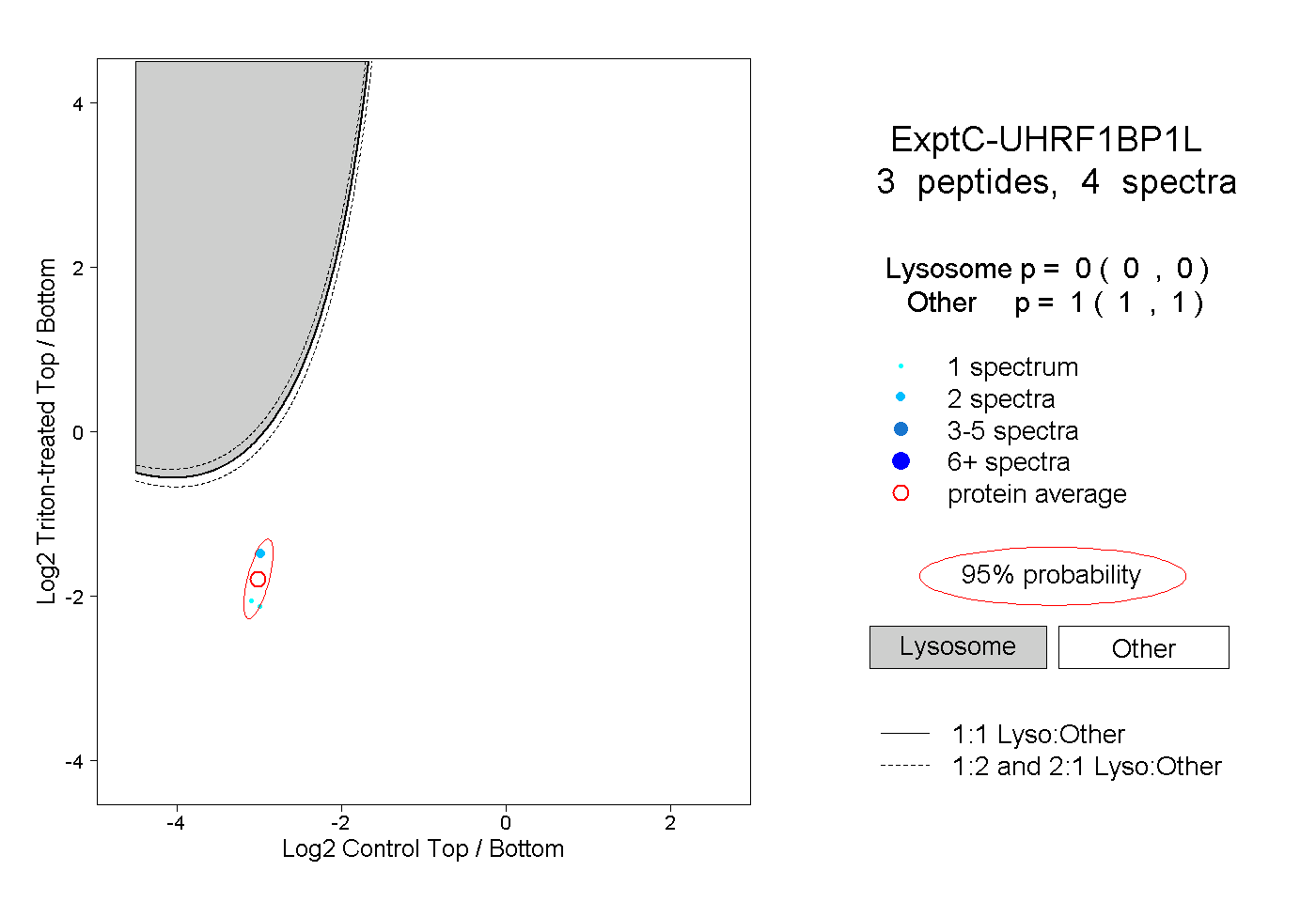 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |