peptides
spectra
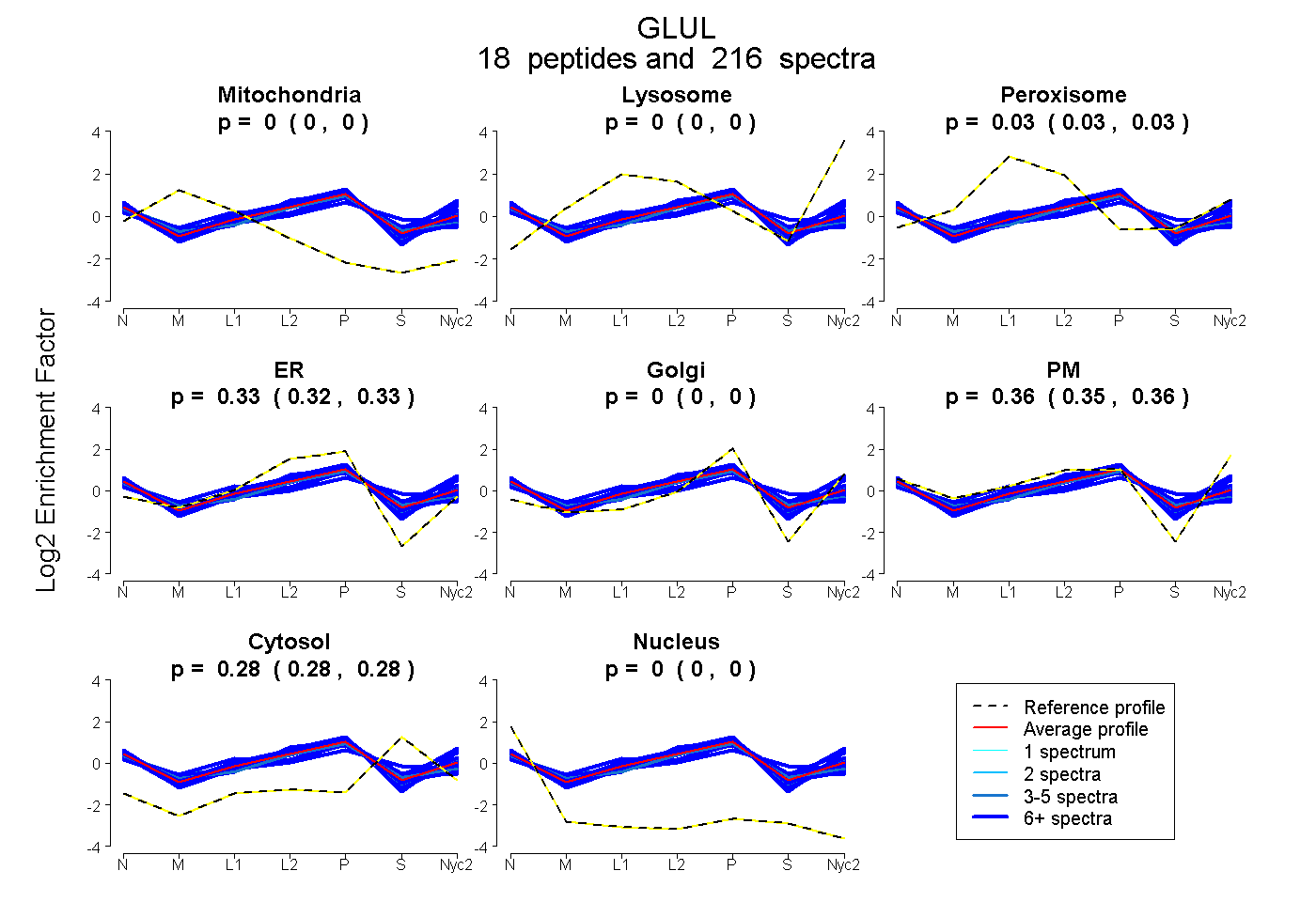
0.000 | 0.000
0.000 | 0.000
0.030 | 0.033
0.322 | 0.329
0.000 | 0.000
0.353 | 0.362
0.281 | 0.284
0.001 | 0.004
peptides
spectra
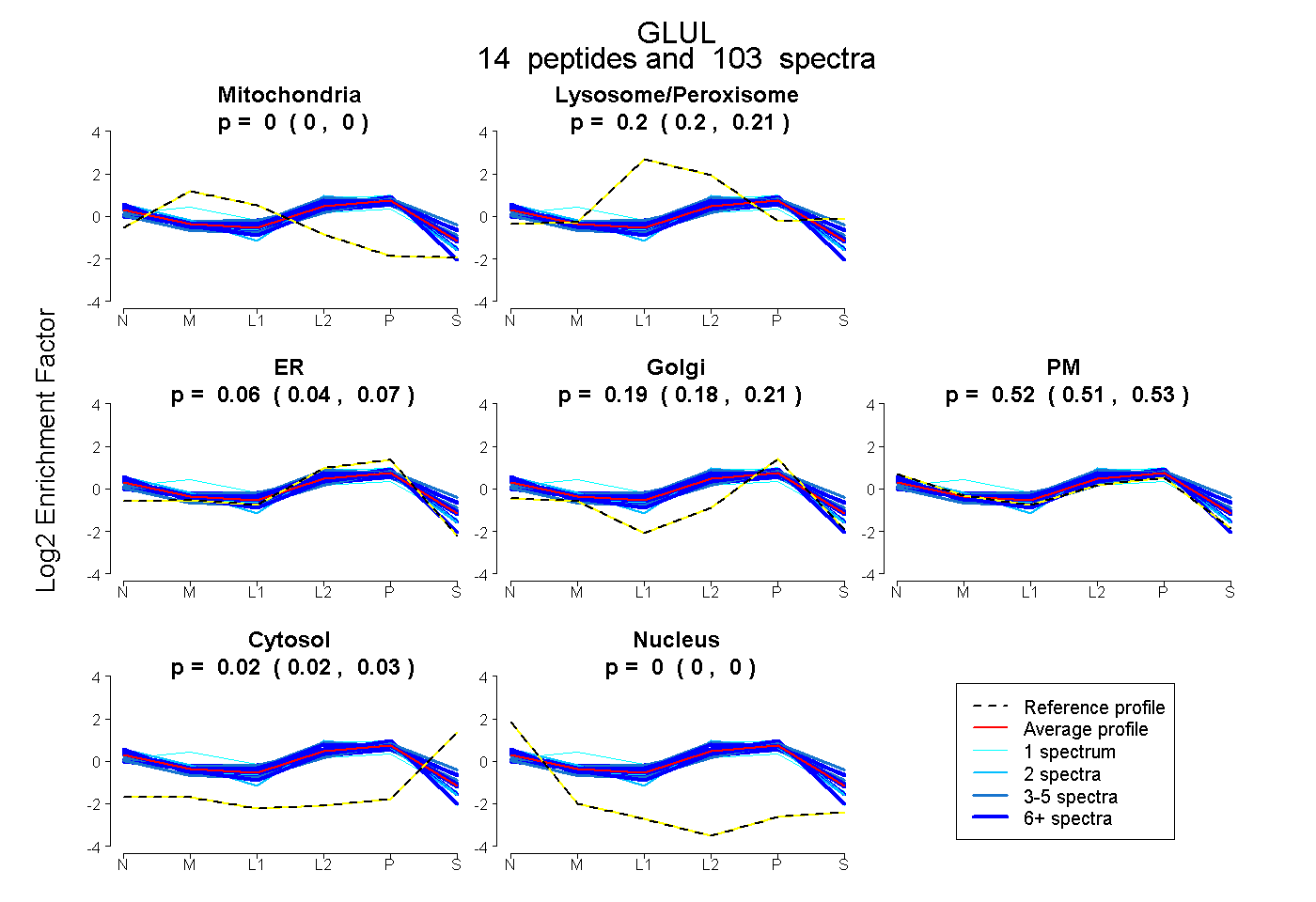
0.000 | 0.000
0.195 | 0.210
0.042 | 0.069
0.178 | 0.206
0.513 | 0.531
0.020 | 0.027
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
216 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.031 0.030 | 0.033 |
0.326 0.322 | 0.329 |
0.000 0.000 | 0.000 |
0.358 0.353 | 0.362 |
0.282 0.281 | 0.284 |
0.002 0.001 | 0.004 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
103 spectra |
 |
0.000 0.000 | 0.000 |
0.203 0.195 | 0.210 |
0.057 0.042 | 0.069 |
0.193 0.178 | 0.206 |
0.523 0.513 | 0.531 |
0.024 0.020 | 0.027 |
0.000 0.000 | 0.000 |
| 9 spectra, GGLDNAR | 0.000 | 0.100 | 0.101 | 0.165 | 0.634 | 0.000 | 0.000 | |||
| 1 spectrum, ATSASSHLNK | 0.195 | 0.180 | 0.017 | 0.171 | 0.438 | 0.000 | 0.000 | |||
| 3 spectra, ACLYAGIK | 0.000 | 0.161 | 0.000 | 0.069 | 0.674 | 0.096 | 0.000 | |||
| 3 spectra, QMYMNLPQGEK | 0.000 | 0.271 | 0.000 | 0.397 | 0.208 | 0.124 | 0.000 | |||
| 9 spectra, LVFCEVFK | 0.000 | 0.168 | 0.143 | 0.000 | 0.667 | 0.022 | 0.000 | |||
| 1 spectrum, GYFEDR | 0.000 | 0.090 | 0.259 | 0.080 | 0.571 | 0.000 | 0.000 | |||
| 6 spectra, KPAETNLR | 0.000 | 0.031 | 0.309 | 0.000 | 0.661 | 0.000 | 0.000 | |||
| 3 spectra, LTGFHETSNINDFSAGVANR | 0.000 | 0.236 | 0.255 | 0.057 | 0.405 | 0.047 | 0.000 | |||
| 2 spectra, HQYHIR | 0.000 | 0.012 | 0.254 | 0.000 | 0.735 | 0.000 | 0.000 | |||
| 24 spectra, MGDHLWVAR | 0.000 | 0.352 | 0.000 | 0.362 | 0.242 | 0.045 | 0.000 | |||
| 16 spectra, RPSANCDPYAVTEAIVR | 0.000 | 0.122 | 0.067 | 0.174 | 0.575 | 0.063 | 0.000 | |||
| 3 spectra, EENGLR | 0.000 | 0.281 | 0.021 | 0.241 | 0.457 | 0.000 | 0.000 | |||
| 22 spectra, DIVEAHYR | 0.000 | 0.332 | 0.000 | 0.272 | 0.307 | 0.089 | 0.000 | |||
| 1 spectrum, CIEEAIDK | 0.000 | 0.016 | 0.378 | 0.000 | 0.606 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
385 spectra |
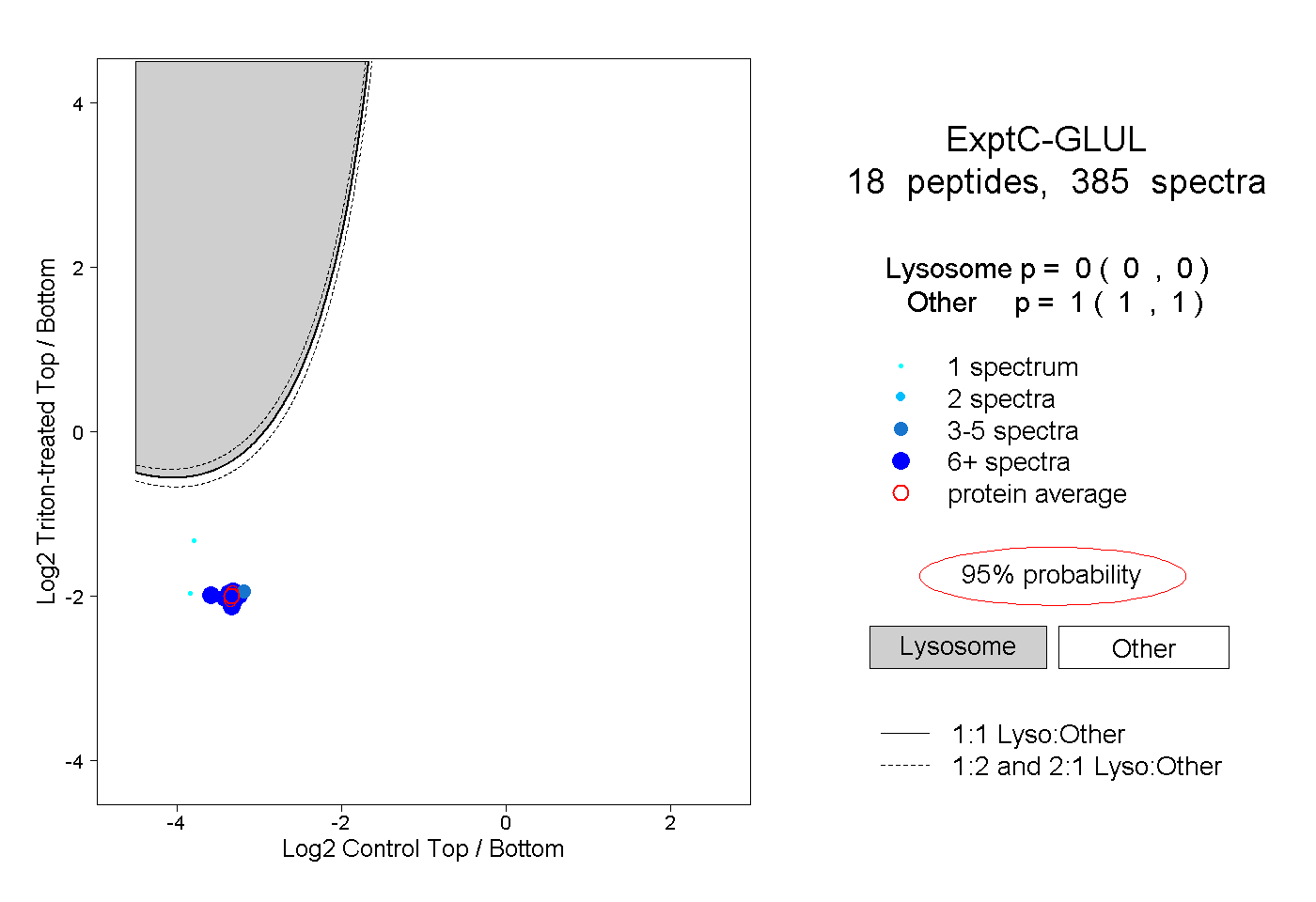 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
31 spectra |
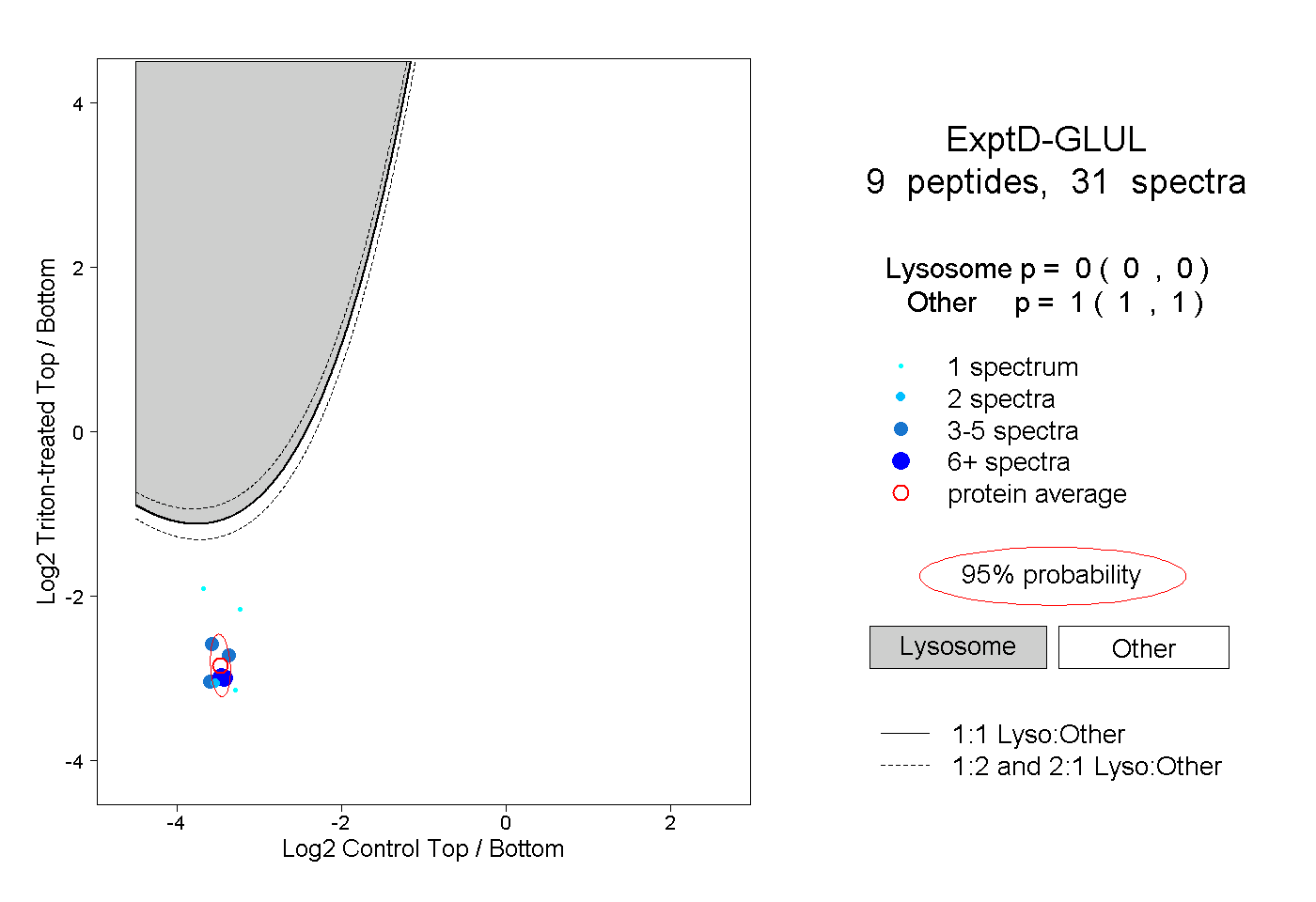 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |