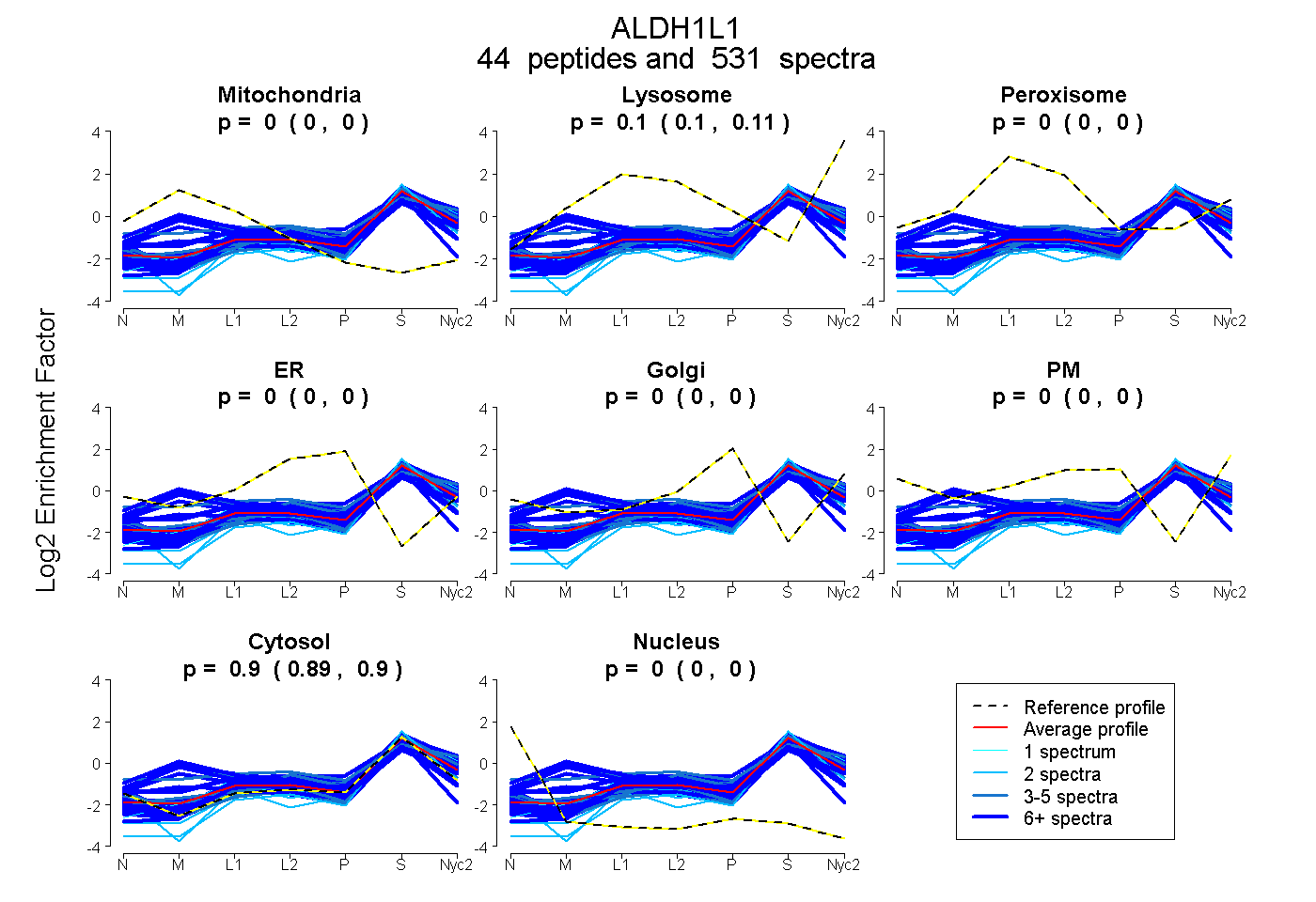
peptides
spectra
0.000 | 0.000
0.104 | 0.105
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.894 | 0.896
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
531 spectra |
 |
0.000 0.000 | 0.000 |
0.105 0.104 | 0.105 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.895 0.894 | 0.896 |
0.000 0.000 | 0.000 |
| 3 spectra, TVTFEY | 0.045 | 0.183 | 0.095 | 0.000 | 0.000 | 0.049 | 0.629 | 0.000 | ||
| 35 spectra, AVQMGMSSVFFNK | 0.000 | 0.105 | 0.000 | 0.000 | 0.000 | 0.000 | 0.895 | 0.000 | ||
| 8 spectra, CPQSEEGATYEGIQK | 0.000 | 0.146 | 0.000 | 0.000 | 0.042 | 0.000 | 0.813 | 0.000 | ||
| 13 spectra, EESFGPIMIISR | 0.000 | 0.055 | 0.000 | 0.000 | 0.000 | 0.000 | 0.945 | 0.000 | ||
| 19 spectra, FADGDVDAVLSR | 0.000 | 0.076 | 0.000 | 0.000 | 0.000 | 0.000 | 0.924 | 0.000 | ||
| 20 spectra, NIQLEDGK | 0.029 | 0.163 | 0.044 | 0.000 | 0.000 | 0.000 | 0.764 | 0.000 | ||
| 9 spectra, GQALPEVVAK | 0.011 | 0.251 | 0.000 | 0.000 | 0.000 | 0.000 | 0.737 | 0.000 | ||
| 32 spectra, IQGATIPINQARPNR | 0.000 | 0.101 | 0.000 | 0.000 | 0.000 | 0.000 | 0.899 | 0.000 | ||
| 4 spectra, NLTLTK | 0.000 | 0.128 | 0.000 | 0.000 | 0.000 | 0.000 | 0.872 | 0.000 | ||
| 34 spectra, LIAEGTAPR | 0.000 | 0.099 | 0.000 | 0.000 | 0.000 | 0.000 | 0.901 | 0.000 | ||
| 7 spectra, DLGEAALNEYLR | 0.000 | 0.149 | 0.000 | 0.000 | 0.000 | 0.000 | 0.851 | 0.000 | ||
| 6 spectra, ILPNVPEVEDSTDFFK | 0.000 | 0.086 | 0.000 | 0.000 | 0.000 | 0.000 | 0.914 | 0.000 | ||
| 8 spectra, DGVPVFK | 0.000 | 0.071 | 0.000 | 0.000 | 0.000 | 0.000 | 0.929 | 0.000 | ||
| 64 spectra, GMVQAVR | 0.000 | 0.075 | 0.000 | 0.000 | 0.000 | 0.000 | 0.925 | 0.000 | ||
| 1 spectrum, LQAGTVFINTYNK | 0.000 | 0.118 | 0.000 | 0.000 | 0.000 | 0.000 | 0.882 | 0.000 | ||
| 3 spectra, IAVIGQSLFGQEVYCQLR | 0.251 | 0.123 | 0.014 | 0.000 | 0.000 | 0.000 | 0.612 | 0.000 | ||
| 5 spectra, GVVNILPGSGSLVGQR | 0.000 | 0.124 | 0.000 | 0.000 | 0.020 | 0.000 | 0.856 | 0.000 | ||
| 16 spectra, LSDHPDVR | 0.000 | 0.104 | 0.000 | 0.000 | 0.000 | 0.000 | 0.896 | 0.000 | ||
| 5 spectra, IGFTGSTEVGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 11 spectra, FAELTLK | 0.000 | 0.066 | 0.000 | 0.000 | 0.000 | 0.000 | 0.934 | 0.000 | ||
| 16 spectra, MMPASQFFK | 0.000 | 0.183 | 0.000 | 0.000 | 0.000 | 0.000 | 0.817 | 0.000 | ||
| 7 spectra, FLFPEGIK | 0.284 | 0.084 | 0.000 | 0.000 | 0.000 | 0.000 | 0.632 | 0.000 | ||
| 11 spectra, SPLIIFADCDLNK | 0.000 | 0.000 | 0.050 | 0.000 | 0.000 | 0.000 | 0.950 | 0.000 | ||
| 24 spectra, GFIQLLVR | 0.000 | 0.024 | 0.000 | 0.000 | 0.000 | 0.000 | 0.976 | 0.000 | ||
| 18 spectra, THVGMSIQTFR | 0.000 | 0.073 | 0.000 | 0.000 | 0.000 | 0.000 | 0.927 | 0.000 | ||
| 5 spectra, ECEVLPDDTVSTLYNR | 0.000 | 0.000 | 0.059 | 0.004 | 0.000 | 0.000 | 0.937 | 0.000 | ||
| 2 spectra, GEDDESECVINYVEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.965 | 0.035 | ||
| 7 spectra, VSLELGGK | 0.316 | 0.115 | 0.025 | 0.000 | 0.000 | 0.000 | 0.545 | 0.000 | ||
| 18 spectra, GENCIAAGR | 0.308 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.692 | 0.000 | ||
| 2 spectra, GSASSDLELTEAELATAEAVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 9 spectra, ADPLGLEAEK | 0.000 | 0.109 | 0.000 | 0.000 | 0.000 | 0.000 | 0.891 | 0.000 | ||
| 3 spectra, TDVAAPFGGFK | 0.000 | 0.107 | 0.000 | 0.000 | 0.000 | 0.000 | 0.893 | 0.000 | ||
| 12 spectra, QSGFGK | 0.226 | 0.197 | 0.006 | 0.000 | 0.000 | 0.000 | 0.571 | 0.000 | ||
| 10 spectra, GASAINWTLIHGDK | 0.000 | 0.137 | 0.000 | 0.000 | 0.000 | 0.000 | 0.863 | 0.000 | ||
| 12 spectra, INWDQPAEAIHNWIR | 0.000 | 0.125 | 0.000 | 0.000 | 0.000 | 0.000 | 0.875 | 0.000 | ||
| 2 spectra, HGSIIYHPSLLPR | 0.000 | 0.073 | 0.000 | 0.000 | 0.000 | 0.000 | 0.927 | 0.000 | ||
| 11 spectra, LVEEVK | 0.000 | 0.014 | 0.000 | 0.000 | 0.000 | 0.000 | 0.986 | 0.000 | ||
| 6 spectra, SCALSNVK | 0.163 | 0.002 | 0.022 | 0.000 | 0.000 | 0.000 | 0.813 | 0.000 | ||
| 22 spectra, AGLILFGNDDR | 0.000 | 0.070 | 0.000 | 0.000 | 0.000 | 0.000 | 0.930 | 0.000 | ||
| 8 spectra, YFAGWCDK | 0.286 | 0.023 | 0.060 | 0.000 | 0.000 | 0.000 | 0.631 | 0.000 | ||
| 12 spectra, ANATEFGLASGVFTR | 0.000 | 0.083 | 0.000 | 0.000 | 0.000 | 0.000 | 0.917 | 0.000 | ||
| 8 spectra, ALYVSDK | 0.000 | 0.011 | 0.000 | 0.000 | 0.000 | 0.000 | 0.989 | 0.000 | ||
| 2 spectra, VPGAWTEACGQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, LFVEESIHNQFVQK | 0.000 | 0.137 | 0.000 | 0.000 | 0.000 | 0.000 | 0.863 | 0.000 |
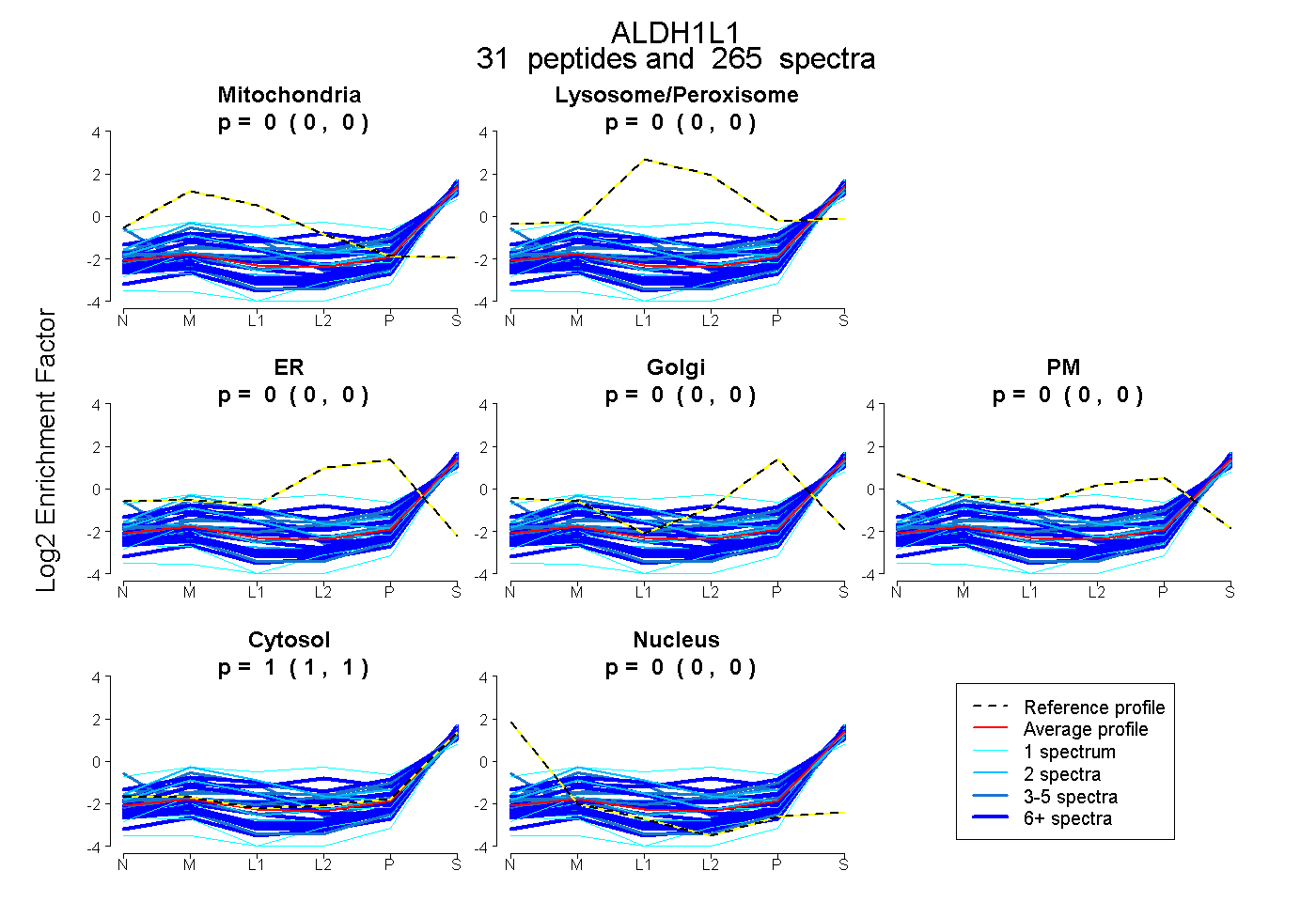
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
265 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
|||
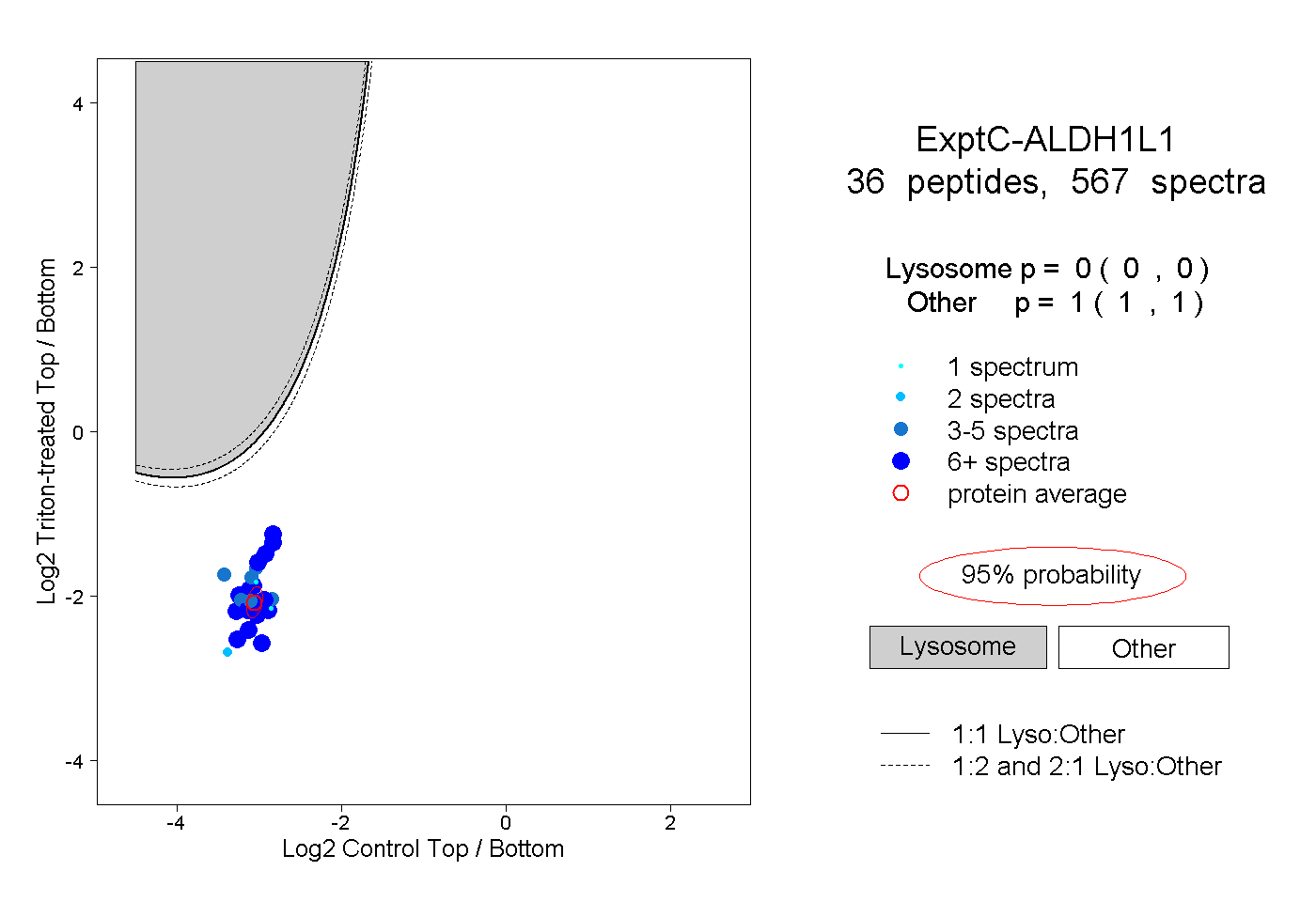
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
567 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
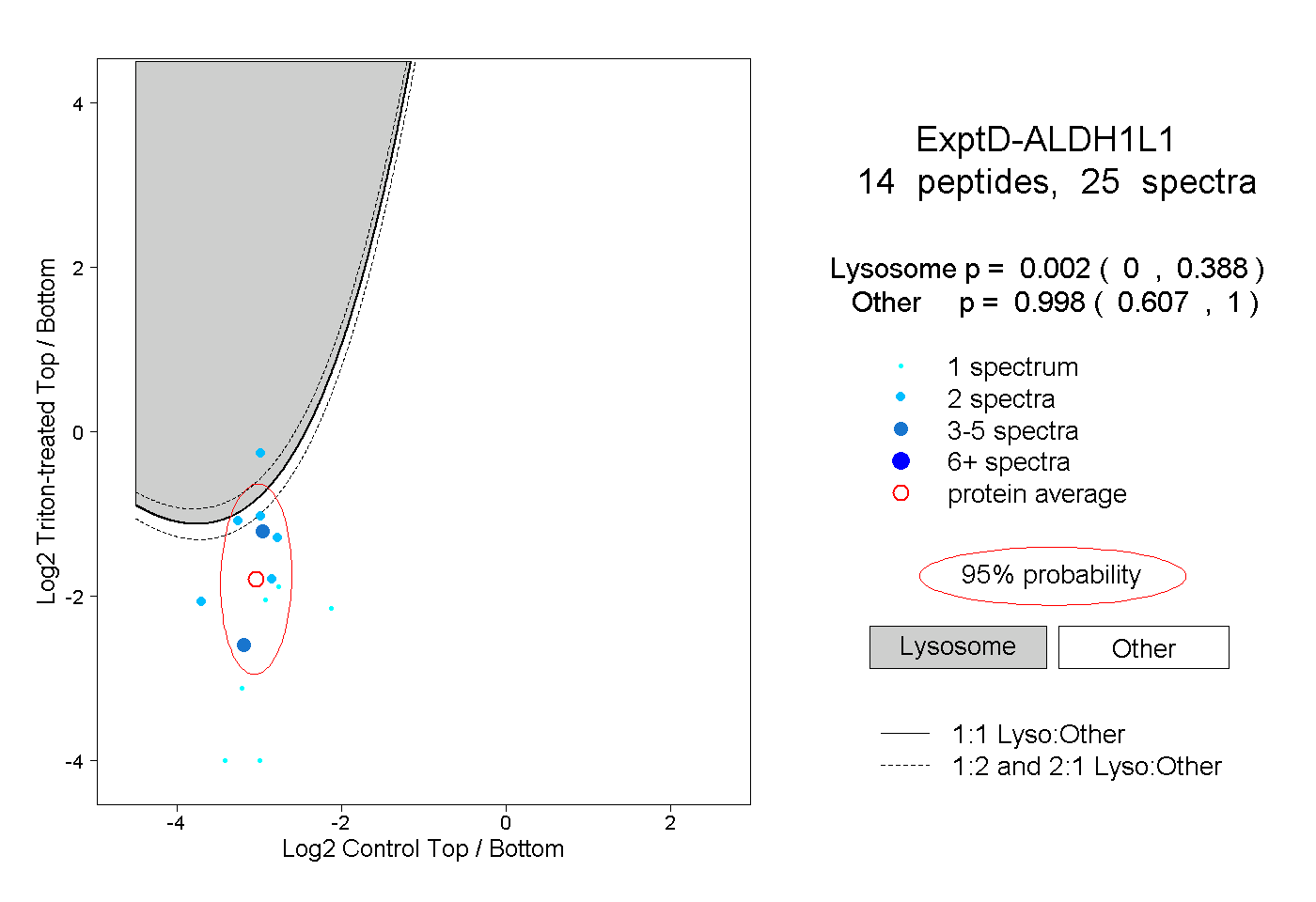
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
25 spectra |
 |
0.002 0.000 | 0.388 |
0.998 0.607 | 1.000 |