peptides
spectra
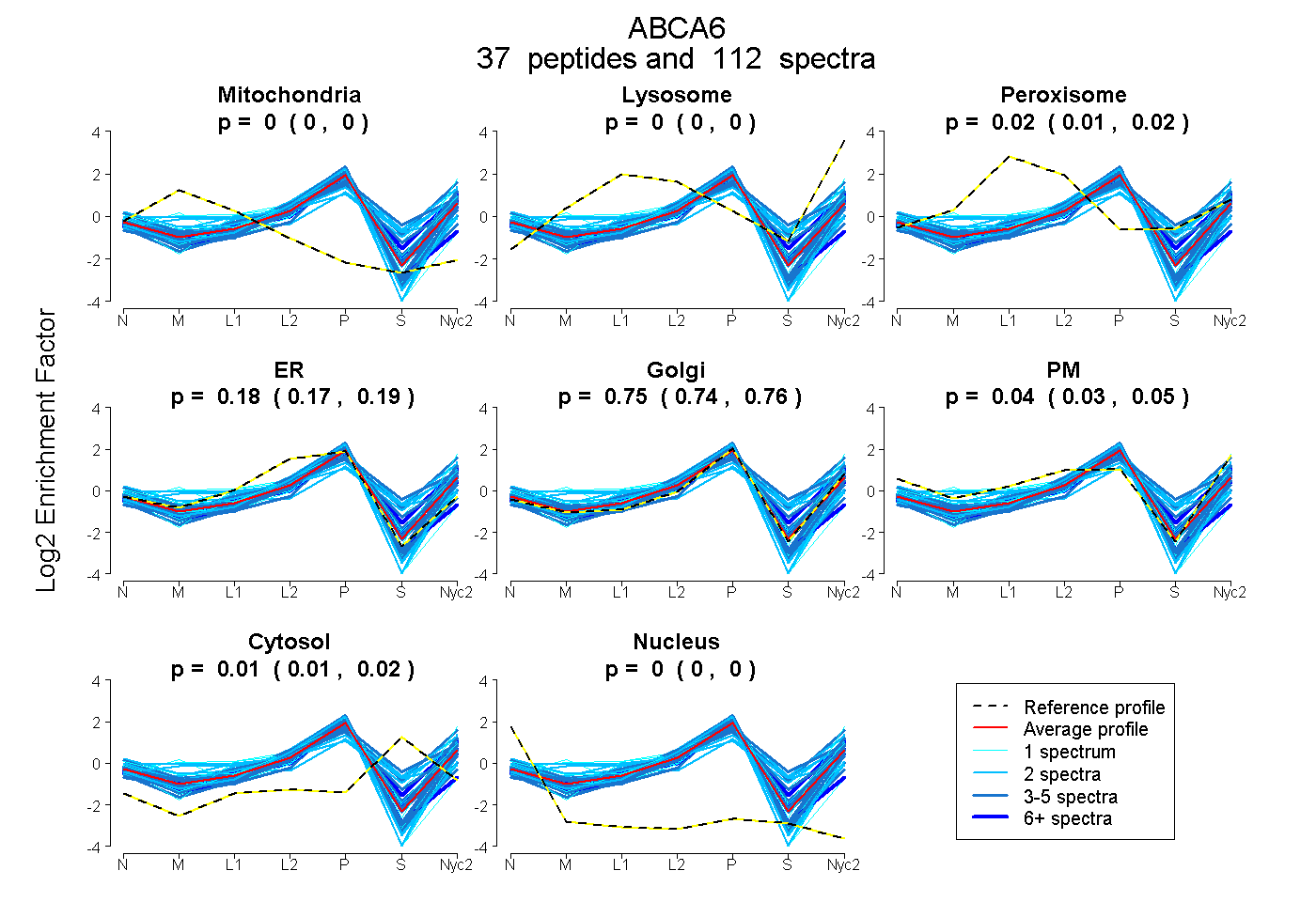
0.000 | 0.000
0.000 | 0.000
0.014 | 0.023
0.171 | 0.188
0.740 | 0.757
0.032 | 0.046
0.009 | 0.015
0.000 | 0.000
peptides
spectra
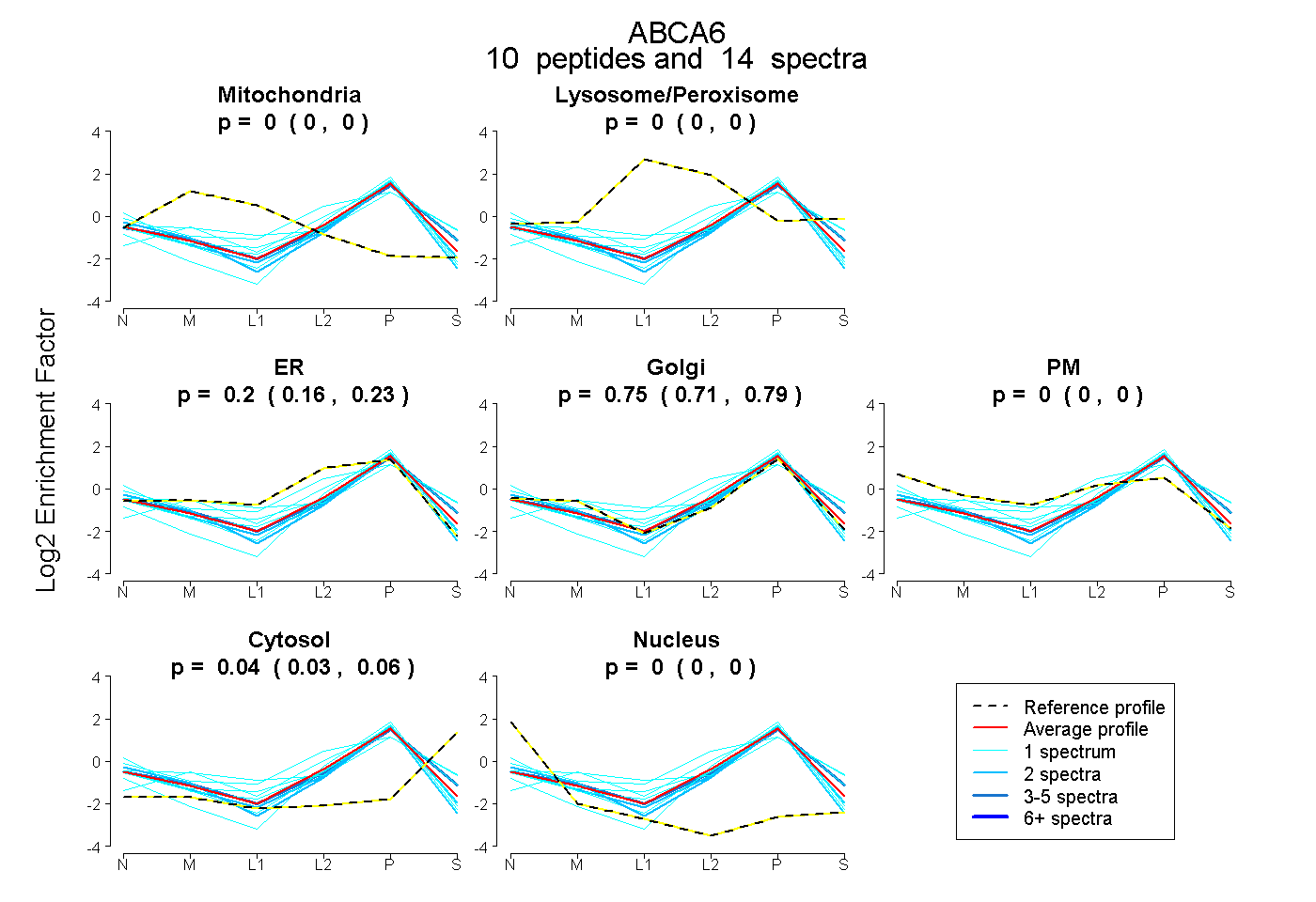
0.000 | 0.000
0.000 | 0.000
0.164 | 0.231
0.709 | 0.790
0.000 | 0.000
0.027 | 0.059
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
112 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.019 0.014 | 0.023 |
0.181 0.171 | 0.188 |
0.749 0.740 | 0.757 |
0.039 0.032 | 0.046 |
0.012 0.009 | 0.015 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
14 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.201 0.164 | 0.231 |
0.754 0.709 | 0.790 |
0.000 0.000 | 0.000 |
0.045 0.027 | 0.059 |
0.000 0.000 | 0.000 |
| 1 spectrum, DYILELR | 0.000 | 0.000 | 0.072 | 0.928 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, ENLTLFANIK | 0.000 | 0.013 | 0.260 | 0.724 | 0.000 | 0.002 | 0.000 | |||
| 1 spectrum, FPEFFSDLDK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, VWGFLK | 0.000 | 0.000 | 0.303 | 0.603 | 0.000 | 0.000 | 0.094 | |||
| 3 spectra, AAIMVSGR | 0.000 | 0.000 | 0.168 | 0.707 | 0.000 | 0.125 | 0.000 | |||
| 2 spectra, NLVVGLTR | 0.000 | 0.000 | 0.000 | 0.987 | 0.000 | 0.000 | 0.013 | |||
| 1 spectrum, LVNAFK | 0.000 | 0.150 | 0.340 | 0.276 | 0.109 | 0.126 | 0.000 | |||
| 1 spectrum, GFNLDDYSLSQCTLDR | 0.000 | 0.226 | 0.000 | 0.653 | 0.000 | 0.121 | 0.000 | |||
| 1 spectrum, LHDQLNVQAR | 0.000 | 0.000 | 0.489 | 0.355 | 0.000 | 0.155 | 0.000 | |||
| 2 spectra, DAVIAISR | 0.000 | 0.000 | 0.037 | 0.963 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
141 spectra |
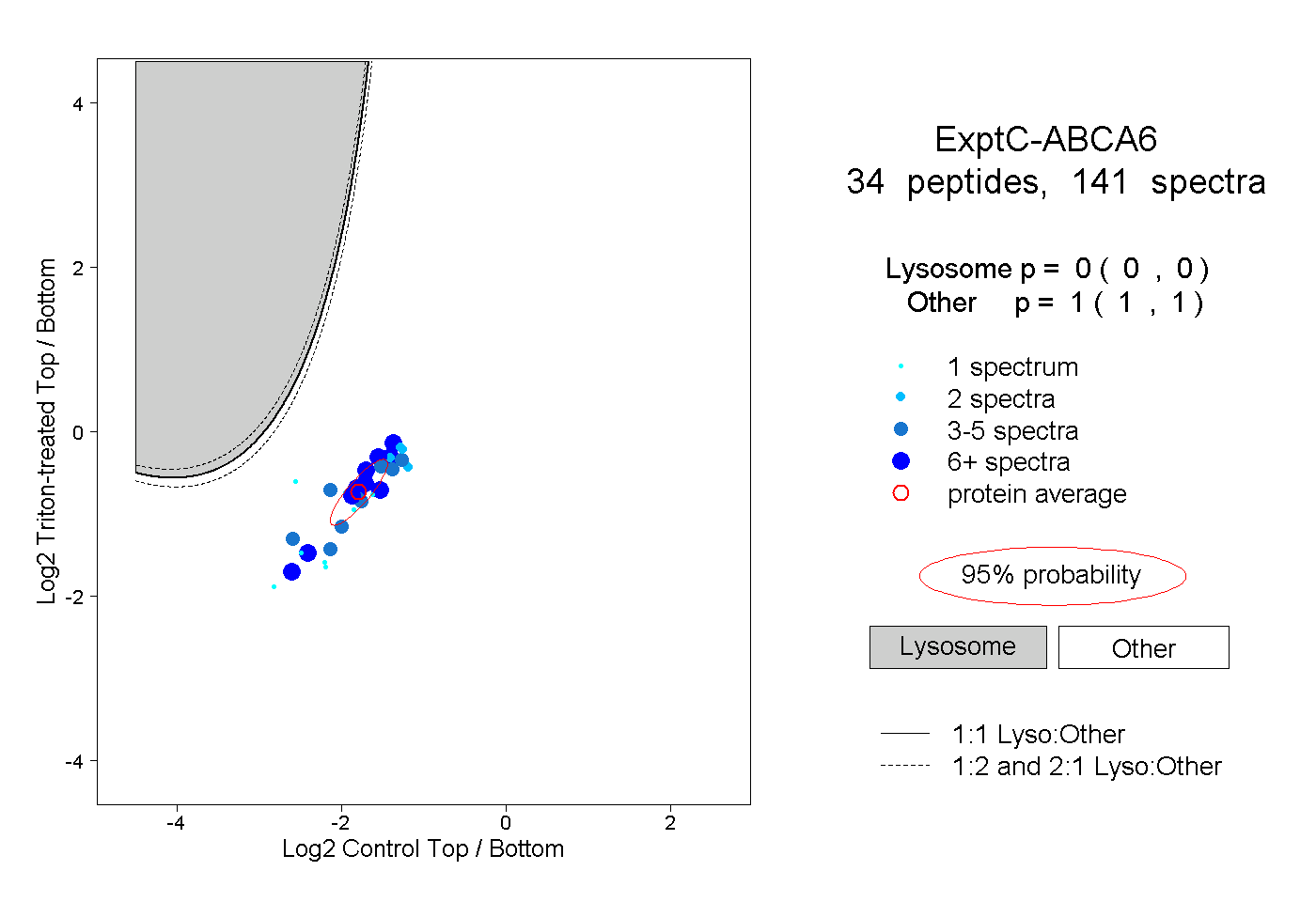 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
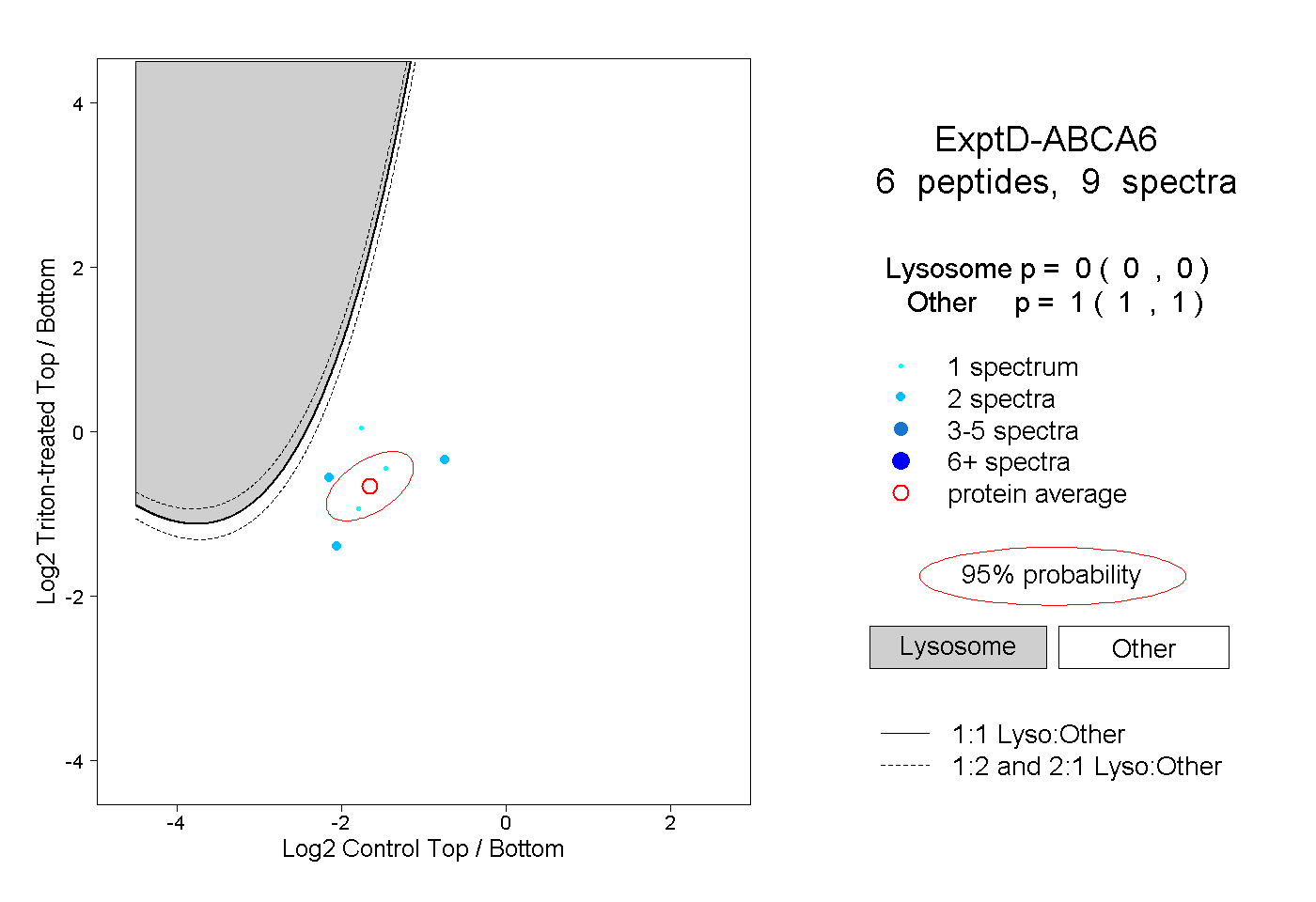 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |