peptides
spectra
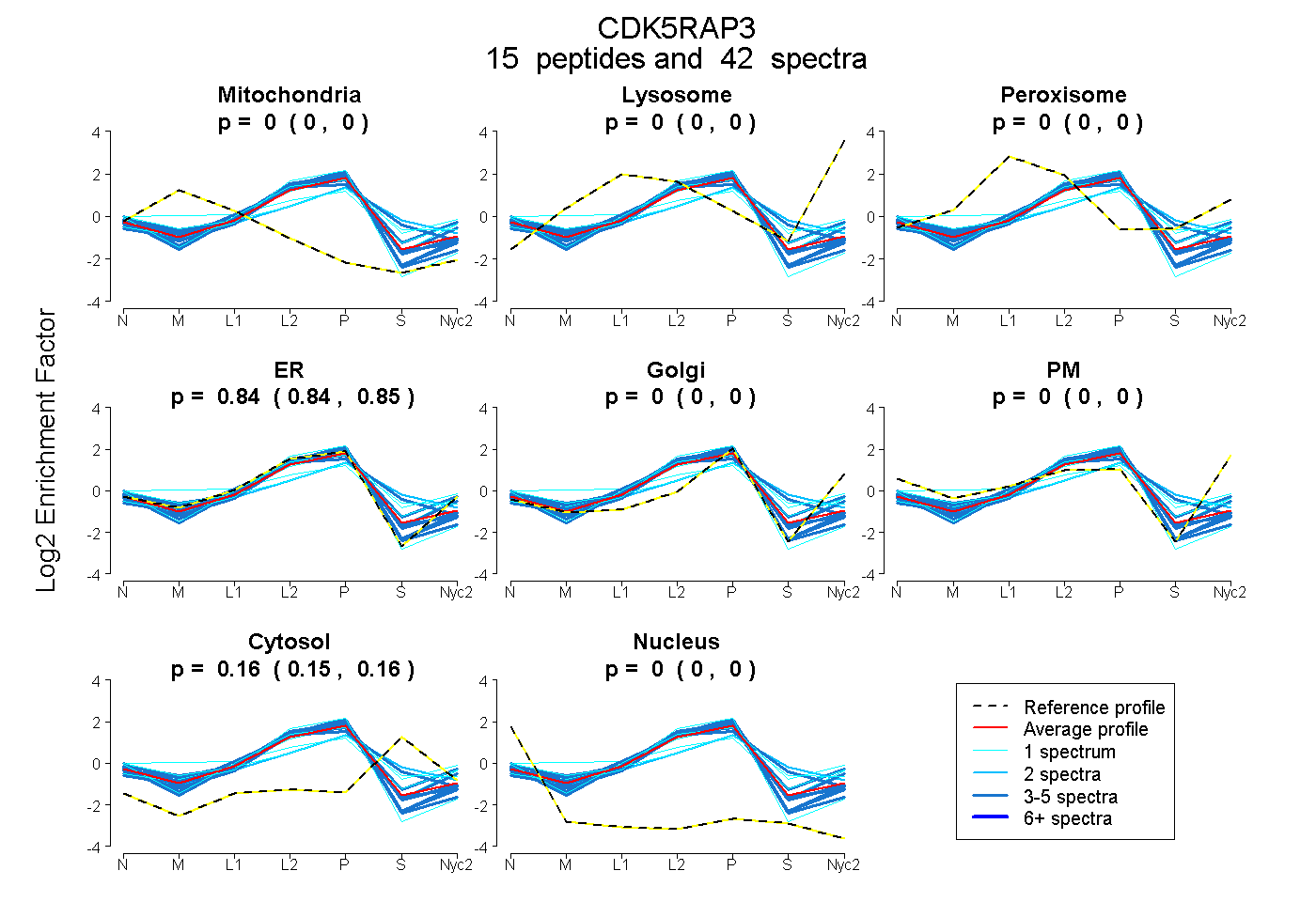
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.835 | 0.847
0.000 | 0.000
0.000 | 0.000
0.152 | 0.164
0.000 | 0.000
peptides
spectra
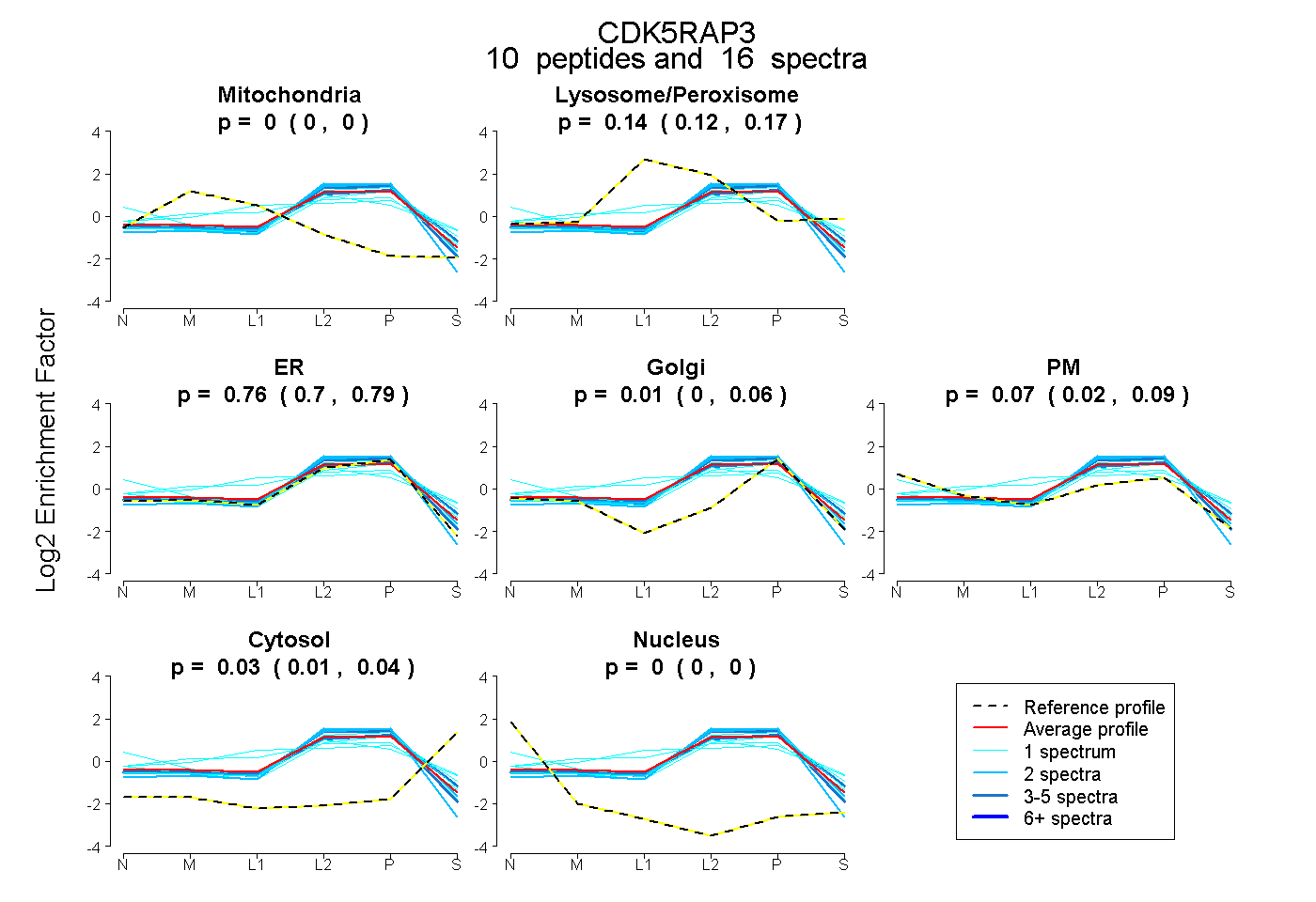
0.000 | 0.000
0.120 | 0.165
0.701 | 0.786
0.000 | 0.058
0.024 | 0.094
0.011 | 0.038
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
42 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.841 0.835 | 0.847 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.159 0.152 | 0.164 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
16 spectra |
 |
0.000 0.000 | 0.000 |
0.139 0.120 | 0.165 |
0.761 0.701 | 0.786 |
0.007 0.000 | 0.058 |
0.066 0.024 | 0.094 |
0.028 0.011 | 0.038 |
0.000 0.000 | 0.000 |
| 2 spectra, LDLLLEK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, EQFYHSCK | 0.000 | 0.193 | 0.161 | 0.000 | 0.555 | 0.091 | 0.000 | |||
| 2 spectra, LLDWLVDR | 0.000 | 0.062 | 0.933 | 0.000 | 0.000 | 0.005 | 0.000 | |||
| 1 spectrum, QYGITGDNVR | 0.000 | 0.107 | 0.830 | 0.000 | 0.000 | 0.063 | 0.000 | |||
| 3 spectra, ELLALVK | 0.000 | 0.166 | 0.709 | 0.058 | 0.000 | 0.067 | 0.000 | |||
| 1 spectrum, VTELLQQK | 0.046 | 0.310 | 0.344 | 0.148 | 0.152 | 0.000 | 0.000 | |||
| 1 spectrum, QQEALQEQAALEPK | 0.000 | 0.550 | 0.000 | 0.448 | 0.001 | 0.000 | 0.000 | |||
| 1 spectrum, CQQLQQDYSR | 0.000 | 0.077 | 0.923 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, IVDLIK | 0.000 | 0.061 | 0.939 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, GTEASTK | 0.000 | 0.150 | 0.549 | 0.130 | 0.082 | 0.089 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
95 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
16 spectra |
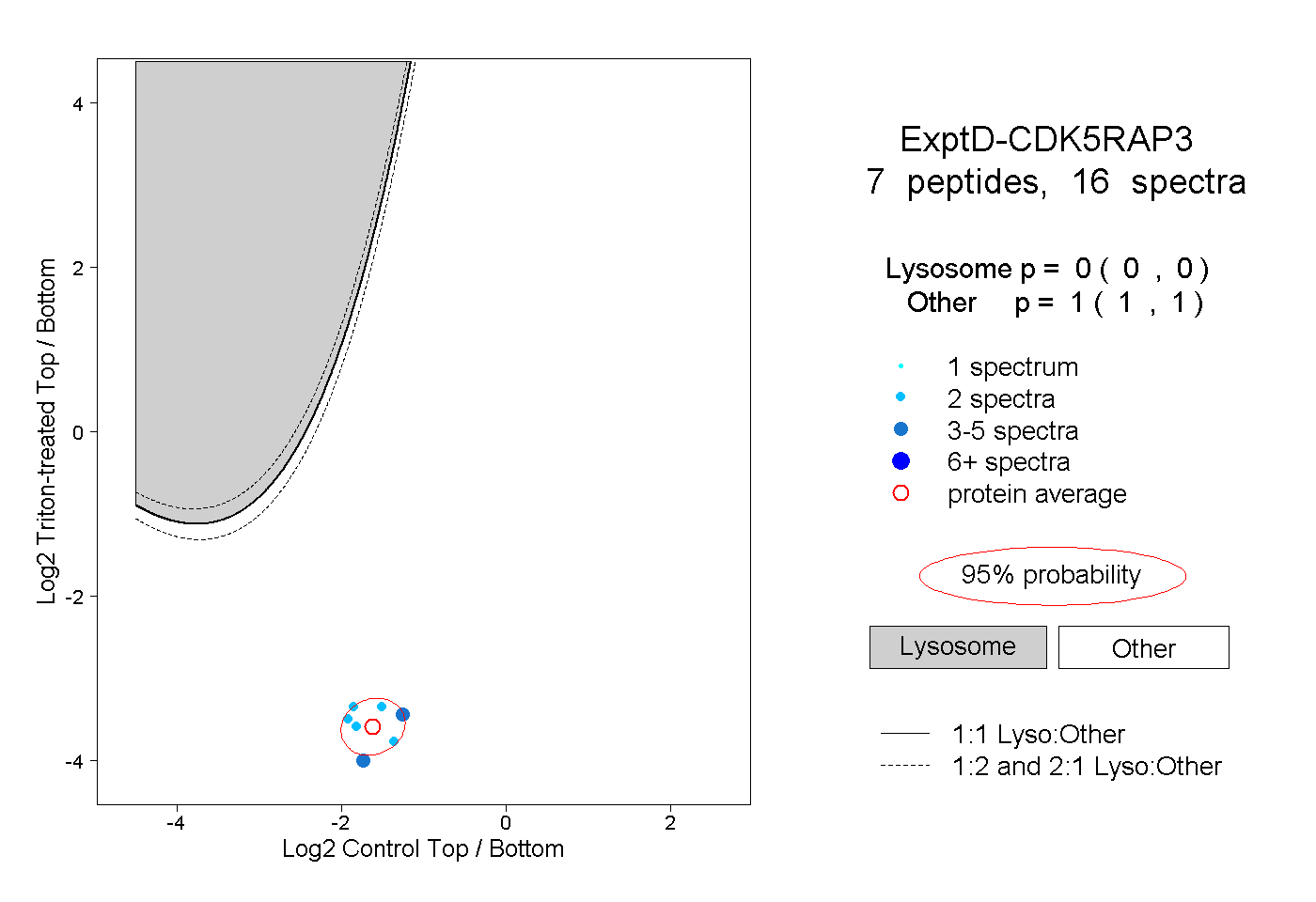 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |