peptides
spectra
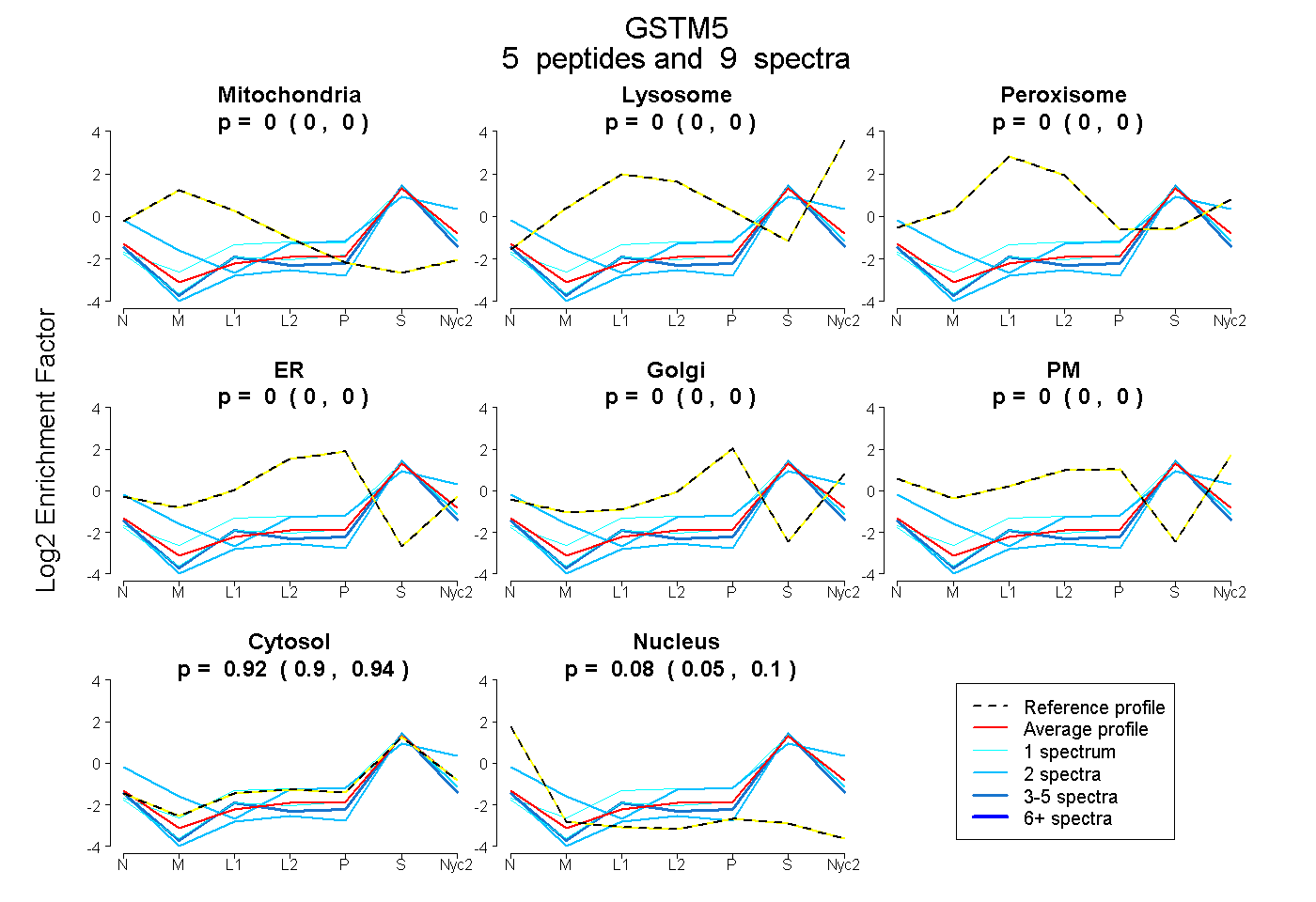
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.900 | 0.944
0.052 | 0.095
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
9 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.923 0.900 | 0.944 |
0.077 0.052 | 0.095 |
| 1 spectrum, VDIMENQIMDFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.952 | 0.048 | ||
| 2 spectra, MLLEFTDTSYEEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.163 | 0.771 | 0.066 | ||
| 1 spectrum, HNMCGDTEEEK | 0.000 | 0.011 | 0.000 | 0.000 | 0.000 | 0.000 | 0.989 | 0.000 | ||
| 3 spectra, QYTCGEAPDYDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.885 | 0.115 | ||
| 2 spectra, FTWFAGEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.846 | 0.154 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
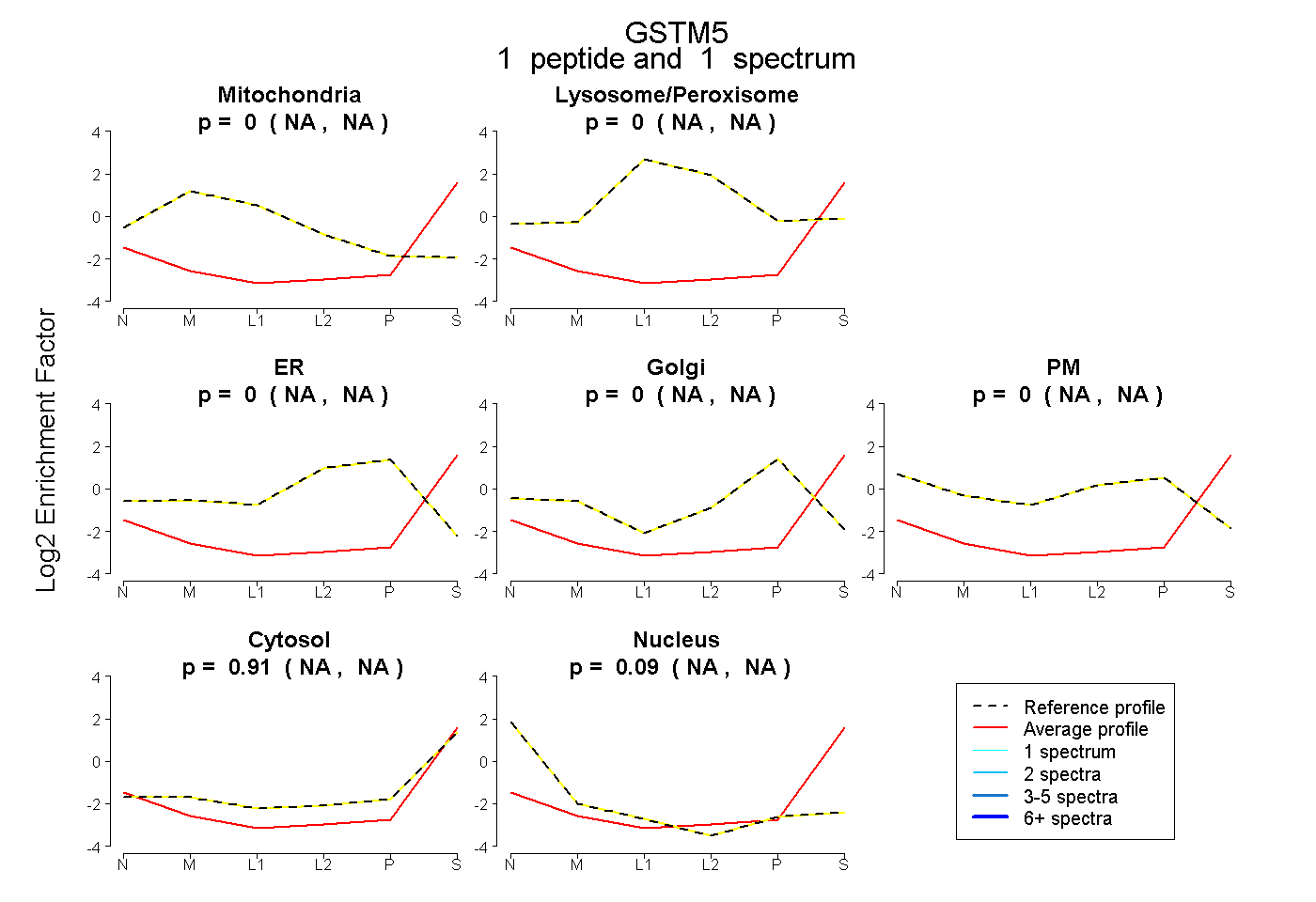 |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.906 NA | NA |
0.094 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
6 spectra |
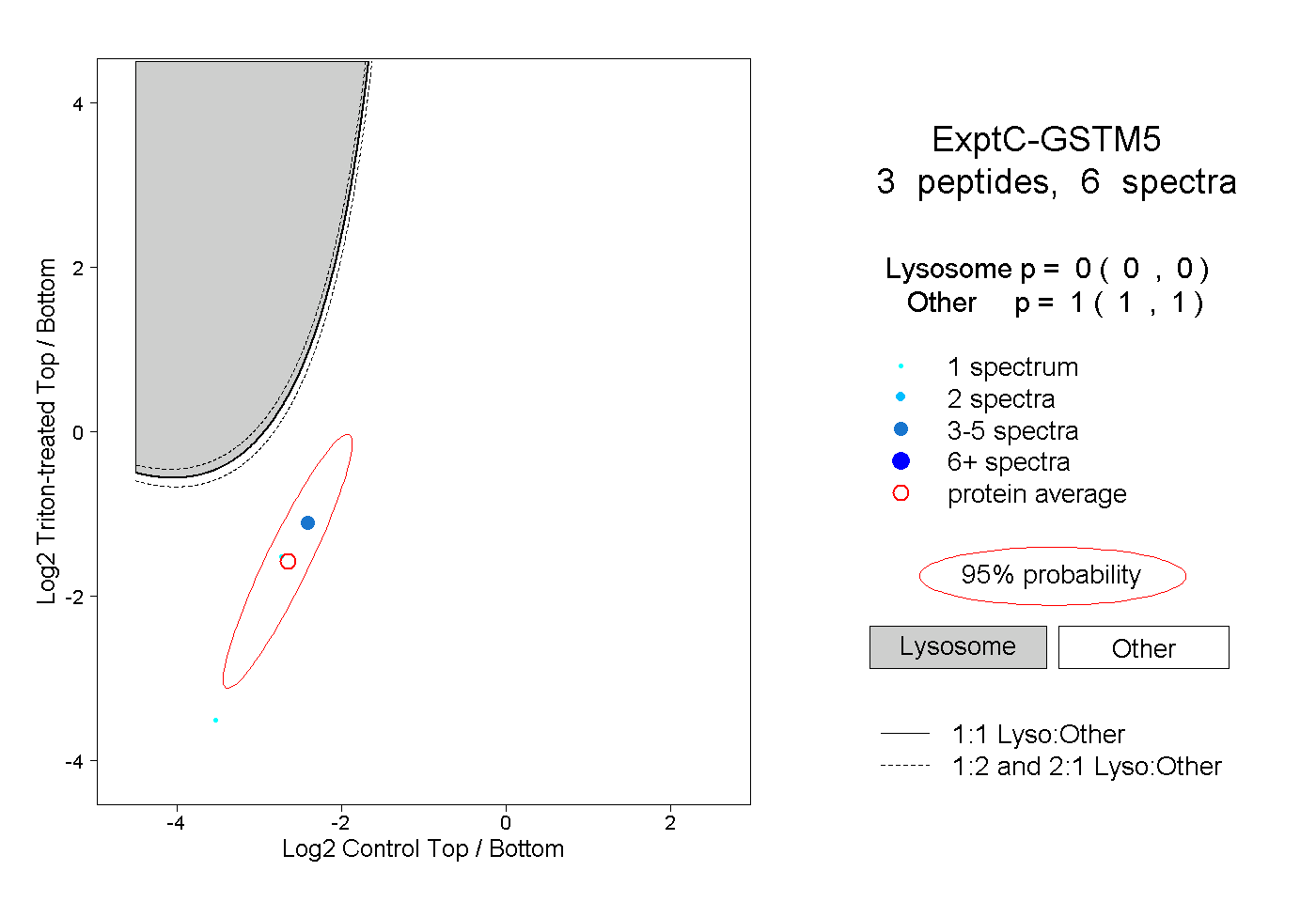 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |