peptides
spectra
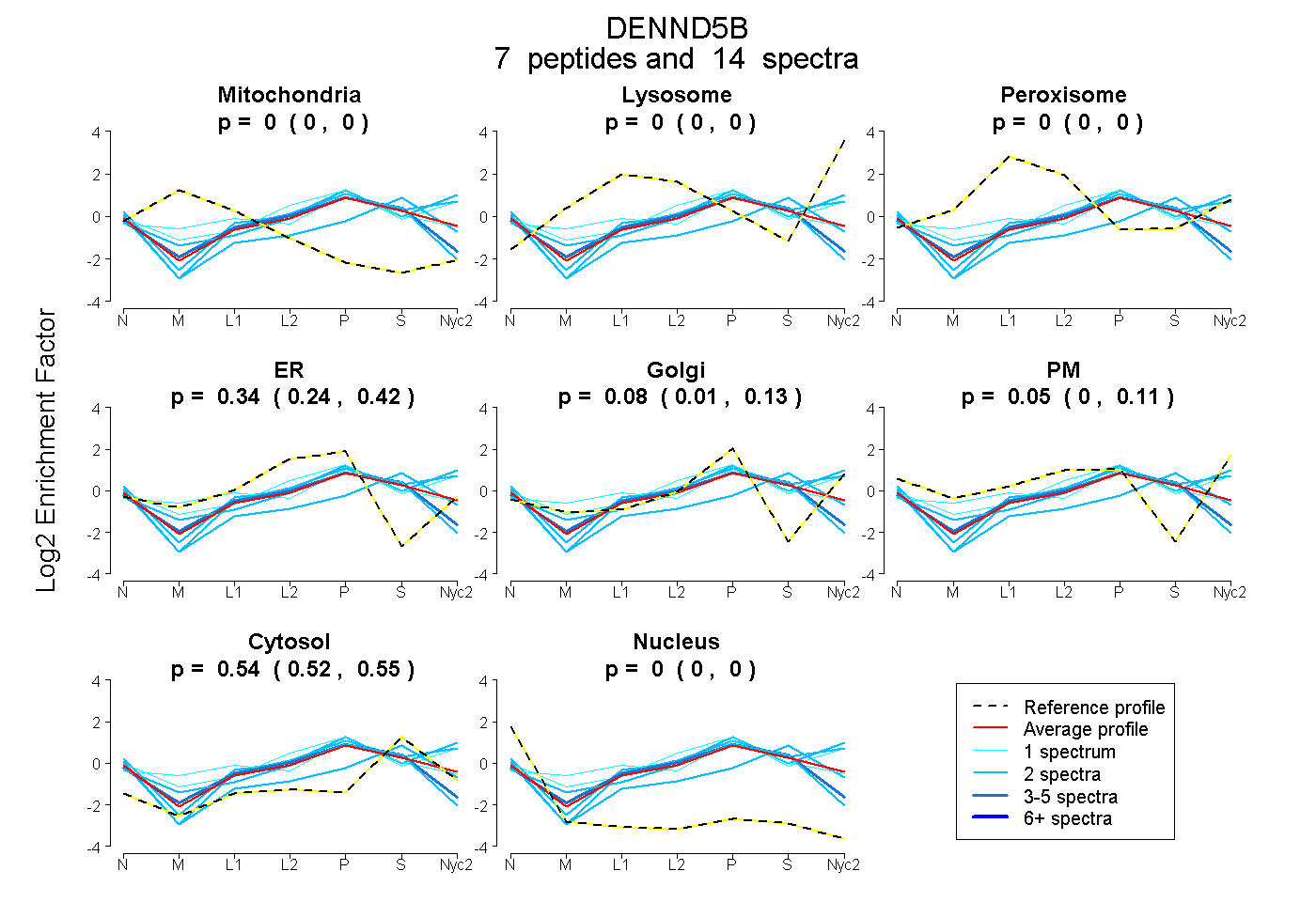
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.244 | 0.417
0.009 | 0.126
0.000 | 0.111
0.516 | 0.552
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
14 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.343 0.244 | 0.417 |
0.076 0.009 | 0.126 |
0.047 0.000 | 0.111 |
0.535 0.516 | 0.552 |
0.000 0.000 | 0.000 |
| 2 spectra, NLLEMTFECQNLGK | 0.000 | 0.000 | 0.000 | 0.018 | 0.198 | 0.300 | 0.484 | 0.000 | ||
| 2 spectra, GVDDGSLER | 0.000 | 0.003 | 0.000 | 0.000 | 0.210 | 0.385 | 0.403 | 0.000 | ||
| 1 spectrum, SALWSHLIQFQDR | 0.021 | 0.000 | 0.189 | 0.113 | 0.322 | 0.000 | 0.355 | 0.000 | ||
| 4 spectra, TFCHYVNAVNTAPR | 0.000 | 0.000 | 0.000 | 0.435 | 0.000 | 0.000 | 0.564 | 0.001 | ||
| 1 spectrum, IWSHGLLVK | 0.000 | 0.055 | 0.000 | 0.114 | 0.182 | 0.319 | 0.331 | 0.000 | ||
| 2 spectra, WLVDCVMVR | 0.000 | 0.000 | 0.000 | 0.423 | 0.000 | 0.000 | 0.530 | 0.047 | ||
| 2 spectra, LQCEEADLR | 0.000 | 0.000 | 0.000 | 0.058 | 0.081 | 0.060 | 0.749 | 0.052 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
2 spectra |
 |
0.000 NA | NA |
0.100 NA | NA |
0.000 NA | NA |
0.304 NA | NA |
0.173 NA | NA |
0.422 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
12 spectra |
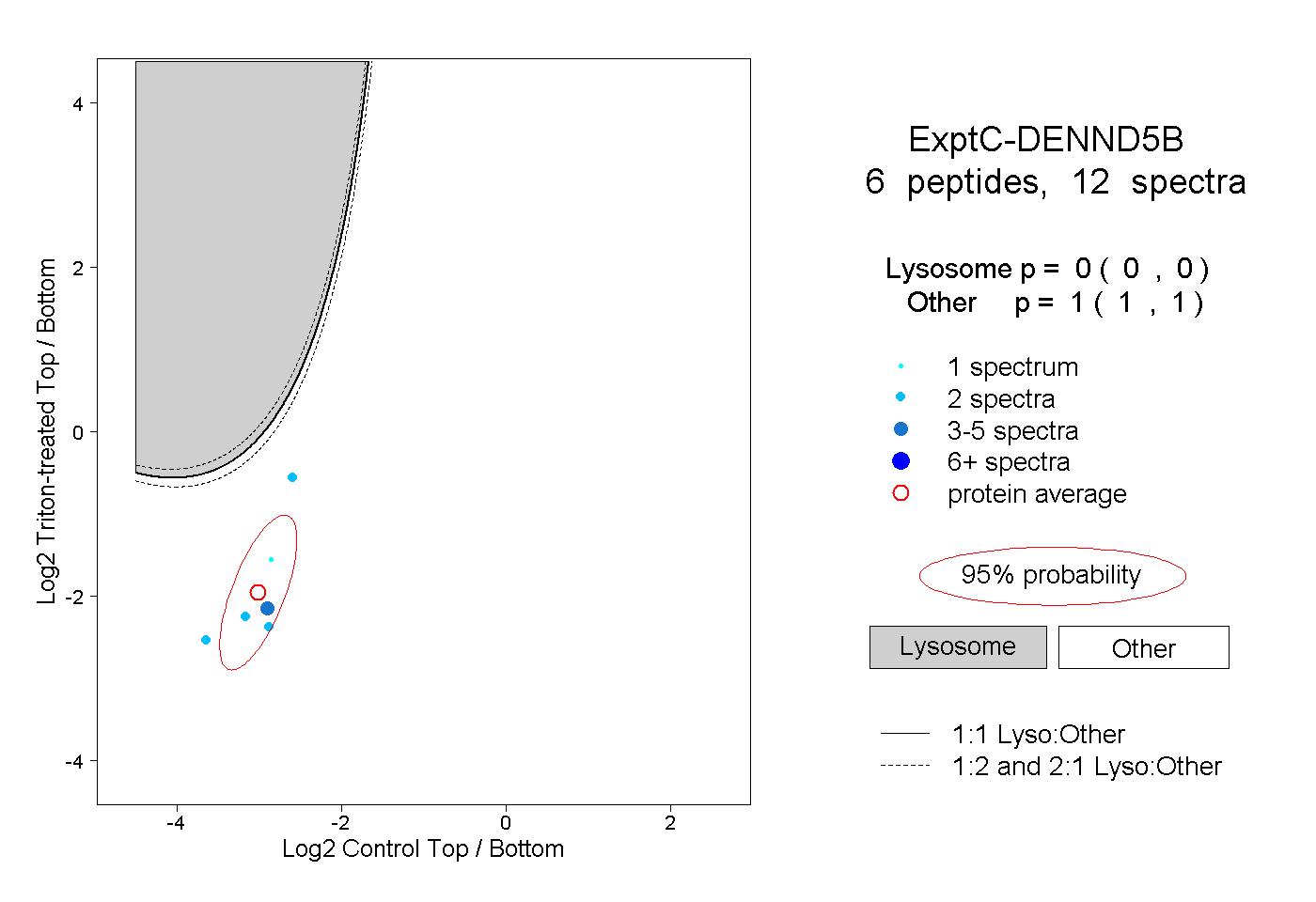 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
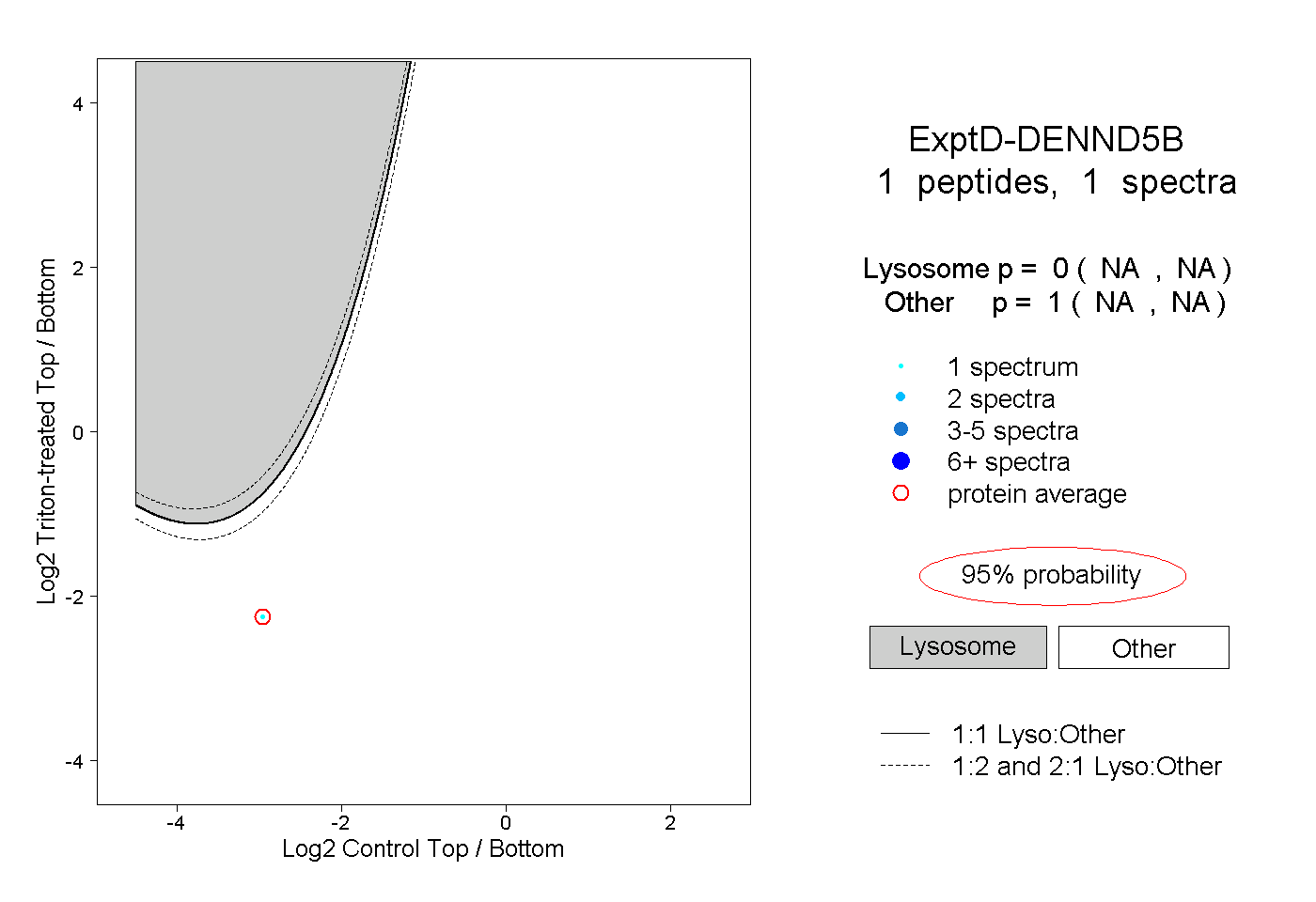 |
0.000 NA | NA |
1.000 NA | NA |