peptides
spectra
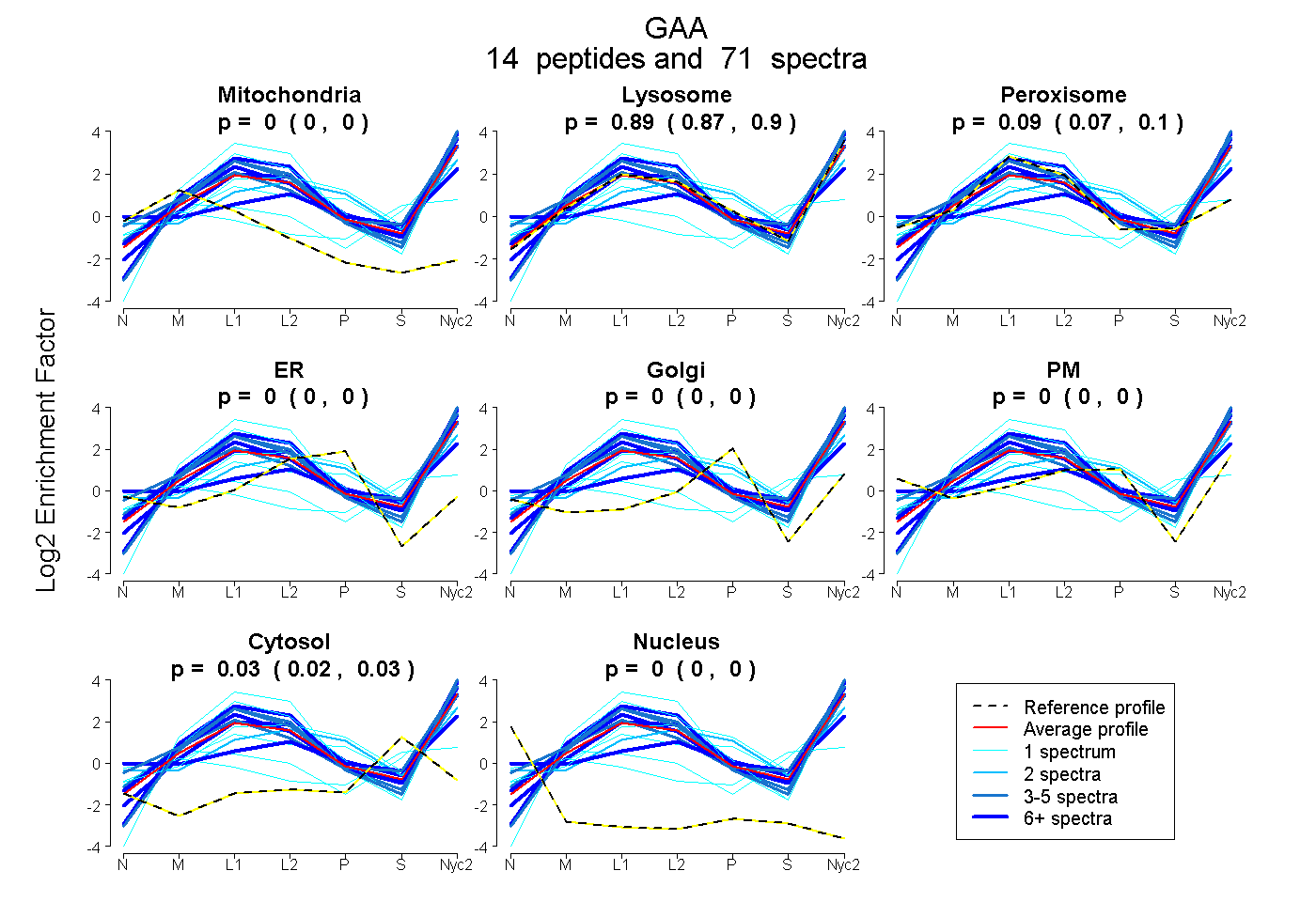
0.000 | 0.000
0.872 | 0.899
0.070 | 0.103
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.018 | 0.031
0.000 | 0.000
peptides
spectra
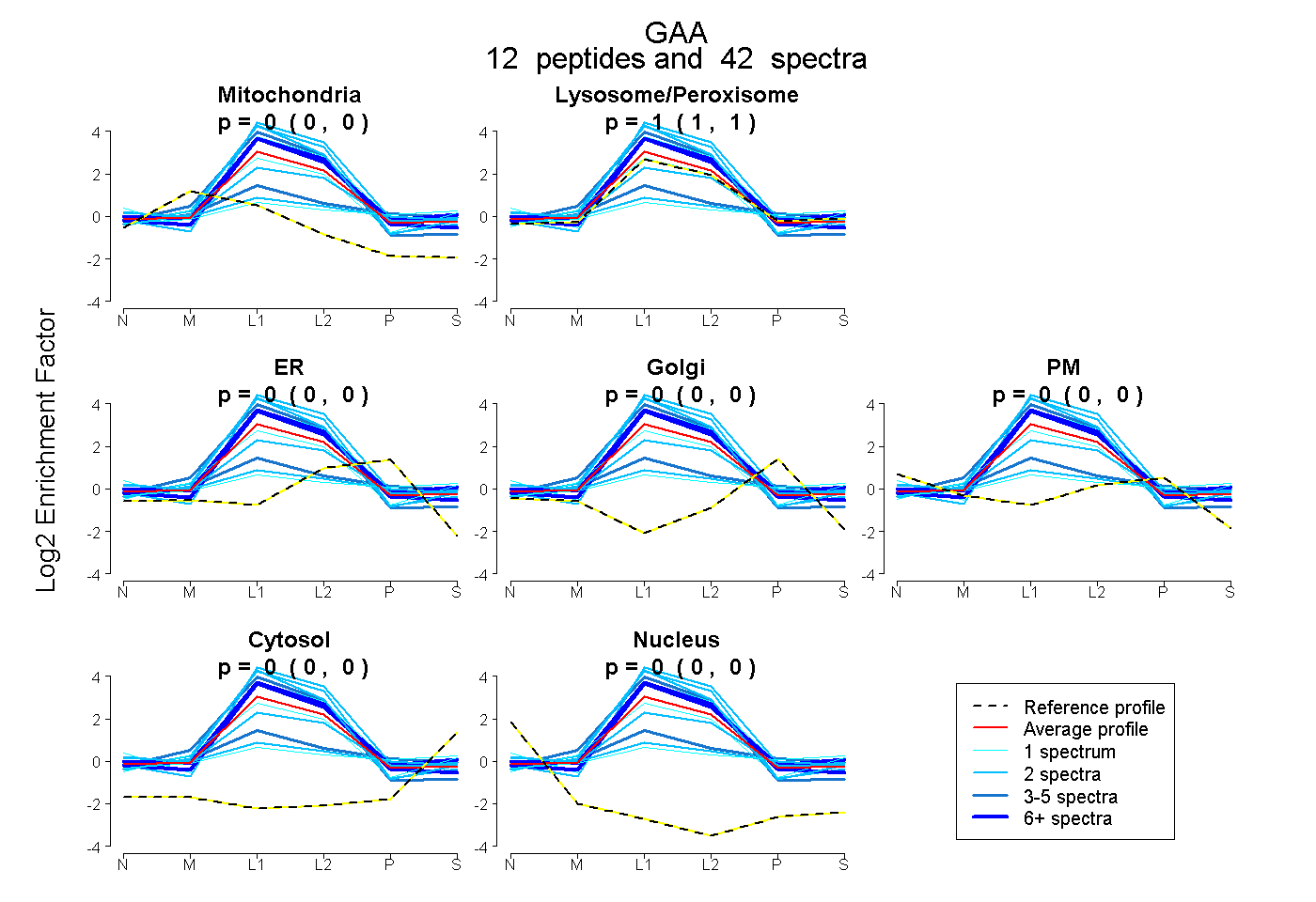
0.000 | 0.000
1.000 | 1.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
71 spectra |
 |
0.000 0.000 | 0.000 |
0.887 0.872 | 0.899 |
0.088 0.070 | 0.103 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.025 0.018 | 0.031 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
42 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, GDTVARPLFLEFPEDPSTWSVDR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, GAYTLVTFSAK | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, EGGELQLR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LVHVTK | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, DFTFNQDGFADFPDMVHELHQGGR | 0.078 | 0.675 | 0.000 | 0.172 | 0.000 | 0.076 | 0.000 | |||
| 14 spectra, GTRPFVISR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, THFPLDVQWNDLDYMDAR | 0.000 | 0.874 | 0.000 | 0.000 | 0.126 | 0.000 | 0.000 | |||
| 2 spectra, NHNDLNSLPQEPYR | 0.039 | 0.493 | 0.000 | 0.000 | 0.340 | 0.128 | 0.000 | |||
| 7 spectra, ITLWNR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, TDVTGYFPK | 0.000 | 0.556 | 0.000 | 0.169 | 0.067 | 0.209 | 0.000 | |||
| 1 spectrum, GITQEQCEAR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LHFMIK | 0.055 | 0.945 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
241 spectra |
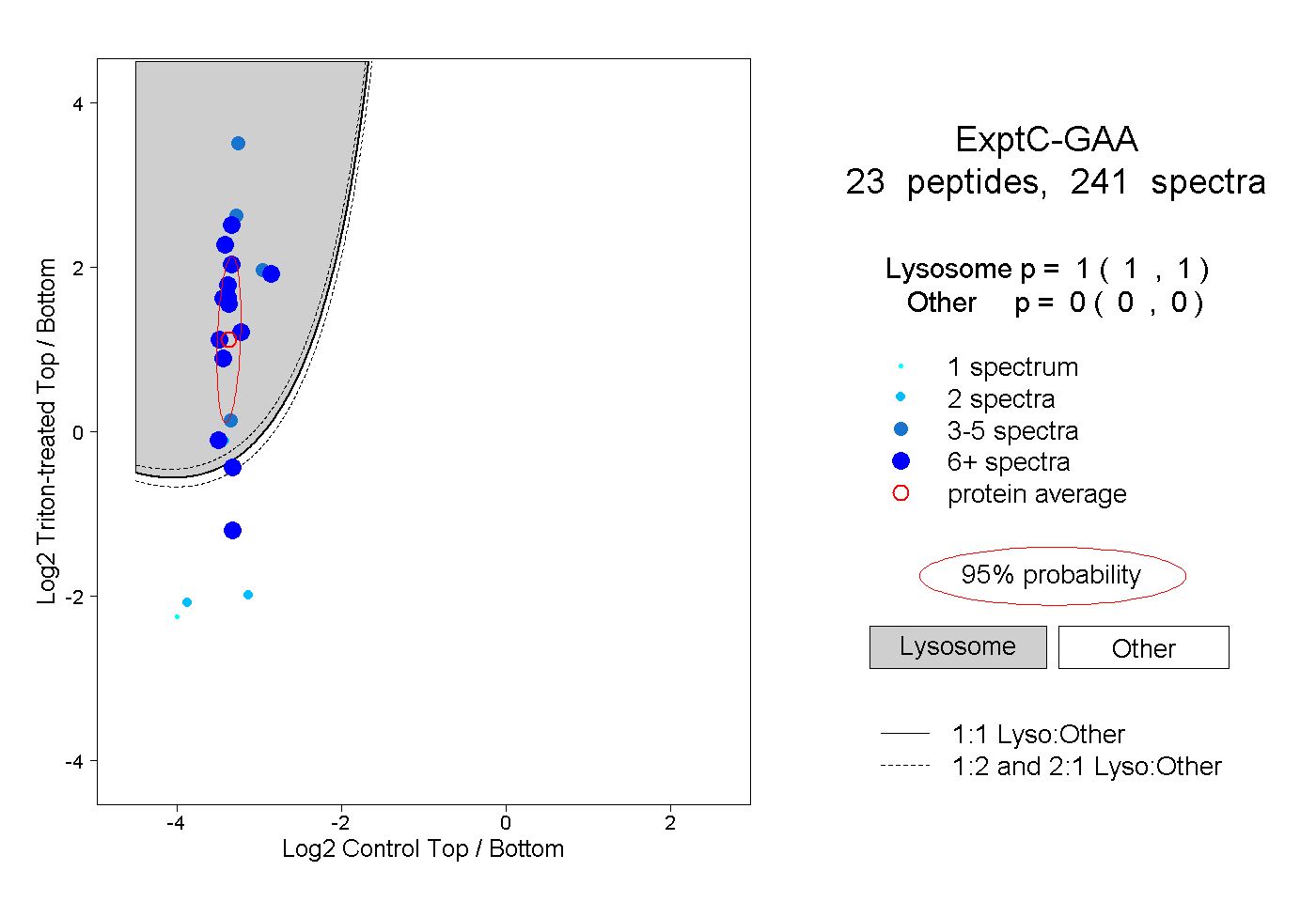 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
15 spectra |
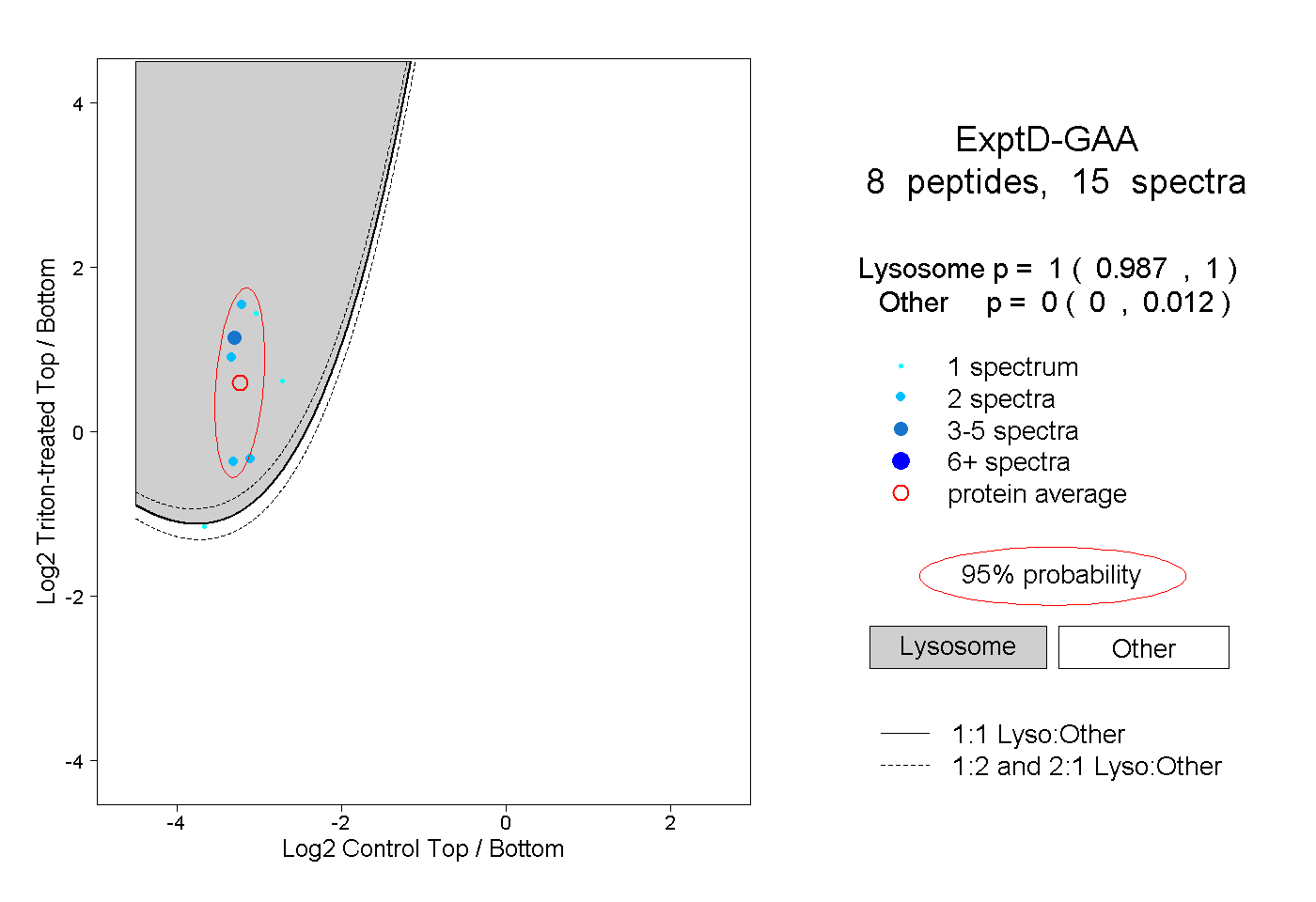 |
1.000 0.987 | 1.000 |
0.000 0.000 | 0.012 |