peptides
spectra
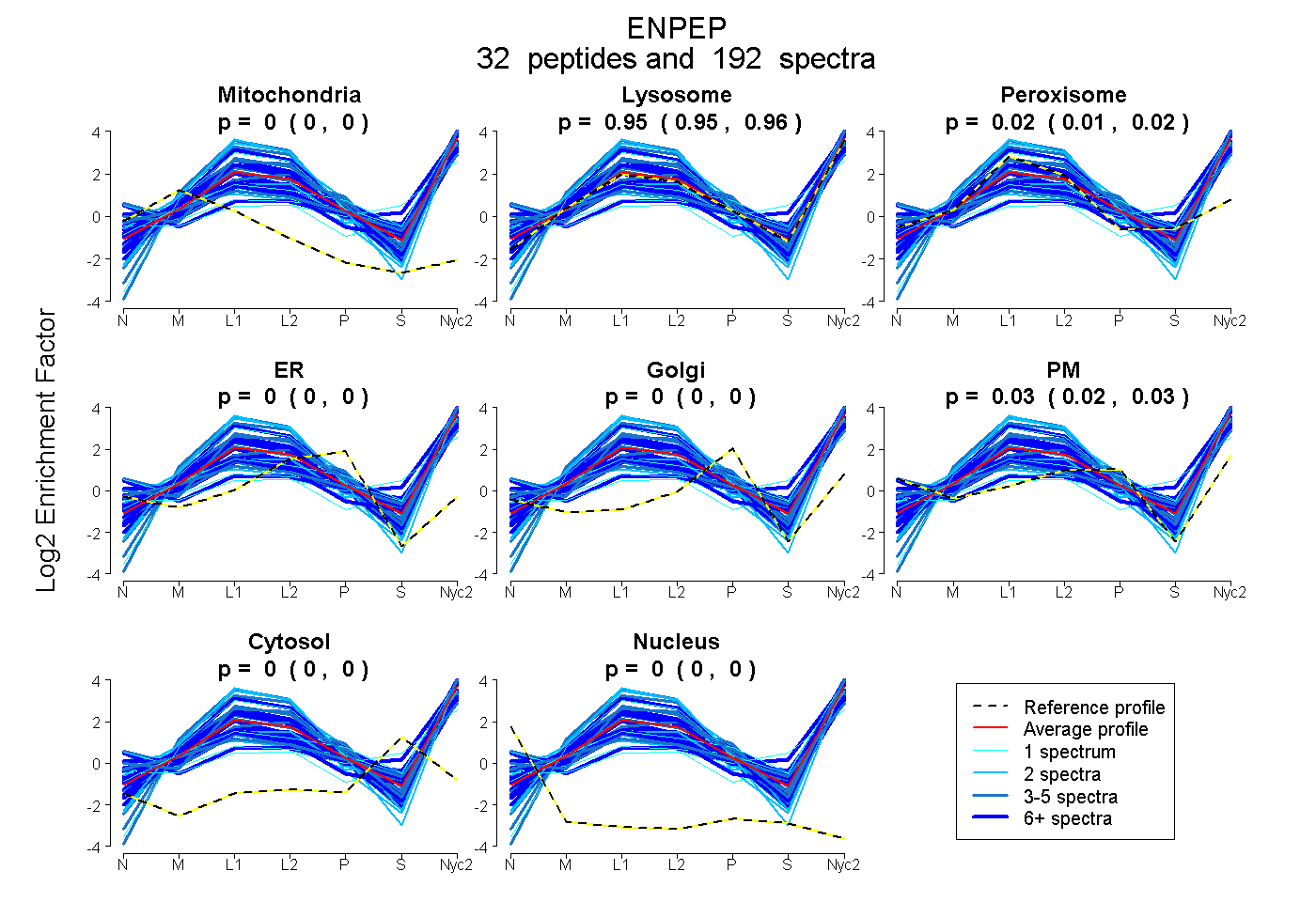
0.000 | 0.000
0.949 | 0.959
0.013 | 0.022
0.000 | 0.000
0.000 | 0.000
0.022 | 0.032
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
192 spectra |
 |
0.000 0.000 | 0.000 |
0.955 0.949 | 0.959 |
0.017 0.013 | 0.022 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.028 0.022 | 0.032 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 13 spectra, INPDHIGFYR | 0.000 | 0.731 | 0.000 | 0.000 | 0.000 | 0.239 | 0.029 | 0.000 | ||
| 1 spectrum, YLTSEK | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, TSDFWDSLEK | 0.000 | 0.881 | 0.000 | 0.000 | 0.000 | 0.000 | 0.119 | 0.000 | ||
| 21 spectra, RPSGEQVPIR | 0.000 | 0.470 | 0.000 | 0.000 | 0.000 | 0.369 | 0.160 | 0.000 | ||
| 3 spectra, YISYNSYGK | 0.000 | 0.618 | 0.037 | 0.000 | 0.000 | 0.248 | 0.097 | 0.000 | ||
| 5 spectra, DFLPWER | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, FLLDYK | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, YLEMLK | 0.000 | 0.917 | 0.000 | 0.000 | 0.000 | 0.068 | 0.015 | 0.000 | ||
| 1 spectrum, EVMDTWTSQMGYPVVTVSGK | 0.013 | 0.861 | 0.000 | 0.000 | 0.000 | 0.000 | 0.076 | 0.050 | ||
| 1 spectrum, TSLAQEK | 0.000 | 0.599 | 0.000 | 0.000 | 0.000 | 0.073 | 0.328 | 0.000 | ||
| 2 spectra, LPDFIQPVHYDLEVK | 0.000 | 0.860 | 0.000 | 0.000 | 0.000 | 0.000 | 0.140 | 0.000 | ||
| 8 spectra, ASNQPVK | 0.000 | 0.874 | 0.025 | 0.000 | 0.000 | 0.101 | 0.000 | 0.000 | ||
| 1 spectrum, SISEWFTSMP | 0.000 | 0.418 | 0.000 | 0.000 | 0.000 | 0.493 | 0.089 | 0.000 | ||
| 8 spectra, EYSALSNMPVEK | 0.000 | 0.721 | 0.000 | 0.000 | 0.096 | 0.183 | 0.000 | 0.000 | ||
| 9 spectra, GASILR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, GCQIYLENFK | 0.000 | 0.873 | 0.127 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 9 spectra, SSFIDDAFALAR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, FTINDR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 9 spectra, SIAATDHEPTDAR | 0.000 | 0.617 | 0.073 | 0.000 | 0.000 | 0.256 | 0.054 | 0.000 | ||
| 8 spectra, AQLLDYEK | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, SFPCFDEPNK | 0.000 | 0.564 | 0.035 | 0.000 | 0.000 | 0.370 | 0.010 | 0.020 | ||
| 5 spectra, ASVLGFACK | 0.000 | 0.698 | 0.173 | 0.000 | 0.000 | 0.129 | 0.000 | 0.000 | ||
| 6 spectra, DVTLLAR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 12 spectra, TQDVFTVIR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, LLYGLASVK | 0.000 | 0.971 | 0.000 | 0.000 | 0.000 | 0.029 | 0.000 | 0.000 | ||
| 25 spectra, DLWLHIR | 0.000 | 0.822 | 0.016 | 0.000 | 0.000 | 0.140 | 0.023 | 0.000 | ||
| 2 spectra, NNIEWLK | 0.000 | 0.795 | 0.000 | 0.000 | 0.000 | 0.205 | 0.000 | 0.000 | ||
| 3 spectra, MLQDWITPEK | 0.000 | 0.949 | 0.000 | 0.000 | 0.000 | 0.051 | 0.000 | 0.000 | ||
| 4 spectra, YPNAGAGAKPR | 0.000 | 0.846 | 0.026 | 0.000 | 0.000 | 0.128 | 0.000 | 0.000 | ||
| 2 spectra, TTYTEDGQTK | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, ELYPLIETYFR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, VLMEEDR | 0.000 | 0.957 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.043 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
80 spectra |
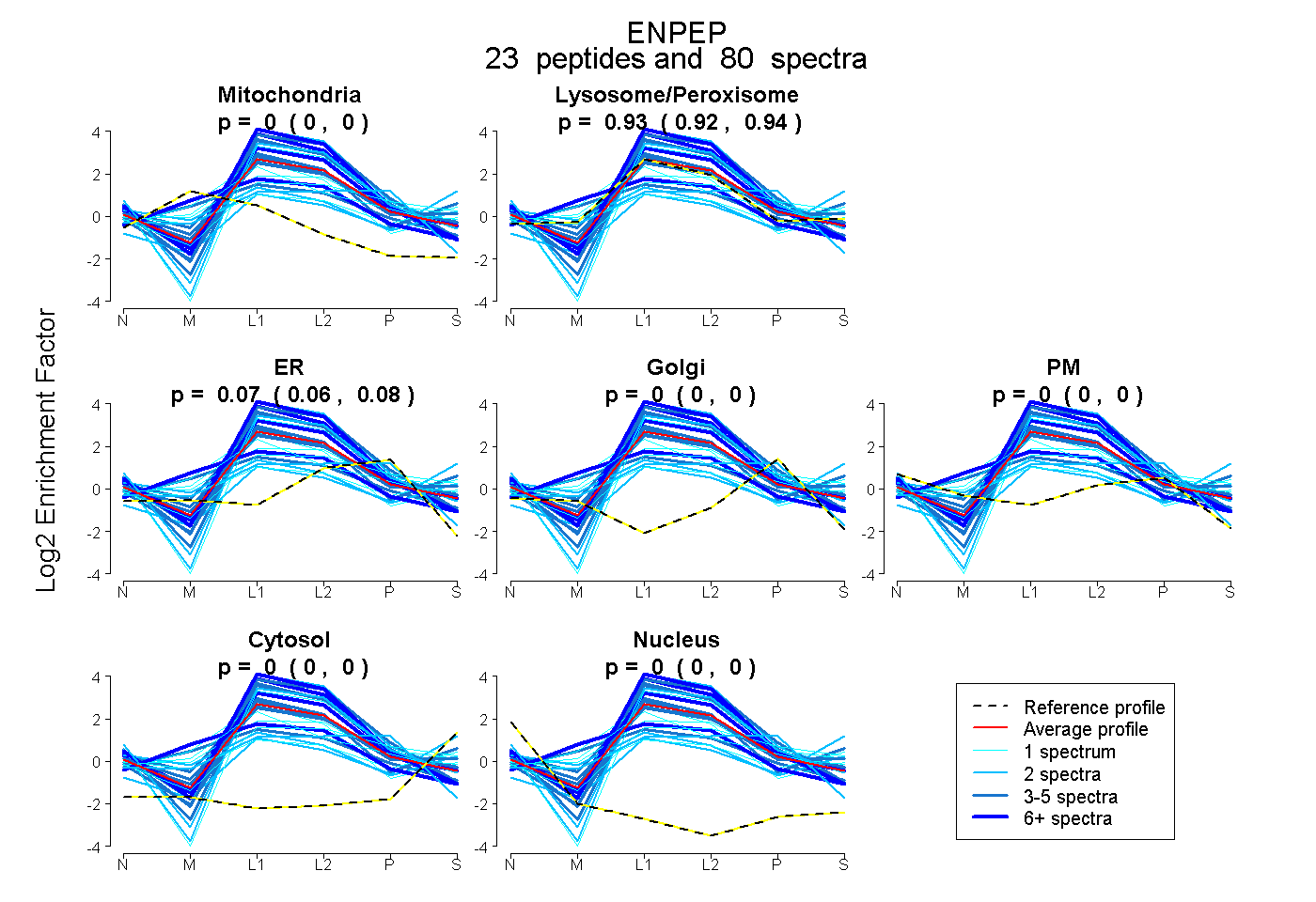 |
0.000 0.000 | 0.000 |
0.931 0.922 | 0.939 |
0.069 0.059 | 0.076 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
770 spectra |
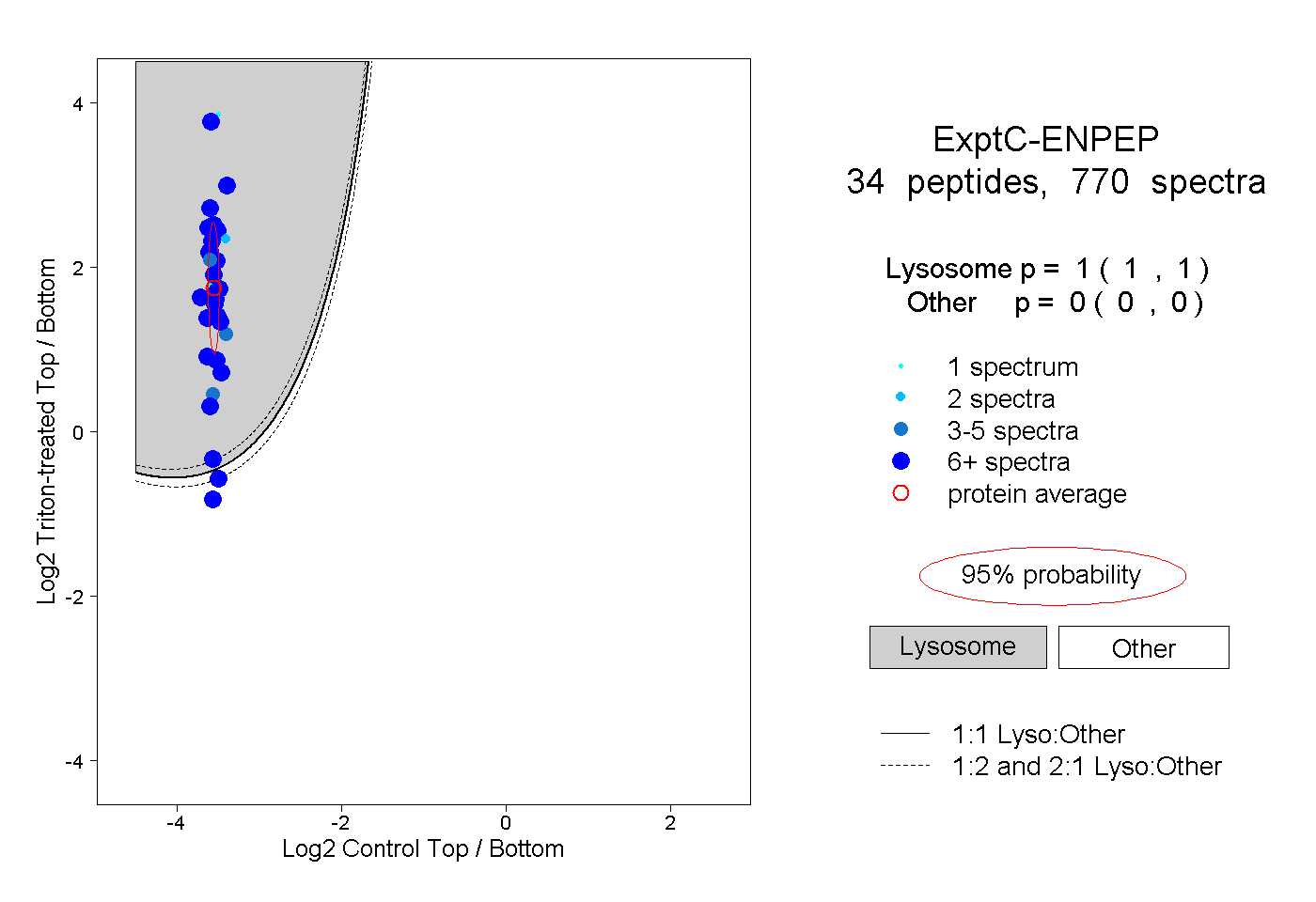 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
59 spectra |
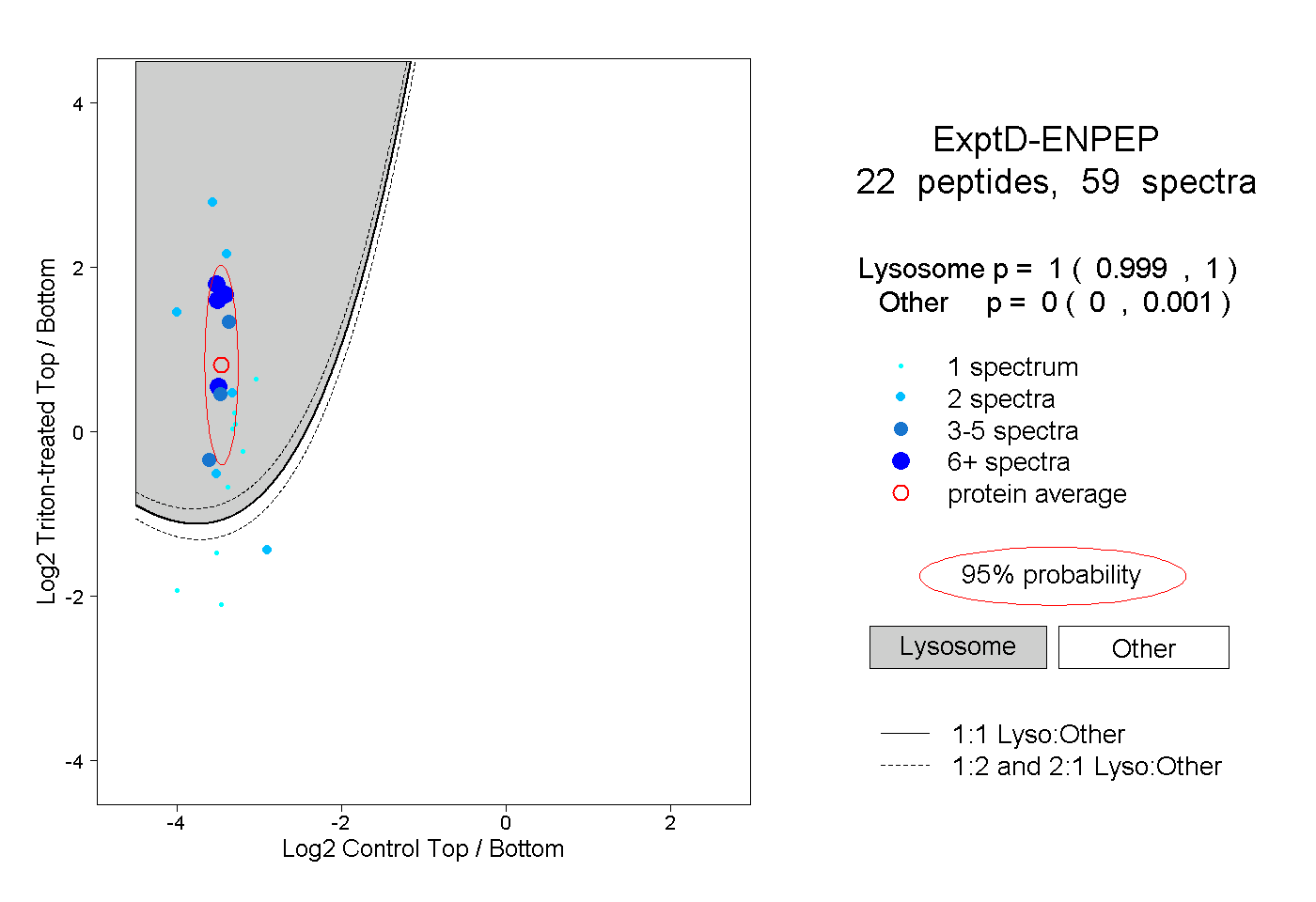 |
1.000 0.999 | 1.000 |
0.000 0.000 | 0.001 |