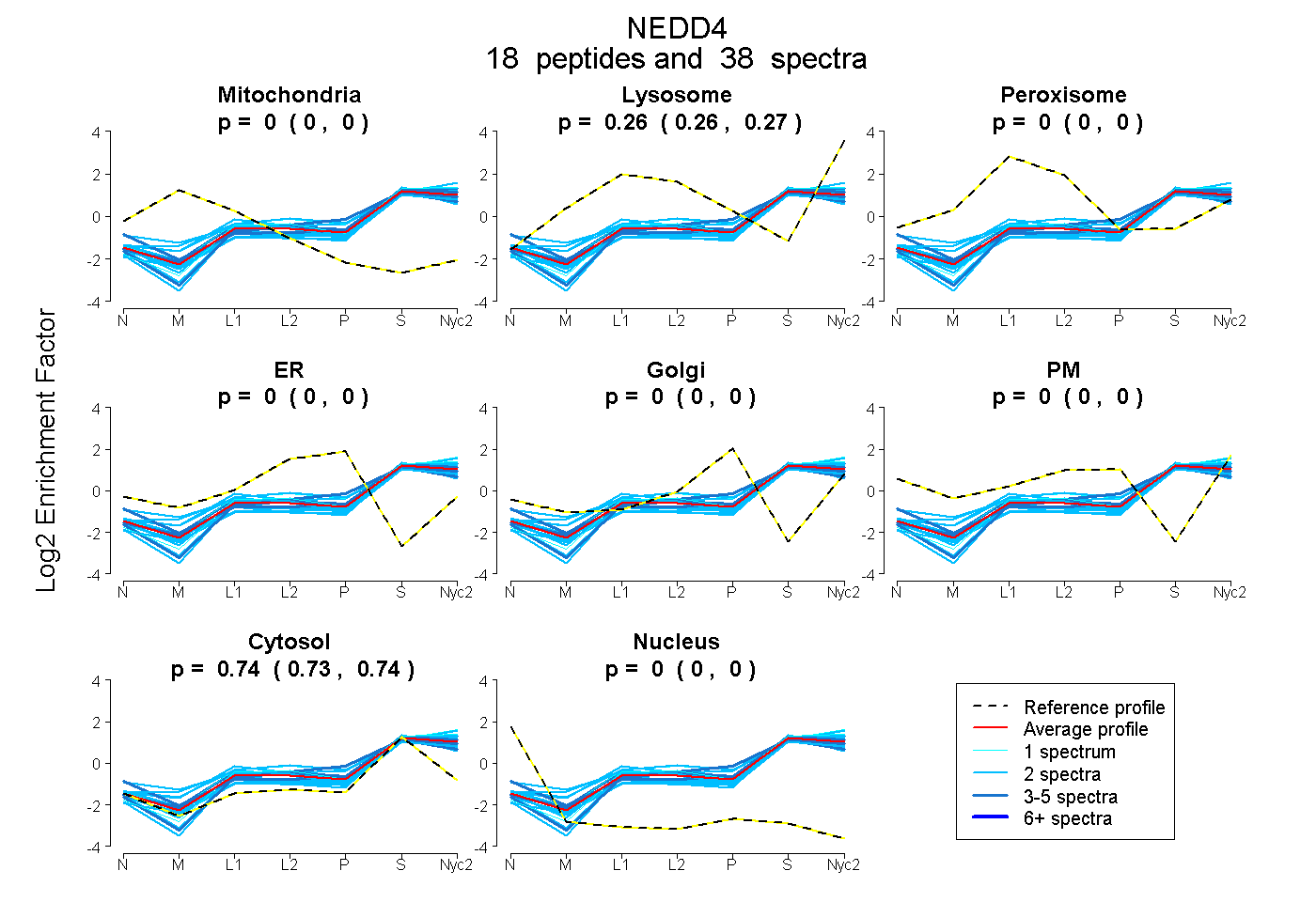
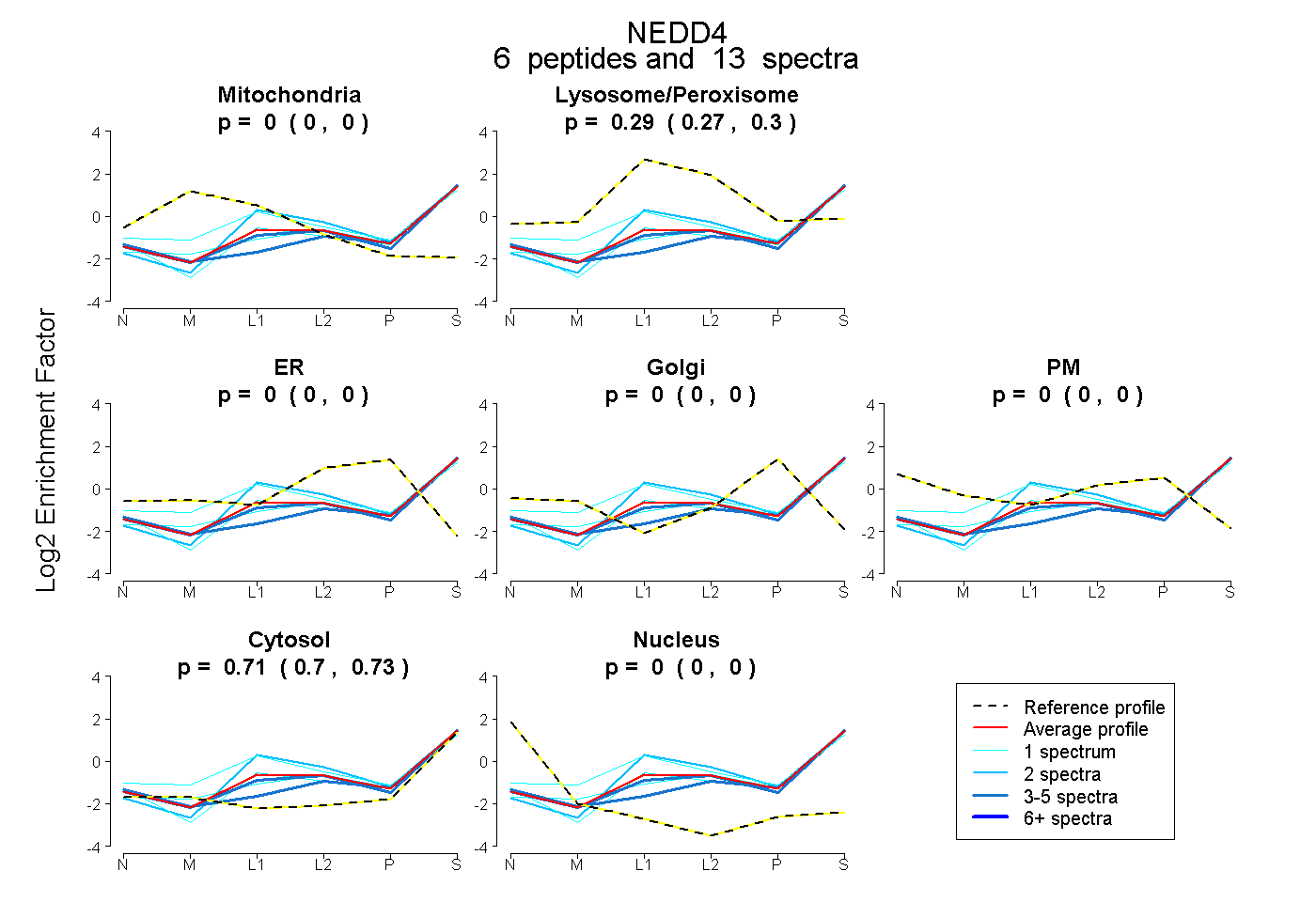
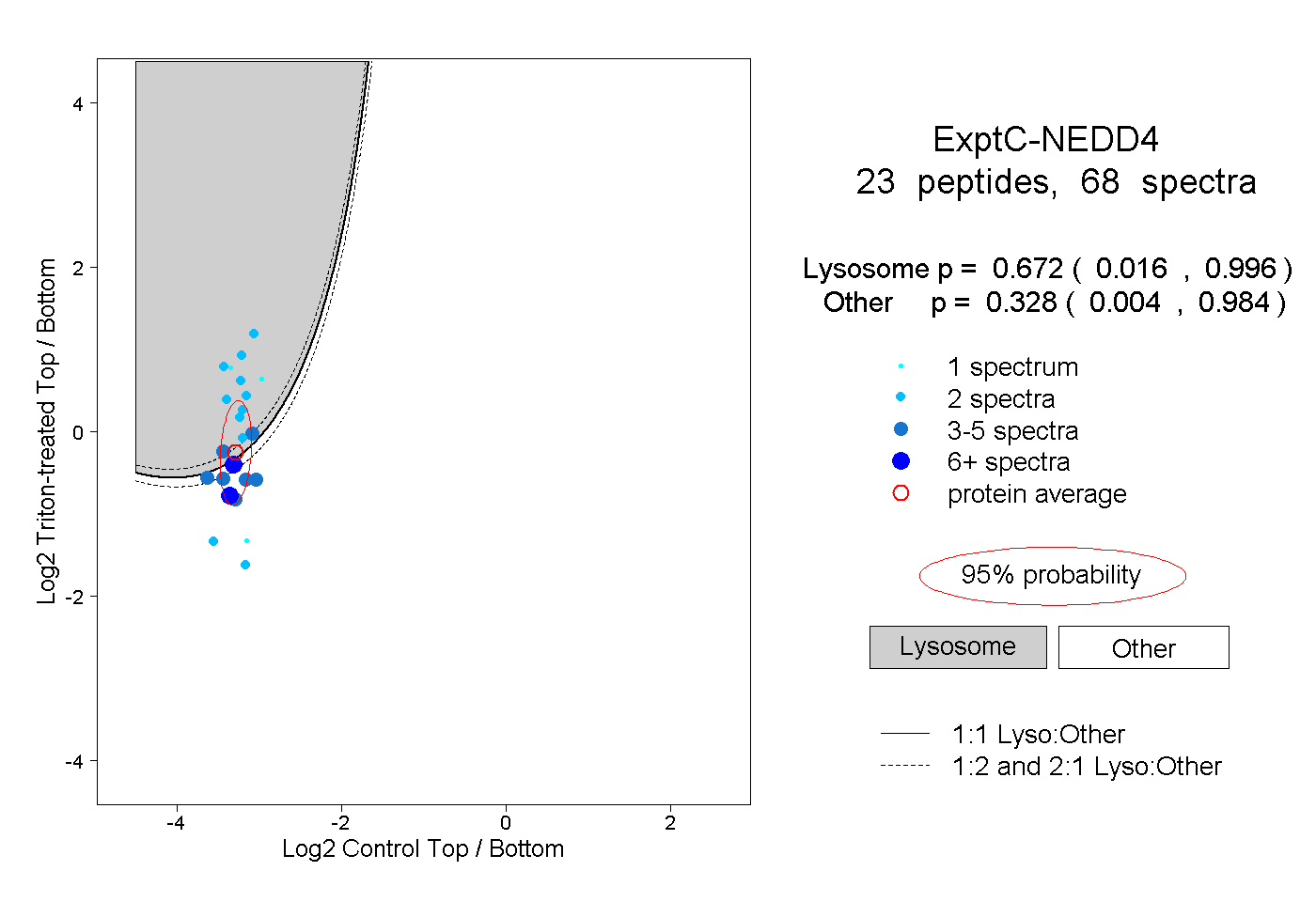
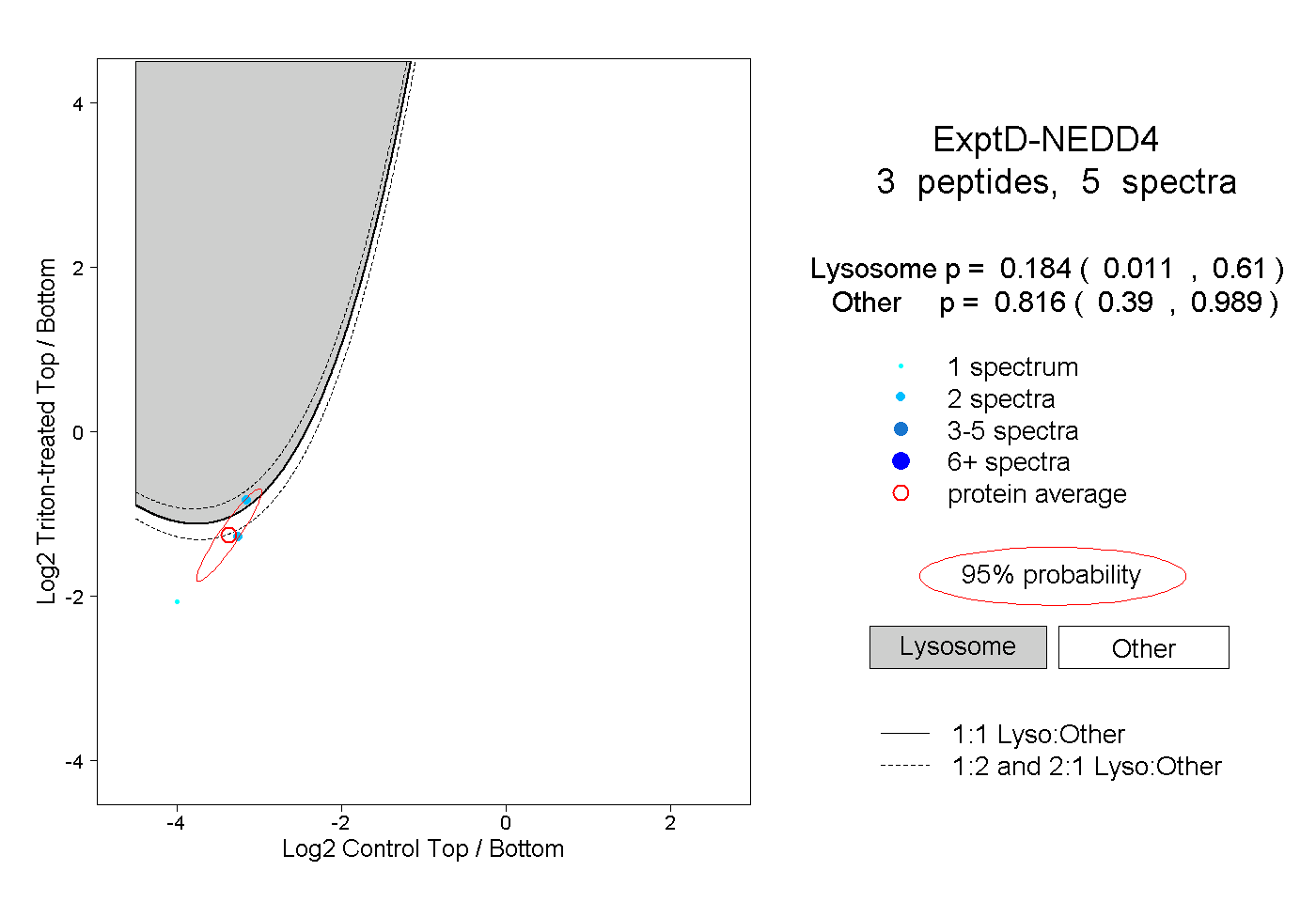
| 2 spectra, QMAAFK |
|
0.999 |
|
|
|
|
|
|
|
0.001 |
| 6 spectra, LAEELDTR |
|
0.012 |
|
|
|
|
|
|
|
0.988 |
| 5 spectra, FIIDEELFGQTHQHELK |
|
0.880 |
|
|
|
|
|
|
|
0.120 |
| 1 spectrum, QTDIPNK |
|
0.998 |
|
|
|
|
|
|
|
0.002 |
| 1 spectrum, MTYLPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GLDYGGVAR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, LLDGFFIRPFYK |
|
0.995 |
|
|
|
|
|
|
|
0.005 |
| 3 spectra, DFVLHPR |
|
0.005 |
|
|
|
|
|
|
|
0.995 |
| 5 spectra, VAGMAVYHGK |
|
0.160 |
|
|
|
|
|
|
|
0.840 |
| 2 spectra, WILENDPTELDLR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 4 spectra, TQWEDPR |
|
0.319 |
|
|
|
|
|
|
|
0.681 |
| 1 spectrum, EGFFELIPQDLIK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, LLQFVTGTSR |
|
0.990 |
|
|
|
|
|
|
|
0.010 |
| 4 spectra, AHTCFNR |
|
0.010 |
|
|
|
|
|
|
|
0.990 |
| 7 spectra, TGGSEVVVTNK |
|
0.346 |
|
|
|
|
|
|
|
0.654 |
| 2 spectra, TTTWSKPTMQDDPR |
|
0.867 |
|
|
|
|
|
|
|
0.133 |
| 2 spectra, LWIEFDGEK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, AVLMMDSEK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, MERPYTFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, AFTTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ANILEDSYR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 5 spectra, IPAHLR |
|
0.800 |
|
|
|
|
|
|
|
0.200 |
| 4 spectra, VFFINHNIK |
|
0.026 |
|
|
|
|
|
|
|
0.974 |