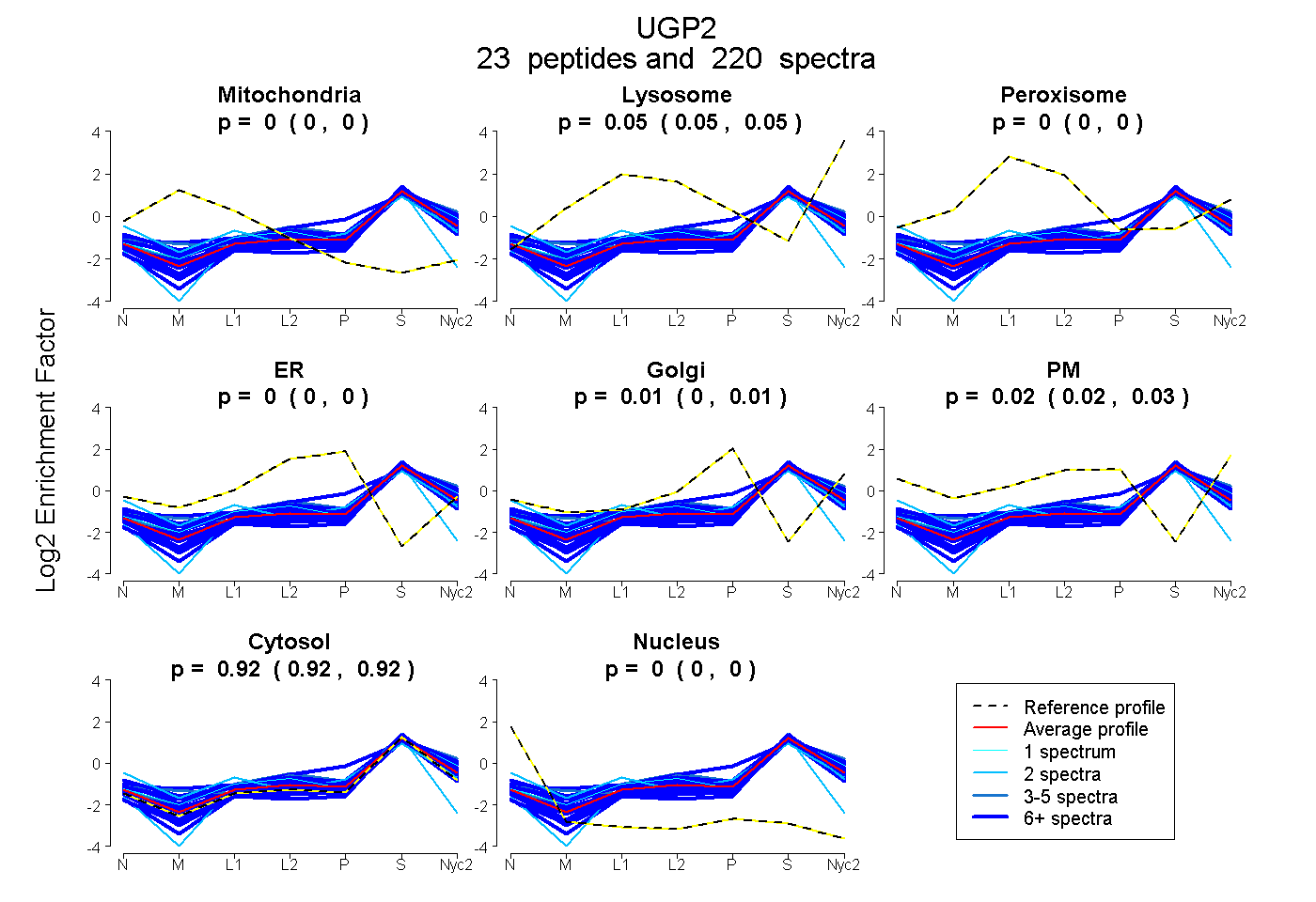
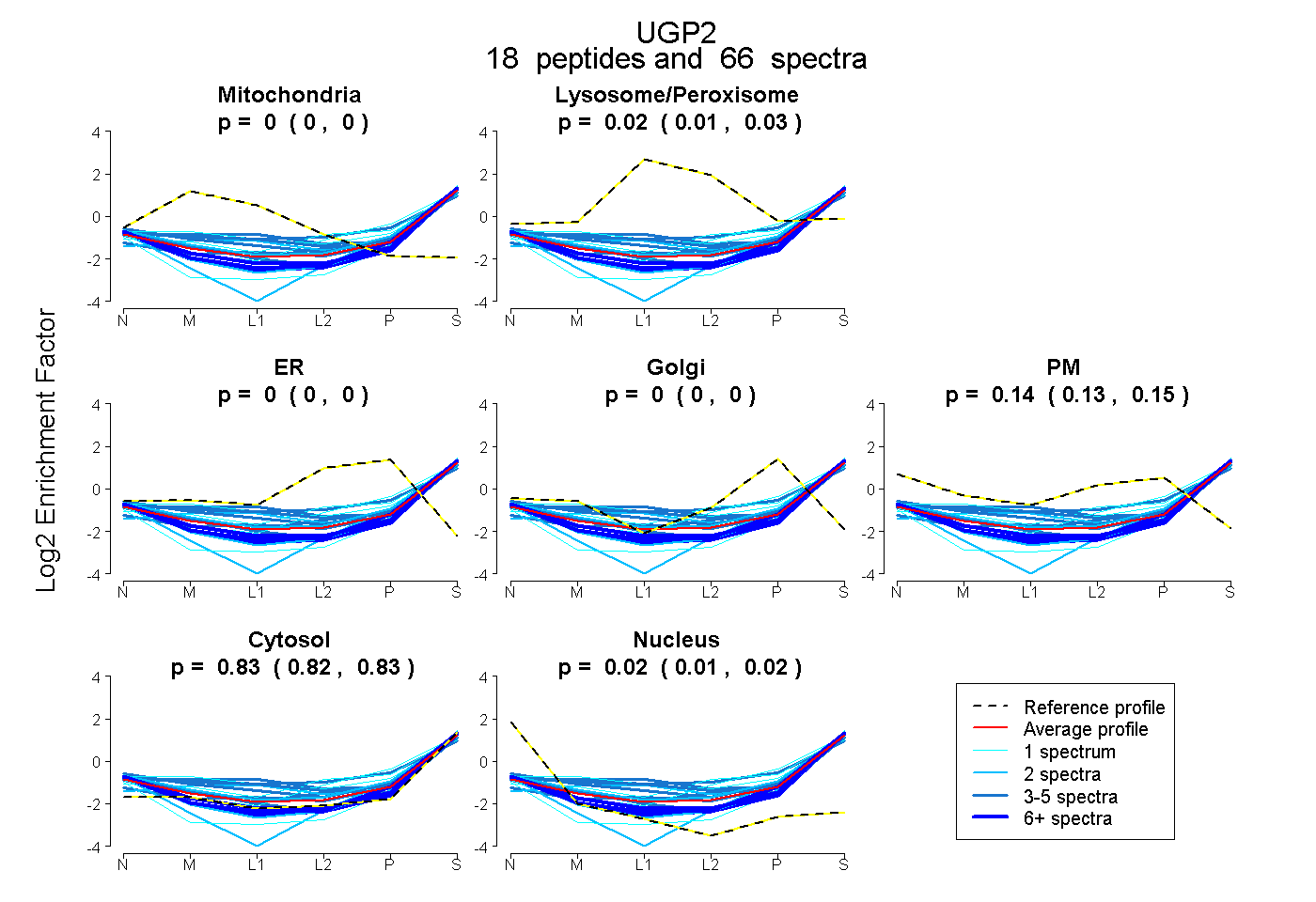
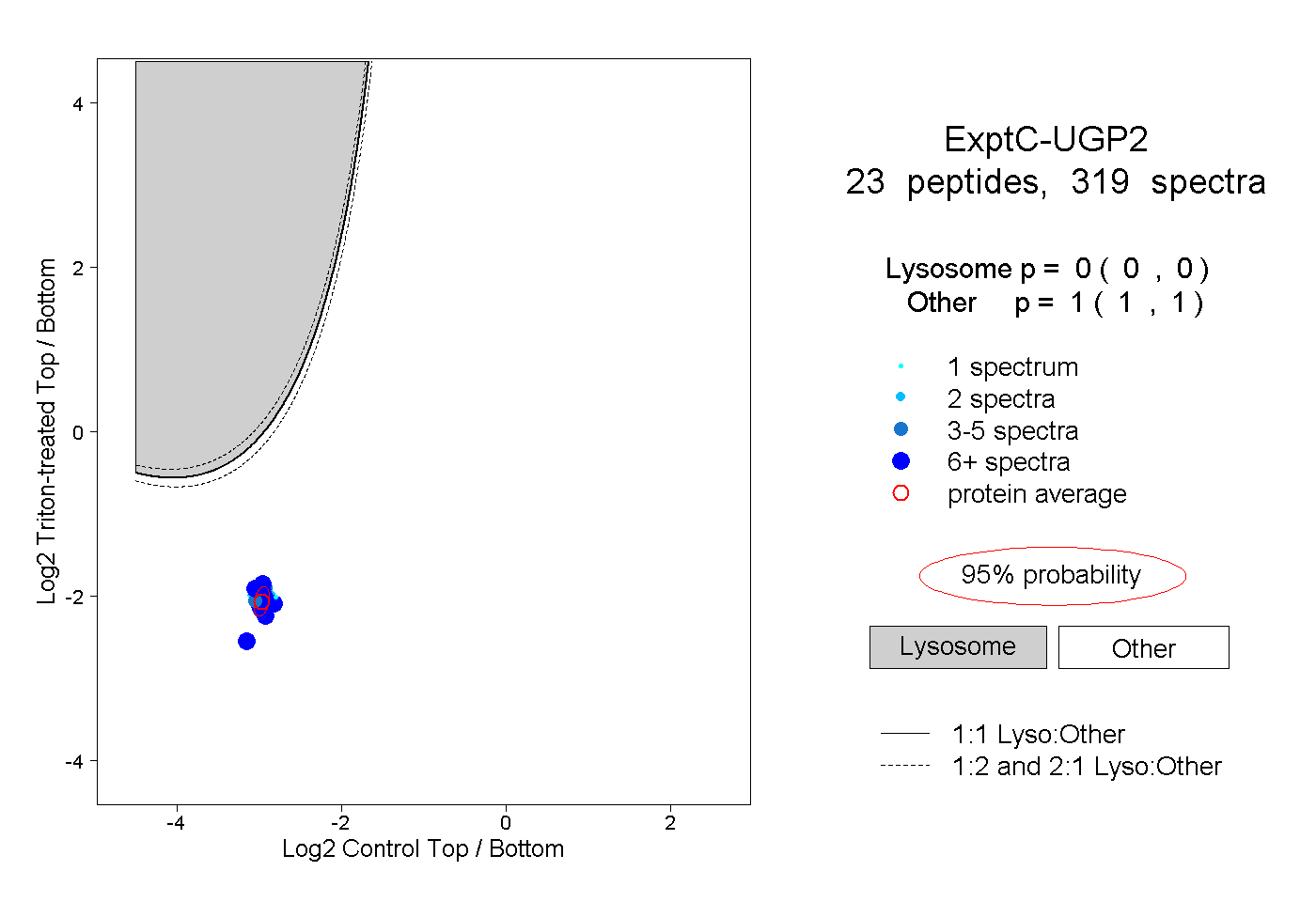
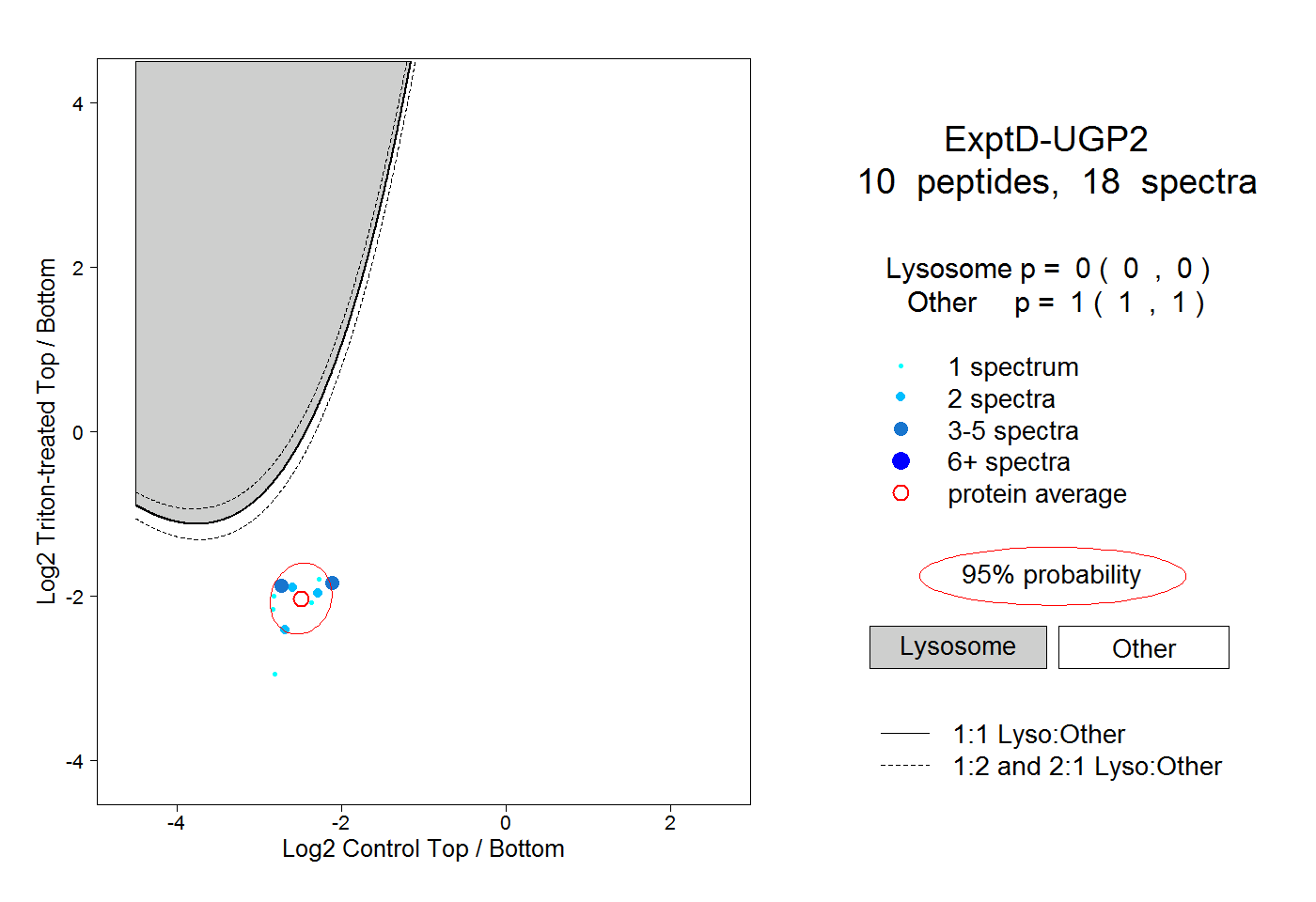
| 5 spectra, SLIGVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, IFNTNNLWISLAAVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, SFENSLGINVPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, LVEIAQVPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 24 spectra, GGTLTQYEGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 26 spectra, AHVDEFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, DLDGFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 32 spectra, LGSSFTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 29 spectra, IQRPPEDSIQPYEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 21 spectra, NENTFLDLTVQQIEHLNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TLDGGLNVIQLETAVGAAIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 15 spectra, FVQDLSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LNGGLGTSMGCK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 32 spectra, VQDYLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, GLPDNISSVLNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 15 spectra, ESLLPIAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, IDIPPGAVLENK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 18 spectra, IVSGNLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, GTVIIIANHGDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, CEFVMEVTNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, EFPTVPLVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 31 spectra, IYTFNQSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, GPSVDWGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |