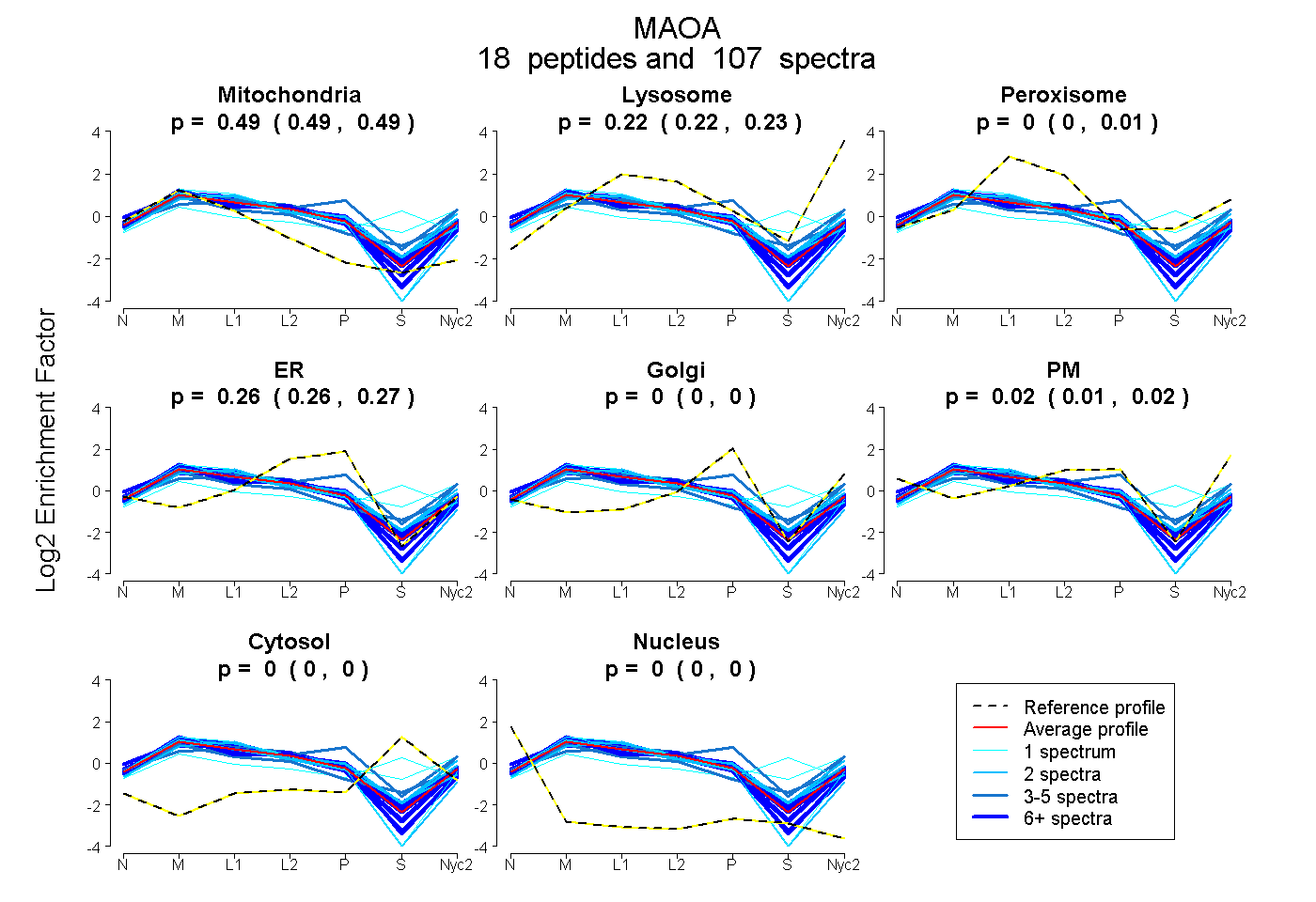
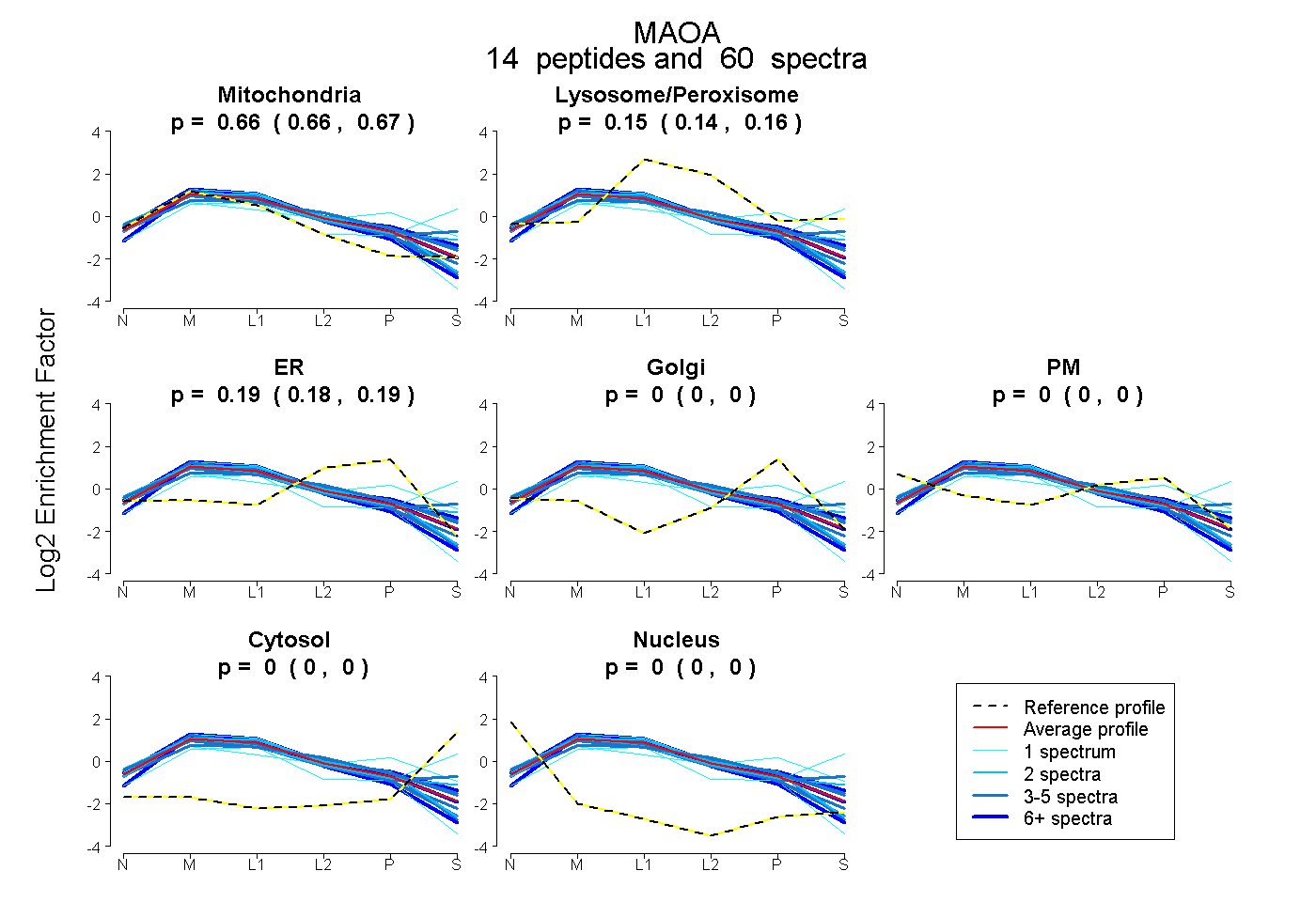
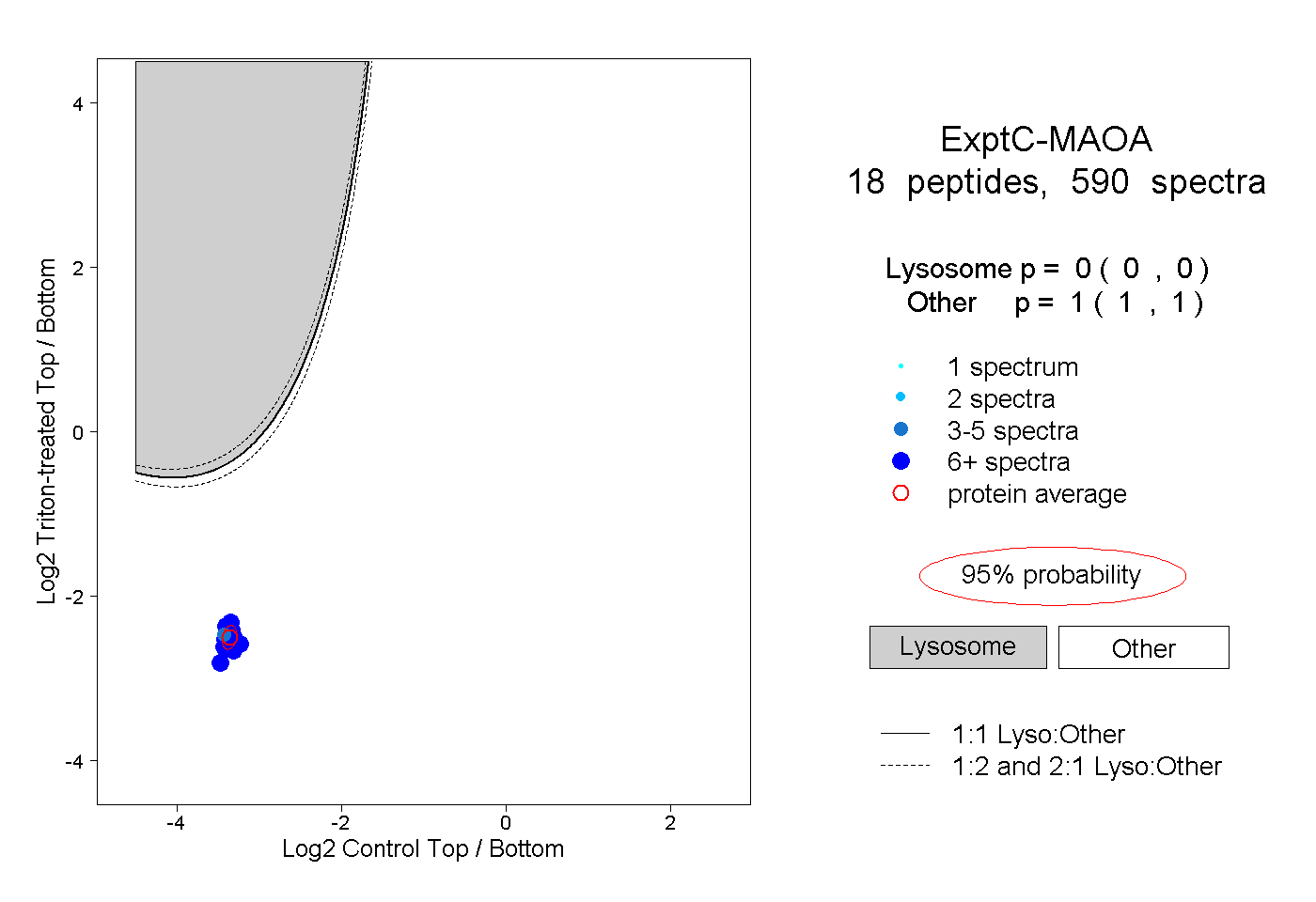
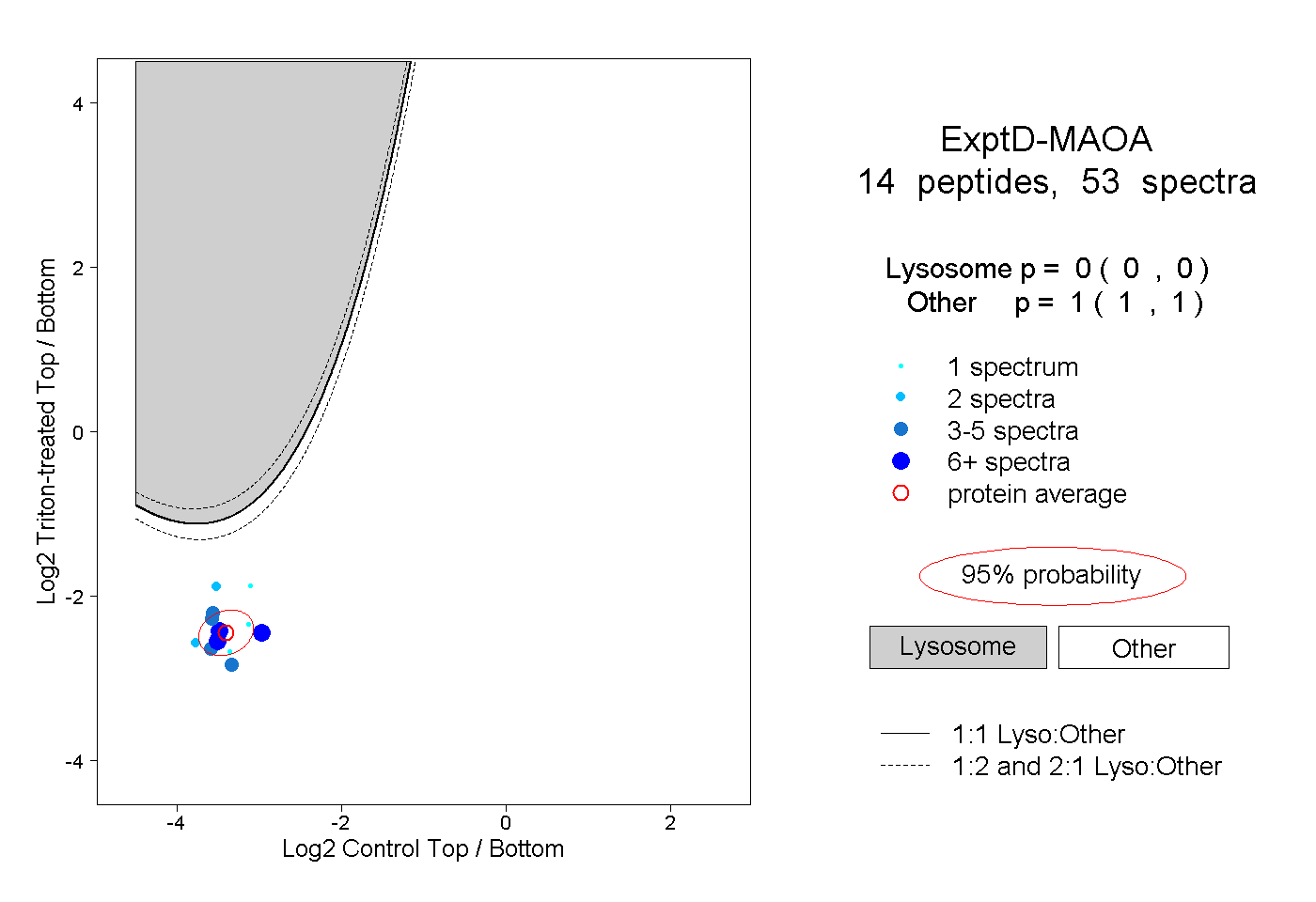
| 44 spectra, VLGSQEALYPVHYEEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, YVISAIPPILTAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 35 spectra, LLSEYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, WVDVGGAYVGPTQNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, DIWVEEPESK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 34 spectra, HAQEWDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 37 spectra, EVLNALGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 32 spectra, NQLLQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 71 spectra, DVPAIEITHTFLER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 27 spectra, IFSVTNGGQER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 36 spectra, EIPVDAPWQAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, NLPSVPGLLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 60 spectra, LPMGAVIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 28 spectra, VNVNER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 23 spectra, IHFKPELPPER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 43 spectra, LVQYVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 64 spectra, INVLVLEAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 28 spectra, TMDEMGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |